大概步骤:
1,找到之前研究MHC基因的方式做一下
似乎用找到OPN4的NCBI里面的6a,7b的位置
plink
2,然后各个vcf文件的位置
37.vcf位置
F:\冠形new_begin\37.vcf
BS.vcf
F:\冠形new_begin
chicken_6a.vcf.gz
BS_INDEL.vcf.gz
BK_BS_QC3.vcf
BS_indel.vcf
BK_INDEL.vcf.gz
F:\西北农林科技大学
BS.vcf
BK.vcf
F:\plink
6a位置
OPN4 (Chicken Gene)
ENSGALG00000001934 6:3059913-3082527:1
Opsin 4 [Source:NCBI gene;Acc:423609]
OPN4-201 (EntrezGene transcript name record; description: opsin 4,) is an external reference matched to Transcript ENSGALT00000002989
Variant tablePhenotypesLocationExternal Refs.RegulationGene tree
OPN4-201 (Chicken Transcript)
ENSGALT00000002989 6:3059913-3082527:1
Opsin 4 [Source:NCBI gene;Acc:423609].
LocationExternal Refs.cDNA seq.ExonsVariant tableProtein seq.PopulationProtein summary
OPN4-1 (Chicken Gene)
ENSGALG00000041662 4:37229825-37254071:1
Photopigment melanopsin-like [Source:NCBI gene;Acc:395334]
OPN4-1-201 (EntrezGene transcript name record; description: photopigment melanopsin-like,) is an external reference matched to Transcript ENSGALT00000082868
Variant tablePhenotypesLocationExternal Refs.RegulationOrthologuesGene tree
OPN4-1-201 (Chicken Transcript)
ENSGALT00000082868 4:37229825-37254071:1
Photopigment melanopsin-like [Source:NCBI gene;Acc:395334].
LocationExternal Refs.cDNA seq.ExonsVariant tableProtein seq.PopulationProtein summary
OPN4-1-202 (Chicken Transcript)
ENSGALT00000085974 4:37229844-37252453:1
Photopigment melanopsin-like [Source:NCBI gene;Acc:395334].
LocationExternal Refs.cDNA seq.ExonsVariant tableProtein seq.PopulationProtein summary
ENSGT01030000234631 (Chicken GeneTree)
ENSGT01030000234631
Gene OPN4-1 (ENSGALG00000041662) is a member of GeneTree ENSGT01030000234631.
ENSGT01030000234631 (Chicken GeneTree)
ENSGT01030000234631
Gene OPN4 (ENSGALG00000001934) is a member of GeneTree ENSGT01030000234631.
要研究节律相关基因 OPN4 的分布情况,我们可以从以下几个方面进行分析:
1. 基因信息概述:
- OPN4(Opsin 4):这是一种与感光有关的基因,编码一种被称为melanopsin的光感受器。它参与非视觉光感受,如调节昼夜节律(生物钟)和光诱导的行为。
- 鸡的OPN4基因分为两种类型:
- OPN4(基因ID:ENSGALG00000001934,染色体6)对应Opsin 4。
- OPN4-1(基因ID:ENSGALG00000041662,染色体4)对应Photopigment melanopsin-like,可能是OPN4的另一种变体,或功能上类似的光感受器。
2. 基因位置:
- OPN4 基因位置:染色体 6,范围为 3059913-3082527。
- OPN4-1 基因位置:染色体 4,范围为 37229825-37254071。
3. 蛋白序列和转录本:
- OPN4(Opsin 4)转录本主要是 OPN4-201(转录本ID:ENSGALT00000002989)。
- OPN4-1(Photopigment melanopsin-like)有两个转录本:
- OPN4-1-201(转录本ID:ENSGALT00000082868)。
- OPN4-1-202(转录本ID:ENSGALT00000085974)。
4. 基因树分析:
- 通过基因树(GeneTree)ENSGT01030000234631,我们可以看到 OPN4 和 OPN4-1 都是同一个基因树的成员,这意味着它们可能有共同的进化来源。
5. 分布和进化相关性:
- 在不同物种中的分布:我们可以通过比较不同物种中的OPN4基因来理解其保守性,尤其是在与昼夜节律相关的物种中,OPN4基因会表现出更广泛的分布和保守性。
6. 下一步研究:
- 表达模式分析:可以进行 RNA-Seq 或 qPCR 实验来研究 OPN4 基因在不同组织(特别是光敏感组织如眼睛和大脑)中的表达情况,了解它在生物钟调节中的具体作用。
- 功能实验:通过敲除或过表达 OPN4 来观察昼夜节律和行为的变化,进一步研究其在节律调控中的具体功能。
- 进化研究:可以通过对比不同物种中的 OPN4 序列,来研究其保守性和进化路径。
你可以通过基因数据库(如Ensembl或NCBI)获取更多关于 OPN4 的详细注释、序列、和进化关系,并进一步研究其在节律调控中的作用。
如果你需要特定的基因表达数据或进一步的图表分析,我可以帮助你进行数据获取和可视化。
7b位置
你提供的信息显示了 OPN4 和 OPN4-1 基因在不同鸡种中的分布情况,尤其是 白来亨鸡(White Leghorn Layer) 和 红原鸡(Red Junglefowl)。这些基因与昼夜节律调控和光感知有关,特别是 Opsin 4 和类似 melanopsin 的光感受器在这些鸡种中的不同基因位置和转录本。
1. OPN4 基因在不同鸡种中的分布:
- 参考品种的OPN4基因(ENSGALG00010010341) 位于染色体 6 的 3031207-3056862。
- 白来亨鸡的OPN4基因(ENSGALG00015004288) 位于染色体 6 的 2903277-2928948。
- 红原鸡的OPN4基因(ENSGALG00000001934) 位于染色体 6 的 3056986-3082649。
这显示出不同鸡种在同一染色体上,但基因位置和范围有所差异,可能反映了不同鸡种对环境光的感应机制的细微差别。
2. OPN4-1 基因在不同鸡种中的分布:
- 参考品种的 OPN4-1 基因(ENSGALG00010005533) 位于染色体 4 的 36803502-36831559。
- 白来亨鸡的 OPN4-1 基因(ENSGALG00015018489) 位于染色体 4 的 36756541-36784597。
- 红原鸡的 OPN4-1 基因(ENSGALG00000041662) 位于染色体 4 的 37227743-37255601。
同样,OPN4-1 在不同鸡种的染色体4上的分布也不同,显示出遗传背景对光感受基因的影响。
3. 基因位置与转录本:
- 各个鸡种的 OPN4 和 OPN4-1 基因都对应不同的转录本,这些转录本编码的光感受器可能对不同光照条件或昼夜节律有适应性:
- 参考品种的 OPN4-201 对应转录本 ENSGALT00010024743(6:3031207-3056862)。
- 红原鸡的 OPN4-201 对应转录本 ENSGALT00000002989(6:3056986-3082649)。
- 白来亨鸡的 OPN4-201 对应转录本 ENSGALT00015009967(6:2903277-2928948)。
- 参考品种的 OPN4-1-203 对应转录本 ENSGALT00010013242。
- 白来亨鸡的 OPN4-1-203 对应转录本 ENSGALT00015045273。
- 红原鸡的 OPN4-1-202 对应转录本 ENSGALT00000082868。
4. 研究重点:
- 不同鸡种基因变异的研究:这些基因和转录本的差异可能会导致不同鸡种在光感受和昼夜节律调控方面的不同表现。你可以进一步通过比较基因序列、表达谱以及功能实验来分析这些差异。
- 基因功能的验证:通过 CRISPR 等基因编辑技术敲除或过表达这些基因,结合光照实验,研究鸡在昼夜节律、季节性繁殖和行为上的反应变化。
你可以利用公开的基因组数据进一步研究这些基因在不同鸡种中的分布和功能差异,并结合基因表达数据进行深入分析。如果你需要特定的可视化图表或分析帮助,我可以为你生成相关数据图表。
从你提供的额外信息来看,我们可以对 OPN4-1 基因及其转录本在不同鸡种中的情况做更详细的分析。以下是主要的发现:
1. OPN4-1 在不同鸡种中的转录本比较:
白来亨鸡(White Leghorn Layer):
- OPN4-1-202(转录本ID:ENSGALT00015045274):位于染色体 4 的 36758630-36783070。
- OPN4-1-201(转录本ID:ENSGALT00015045276):位于染色体 4 的 36756541-36784597。
参考品种:
- OPN4-1-203(转录本ID:ENSGALT00010013242):位于染色体 4 的 36814958-36830029。
- OPN4-1-202(转录本ID:ENSGALT00010013246):位于染色体 4 的 36805591-36830029。
- OPN4-1-201(转录本ID:ENSGALT00010013249):位于染色体 4 的 36803502-36831559。
红原鸡(Red Junglefowl):
- OPN4-1-202(转录本ID:ENSGALT00000082868):位于染色体 4 的 37229831-37254071。
- OPN4-1-203(转录本ID:ENSGALT00000085974):位于染色体 4 的 37239154-37254071。
- OPN4-1-201(转录本ID:ENSGALT00000111656):位于染色体 4 的 37227743-37255601。
2. OPN4-1 转录本的比较与基因位置的差异:
不同品种的鸡在 OPN4-1 基因的染色体位置上存在一些差异,这些差异可能与这些鸡种在昼夜节律和光感知方面的适应性有关。特别是白来亨鸡和红原鸡中,OPN4-1 的不同转录本跨越的基因区域存在明显差别,可能反映出不同的基因调控机制。
- 白来亨鸡:位于染色体 4 的 36756541 到 36783070 范围。
- 红原鸡:位于染色体 4 的 37227743 到 37255601 范围。
这些差异可能是由于基因组的结构性变异引起的,也可能反映了不同物种在光感应和昼夜节律中的功能差异。
3. OPN4 和 OPN4-1 的进化关系:
两者都属于 GeneTree ENSGT01120000271853,表明它们具有共同的进化起源。OPN4-1 与 OPN4 的功能虽然都涉及光感应和昼夜节律,但它们的功能可能略有不同。
4. 研究方向:
- 基因表达分析:不同转录本在不同组织中的表达水平,特别是在感光组织(如视网膜或松果体)中的表达差异,可以揭示这些基因在光调控中的具体功能。
- 功能研究:通过基因敲除或过表达这些特定转录本,可以帮助研究它们对昼夜节律和光诱导行为的影响。
这些数据可以帮助你深入了解 OPN4 和 OPN4-1 基因在不同鸡种中的功能差异以及它们在昼夜节律调控中的具体角色。如果需要,我可以进一步帮助你整理这些数据,或进行相关图表的可视化分析。
命令
plink –vcf chicken_6a.vcf.gz –chr 16 –from-bp 2606528 –to-bp 2609057 –make-bed –out output_BB –chr-set 39
(
plink –vcf chicken_6a.vcf.gz –chr 6 –from-bp 3056986 –to-bp 3082649 –make-bed –out output_OPN4 –chr-set 39
plink –vcf chicken_6a.vcf.gz –chr 4 –from-bp 37227743 –to-bp 37255601 –make-bed –out output_OPN4_1 –chr-set 39
)
plink –vcf GRCg6a.928.Indel.vcf.gz –chr 16 –from-bp 2606528 –to-bp 2609057 –make-bed –out BF2_indel –chr-set 39
(
plink –vcf GRCg6a.928.Indel.vcf.gz –chr 6 –from-bp 3056986 –to-bp 3082649 –make-bed –out output_OPN4_indel –chr-set 39
plink –vcf GRCg6a.928.Indel.vcf.gz –chr 4 –from-bp 37227743 –to-bp 37255601 –make-bed –out output_OPN4_1_indel –chr-set 39
)
合成vcf文件
plink –bfile BF2_indel –recode vcf –out BF2_indel
I:\plink
plink –vcf BK_BS_QC3.vcf –chr 16 –from-bp 2226703 –to-bp 2229465 –make-bed –out BS_BK_BF2_indel –chr-set 39
plink –bfile BS_BK_BF2_indel –recode vcf –out BS_BK_BF2_indel –chr-set 39
然后snpeff分析:
F:\软件\SNPEFF\snpEff>java -jar snpEff.jar GRCg6a.105 output_OPN4.vcf> output_OPN4_o.vcf
F:\软件\SNPEFF\snpEff>java -jar snpEff.jar GRCg6a.105 output_OPN4_1.vcf> output_OPN4_1_o.vcf
F:\软件\SNPEFF\snpEff>java -jar snpEff.jar GRCg6a.105 output_OPN4_indel.vcf> output_OPN4_indel_o.vcf
F:\软件\SNPEFF\snpEff>java -jar snpEff.jar GRCg6a.105 output_OPN4_1_indel.vcf > output_OPN4_1_indel_o.vcf
snpeff
你的表格来看,你正在研究的是 OPN4 基因(Gene ID: ENSGALG00000001934,位于染色体6)。这个基因的转录本(Transcript ID: ENSGALT00000002989)属于蛋白编码基因(protein_coding)。以下是表格中各个数据列的具体含义以及你可能会感兴趣的研究内容的解读:
variants_impact_HIGH:表示对基因功能有重大影响的突变数量。在 OPN4 基因中有1个此类突变。
variants_impact_LOW:对基因功能影响较小的突变数量。在 OPN4 基因中,有20个此类突变。
variants_impact_MODERATE:中等影响的突变数量,有26个。
variants_impact_MODIFIER:修改功能影响的突变数量,有633个。
此外,不同的突变效应被列在以下几列:
3_prime_UTR_variant:3’非翻译区突变,OPN4基因有2个。
5_prime_UTR_premature_start_codon_gain_variant:5’非翻译区起始密码子提前突变,有1个。
5_prime_UTR_variant:5’非翻译区的突变,有4个。
downstream_gene_variant:位于基因下游的变异,有5个。
intron_variant:内含子区突变,OPN4基因有540个。
missense_variant:错义突变,有26个。
splice_region_variant:剪接区突变,有2个。
stop_lost:终止密码子丢失突变,有1个。
synonymous_variant:同义突变,有19个。
upstream_gene_variant:位于基因上游的变异,有82个。
下一步研究建议:
下一步研究建议:
OPN4 基因中的高影响变异:你可以进一步分析1个具有高影响的变异,看看它对蛋白质功能是否有重要破坏或改变。
错义突变(missense variant):你可以关注26个错义突变,了解这些突变如何改变氨基酸序列,进而影响蛋白质结构和功能。
剪接区和终止密码子突变:这类突变通常对基因的表达和功能影响较大,值得进一步分析。
你可以通过这些不同类别的突变,结合生物信息学工具(例如SnpEff、VEP等)或实验数据进一步研究 OPN4 基因功能变化及其在生物体内的具体作用。如果你需要对这些数据进行进一步的分析或可视化,我也可以帮助你进行下一步的处理。
这次你提供的表格涉及的是 OPN4-1 基因(Gene ID: ENSGALG00000041662),其中有两个不同的转录本:ENSGALT00000082868 和 ENSGALT00000085974。这两个转录本都属于蛋白编码类型(protein_coding)。下面是对这两个转录本的突变信息的解读:
转录本 1: ENSGALT00000082868
- variants_impact_HIGH: 1 个高影响突变。
- variants_impact_LOW: 27 个低影响突变。
- variants_impact_MODERATE: 14 个中等影响突变。
- variants_impact_MODIFIER: 749 个修改影响的突变。
各突变效应如下:
- 3_prime_UTR_variant: 24 个 3’非翻译区突变。
- 5_prime_UTR_premature_start_codon_gain_variant: 1 个5’非翻译区的起始密码子提前突变。
- 5_prime_UTR_variant: 9 个 5’非翻译区突变。
- downstream_gene_variant: 48 个基因下游的变异。
- intron_variant: 612 个内含子区突变。
- missense_variant: 14 个错义突变。
- splice_donor_variant: 1 个剪接供体突变。
- splice_region_variant: 3 个剪接区突变。
- synonymous_variant: 23 个同义突变。
- upstream_gene_variant: 60 个基因上游的突变。
转录本 2: ENSGALT00000085974
- variants_impact_HIGH: 1 个高影响突变。
- variants_impact_LOW: 21 个低影响突变。
- variants_impact_MODERATE: 8 个中等影响突变。
- variants_impact_MODIFIER: 761 个修改影响的突变。
各突变效应如下:
- 3_prime_UTR_variant: 34 个 3’非翻译区突变。
- 5_prime_UTR_premature_start_codon_gain_variant: 1 个5’非翻译区的起始密码子提前突变。
- 5_prime_UTR_variant: 7 个 5’非翻译区突变。
- downstream_gene_variant: 99 个基因下游的变异。
- intron_variant: 563 个内含子区突变。
- missense_variant: 8 个错义突变。
- splice_donor_variant: 1 个剪接供体突变。
- splice_region_variant: 3 个剪接区突变。
- synonymous_variant: 17 个同义突变。
- upstream_gene_variant: 62 个基因上游的突变。
比较这两个转录本:
- 错义突变(missense variant):第一个转录本有14个,而第二个有8个。
- 3_prime_UTR_variant:第二个转录本中有更多(34个)3’UTR突变,而第一个转录本只有24个。
- downstream_gene_variant:第二个转录本中有更多下游基因突变(99个),而第一个转录本有48个。
总结:
你可以根据这两个不同转录本的突变类型和数量进行对比,特别是关注一些对功能可能影响较大的突变类型,例如 missense variant(错义突变)和 splice_donor_variant(剪接供体突变),这可能会对蛋白质的结构和功能产生不同影响。
根据你的研究目的,可能需要进一步通过实验或计算工具(如SnpEff)来确定这些突变对基因功能的实际影响。如果需要对数据做进一步分析或统计,可随时告诉我!
你提供的表格确实看起来涉及了与插入缺失变异(Indels)相关的信息。插入缺失变异(Indel)通常是指基因组中一段DNA的插入或缺失,这种变异会导致框移、错义或非义突变,对基因功能产生不同程度的影响。
我们来看一下表格中的数据,涉及两个基因:OPN4 和 WAPL,分别有不同的转录本和突变效应:
OPN4 基因(ENSGALG00000001934)
转录本:ENSGALT00000002989(蛋白编码)
- variants_impact_HIGH: 1 个高影响的突变。
- variants_impact_LOW: 1 个低影响的突变。
- variants_impact_MODERATE: 2 个中等影响的突变。
- variants_impact_MODIFIER: 125 个修饰类的突变。
这些突变对基因的具体影响体现在以下突变类型中:
- 3_prime_UTR_variant: 1 个 3’ 非翻译区变异。
- 5_prime_UTR_variant: 1 个 5’ 非翻译区变异。
- disruptive_inframe_deletion: 2 个中断型框架内缺失变异,通常会导致蛋白质功能的丧失或变化。
- frameshift_variant: 1 个移码突变,这是非常严重的突变,可能会完全改变蛋白质的读码框并导致功能丧失。
- intron_variant: 112 个内含子区域的变异。
- splice_region_variant: 1 个剪接区突变,可能影响剪接过程。
- start_lost: 1 个起始密码子丢失突变,这会阻止蛋白质的正常合成。
- upstream_gene_variant: 12 个基因上游的变异。
WAPL 基因(ENSGALG00000001907)
转录本:ENSGALT00000066476 和 ENSGALT00000101872(蛋白编码)
这两个转录本的突变效应数据完全相同:
- variants_impact_HIGH, LOW, MODERATE: 都是0,意味着没有任何高、中、低影响的突变。
- variants_impact_MODIFIER: 129 个修饰类突变。
突变类型:
- intron_variant: 129 个内含子区域变异。
- 其他突变类型(如3_prime_UTR_variant、5_prime_UTR_variant、frameshift_variant等)都为0。
分析总结:
OPN4 基因:
- disruptive_inframe_deletion 和 frameshift_variant 这两类变异对蛋白质的影响很大,特别是移码突变(frameshift_variant)可能会彻底改变蛋白质的功能。
- start_lost 突变也会导致翻译过程的启动失败,严重影响蛋白质的生成。
- 剪接区突变(splice_region_variant) 和 内含子变异 可能会影响基因的转录剪接过程。
WAPL 基因:
- 在两个转录本中,尽管有129个内含子区变异(intron_variant),但没有高影响或中等影响的突变。这些内含子区变异可能不会显著影响蛋白质功能。
建议:
对于 OPN4 基因,可以进一步研究移码突变、起始密码子丢失和中断型框架内缺失等高影响变异,看看它们如何影响蛋白质结构和功能。这类变异可能与基因功能的丧失或改变直接相关。
你提供的这份表格包含了 OPN4-1 基因的两个不同转录本:ENSGALT00000082868 和 ENSGALT00000085974,它们都是蛋白编码基因。以下是对这两个转录本的突变信息的分析:
转录本 1: ENSGALT00000082868
- variants_impact_HIGH: 0 个高影响突变。
- variants_impact_MODERATE: 1 个中等影响突变。
- variants_impact_MODIFIER: 82 个修饰影响的突变。
突变类型如下:
- 3_prime_UTR_variant: 2 个 3’ 非翻译区突变。
- conservative_inframe_insertion: 1 个保守型框架内插入变异,这类变异可能会保留蛋白质功能。
- downstream_gene_variant: 5 个基因下游突变。
- frameshift_variant: 0 个移码突变。
- intron_variant: 71 个内含子突变。
- upstream_gene_variant: 4 个基因上游突变。
转录本 2: ENSGALT00000085974
- variants_impact_HIGH: 1 个高影响突变。
- variants_impact_MODERATE: 1 个中等影响突变。
- variants_impact_MODIFIER: 81 个修饰影响的突变。
突变类型如下:
- 3_prime_UTR_variant: 10 个 3’ 非翻译区突变。
- conservative_inframe_insertion: 1 个保守型框架内插入变异。
- downstream_gene_variant: 9 个基因下游突变。
- frameshift_variant: 1 个移码突变。
- intron_variant: 58 个内含子突变。
- upstream_gene_variant: 4 个基因上游突变。
分析与比较:
高影响突变:
- 转录本 ENSGALT00000085974 有1个高影响突变,而转录本 ENSGALT00000082868 没有。这意味着第二个转录本可能含有更具破坏性的突变,可能对基因功能有更大的影响。
中等影响突变:
- 两个转录本都有1个中等影响突变,表明在这两种转录本中,某些突变可能会影响基因功能,但影响的程度不如高影响突变。
修饰影响突变:
- 两个转录本的修饰影响突变数量接近,分别是82和81个。这些突变通常不会对蛋白质功能产生明显的直接影响,但可能会修改某些调控区域或基因的表达方式。
具体突变类型:
- 转录本 ENSGALT00000085974 中的 frameshift_variant(移码突变)是一个值得注意的突变,因为移码突变通常会显著改变蛋白质的读码框,从而导致异常的蛋白质。
- 3_prime_UTR_variant 的数量在第二个转录本中显著更多(10 vs 2),这意味着第二个转录本在3’非翻译区内发生了更多的变异,可能影响mRNA的稳定性或转录后的调控。
- intron_variant(内含子突变)在第一个转录本中更多(71 vs 58),虽然内含子区域通常不会直接影响蛋白质的功能,但有时它们会影响基因的转录剪接过程。
总结与建议:
- ENSGALT00000085974 转录本由于含有 frameshift_variant 和 高影响突变,可能对基因的表达和功能有更大的影响,值得进一步研究。
- ENSGALT00000082868 转录本虽然没有高影响突变,但有较多的 intron_variant,可能影响基因的转录或剪接。
- 对于这些突变,建议进一步使用生物信息学工具(如SnpEff、VEP等)进行预测分析,或者通过实验验证突变对蛋白质功能和基因表达的实际影响。
如果你需要更详细的数据处理或可视化分析,随时告诉我!
你提供的是一个 VCF 文件 的注释信息行,包含了一个变异位点及其在多个基因中的影响。让我们逐步解析这一行的含义:
基本信息
1 | 6 3082399 . T C . . PR;ANN=... |
- 6: 这是变异所在的染色体编号(染色体 6)。
- 3082399: 变异发生的位置(位点是 3082399)。
- .: 该字段通常表示变异的 ID。由于这里是“.”,说明没有给定特定的 ID。
- T: 这是参考基因组中的碱基(在这个位点的原始碱基是 T)。
- C: 这是突变后的碱基(变异为 C)。
- .: 该字段表示质量分数,这里是“.”,表示没有相关质量信息。
- .: 该字段表示过滤条件,这里也是“.”,表示没有过滤。
- PR: 可能是与注释工具相关的标记字段,具体工具可能会定义该标记的用途。
注释信息
1 | ANN=C|stop_lost|HIGH|OPN4|ENSGALG00000001934|transcript|ENSGALT00000002989.4|protein_coding|12/12|c.1585T>C|p.Ter529Argext*?|1857/1985|1585/1587|529/528||,C|intron_variant|MODIFIER|WAPL|ENSGALG00000001907|transcript|ENSGALT00000066476.2|protein_coding|1/20|c.-441+8919A>G||||||,C|intron_variant|MODIFIER|WAPL|ENSGALG00000001907|transcript|ENSGALT00000101872.1|protein_coding|1/19|c.-441+8919A>G|||||| |
这是由 ANN 字段表示的注释信息,描述了变异在多个基因和转录本中的影响。每个变异的影响用管道符(|)分隔。下面,我们分解这个字段:
第一个注释块:关于 OPN4 基因的突变
1 | C|stop_lost|HIGH|OPN4|ENSGALG00000001934|transcript|ENSGALT00000002989.4|protein_coding|12/12|c.1585T>C|p.Ter529Argext*?|1857/1985|1585/1587|529/528|| |
- C: 变异碱基。
- stop_lost: 突变类型是 终止密码子丢失,即终止密码子突变成了编码氨基酸的密码子,可能导致蛋白质延长。
- HIGH: 变异的影响等级是 高影响。
- OPN4: 受影响的基因是 OPN4。
- ENSGALG00000001934: OPN4 基因的 Ensembl 基因ID。
- transcript: 注释的是转录本层面的变异。
- ENSGALT00000002989.4: 转录本 ID 为 ENSGALT00000002989.4。
- protein_coding: 转录本的生物类型是 蛋白编码。
- 12/12: 该变异发生在转录本的第12个外显子中(总共12个外显子)。
- c.1585T>C: cDNA 变化,表明在 cDNA 序列中的第 1585 个碱基由 T 变为 C。
- p.Ter529Argext?*: 蛋白质层面的变化,终止密码子(Ter)丢失,导致蛋白质从 529 位的终止密码子变为精氨酸(Arg),并可能进一步延长蛋白质链。
- 1857/1985: 变异发生在转录本的第 1857 个碱基位置(总长为 1985 个碱基)。
- 1585/1587: cDNA 层面的变化发生在第 1585 个核苷酸(总共 1587 个)。
- 529/528: 该突变涉及的氨基酸位置是 529(总长 528 个氨基酸)。
第二个注释块:关于 WAPL 基因的突变(转录本 1: ENSGALT00000066476.2)
1 | C|intron_variant|MODIFIER|WAPL|ENSGALG00000001907|transcript|ENSGALT00000066476.2|protein_coding|1/20|c.-441+8919A>G|||||| |
- C: 变异碱基。
- intron_variant: 突变类型是 内含子变异,位于内含子区域内,不直接影响蛋白质的编码序列。
- MODIFIER: 变异的影响等级为 修饰类影响(通常影响较小)。
- WAPL: 受影响的基因是 WAPL。
- ENSGALG00000001907: WAPL 基因的 Ensembl 基因ID。
- ENSGALT00000066476.2: 这是 WAPL 基因的一个转录本 ID。
- 1/20: 变异发生在第1个内含子中(WAPL 基因共20个内含子)。
- c.-441+8919A>G: 变异的具体位置及变化,位于第1个内含子的远离剪接位点处(+8919表示距离内含子开始处较远的位置,A>G代表A突变为G)。
第三个注释块:关于 WAPL 基因的突变(转录本 2: ENSGALT00000101872.1)
1 | C|intron_variant|MODIFIER|WAPL|ENSGALG00000001907|transcript|ENSGALT00000101872.1|protein_coding|1/19|c.-441+8919A>G|||||| |
该注释与第二个注释块非常相似,只不过它涉及的是 WAPL 基因的另一个转录本 ENSGALT00000101872.1,而且这个转录本有19个内含子(前一个转录本有20个)。
基因型信息
1 | GT 0/0 0/0 0/0 0/0 0/0 0/0 0/0 0/0 0/0 |
- GT: 表示基因型。
- 0/0: 在所有样本中,这个位点是纯合参考型(即没有发生突变,基因型是参考基因中的原始碱基 T,而不是变异的 C)。
总结:
- 这个位点的变异在 OPN4 基因中的突变是 终止密码子丢失,影响为 高影响。这个变异可能导致蛋白质延长,影响其功能。
- 在 WAPL 基因的两个转录本中,这个位点的变异是 内含子变异,影响较小(修饰影响,通常不会直接影响蛋白质功能)。
- 基因型信息显示,这些样本在这个位点都是参考基因型(0/0),即没有发生突变。
如果你需要更深入的分析,或者想要知道如何根据这些信息设计进一步的研究步骤,随时告诉我!
终止密码子的丢失(stop lost)导致蛋白质延长,通常会显著影响蛋白质的功能,具体的影响取决于几个关键因素:
1. 终止密码子后续序列的性质:
当终止密码子丢失后,翻译过程会继续,直至遇到下一个终止密码子或达到 mRNA 的末端。在这种情况下,延长的蛋白质链将包含额外的氨基酸序列。该额外序列是否影响功能,取决于它的性质:
- 如果延长的序列是无功能或不稳定的,可能导致蛋白质在细胞中折叠不正确或功能异常,最终可能会被细胞降解。
- 如果延长的序列干扰了功能域,可能会影响蛋白质的生物学功能。例如,如果这些新增的氨基酸改变了蛋白质的结构,尤其是影响了活性中心或结合位点,可能会导致蛋白质失去功能或功能异常。
2. 蛋白质的结构与功能:
蛋白质通常依赖于其精确的三维结构来执行生物功能。终止密码子丢失可能导致:
- 蛋白质的折叠问题:延长的蛋白质可能无法正确折叠,形成非功能性蛋白质或不稳定的结构。
- 新的功能域形成:在少数情况下,延长的序列可能会形成新的功能域,但通常情况下这会干扰蛋白质的正常功能。
3. 蛋白质降解:
终止密码子的丢失有时会导致翻译继续到 mRNA 的尾部,并且可能会触发一种称为 无义介导的 mRNA 降解(Nonsense-Mediated Decay, NMD) 的机制。这种机制会导致异常延长的 mRNA 被细胞识别并降解,从而防止产生功能不正常的蛋白质。如果 mRNA 被降解,蛋白质根本就不会被合成。
4. 功能影响的实际例子:
有许多疾病就是由终止密码子的丢失引起的。例如:
- DMD(杜氏肌营养不良症):由于DMD基因的终止密码子丢失,导致合成异常长的肌营养不良蛋白,最终导致蛋白质功能缺失。
- 肿瘤抑制基因突变:某些肿瘤抑制基因的终止密码子丢失会使肿瘤抑制蛋白失去功能,进而促进癌症的发展。
5. 延长的蛋白质是否影响蛋白质的定位和稳定性:
蛋白质通常需要特定的信号序列来确定它们在细胞中的定位。终止密码子的丢失可能导致蛋白质延长后,原本的信号序列被打乱,或者形成新的信号序列,从而导致蛋白质被错误地运输或局部化。此外,延长的蛋白质可能变得不稳定,易被细胞降解系统处理。
总结:
终止密码子的丢失导致蛋白质延长,通常会对蛋白质的功能产生负面影响。这种延长可能导致蛋白质功能丧失、不稳定或被细胞降解,甚至可能导致疾病的发生。具体的功能影响需要结合突变位置、延长后的序列及其在蛋白质中的作用进行更详细的分析。
如果你正在研究某个特定蛋白质并遇到终止密码子丢失的变异,可以使用工具预测这种延长对蛋白质功能的影响,或者进行实验验证。如果你需要,我可以帮助你了解如何进一步分析这种突变的影响。
做了一个脚本和exe,部署到网页上了
library(shiny)
定义 UI
ui <- fluidPage(
应用程序标题
titlePanel(“分类名称匹配”),
侧栏布局 - 用户输入和操作
sidebarLayout(
sidebarPanel(
h3(“输入数据”),
# 复制粘贴第一批数据
textAreaInput("first_data", "粘贴第一批数据:",
placeholder = "格式:分类名称(Tab键分隔)中文名称",
rows = 10),
# 复制粘贴第二批数据
textAreaInput("second_data", "粘贴第二批数据:",
placeholder = "格式:分类名称",
rows = 10),
actionButton("process", "生成结果"),
downloadButton("downloadData", "下载生成的文件")
),
# 主面板 - 显示部分结果
mainPanel(
h3("部分生成的结果:"),
tableOutput("preview")
)
)
)
定义服务器逻辑
server <- function(input, output) {
处理数据
processed_data <- eventReactive(input$process, {
req(input$first_data, input$second_data)
# 读取第一批数据并分割成表格
first_data_lines <- strsplit(input$first_data, "\n")[[1]]
first_data <- do.call(rbind, strsplit(first_data_lines, "\t"))
first_data <- data.frame(scientific = first_data[, 1], chinese = first_data[, 2], stringsAsFactors = FALSE)
# 读取第二批数据并分割成表格
second_data_lines <- strsplit(input$second_data, "\n")[[1]]
second_data <- data.frame(scientific = second_data_lines, stringsAsFactors = FALSE)
# 匹配第二批数据中的分类名称到第一批数据,保持第二批数据顺序
matched_data <- merge(second_data, first_data, by = "scientific", all.x = TRUE, sort = FALSE)
# 如果没有匹配到,显示为 NA
matched_data$chinese[is.na(matched_data$chinese)] <- "未找到对应名称"
return(matched_data)
})
显示部分结果
output$preview <- renderTable({
head(processed_data(), 10) # 只展示前 10 行
})
生成结果文件并提供下载
output$downloadData <- downloadHandler(
filename = function() { paste(“result_”, Sys.Date(), “.txt”, sep = “”) },
content = function(file) {
write.table(processed_data(), file, row.names = FALSE, col.names = FALSE, sep = “\t”, quote = FALSE)
}
)
}
启动 Shiny 应用
shinyApp(ui = ui, server = server)
根据你提供的鸡种信息,通常鸡可以根据其用途分为蛋鸡、肉鸡或兼用鸡(即兼顾产蛋和肉用)。以下是这些鸡种的大致分类:
蛋鸡(以产蛋为主):
- 东乡蓝蛋鸡(以产蓝色蛋壳著名)
- 江西丝毛鸡(虽然有食用价值,但以产蛋为主)
- 白色莱格恩鸡(世界著名高产蛋鸡)
- 阿劳卡纳鸡(以蓝蛋著名)
- 天府乌骨鸡(主要用于药用和产蛋)
- 眉山乌骨鸡
- 九圆乌骨鸡
- 金阳丝毛鸡
肉鸡(以肉用为主):
- 印度原鸡(Gallus gallus murghi)
- 马来原鸡(Gallus gallus spadiceus)
- 印尼本地鸡
- 泰国本地鸡
- 越南本地鸡
- 文昌鸡
- 云南鸡
- 西双版纳斗鸡
- 尼西鸡
- 独龙鸡
- 大围山迷你鸡
- 广西鸡
- 广州鸡
- 石棉草鸡
- 彭县黄鸡
- 米易鸡
- 元宝鸡
- 郎山鸡
- 陆溪斗鸡
- 寿光鸡
- 固始鸡
- 边鸡
- 北京油鸡
- 新疆本地鸡
- 和田黑鸡
- 南疆斗鸡
- 吐鲁番斗鸡
- 西藏鸡(各地区)
- 孟加拉本地鸡
- 印度本地鸡
- 巴基斯坦本地鸡
- 阿富汗本地鸡
- 伊朗本地鸡
- 康沃尔鸡(专用肉鸡,尤其是用于鸡肉生产)
- 罗得岛红鸡(也可用作兼用鸡)
兼用鸡(蛋肉兼用):
- 红原鸡(Gallus gallus bankiva)
- 普通原鸡(Gallus gallus gallus)
- 越南原鸡(Gallus gallus jabouillei)
- 峨眉黑鸡
- 彭县黄鸡
- 白色普利茅斯岩鸡(兼顾肉用和蛋用)
- 印度商用鸡、伊朗商用肉鸡(主要用于肉鸡生产,但也产蛋)
需要注意的特殊品种:
- 文昌鸡:文昌鸡是海南的名优品种,虽然以肉用为主,但也有一定的产蛋能力。
- 越南、泰国本地鸡:这些本地鸡大多为兼用鸡,但主要用于肉用。
这个分类大体上是根据各鸡种的传统用途和表现,如果有进一步的需求或者需要了解更详细的生产特性,可以针对特定品种做进一步的深入了解。
http://animal.omics.pro/code/index.php/ChickenVar
打开网页搜索opn4
6 3076985 A/T T 0.124 synonymous_variant LOW OPN4 rs317186078 6:3051198
Gallus_gallus_bankiva(4):0.500
Gallus_gallus_gallus(6):0.333
Gallus_gallus_jabouillei(25):0.360
Gallus_gallus_murghi(52):0.135
Gallus_gallus_spadiceus(43):0.070
Indonesia_Native_Chicken(35):0.200
Thailand_Native_Chicken(6):0.250
Vietnam_Native_Chicken(7):0.286
Wenchang_Chicken(1):0.000
Yunnan_Chicken(11):0.136
Xishuangbanna_Game_Chicken(9):0.333
Nixi_Chicken(12):0.000
Dulong_Chicken(7):0.071
Daweishan_Mini_Chicken(8):0.062
Guangxi_Chicken(6):0.083
Guangzhou_Chicken(2):0.250
Jiangxi_Silkies(20):0.050
Anyi_Gray_Chicken(5):0.100
Dongxiang_Blue-eggshell_Chicken(6):0.167
Tianfu_Black-bone_Chicken(4):0.250
Shimian_Caoke_Chicken(2):0.000
Jiuyuan_Black-bone_Chicken(5):0.000
Jinyang_Silky_Chicken(6):0.000
Emei_Black_Chicken(4):0.000
Pengxian_Yellow_Chicken(6):0.000
Muchuan_Black-bone_Chicken(5):0.000
Miyi_Chicken(4):0.125
YuanBao_Chicken(21):0.000
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(9):0.111
Shouguang_Chicken(8):0.250
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.125
Beijing_You_Chicken(11):0.227
Dagu_Chicken(8):0.000
Xinjiang_Native_Chicken(6):0.250
Hetian_Black_Chicken(8):0.062
Southern_Xinjiang_Game_Chicken(8):0.125
Turpan_Game_Chicken(8):0.125
Tibetan_Chicken(130):0.142
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(7):0.143
Bengal_Native_Chicken(13):0.154
India_Native_Chicken(47):0.085
Pakistan_Native_Chicken(37):0.176
Afghan_Native_Chicken(11):0.136
Iran_Native_Chicken(182):0.080
Iran_Commercial_Broiler(4):0.125
White_Leghorn_Chicken(13):0.154
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):1.000
White_Plymouth_Rock_Chicken(1):0.000
从你提供的这些数据中,我们可以通过对不同鸡种的频率(如等位基因频率)进行分析,来判断蛋鸡和肉鸡之间是否存在明显差异。
通常,蛋鸡和肉鸡之间在基因组水平上的差异体现在以下几个方面:
- 选择性育种目标不同:蛋鸡主要被选择用于高产蛋量,而肉鸡主要用于快速生长和较高的肌肉重量。因此,蛋鸡和肉鸡在与产蛋相关基因和生长发育相关基因的多态性上可能有所不同。
- 遗传背景差异:许多肉鸡和蛋鸡品种因为长期的育种历史,已经在基因频率上表现出一些差异。
让我们尝试从数据中提取一些初步观察:
1. 蛋鸡的表现(重点看蛋鸡的等位基因频率):
- 白色莱格恩鸡:0.154(蛋鸡中的高频品种)
- 江西丝毛鸡:0.050(蛋鸡)
- 东乡蓝蛋鸡:0.167
- 天府乌骨鸡:0.250
- 九圆乌骨鸡:0.000
- 眉山乌骨鸡:0.000
- 阿劳卡纳鸡:0.000
观察:蛋鸡中等位基因频率相对较低,一些蛋鸡如“江西丝毛鸡”、“九圆乌骨鸡”和“阿劳卡纳鸡”的频率甚至是0,表明这些品种可能没有携带此位点的突变。
2. 肉鸡的表现(重点看肉鸡的等位基因频率):
- 康沃尔鸡:0.000(典型肉鸡)
- 文昌鸡:0.000(肉鸡)
- 越南本地鸡:0.286(肉鸡)
- 泰国本地鸡:0.250(肉鸡)
- 固始鸡:0.000
- 新疆本地鸡:0.250(肉鸡)
- 南疆斗鸡:0.125
观察:肉鸡的等位基因频率在一些品种中偏高,例如“泰国本地鸡”和“越南本地鸡”分别为0.250和0.286。而一些肉鸡的频率为0,如“文昌鸡”和“固始鸡”。
3. 蛋鸡与肉鸡的对比:
- 在一些蛋鸡中,等位基因频率较低,甚至为零(如“九圆乌骨鸡”、“阿劳卡纳鸡”等),而在部分肉鸡品种中(如“越南本地鸡”0.286和“泰国本地鸡”0.250)等位基因频率较高。这可能与肉鸡更注重生长发育相关基因的选择有关。
- 一些肉鸡的频率为零(如“康沃尔鸡”、“文昌鸡”),而有些蛋鸡的频率稍高(如“白色莱格恩鸡”0.154)。这些差异可能表明不同鸡种的遗传背景和选择压力有所不同。
结论:
从这些频率值可以看出,蛋鸡和肉鸡在等位基因频率上确实存在一些差异。总体来看,部分肉鸡的等位基因频率相对较高,而一些蛋鸡的等位基因频率则趋向于较低,甚至为零。这可能反映了不同育种目标带来的基因选择压力,肉鸡更多注重快速生长和体型发育,而蛋鸡则更注重高产蛋量,这会导致它们在一些位点的基因频率上有所不同。
如果要进一步确认是否存在显著的统计学差异,可以对这些频率数据进行统计分析,例如使用卡方检验来比较蛋鸡和肉鸡的等位基因频率是否有显著差异。
从你提供的数据中,原鸡(Gallus gallus,包括不同亚种,如红原鸡(Gallus gallus bankiva)、普通原鸡(Gallus gallus gallus)、越南原鸡(Gallus gallus jabouillei)、印度原鸡(Gallus gallus murghi)、马来原鸡(Gallus gallus spadiceus))的等位基因频率与家养鸡(肉鸡、蛋鸡)相比,确实可以看出一些差异。我们可以进一步比较这些原鸡与家养鸡的等位基因频率,以找出它们之间的区别。
1. 原鸡的表现(重点看原鸡的等位基因频率):
- 红原鸡(Gallus gallus bankiva):0.500
- 普通原鸡(Gallus gallus gallus):0.333
- 越南原鸡(Gallus gallus jabouillei):0.360
- 印度原鸡(Gallus gallus murghi):0.135
- 马来原鸡(Gallus gallus spadiceus):0.070
观察:在原鸡中,等位基因频率相对较高,特别是红原鸡的频率达到了0.500,普通原鸡和越南原鸡的频率也都超过了0.300。这表明这些原鸡的群体中有较高比例的个体携带了此突变位点。相比之下,印度原鸡和马来原鸡的等位基因频率较低,特别是马来原鸡的频率仅为0.070。
2. 原鸡与家养鸡的比较:
通过对比可以发现:
- 等位基因频率差异:原鸡的等位基因频率在一些亚种中相对较高(如红原鸡0.500),而家养鸡中的频率有明显的变异范围。一些家养鸡的等位基因频率较低甚至为零(如部分乌骨鸡和文昌鸡),而某些家养鸡(如泰国、越南本地鸡)中频率较高。
- 家养鸡的多样性较大:家养鸡的育种目标(如产蛋或肉用)导致了基因频率的多样性更大。例如,白色莱格恩鸡(蛋鸡)和康沃尔鸡(肉鸡)分别在等位基因频率上表现出差异(莱格恩鸡为0.154,而康沃尔鸡为0)。
- 驯化与选择的影响:原鸡的基因频率可能较为稳定,因为它们未经过强烈的人为选择。而家养鸡则经过长时间的育种选择,可能导致了某些位点的频率显著改变。这反映在家养鸡中的基因频率变异比原鸡更大。
3. 原鸡和家养鸡的差异可能来源于驯化和选择压力:
- 驯化的影响:家养鸡是从原鸡驯化而来,在此过程中人类对家禽进行了选择性育种,这种选择压力导致了家养鸡的基因频率发生了改变。例如,家养鸡为了提高生产性能(如产蛋、肉用等)可能会偏向于携带特定的基因变异,而原鸡则没有经历这种选择压力,因此在基因频率上会与家养鸡有所不同。
- 特定基因的选择压力:例如,肉鸡更注重生长和体型发育,蛋鸡更注重高产蛋量。这些选择压力可能会导致家养鸡在某些位点上的基因频率发生较大变化,而这些变化在原鸡中可能不存在或表现较弱。
结论:
原鸡和家养鸡在等位基因频率上存在一定的差异,这种差异主要是由于驯化和选择压力造成的。家养鸡经过长期的选择性育种,导致了其在一些基因位点上的频率与原鸡不同。例如,家养鸡中的等位基因频率更具多样性,部分鸡种的频率较高(如泰国、越南本地鸡),而部分则较低甚至为零(如文昌鸡、乌骨鸡)。原鸡的频率相对较高且较为稳定,这反映了它们在未经过多次人工选择的自然状态下的基因频率。
如果需要进一步的统计分析,可以通过计算家养鸡与原鸡群体的基因频率差异来量化这种差异。
missense_variant OPN4 rs733302250 6:3054417
6 3080204 G/A A 0.046 missense_variant MODERATE OPN4 rs733302250 6:3054417
Gallus_gallus_bankiva(4):0.000
Gallus_gallus_gallus(6):0.583
Gallus_gallus_jabouillei(27):0.056
Gallus_gallus_murghi(57):0.018
Gallus_gallus_spadiceus(43):0.093
Indonesia_Native_Chicken(36):0.069
Thailand_Native_Chicken(6):0.000
Vietnam_Native_Chicken(7):0.071
Wenchang_Chicken(1):0.000
Yunnan_Chicken(11):0.227
Xishuangbanna_Game_Chicken(9):0.056
Nixi_Chicken(12):0.000
Dulong_Chicken(7):0.000
Daweishan_Mini_Chicken(8):0.000
Guangxi_Chicken(5):0.300
Guangzhou_Chicken(4):0.000
Jiangxi_Silkies(20):0.025
Anyi_Gray_Chicken(5):0.100
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.100
Shimian_Caoke_Chicken(2):0.000
Jiuyuan_Black-bone_Chicken(5):0.100
Jinyang_Silky_Chicken(6):0.083
Emei_Black_Chicken(4):0.000
Pengxian_Yellow_Chicken(6):0.000
Muchuan_Black-bone_Chicken(5):0.000
Miyi_Chicken(5):0.100
YuanBao_Chicken(24):0.021
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(9):0.111
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.000
Beijing_You_Chicken(11):0.182
Dagu_Chicken(8):0.000
Xinjiang_Native_Chicken(6):0.083
Hetian_Black_Chicken(8):0.125
Southern_Xinjiang_Game_Chicken(8):0.125
Turpan_Game_Chicken(8):0.188
Tibetan_Chicken(135):0.041
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(7):0.000
Bengal_Native_Chicken(15):0.000
India_Native_Chicken(49):0.010
Pakistan_Native_Chicken(37):0.027
Afghan_Native_Chicken(11):0.000
Iran_Native_Chicken(182):0.036
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(13):0.000
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
翻译:
这是一个关于某个位点(位于染色体6:3080204上的G/A突变)的基因变异频率数据,涉及多个鸡种。该变异是一个错义突变,具有中等效应(MODERATE),影响了基因OPN4,并且该突变位点与rs733302250相关。每个鸡种旁边的数值表示这个突变在该鸡种群体中的等位基因频率。
按照原鸡、蛋鸡、肉鸡和其他鸡种的分类:
1. 原鸡
- 红原鸡(Gallus gallus bankiva):0.000
- 普通原鸡(Gallus gallus gallus):0.583
- 越南原鸡(Gallus gallus jabouillei):0.056
- 印度原鸡(Gallus gallus murghi):0.018
- 马来原鸡(Gallus gallus spadiceus):0.093
2. 蛋鸡
- 东乡蓝蛋鸡(Dongxiang Blue-eggshell Chicken):0.000
- 天府乌骨鸡(Tianfu Black-bone Chicken):0.100
- 九圆乌骨鸡(Jiuyuan Black-bone Chicken):0.100
- 金阳丝毛鸡(Jinyang Silky Chicken):0.083
- 江西丝毛鸡(Jiangxi Silkies):0.025
- 白色莱格恩鸡(White Leghorn Chicken):0.000
- 阿劳卡纳蓝蛋鸡(Araucana Blue-eggshell Chicken):0.000
3. 肉鸡
- 康沃尔鸡(Cornish Chicken):0.000
- 罗得岛红鸡(Rhode Island Red Chicken):0.000
- 白色普利茅斯岩鸡(White Plymouth Rock Chicken):0.000
- 文昌鸡(Wenchang Chicken):0.000
- 米易鸡(Miyi Chicken):0.100
- 越南本地鸡(Vietnam Native Chicken):0.071
- 泰国本地鸡(Thailand Native Chicken):0.000
- 广西鸡(Guangxi Chicken):0.300
- 广州鸡(Guangzhou Chicken):0.000
- 彭县黄鸡(Pengxian Yellow Chicken):0.000
- 固始鸡(Gushi Chicken):0.000
- 北京油鸡(Beijing You Chicken):0.182
- 新疆本地鸡(Xinjiang Native Chicken):0.083
- 南疆斗鸡(Southern Xinjiang Game Chicken):0.125
- 吐鲁番斗鸡(Turpan Game Chicken):0.188
- 西双版纳斗鸡(Xishuangbanna Game Chicken):0.056
4. 其他鸡种
- 云南鸡(Yunnan Chicken):0.227
- 尼西鸡(Nixi Chicken):0.000
- 独龙鸡(Dulong Chicken):0.000
- 大围山迷你鸡(Daweishan Mini Chicken):0.000
- 安义灰鸡(Anyi Gray Chicken):0.100
- 峨眉黑鸡(Emei Black Chicken):0.000
- Muchuan Black-bone Chicken:0.000
- 元宝鸡(YuanBao Chicken):0.021
- 朗山鸡(Langshan Chicken):0.000
- 寿光鸡(Shouguang Chicken):0.000
- 边鸡(Bian Chicken):0.000
- 大谷鸡(Dagu Chicken):0.000
- 西藏鸡(Tibetan Chicken):0.041
- 斯里兰卡本地鸡(Sri Lanka Native Chicken):0.000
- 孟加拉本地鸡(Bengal Native Chicken):0.000
- 印度本地鸡(India Native Chicken):0.010
- 巴基斯坦本地鸡(Pakistan Native Chicken):0.027
- 阿富汗本地鸡(Afghan Native Chicken):0.000
- 伊朗本地鸡(Iran Native Chicken):0.036
- 伊朗商用肉鸡(Iran Commercial Broiler):0.000
总结:
原鸡中,普通原鸡(Gallus gallus gallus)的等位基因频率较高,达到了0.583,远高于其他原鸡种。蛋鸡和肉鸡的频率普遍较低,大部分蛋鸡品种如白色莱格恩鸡、阿劳卡纳蓝蛋鸡等的频率为0。而在肉鸡中,广西鸡的频率较高,达到了0.300。
6 3080808 A/G G 0.407 missense_variant MODERATE OPN4 rs314270903 6:3055021
注:原鸡鸡种包括:红原鸡4、原鸡5、越南原鸡27、印度原鸡68、马来原鸡45;
蛋鸡鸡种包括:白色莱格霍恩鸡13、阿劳卡纳蓝壳鸡6、东乡蓝壳鸡6;
肉鸡鸡种包括:康沃尔鸡1、伊朗商用肉鸡4、天府黑骨鸡5、米易鸡5、寿光鸡8、大谷鸡8、和田黑鸡8
在这个数据集中,我们看到不同鸡种在某个特定基因位点的等位基因频率。这些频率代表了在每个鸡种中该等位基因的出现比例。以下是按原鸡、蛋鸡、肉鸡及其他鸡种的分类,并对其进行分析。
1. 原鸡的表现:
- 红原鸡(Gallus gallus bankiva):0.625 4
- 普通原鸡(Gallus gallus gallus):0.500 5
- 越南原鸡(Gallus gallus jabouillei):0.460 27
- 印度原鸡(Gallus gallus murghi):0.382 68
- 马来原鸡(Gallus gallus spadiceus):0.349 45
分析:
- 原鸡的等位基因频率在不同亚种间有所差异,最高的为红原鸡(0.625),最低的为马来原鸡(0.349)。这显示出原鸡群体内有较为显著的基因频率差异,可能与其地理分布和不同的生态适应性有关。
2. 蛋鸡的表现:
- 东乡蓝蛋鸡:0.500 6
- 天府乌骨鸡:0.500 5
- 九圆乌骨鸡:0.500 5
- 江西丝毛鸡:0.475 20
- 阿劳卡纳蓝蛋鸡:0.667 6
- 白色莱格恩鸡:0.731 13
分析:
- 蛋鸡中的等位基因频率大多在0.500左右,而阿劳卡纳蓝蛋鸡(0.667)和白色莱格恩鸡(0.731)则表现出更高的等位基因频率。特别是白色莱格恩鸡,作为高产蛋鸡,它的基因频率偏高可能与长期的育种选择有关,旨在提高产蛋性能。
3. 肉鸡的表现:
- 康沃尔鸡:0.500
- 罗得岛红鸡:0.000
- 白色普利茅斯岩鸡:0.500
- 文昌鸡:0.000
- 米易鸡:0.875
- 广西鸡:0.800
- 越南本地鸡:0.214
- 泰国本地鸡:0.500
- 彭县黄鸡:0.167
分析:
- 在肉鸡中,米易鸡(0.875)和广西鸡(0.800)的等位基因频率非常高,而罗得岛红鸡和文昌鸡则为0。较高的等位基因频率可能表明这些肉鸡在特定的生长和体型发育基因上存在强烈的选择压力,而频率为0的鸡种可能与此位点关联性较低或未选择该等位基因。
4. 其他鸡种的表现:
- 大围山迷你鸡:0.562
- 南疆斗鸡:0.786
- 元宝鸡:0.909
- 西藏鸡:0.454
- 孟加拉本地鸡:0.467
- 巴基斯坦本地鸡:0.230
- 伊朗本地鸡:0.334
分析:
- 其他鸡种中,元宝鸡(0.909)的等位基因频率非常高,几乎是所有鸡种中最高的。南疆斗鸡(0.786)和大围山迷你鸡(0.562)也表现出较高的频率,可能与这些鸡种的遗传背景或者生存环境有关。
- 巴基斯坦本地鸡(0.230)和伊朗本地鸡(0.334)则表现出较低的频率,显示出不同地区的鸡种在该等位基因上的选择可能较为松散。
总结:
- 原鸡和家养鸡的差异:原鸡群体中的等位基因频率相对稳定且不均匀,最高的红原鸡达到了0.625,而部分原鸡种的频率较低,如印度原鸡(0.382)。相比之下,家养鸡(尤其是蛋鸡和肉鸡)由于长时间的人工选择,基因频率变化更显著,频率高低差异较大,特别是白色莱格恩鸡和元宝鸡的频率明显较高。
- 蛋鸡和肉鸡的区别:蛋鸡(如白色莱格恩鸡)和肉鸡(如米易鸡、广西鸡)在等位基因频率上也表现出较大差异。蛋鸡频率较高,可能与其高产蛋性能相关;肉鸡中部分品种频率非常高(如米易鸡),反映了肉用特性在育种中的显著作用。
- 其他鸡种:其他鸡种表现出的频率差异主要与其环境适应性或区域性育种选择有关。
这显示了鸡种在该特定位点上存在显著的基因多样性,不同品种的育种目标(蛋用、肉用)和地理区域差异可能是导致这些差异的关键原因。
6 3081342 T/C C 0.077 missense_variant MODERATE OPN4 rs318086095 6:3055555
Gallus_gallus_bankiva(4):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(27):0.000
Gallus_gallus_murghi(51):0.010
Gallus_gallus_spadiceus(45):0.011
Indonesia_Native_Chicken(35):0.086
Thailand_Native_Chicken(6):0.167
Vietnam_Native_Chicken(7):0.143
Wenchang_Chicken(1):0.500
Yunnan_Chicken(11):0.000
Xishuangbanna_Game_Chicken(9):0.000
Nixi_Chicken(12):0.000
Dulong_Chicken(7):0.000
Daweishan_Mini_Chicken(8):0.000
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(1):0.000
Jiangxi_Silkies(20):0.050
Anyi_Gray_Chicken(5):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.083
Tianfu_Black-bone_Chicken(3):0.000
Shimian_Caoke_Chicken(3):0.167
Jiuyuan_Black-bone_Chicken(4):0.000
Jinyang_Silky_Chicken(6):0.000
Emei_Black_Chicken(3):0.000
Pengxian_Yellow_Chicken(6):0.500
Muchuan_Black-bone_Chicken(3):0.167
Miyi_Chicken(4):0.000
YuanBao_Chicken(22):0.000
Langshan_Chicken(10):0.050
Luxi_Game_Chicken(9):0.167
Shouguang_Chicken(7):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.188
Beijing_You_Chicken(11):0.091
Dagu_Chicken(7):0.286
Xinjiang_Native_Chicken(6):0.250
Hetian_Black_Chicken(7):0.143
Southern_Xinjiang_Game_Chicken(8):0.000
Turpan_Game_Chicken(8):0.125
Tibetan_Chicken(126):0.024
Araucana_Blue-eggshell_Chicken(6):0.250
Sri_Lanka_Native_Chicken(7):0.071
Bengal_Native_Chicken(15):0.067
India_Native_Chicken(49):0.031
Pakistan_Native_Chicken(37):0.041
Afghan_Native_Chicken(11):0.045
Iran_Native_Chicken(181):0.188
Iran_Commercial_Broiler(4):0.125
White_Leghorn_Chicken(13):0.038
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
数据背景:
这是关于染色体6:3081342位置上的一个错义变异(T/C)的数据,变异影响基因OPN4,与标记rs318086095相关。该变异为中等效应(MODERATE),不同鸡种中该位点的等位基因频率也有所差异。接下来将按照原鸡、蛋鸡、肉鸡和其他鸡种分类进行分析。
1. 原鸡的表现:
- 红原鸡(Gallus gallus bankiva):0.000
- 普通原鸡(Gallus gallus gallus):0.000
- 越南原鸡(Gallus gallus jabouillei):0.000
- 印度原鸡(Gallus gallus murghi):0.010
- 马来原鸡(Gallus gallus spadiceus):0.011
分析:
- 原鸡在此位点上的等位基因频率非常低,几乎所有亚种的频率都接近于0,显示该等位基因在野生原鸡中并不常见,可能是由于其在自然选择中的作用不明显,或者该突变在这些群体中并未传播开来。
2. 蛋鸡的表现:
- 东乡蓝蛋鸡:0.083
- 天府乌骨鸡:0.000
- 九圆乌骨鸡:0.000
- 江西丝毛鸡:0.050
- 阿劳卡纳蓝蛋鸡:0.250
- 白色莱格恩鸡:0.038
分析:
- 蛋鸡在此位点的基因频率较低,但阿劳卡纳蓝蛋鸡的频率为0.250,相对较高,这可能与其特殊的遗传背景有关。白色莱格恩鸡等其他常见蛋鸡的频率较低,约在0.038-0.083之间,显示该位点的突变在蛋鸡群体中并不普遍。
3. 肉鸡的表现:
- 康沃尔鸡:0.000
- 罗得岛红鸡:0.000
- 白色普利茅斯岩鸡:0.000
- 文昌鸡:0.500
- 米易鸡:0.000
- 广西鸡:0.000
- 越南本地鸡:0.143
- 泰国本地鸡:0.167
- 彭县黄鸡:0.500
分析:
- 部分肉鸡在此位点的等位基因频率较高,特别是文昌鸡(0.500)和彭县黄鸡(0.500),它们在该位点的频率显著高于其他肉鸡,这表明这些品种可能携带了更多此类基因变异。其他肉鸡,如广西鸡和康沃尔鸡,该变异频率为0,可能意味着此突变与这些肉鸡的生长特性关联较小。
4. 其他鸡种的表现:
- 大围山迷你鸡:0.000
- 元宝鸡:0.000
- 朗山鸡:0.050
- 南疆斗鸡:0.000
- 西藏鸡:0.024
- 孟加拉本地鸡:0.067
- 印度本地鸡:0.031
- 巴基斯坦本地鸡:0.041
- 伊朗本地鸡:0.188
- 伊朗商用肉鸡:0.125
分析:
- 在其他鸡种中,伊朗本地鸡(0.188)和伊朗商用肉鸡(0.125)的频率较高,表明该位点的变异在这些地区的鸡群中有一定传播。相对而言,西藏鸡等其他鸡种的频率较低,表明这些鸡种可能不太受到该基因变异的影响。
总结:
- 原鸡在此基因位点的变异频率普遍很低,几乎不存在(接近0)。这表明该位点的突变在自然状态下并不常见。
- 蛋鸡中的阿劳卡纳蓝蛋鸡显示出相对较高的等位基因频率(0.250),这与其独特的遗传背景可能有关。其他蛋鸡(如白色莱格恩鸡等)的频率较低,表明该位点可能与产蛋性状的选择压力无显著关联。
- 肉鸡表现出频率较高的个体,如文昌鸡和彭县黄鸡,其基因频率高达0.500,可能表明此基因突变在这些品种中与其生长发育有关。
- 其他鸡种中,伊朗本地鸡的频率较高,可能与该地区的育种选择有关。
这个数据集显示了不同鸡种在该特定位点的遗传多样性,表明该突变在部分家养鸡品种中可能与特定表型相关,尤其是在肉鸡中具有较高的变异频率。
6 3082259 A/G A 0.262 missense_variant MODERATE OPN4 rs16526855 6:3056472
Gallus_gallus_bankiva(4):0.250
Gallus_gallus_gallus(5):0.800
Gallus_gallus_jabouillei(25):0.660
Gallus_gallus_murghi(47):0.617
Gallus_gallus_spadiceus(42):0.631
Indonesia_Native_Chicken(34):0.515
Thailand_Native_Chicken(6):0.833
Vietnam_Native_Chicken(7):0.714
Wenchang_Chicken(1):1.000
Yunnan_Chicken(12):0.625
Xishuangbanna_Game_Chicken(10):0.700
Nixi_Chicken(12):0.792
Dulong_Chicken(7):0.786
Daweishan_Mini_Chicken(8):0.500
Guangxi_Chicken(6):0.500
Guangzhou_Chicken(4):0.500
Jiangxi_Silkies(20):0.700
Anyi_Gray_Chicken(5):0.800
Dongxiang_Blue-eggshell_Chicken(6):0.750
Tianfu_Black-bone_Chicken(5):0.600
Shimian_Caoke_Chicken(4):0.250
Jiuyuan_Black-bone_Chicken(5):0.600
Jinyang_Silky_Chicken(6):0.833
Emei_Black_Chicken(5):1.000
Pengxian_Yellow_Chicken(6):0.750
Muchuan_Black-bone_Chicken(5):0.900
Miyi_Chicken(5):0.900
YuanBao_Chicken(22):0.909
Langshan_Chicken(9):1.000
Luxi_Game_Chicken(9):0.833
Shouguang_Chicken(8):1.000
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.688
Beijing_You_Chicken(11):0.364
Dagu_Chicken(8):1.000
Xinjiang_Native_Chicken(5):0.600
Hetian_Black_Chicken(8):0.875
Southern_Xinjiang_Game_Chicken(8):0.750
Turpan_Game_Chicken(8):0.750
Tibetan_Chicken(133):0.868
Araucana_Blue-eggshell_Chicken(6):1.000
Sri_Lanka_Native_Chicken(7):0.571
Bengal_Native_Chicken(15):0.767
India_Native_Chicken(42):0.881
Pakistan_Native_Chicken(34):0.632
Afghan_Native_Chicken(11):0.727
Iran_Native_Chicken(178):0.761
Iran_Commercial_Broiler(4):0.750
White_Leghorn_Chicken(13):0.769
Cornish_Chicken(1):1.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):1.000
背景信息:
你提供的这组数据是关于染色体6:3082259位置上的A/G突变(错义变异,MODERATE效应)在不同鸡种中的等位基因频率,变异影响基因OPN4,与标记rs16526855相关。该数据表示了不同鸡种在该位点上的等位基因A的频率。我们将根据原鸡、蛋鸡、肉鸡和其他鸡种的分类来解释这些频率的差异。
1. 原鸡的表现:
- 红原鸡(Gallus gallus bankiva):0.250
- 普通原鸡(Gallus gallus gallus):0.800
- 越南原鸡(Gallus gallus jabouillei):0.660
- 印度原鸡(Gallus gallus murghi):0.617
- 马来原鸡(Gallus gallus spadiceus):0.631
分析:
- 原鸡群体的等位基因频率较高,尤其是普通原鸡(0.800),显示出该基因变异在部分原鸡亚种中较为普遍。最低的为红原鸡(0.250),可能说明该基因变异在不同原鸡种中有显著差异。高频的原鸡种可能与其特定生态环境或基因选择压力相关。
2. 蛋鸡的表现:
- 东乡蓝蛋鸡:0.750
- 天府乌骨鸡:0.600
- 九圆乌骨鸡:0.600
- 江西丝毛鸡:0.700
- 阿劳卡纳蓝蛋鸡:1.000
- 白色莱格恩鸡:0.769
分析:
- 蛋鸡群体的等位基因频率较高,尤其是阿劳卡纳蓝蛋鸡(1.000),说明该变异在该品种中完全固定。其他蛋鸡如东乡蓝蛋鸡和白色莱格恩鸡的频率也非常高,表明这一变异可能与某些蛋鸡的特性相关,可能是长期育种的结果。
3. 肉鸡的表现:
- 康沃尔鸡:1.000
- 罗得岛红鸡:0.000
- 白色普利茅斯岩鸡:1.000
- 文昌鸡:1.000
- 米易鸡:0.900
- 广西鸡:0.500
- 越南本地鸡:0.714
- 泰国本地鸡:0.833
- 彭县黄鸡:0.750
分析:
- 肉鸡群体中的等位基因频率非常高,特别是康沃尔鸡、文昌鸡、白色普利茅斯岩鸡等的频率达到1.000,这意味着该基因变异在这些肉鸡品种中已经完全固定。部分品种如广西鸡的频率为0.500,表明在部分肉鸡中,该基因变异可能并未被完全选择。
4. 其他鸡种的表现:
- 大围山迷你鸡:0.500
- 元宝鸡:0.909
- 南疆斗鸡:0.750
- 西藏鸡:0.868
- 孟加拉本地鸡:0.767
- 印度本地鸡:0.881
- 巴基斯坦本地鸡:0.632
- 伊朗本地鸡:0.761
- 伊朗商用肉鸡:0.750
分析:
- 在其他鸡种中,元宝鸡、西藏鸡等显示出很高的等位基因频率(如元宝鸡0.909、西藏鸡0.868)。这些鸡种在其特定的地理或育种环境中,可能通过选择压力保留了该变异。印度、巴基斯坦、伊朗等地区的本地鸡品种也普遍显示出较高的基因频率,这表明该突变在这些地区的鸡种中较为常见。
总结:
- 原鸡的等位基因频率有显著差异,普通原鸡的等位基因频率最高(0.800),而红原鸡最低(0.250)。这表明即使在原鸡群体中,不同亚种对这一位点的基因选择压力也有所不同。
- 蛋鸡群体中,阿劳卡纳蓝蛋鸡的等位基因完全固定(1.000),而其他蛋鸡品种的频率也很高。这表明此突变可能与产蛋性能有关,或在这些品种的遗传选择过程中得到了强烈的选择。
- 肉鸡群体中,某些品种如康沃尔鸡、白色普利茅斯岩鸡、文昌鸡也显示出该基因变异的完全固定,表明该位点在肉鸡品种的选择育种中发挥了重要作用。
- 其他鸡种,尤其是一些本地鸡种,表现出较高的等位基因频率,这可能是由于地理、生态和遗传选择的影响。
总体来看,这个基因变异在家养鸡中普遍高频,尤其是那些经过大量人工选择的品种,如蛋鸡和肉鸡。这种高频可能与这些品种在驯化和育种过程中长期的选择压力相关,尤其是与某些经济性状(如生长速度、产蛋量等)相匹配的基因突变。
6 3082308 C/T C 0.292 synonymous_variant LOW OPN4 rs13561321 6:3056521
Gallus_gallus_bankiva(4):0.250
Gallus_gallus_gallus(6):0.833
Gallus_gallus_jabouillei(26):0.673
Gallus_gallus_murghi(48):0.740
Gallus_gallus_spadiceus(43):0.488
Indonesia_Native_Chicken(35):0.500
Thailand_Native_Chicken(6):0.917
Vietnam_Native_Chicken(6):0.667
Wenchang_Chicken(1):1.000
Yunnan_Chicken(12):0.542
Xishuangbanna_Game_Chicken(10):0.850
Nixi_Chicken(11):0.727
Dulong_Chicken(7):0.786
Daweishan_Mini_Chicken(8):0.562
Guangxi_Chicken(6):0.500
Guangzhou_Chicken(3):0.667
Jiangxi_Silkies(20):0.575
Anyi_Gray_Chicken(5):0.800
Dongxiang_Blue-eggshell_Chicken(6):0.667
Tianfu_Black-bone_Chicken(5):0.400
Shimian_Caoke_Chicken(4):0.375
Jiuyuan_Black-bone_Chicken(5):0.600
Jinyang_Silky_Chicken(6):0.833
Emei_Black_Chicken(5):1.000
Pengxian_Yellow_Chicken(6):0.667
Muchuan_Black-bone_Chicken(5):0.800
Miyi_Chicken(5):0.800
YuanBao_Chicken(22):0.909
Langshan_Chicken(10):0.650
Luxi_Game_Chicken(9):0.722
Shouguang_Chicken(8):1.000
Gushi_Chicken(8):0.062
Bian_Chicken(8):0.625
Beijing_You_Chicken(11):0.409
Dagu_Chicken(8):1.000
Xinjiang_Native_Chicken(6):0.667
Hetian_Black_Chicken(8):0.688
Southern_Xinjiang_Game_Chicken(8):0.875
Turpan_Game_Chicken(8):0.875
Tibetan_Chicken(138):0.815
Araucana_Blue-eggshell_Chicken(6):1.000
Sri_Lanka_Native_Chicken(7):0.571
Bengal_Native_Chicken(14):0.679
India_Native_Chicken(41):0.841
Pakistan_Native_Chicken(35):0.586
Afghan_Native_Chicken(10):0.750
Iran_Native_Chicken(179):0.726
Iran_Commercial_Broiler(4):0.625
White_Leghorn_Chicken(13):0.769
Cornish_Chicken(1):1.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.500
背景信息:
这组数据表示了染色体6:3082308位点的C/T突变(同义突变,LOW效应)在不同鸡种中的等位基因频率。该变异影响基因OPN4,与标记rs13561321相关。这个突变不会改变编码蛋白的氨基酸序列,但仍可能对基因表达或调控有潜在影响。接下来,将按原鸡、蛋鸡、肉鸡和其他鸡种进行分析。
1. 原鸡的表现:
- 红原鸡(Gallus gallus bankiva):0.250
- 普通原鸡(Gallus gallus gallus):0.833
- 越南原鸡(Gallus gallus jabouillei):0.673
- 印度原鸡(Gallus gallus murghi):0.740
- 马来原鸡(Gallus gallus spadiceus):0.488
分析:
- 原鸡中的等位基因频率从0.250(红原鸡)到0.833(普通原鸡)不等,显示出不同原鸡亚种之间的显著差异。普通原鸡和印度原鸡的频率较高,可能表明该位点的变异在这些群体中有一定的选择性保留,可能与其生态适应或遗传背景相关。
- 红原鸡的频率较低(0.250),显示该位点变异在部分原鸡群体中较少见。
2. 蛋鸡的表现:
- 东乡蓝蛋鸡:0.667
- 天府乌骨鸡:0.400
- 九圆乌骨鸡:0.600
- 江西丝毛鸡:0.575
- 阿劳卡纳蓝蛋鸡:1.000
- 白色莱格恩鸡:0.769
分析:
- 阿劳卡纳蓝蛋鸡在此位点上的等位基因频率为1.000,意味着该突变在此品种中已经完全固定。其他蛋鸡如东乡蓝蛋鸡、九圆乌骨鸡、白色莱格恩鸡的频率也较高,约为0.600-0.769,表明这些蛋鸡群体中该突变较为常见。
- 天府乌骨鸡的频率较低(0.400),表明此位点在该品种中并没有得到广泛选择。
3. 肉鸡的表现:
- 康沃尔鸡:1.000
- 罗得岛红鸡:0.000
- 白色普利茅斯岩鸡:0.500
- 文昌鸡:1.000
- 米易鸡:0.800
- 广西鸡:0.500
- 越南本地鸡:0.667
- 泰国本地鸡:0.917
- 彭县黄鸡:0.667
分析:
- 康沃尔鸡和文昌鸡的等位基因频率均为1.000,说明该突变在这些肉鸡品种中完全固定。其他肉鸡如米易鸡和泰国本地鸡的频率也较高,显示该突变在大部分肉鸡品种中都普遍存在。
- 罗得岛红鸡为0.000,可能是因为此品种没有经历针对该变异的选择压力。
4. 其他鸡种的表现:
- 大围山迷你鸡:0.562
- 元宝鸡:0.909
- 南疆斗鸡:0.875
- 西藏鸡:0.815
- 孟加拉本地鸡:0.679
- 印度本地鸡:0.841
- 巴基斯坦本地鸡:0.586
- 伊朗本地鸡:0.726
- 伊朗商用肉鸡:0.625
分析:
- 在其他鸡种中,元宝鸡(0.909)、南疆斗鸡(0.875)和西藏鸡(0.815)的频率较高,这表明这些鸡种在其特定生态或遗传背景下可能对该位点有一定的选择性保留。南亚及中东地区的本地鸡,如印度本地鸡(0.841)和伊朗本地鸡(0.726),也显示出较高的基因频率,表明该位点的突变可能在这些地区的鸡种中较为普遍。
- 部分鸡种如大围山迷你鸡(0.562)和巴基斯坦本地鸡(0.586)频率中等,显示这些群体可能存在一定的多样性。
总结:
原鸡与家养鸡的差异:
- 原鸡群体的等位基因频率较为分散,最高为普通原鸡(0.833),最低为红原鸡(0.250),这可能反映了原鸡在自然选择中的多样性。
- 家养鸡(蛋鸡和肉鸡)的频率普遍较高,特别是阿劳卡纳蓝蛋鸡(1.000)、康沃尔鸡(1.000)和文昌鸡(1.000),显示该位点的突变在家养鸡中经过了显著的选择压力,可能与其经济性状相关。
蛋鸡与肉鸡的差异:
- 蛋鸡和肉鸡都显示出较高的等位基因频率,但阿劳卡纳蓝蛋鸡和一些高产肉鸡(如康沃尔鸡、文昌鸡)完全固定该突变。相较而言,部分肉鸡如广西鸡和白色普利茅斯岩鸡的频率略低,可能与其选择压力的差异有关。
其他鸡种的表现:
- 元宝鸡、南疆斗鸡和西藏鸡等地区性品种的高频率可能表明该突变在其特定生态环境中具有适应性优势。
- 来自南亚、中东地区的本地鸡也表现出较高的频率,可能反映了这些地区对该基因变异的长期选择。
整体总结:
该位点的等位基因变异在家养鸡(尤其是肉鸡和蛋鸡)中普遍较高,表明它在某些重要经济性状中的潜在作用。原鸡中的多样性较大,显示自然选择对该位点的影响较弱。而其他地区性鸡种则表现出较高的等位基因频率,可能与当地的生态环境和遗传选择有关。
6 3082328 A/C A 0.136 missense_variant MODERATE OPN4 rs13561322 6:3056541
Gallus_gallus_bankiva(4):1.000
Gallus_gallus_gallus(6):0.917
Gallus_gallus_jabouillei(25):0.700
Gallus_gallus_murghi(42):0.750
Gallus_gallus_spadiceus(41):0.829
Indonesia_Native_Chicken(35):0.714
Thailand_Native_Chicken(6):0.917
Vietnam_Native_Chicken(7):0.786
Wenchang_Chicken(1):1.000
Yunnan_Chicken(12):1.000
Xishuangbanna_Game_Chicken(10):0.900
Nixi_Chicken(11):0.727
Dulong_Chicken(7):0.929
Daweishan_Mini_Chicken(8):1.000
Guangxi_Chicken(6):0.917
Guangzhou_Chicken(3):1.000
Jiangxi_Silkies(20):1.000
Anyi_Gray_Chicken(4):1.000
Dongxiang_Blue-eggshell_Chicken(6):1.000
Tianfu_Black-bone_Chicken(5):0.800
Shimian_Caoke_Chicken(4):0.625
Jiuyuan_Black-bone_Chicken(5):0.900
Jinyang_Silky_Chicken(6):0.917
Emei_Black_Chicken(5):1.000
Pengxian_Yellow_Chicken(6):0.917
Muchuan_Black-bone_Chicken(5):1.000
Miyi_Chicken(5):1.000
YuanBao_Chicken(22):0.955
Langshan_Chicken(10):1.000
Luxi_Game_Chicken(9):0.944
Shouguang_Chicken(8):1.000
Gushi_Chicken(8):0.938
Bian_Chicken(8):1.000
Beijing_You_Chicken(11):1.000
Dagu_Chicken(8):1.000
Xinjiang_Native_Chicken(6):0.750
Hetian_Black_Chicken(8):1.000
Southern_Xinjiang_Game_Chicken(8):0.938
Turpan_Game_Chicken(7):1.000
Tibetan_Chicken(139):0.950
Araucana_Blue-eggshell_Chicken(6):1.000
Sri_Lanka_Native_Chicken(7):0.571
Bengal_Native_Chicken(14):0.786
India_Native_Chicken(42):0.917
Pakistan_Native_Chicken(34):0.735
Afghan_Native_Chicken(11):0.818
Iran_Native_Chicken(180):0.811
Iran_Commercial_Broiler(4):0.875
White_Leghorn_Chicken(13):0.808
Cornish_Chicken(1):1.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):1.000
背景信息:
这组数据展示了染色体6:3082328位置上的一个A/C错义变异(MODERATE效应),影响基因OPN4,与标记rs13561322相关。该变异会导致氨基酸的改变,因此可能对蛋白质功能有中等程度的影响。数据中的数值表示不同鸡种中等位基因A的频率。接下来,我们按原鸡、蛋鸡、肉鸡及其他鸡种的分类进行分析。
1. 原鸡的表现:
- 红原鸡(Gallus gallus bankiva):1.000
- 普通原鸡(Gallus gallus gallus):0.917
- 越南原鸡(Gallus gallus jabouillei):0.700
- 印度原鸡(Gallus gallus murghi):0.750
- 马来原鸡(Gallus gallus spadiceus):0.829
分析:
- 原鸡的等位基因A频率普遍较高,红原鸡达到1.000,显示该变异在红原鸡中已经完全固定。普通原鸡和马来原鸡等其他原鸡的频率也接近1.000,说明这个变异在原鸡群体中非常常见。越南原鸡的频率相对较低(0.700),可能存在一定的遗传多样性。
2. 蛋鸡的表现:
- 东乡蓝蛋鸡:1.000
- 天府乌骨鸡:0.800
- 九圆乌骨鸡:0.900
- 江西丝毛鸡:1.000
- 阿劳卡纳蓝蛋鸡:1.000
- 白色莱格恩鸡:0.808
分析:
- 蛋鸡群体中的等位基因A频率非常高,多个品种如东乡蓝蛋鸡、江西丝毛鸡、阿劳卡纳蓝蛋鸡都已完全固定该突变(1.000)。这是很有趣的现象,可能反映了这些蛋鸡品种在育种过程中对这个位点的强选择。
- 天府乌骨鸡的频率相对较低(0.800),显示出该鸡种中存在更多的遗传变异。
3. 肉鸡的表现:
- 康沃尔鸡:1.000
- 罗得岛红鸡:0.000
- 白色普利茅斯岩鸡:1.000
- 文昌鸡:1.000
- 米易鸡:1.000
- 广西鸡:0.917
- 越南本地鸡:0.786
- 泰国本地鸡:0.917
- 彭县黄鸡:0.917
分析:
- 康沃尔鸡、白色普利茅斯岩鸡、文昌鸡等肉鸡的等位基因A频率已经完全固定(1.000),说明这些肉鸡品种可能在育种过程中对该位点进行了强选择。
- 罗得岛红鸡的频率为0.000,这可能是由于该品种并没有经历类似的选择压力,因此表现出完全不同的基因频率。
- 部分肉鸡品种如越南本地鸡和泰国本地鸡的频率稍低(约0.786-0.917),显示该变异并没有在所有肉鸡中完全固定。
4. 其他鸡种的表现:
- 大围山迷你鸡:1.000
- 元宝鸡:0.955
- 南疆斗鸡:0.938
- 西藏鸡:0.950
- 孟加拉本地鸡:0.786
- 印度本地鸡:0.917
- 巴基斯坦本地鸡:0.735
- 伊朗本地鸡:0.811
- 伊朗商用肉鸡:0.875
分析:
- 在其他鸡种中,许多品种如大围山迷你鸡、元宝鸡、西藏鸡等的等位基因A频率接近或达到1.000,显示出这些品种也经历了类似的选择压力。
- 孟加拉本地鸡、巴基斯坦本地鸡等南亚本地鸡品种的频率略低,说明这些群体可能存在更多的基因多样性或选择压力较弱。
- 伊朗本地鸡和伊朗商用肉鸡的频率较高,但未完全固定,显示出这些鸡种在育种过程中存在一定程度的遗传变异。
总结:
原鸡与家养鸡的差异:
- 原鸡中,等位基因A频率普遍较高,红原鸡达到1.000。家养鸡(包括蛋鸡和肉鸡)的频率同样非常高,显示出该位点在驯化过程中可能受到了强烈的选择压力。
蛋鸡与肉鸡的差异:
- 蛋鸡和肉鸡的等位基因A频率普遍较高,许多品种如东乡蓝蛋鸡、康沃尔鸡等完全固定该变异,显示出强选择压力。只有少数品种如天府乌骨鸡和越南本地鸡显示出较低频率,可能存在更多的遗传变异。
其他鸡种的表现:
- 地区性鸡种如元宝鸡、西藏鸡等表现出很高的频率,接近1.000,可能反映了其长期在特定环境下的选择压力。而南亚及中东地区的鸡种如孟加拉本地鸡和伊朗本地鸡则显示出更大的基因多样性。
整体总结:
这个A/C错义突变在家养鸡和原鸡中普遍存在,且等位基因A的频率普遍很高,尤其是在蛋鸡和肉鸡品种中。该位点的高频率可能与重要的经济性状(如生长速度或产蛋量)相关,并在长期育种过程中得到了保留或选择。不同鸡种的频率差异可能反映了各自的育种历史、生态适应及选择压力。
6 3082412 A/C A 0.132 3_prime_UTR_variant MODIFIER OPN4 rs14560552 6:3056625
Gallus_gallus_bankiva(4):1.000
Gallus_gallus_gallus(5):1.000
Gallus_gallus_jabouillei(27):0.778
Gallus_gallus_murghi(42):0.750
Gallus_gallus_spadiceus(42):0.869
Indonesia_Native_Chicken(36):0.722
Thailand_Native_Chicken(6):0.917
Vietnam_Native_Chicken(7):0.786
Wenchang_Chicken(1):1.000
Yunnan_Chicken(12):1.000
Xishuangbanna_Game_Chicken(10):0.800
Nixi_Chicken(12):0.875
Dulong_Chicken(7):0.929
Daweishan_Mini_Chicken(8):1.000
Guangxi_Chicken(6):0.917
Guangzhou_Chicken(2):1.000
Jiangxi_Silkies(20):1.000
Anyi_Gray_Chicken(5):0.900
Dongxiang_Blue-eggshell_Chicken(6):1.000
Tianfu_Black-bone_Chicken(5):0.800
Shimian_Caoke_Chicken(4):0.875
Jiuyuan_Black-bone_Chicken(5):0.900
Jinyang_Silky_Chicken(6):0.917
Emei_Black_Chicken(5):1.000
Pengxian_Yellow_Chicken(6):0.917
Muchuan_Black-bone_Chicken(5):1.000
Miyi_Chicken(5):1.000
YuanBao_Chicken(22):0.955
Langshan_Chicken(10):1.000
Luxi_Game_Chicken(8):0.875
Shouguang_Chicken(8):1.000
Gushi_Chicken(7):0.929
Bian_Chicken(8):1.000
Beijing_You_Chicken(11):1.000
Dagu_Chicken(8):1.000
Xinjiang_Native_Chicken(6):0.750
Hetian_Black_Chicken(7):1.000
Southern_Xinjiang_Game_Chicken(8):0.875
Turpan_Game_Chicken(8):1.000
Tibetan_Chicken(137):0.945
Araucana_Blue-eggshell_Chicken(6):1.000
Sri_Lanka_Native_Chicken(7):0.643
Bengal_Native_Chicken(14):0.786
India_Native_Chicken(45):0.900
Pakistan_Native_Chicken(35):0.771
Afghan_Native_Chicken(11):0.818
Iran_Native_Chicken(181):0.809
Iran_Commercial_Broiler(4):0.875
White_Leghorn_Chicken(13):0.808
Cornish_Chicken(1):1.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):1.000
背景信息:
此数据展示了染色体6:3082412位置上的A/C变异,属于3’ UTR变异(非编码区的变异,MODIFIER效应)。3’ UTR变异不会改变蛋白质序列,但可能影响mRNA的稳定性或转录后的调控,因此可能对基因表达有间接的影响。数据表示不同鸡种中等位基因A的频率。
1. 原鸡的表现:
- 红原鸡(Gallus gallus bankiva):1.000
- 普通原鸡(Gallus gallus gallus):1.000
- 越南原鸡(Gallus gallus jabouillei):0.778
- 印度原鸡(Gallus gallus murghi):0.750
- 马来原鸡(Gallus gallus spadiceus):0.869
分析:
- 红原鸡和普通原鸡的等位基因A频率为1.000,表明该变异在这些原鸡中已完全固定。其他原鸡亚种如越南原鸡、印度原鸡和马来原鸡的频率较高,但未完全固定,显示出一定的遗传多样性。高频率可能表明该位点在原鸡中受到某种自然选择压力。
2. 蛋鸡的表现:
- 东乡蓝蛋鸡:1.000
- 天府乌骨鸡:0.800
- 九圆乌骨鸡:0.900
- 江西丝毛鸡:1.000
- 阿劳卡纳蓝蛋鸡:1.000
- 白色莱格恩鸡:0.808
分析:
- 蛋鸡群体中,多个品种(如东乡蓝蛋鸡、江西丝毛鸡、阿劳卡纳蓝蛋鸡)的等位基因A频率已完全固定,显示出这些品种可能在育种过程中对该位点进行了强选择。
- 天府乌骨鸡的频率为0.800,较其他蛋鸡稍低,表明其遗传多样性较高。
3. 肉鸡的表现:
- 康沃尔鸡:1.000
- 罗得岛红鸡:0.000
- 白色普利茅斯岩鸡:1.000
- 文昌鸡:1.000
- 米易鸡:1.000
- 广西鸡:0.917
- 越南本地鸡:0.786
- 泰国本地鸡:0.917
- 彭县黄鸡:0.917
分析:
- 康沃尔鸡、白色普利茅斯岩鸡、文昌鸡等肉鸡品种的等位基因A频率为1.000,显示这些品种在育种过程中对该位点进行了强选择。
- 罗得岛红鸡的等位基因频率为0.000,表明该品种未经历与其他肉鸡类似的选择压力。
- 广西鸡、越南本地鸡和泰国本地鸡的频率较高,但未完全固定,显示这些鸡种中存在较大的遗传多样性。
4. 其他鸡种的表现:
- 大围山迷你鸡:1.000
- 元宝鸡:0.955
- 南疆斗鸡:0.875
- 西藏鸡:0.945
- 孟加拉本地鸡:0.786
- 印度本地鸡:0.900
- 巴基斯坦本地鸡:0.771
- 伊朗本地鸡:0.809
- 伊朗商用肉鸡:0.875
分析:
- 在其他鸡种中,许多品种如大围山迷你鸡、元宝鸡、西藏鸡等的等位基因A频率接近1.000,显示出这些品种可能在特定的环境下对该位点进行了选择。
- 孟加拉本地鸡和巴基斯坦本地鸡的频率较低,表明这些品种中存在较大的遗传变异。
总结:
原鸡与家养鸡的差异:
- 原鸡中的红原鸡和普通原鸡已完全固定该变异(1.000),表明该位点在这些原鸡亚种中经过了长期的选择。家养鸡中(如蛋鸡和肉鸡),多个品种也显示出很高的频率,表明该位点在家养鸡的驯化过程中发挥了重要作用。
蛋鸡与肉鸡的差异:
- 蛋鸡和肉鸡的等位基因A频率普遍较高,特别是在多个品种中已经完全固定(如东乡蓝蛋鸡和康沃尔鸡)。这表明该位点在经济性状(如产蛋量或生长速度)中可能扮演了重要角色。
- 罗得岛红鸡是个特殊的例子,其等位基因频率为0.000,显示出与其他肉鸡不同的遗传背景。
其他鸡种的表现:
- 地区性鸡种如元宝鸡、西藏鸡等显示出高频率,可能与其长期的生态适应有关。南亚及中东地区的鸡种如孟加拉本地鸡、伊朗本地鸡则表现出较大的遗传多样性,表明这些群体未受到同样的选择压力。
整体总结:
该位点的等位基因A在多个鸡种中表现出高频率,尤其是在原鸡、蛋鸡和肉鸡品种中。它可能与家养鸡的重要经济性状有关,特别是在长期的驯化和选择过程中被保留下来。不同地区和品种的频率差异反映了各自的育种历史、遗传背景和环境选择压力。
罗得岛红鸡:
体型中等,羽毛呈深红色或栗色,性情活泼,适应性强,能适应多种气候条件。
其强健的体质和耐寒性,使它能在不同的养殖环境中表现出良好的生产性能
Species
Gallus gallus
Aves; Galliformes; Phasianidae; Gallus
Assay
44 tissues at different stages (A total of 429 samples)
- Muscular System: 46
- Integumentary System: 36
- Immune System: 115
- Nervous System: 45
- Reproductive System: 11
- Digestive System: 51
- Vision: 29
- Limb, fat, heart, lung, and others: 96
Link Sample information
这个数据集提供了有关鸡(Gallus gallus)基因OPN4在不同组织中的组织特异性表达的信息,特别是通过组织特异性指数(Tau value)来表示其在不同组织中的表达差异。以下是对数据的详细解释:
1. 基本信息解释:
- Chr, Start, End: 基因的染色体位置,在这里是第6号染色体,起始和结束位置分别是3059653到3086509。这表明基因OPN4在染色体6上的具体位置。
- Gene Symbol: OPN4是该基因的符号,它编码一种视蛋白,通常与光感受相关,但也可能在其他组织中具有不同的功能。
- Position of GRCg7b: 在GRCg7b版本的鸡基因组中的位置,这个范围为6:3034133-3056740。
- Tau value: Tau值用于表示基因的组织特异性,它可以描述一个基因在不同组织中的表达差异。Tau值接近1表明该基因在特定组织中表达较高,而在其他组织中的表达较低。Tau值为0表示该基因在所有组织中都有类似的表达。
- Tau值0.92099表明OPN4基因具有较高的组织特异性,即该基因主要在某些组织中特异性表达,而在其他组织中的表达较低。
2. 组织特异性表达:
- 该数据指出,鸡的OPN4基因在以下几个系统或组织中进行了表达分析,总共包括了44个组织(429个样本),其中包含:
- Muscular System(肌肉系统): 46个样本
- Integumentary System(外皮系统): 36个样本
- Immune System(免疫系统): 115个样本
- Nervous System(神经系统): 45个样本
- Reproductive System(生殖系统): 11个样本
- Digestive System(消化系统): 51个样本
- Vision(视觉相关组织): 29个样本
- Limb, fat, heart, lung, and others(四肢、脂肪、心脏、肺和其他组织): 96个样本
3. 关于Tau值的含义:
- Tau值0.92099表明,OPN4基因在特定的组织中表达较高,而在其他许多组织中表达较低。
由于OPN4基因传统上与视觉有关,主要作用是感光,因此它可能在视觉相关组织中的表达较为特异。但同时,OPN4在其他系统(如神经系统、肌肉系统等)中也可能有一些特定的功能或表达水平。
具体来说,OPN4基因可能在鸡的不同发育阶段或不同器官中具有不同的功能。例如:
- 在视觉系统中,OPN4可能主要参与光感受的调节功能。
- 在肌肉系统或其他非视觉组织中,OPN4可能具有与生物节律或代谢调节相关的功能。
4. 物种和系统的概述:
- 物种为Gallus gallus(家禽鸡),属于鸟纲(Aves)下的鸡形目(Galliformes),雉科(Phasianidae),基因表达分析共涉及44种组织,包括多个系统(如肌肉系统、免疫系统、神经系统、视觉系统等)。
5. 总结:
这个数据集中重点显示了OPN4基因在鸡的不同组织中的表达情况,并通过Tau值来量化其在特定组织中的表达特异性。Tau值接近1(0.92099)表明,OPN4基因可能在一些特定组织中具有高表达,例如在视觉系统或神经系统中,它可能与光感受或昼夜节律调节有关。而在其他组织中,表达较低,但可能仍具有一些非视觉相关的生物学功能。
这些数据可用于进一步研究OPN4基因在非传统光感受组织中的功能,例如肌肉或脂肪组织中的代谢调控、昼夜节律调节等潜在作用。
的重要标记物接近参与鸡饲料转化率 (NOX4) [35] 和饲料效率 (TMEM135) [36] 的候选基因
189038114 A/G G 0.103 start_lost HIGH NOX4 rs735740939 1:187637823
Group (number): frequence
Gallus_gallus_bankiva(4):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(27):0.074
Gallus_gallus_murghi(54):0.000
Gallus_gallus_spadiceus(43):0.267
Indonesia_Native_Chicken(36):0.028
Thailand_Native_Chicken(6):0.167
Vietnam_Native_Chicken(7):0.000
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.167
Xishuangbanna_Game_Chicken(10):0.050
Nixi_Chicken(11):0.091
Dulong_Chicken(6):0.000
Daweishan_Mini_Chicken(8):0.062
Guangxi_Chicken(6):0.333
Guangzhou_Chicken(5):0.000
Jiangxi_Silkies(20):0.100
Anyi_Gray_Chicken(5):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.583
Tianfu_Black-bone_Chicken(5):0.200
Shimian_Caoke_Chicken(4):0.375
Jiuyuan_Black-bone_Chicken(5):0.100
Jinyang_Silky_Chicken(6):0.000
Emei_Black_Chicken(6):0.083
Pengxian_Yellow_Chicken(6):0.083
Muchuan_Black-bone_Chicken(5):0.200
Miyi_Chicken(5):0.400
YuanBao_Chicken(23):0.435
Langshan_Chicken(9):0.222
Luxi_Game_Chicken(9):0.167
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.000
Beijing_You_Chicken(11):0.182
Dagu_Chicken(8):0.250
Xinjiang_Native_Chicken(6):0.083
Hetian_Black_Chicken(8):0.188
Southern_Xinjiang_Game_Chicken(8):0.062
Turpan_Game_Chicken(8):0.000
Tibetan_Chicken(140):0.125
Araucana_Blue-eggshell_Chicken(6):0.333
Sri_Lanka_Native_Chicken(7):0.143
Bengal_Native_Chicken(14):0.000
India_Native_Chicken(47):0.021
Pakistan_Native_Chicken(37):0.068
Afghan_Native_Chicken(11):0.000
Iran_Native_Chicken(179):0.073
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(13):0.000
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.500
White_Plymouth_Rock_Chicken(1):0.000
根据你提供的数据,我们可以对原鸡、蛋鸡和肉鸡的基因突变进行比较。这组数据展示了189038114位点的A/G变异,并且该变异是start_lost类型的突变,影响基因NOX4,具有HIGH效应,这意味着该突变可能导致蛋白质翻译起始密码子丢失,可能严重影响基因功能。
我们将按照原鸡、蛋鸡和肉鸡的分类,对这些鸡种的等位基因频率进行分析。
- 原鸡的表现:
Gallus gallus bankiva(红原鸡):0.000
Gallus gallus gallus(普通原鸡):0.000
Gallus gallus jabouillei(越南原鸡):0.074
Gallus gallus murghi(印度原鸡):0.000
Gallus gallus spadiceus(马来原鸡):0.267
分析:
红原鸡、普通原鸡和印度原鸡在这个位点上的等位基因频率为0.000,这表明这些原鸡亚种没有携带这个突变。
越南原鸡的频率为0.074,表明其群体中有少量个体携带此突变。
马来原鸡的频率较高,为0.267,表明该基因变异在马来原鸡中保留了一定程度,可能与其生态适应性或进化压力有关。
总结:总体来看,原鸡群体中,大多数品种的突变频率较低,除了马来原鸡外,其他原鸡种携带该突变的比例极少或为零。
- 蛋鸡的表现:
White Leghorn Chicken(白色莱格恩鸡):0.000
Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.583
Jiangxi Silkies(江西丝毛鸡):0.100
Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.333
分析:
白色莱格恩鸡的突变频率为0.000,这表明在这个常见的高产蛋鸡品种中,这个突变未被保留,可能与该品种的高产蛋性能无关,甚至有可能与产蛋性能相冲突。
东乡蓝蛋鸡的等位基因频率较高(0.583),表明在这一品种中,该基因突变可能在育种过程中得到了保留。
阿劳卡纳蓝蛋鸡的频率为0.333,这可能反映了该品种在育种过程中保留了一定的遗传多样性,包括这个基因突变。
总结:蛋鸡群体在这个位点的突变频率差异较大,部分品种(如白色莱格恩鸡)没有保留该突变,而其他品种(如东乡蓝蛋鸡和阿劳卡纳蓝蛋鸡)则显示出较高的突变频率,可能与它们的育种方向和特殊产蛋性能相关。
- 肉鸡的表现:
Cornish Chicken(康沃尔鸡):0.000
White Plymouth Rock Chicken(白色普利茅斯岩鸡):0.000
Rhode Island Red Chicken(罗得岛红鸡):0.500
Miyi Chicken(米易鸡):0.400
Guangxi Chicken(广西鸡):0.333
分析:
康沃尔鸡和白色普利茅斯岩鸡的等位基因频率为0.000,这表明这些商业化肉鸡品种没有携带这个突变。由于这些品种的育种重点是快速生长和高肉产量,该突变可能不利于这些目标,或在育种过程中被淘汰。
罗得岛红鸡的等位基因频率为0.500,表明该蛋肉兼用鸡品种中携带此突变的比例较高。
米易鸡和广西鸡的突变频率也较高,分别为0.400和0.333,显示这些地方性鸡种中该突变相对常见,可能与其特定的生态环境或遗传背景有关。
总结:肉鸡群体在这个位点的表现有很大差异,商业肉鸡(如康沃尔鸡)未保留该突变,而地方性肉鸡(如米易鸡和广西鸡)和蛋肉兼用鸡种(如罗得岛红鸡)则表现出较高的突变频率。
整体总结:
原鸡:大多数原鸡种的突变频率为零,只有马来原鸡表现出较高的频率(0.267),显示出该位点在自然选择压力下没有显著保留。
蛋鸡:蛋鸡中的突变频率差异较大。高产蛋鸡(如白色莱格恩鸡)的频率为0,表明该突变可能不利于高产蛋性能。而在一些特色蛋鸡(如东乡蓝蛋鸡和阿劳卡纳蓝蛋鸡)中,该突变频率较高,可能是由于特定的遗传背景和育种目标。
肉鸡:商业肉鸡(如康沃尔鸡、白色普利茅斯岩鸡)的突变频率为零,这可能与其专注于快速增长和高肉产量有关。相比之下,一些地方性肉鸡(如米易鸡、广西鸡)和蛋肉兼用鸡种(如罗得岛红鸡)则有较高的突变频率,可能反映了它们在不同生态环境中的适应性或遗传多样性。
总的来说,原鸡、蛋鸡和肉鸡在这个位点的等位基因频率确实存在显著差异,这可能反映了不同的育种选择压力和遗传背景对基因突变的保留和淘汰。
根据你提供的数据,我将不同鸡种按照原鸡、蛋鸡、肉蛋兼用鸡、肉鸡和其他鸡进行分类,并分析它们在该位点(189038114 A/G,start lost,NOX4基因)上的等位基因频率。
1. 原鸡:
- Gallus gallus bankiva(红原鸡):0.000
- Gallus gallus gallus(普通原鸡):0.000
- Gallus gallus jabouillei(越南原鸡):0.074
- Gallus gallus murghi(印度原鸡):0.000
- Gallus gallus spadiceus(马来原鸡):0.267
分析:
- 大多数原鸡(如红原鸡、普通原鸡、印度原鸡)在此位点上没有突变(频率为 0.000),显示该位点突变在自然选择压力下未被保留。
- 马来原鸡的频率较高(0.267),表明这一群体可能受到了特定的环境或遗传压力,使得这一突变得以保留。
2. 蛋鸡:
- White Leghorn Chicken(白色莱格恩鸡):0.000
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.583
- Jiangxi Silkies(江西丝毛鸡):0.100
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.333
分析:
- 白色莱格恩鸡是典型的高产蛋鸡,突变频率为 0.000,表明这个突变与蛋鸡高产性能无关,甚至可能有负面影响。
- 东乡蓝蛋鸡和阿劳卡纳蓝蛋鸡等特色蛋鸡的突变频率较高(分别为 0.583 和 0.333),显示这些鸡种可能在育种过程中保留了这一突变,可能与它们独特的产蛋特性有关。
3. 肉蛋兼用鸡(双重用途鸡):
- Rhode Island Red Chicken(罗得岛红鸡):0.500
- Beijing You Chicken(北京油鸡):0.182
- Dagu Chicken(大谷鸡):0.250
分析:
- 罗得岛红鸡是著名的肉蛋兼用鸡,其突变频率为 0.500,表明该突变在这个品种中得到了相对广泛的保留。这可能与其在肉用和蛋用上的双重选择压力有关。
- 北京油鸡和大谷鸡的突变频率分别为 0.182 和 0.250,显示这些兼用鸡种群中也有部分个体携带这一突变,可能与育种方向和遗传背景有关。
4. 肉鸡:
- Cornish Chicken(康沃尔鸡):0.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):0.000
- Miyi Chicken(米易鸡):0.400
- Guangxi Chicken(广西鸡):0.333
分析:
- 康沃尔鸡和白色普利茅斯岩鸡是典型的商业肉鸡,突变频率为 0.000,表明这一突变可能对快速生长和高肉产量不利,因此未在这些肉鸡中保留。
- 米易鸡和广西鸡等地方性肉鸡的突变频率较高(分别为 0.400 和 0.333),这可能与其地方环境适应性和遗传选择压力有关。
5. 其他鸡种:
- Bengal Native Chicken(孟加拉本地鸡):0.000
- India Native Chicken(印度本地鸡):0.021
- Pakistan Native Chicken(巴基斯坦本地鸡):0.068
- Iran Native Chicken(伊朗本地鸡):0.073
- Sri Lanka Native Chicken(斯里兰卡本地鸡):0.143
- Tibetan Chicken(西藏鸡):0.125
- Luxi Game Chicken(鲁西斗鸡):0.167
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.333
分析:
- 孟加拉本地鸡、印度本地鸡、巴基斯坦本地鸡等南亚品种的突变频率较低,显示这些群体中该位点突变较为稀有。
- 西藏鸡、鲁西斗鸡和阿劳卡纳蓝蛋鸡的突变频率较高,显示这些群体可能在特定环境或育种过程中保留了该突变。
- 这些“其他鸡种”中,大多数为本地品种,突变频率显示了地理和育种背景对该基因突变的选择性影响。
总结:
原鸡:大多数原鸡(如红原鸡、普通原鸡)突变频率为零,说明在自然环境下未受到强选择压力。马来原鸡的突变频率较高,可能是例外情况。
蛋鸡:高产蛋鸡(如白色莱格恩鸡)的突变频率为零,而特色蛋鸡(如东乡蓝蛋鸡、阿劳卡纳蓝蛋鸡)突变频率较高,可能与其育种目标有关。
肉蛋兼用鸡:这些鸡种的突变频率从 0.182 到 0.500 不等,显示出在双重用途鸡种中的保留程度较高,可能与其双重育种目标相关。
肉鸡:商业肉鸡(如康沃尔鸡)突变频率为零,地方性肉鸡(如米易鸡、广西鸡)频率较高,显示这些地方鸡种在遗传多样性方面的不同选择压力。
其他鸡种:本地鸡种的突变频率差异较大,显示了不同地理区域和育种历史对基因变异的选择性影响。
总体来看,原鸡、蛋鸡、肉蛋兼用鸡、肉鸡和其他鸡种在这个基因位点上确实表现出了显著的频率差异,反映了它们各自在育种历史和选择压力下对基因变异的不同适应性。
你提到的观察——“越靠近高海拔的东边,变异的越多”——是一个有趣的假设。从当前的数据中,可以看到不同鸡种在该位点上的等位基因频率存在显著差异。我们可以通过分析这些鸡种的地理分布和海拔高度,进一步探讨变异频率与海拔高度的潜在关系。
首先,了解这些鸡种的地理和海拔分布:
高海拔区域的鸡种:
- 西藏鸡(Tibetan Chicken):生活在中国西藏地区,平均海拔在4000米左右,突变频率为0.125,属于中等频率。
- 鲁西斗鸡(Luxi Game Chicken):分布于山东和中国北方的部分地区,海拔较低(约500米以下),突变频率为0.167。
- 四川地区的鸡种(如峨眉黑鸡、天府黑骨鸡、米易鸡、彭县黄鸡):四川有一些较高海拔的山地(1000米到3000米),这些品种的变异频率中等或较高,例如米易鸡的频率为0.400,天府黑骨鸡的频率为0.200。
- 云南鸡(分布在云南省,地势起伏较大,部分地区海拔较高,突变频率为0.167)。
中低海拔区域的鸡种:
- 东南亚和南亚鸡种(如越南本地鸡、泰国本地鸡、印度本地鸡、斯里兰卡本地鸡):这些鸡种分布在较低的海拔区域,突变频率普遍较低(如越南本地鸡为0.000,印度本地鸡为0.021,斯里兰卡本地鸡为0.143)。
- 伊朗、阿富汗本地鸡等中东地区的鸡种,突变频率较低(伊朗本地鸡为0.073,阿富汗本地鸡为0.000)。
是否存在海拔与突变频率的联系?
从以上的数据可以看出,部分高海拔地区的鸡种确实显示出较高的突变频率,例如:
- 米易鸡(Miyi Chicken):位于四川省,突变频率为0.400,这是一个高频率值,四川的部分地区海拔较高。
- 西藏鸡(Tibetan Chicken):虽然生活在海拔极高的西藏地区,但突变频率为0.125,属于中等频率。
- 彭县黄鸡、峨眉黑鸡等四川的鸡种,突变频率较低或中等(频率为0.083~0.375)。
- 广西鸡的突变频率为0.333,该地区也存在一些高海拔山地。
同时,一些低海拔地区的鸡种突变频率则相对较低,如印度本地鸡、巴基斯坦本地鸡等。
需要考虑的因素:
自然选择和遗传漂变:
- 高海拔环境中的低氧、寒冷等极端条件可能促使一些基因突变被保留,因为这些突变可能与适应这些环境条件相关。突变的保留可能提高了这些鸡种在高海拔地区的生存能力。
- 然而,不是所有高海拔鸡种的突变频率都高。例如,西藏鸡的突变频率为0.125,这可能表明该突变与其海拔适应性并没有直接关系,或者说其他基因更重要。
其他环境和育种压力:
- 变异频率不仅受到海拔的影响,还可能与其他环境因素和育种方向有关。例如,在四川的某些鸡种中(如米易鸡),育种目标可能是通过选择特定性状(如耐寒、耐缺氧)保留了某些突变。
- 地方性育种:有些鸡种的变异频率高可能是因为特定区域内遗传漂变的结果,而不是因为它们处于高海拔地区。
基因与环境适应的复杂性:
- 单一的基因位点变异不一定能完全解释鸡种对特定环境的适应。可能多个基因共同作用,形成复杂的适应性机制。因此,即使在高海拔地区,也未必所有鸡种在此位点上表现出较高的突变频率。
总结:
根据数据中的突变频率,海拔与该位点的突变频率之间可能存在一定的联系。部分高海拔地区的鸡种(如米易鸡、四川地区的鸡种)表现出较高的变异频率,而低海拔地区的鸡种(如印度本地鸡、巴基斯坦本地鸡)突变频率较低。
不过,需要注意的是,并非所有高海拔鸡种的突变频率都较高,例如西藏鸡的突变频率相对较低。变异的保留可能受到多个因素的影响,包括自然选择、育种目标、生态环境等。海拔可能是影响突变保留的一个因素,但还不能完全解释所有鸡种的变异分布。
在你提供的数据中,不同鸡种在特定位点的突变频率存在显著差异。通过观察这些频率,可以尝试总结一些可能的规律或解释,从而理解不同鸡种的变异频率是否受到某些因素的影响。
1. 地理分布和突变频率的关系:
从数据来看,地理分布可能是影响这些鸡种突变频率的重要因素。以下是一些可能的模式:
高突变频率的鸡种:
- 马来原鸡(Gallus gallus spadiceus):0.267
- 广西鸡:0.333
- 东乡蓝蛋鸡:0.583
- 米易鸡:0.400
- 元宝鸡:0.435
- 罗得岛红鸡:0.500
这些鸡种中,尤其是东乡蓝蛋鸡(0.583)、元宝鸡(0.435)和罗得岛红鸡(0.500)的突变频率非常高。部分这些鸡种来自中国南部和西南部的高海拔地区,如米易鸡和广西鸡,这可能表明高海拔环境中的鸡种更容易保留某些突变,以适应更为恶劣的环境。
低突变频率的鸡种:
- 红原鸡(Gallus gallus bankiva):0.000
- 普通原鸡(Gallus gallus gallus):0.000
- 印度原鸡(Gallus gallus murghi):0.000
- 越南本地鸡:0.000
- 白色莱格恩鸡:0.000
- 康沃尔鸡:0.000
这些鸡种大多数来自低海拔或温暖的亚热带和热带地区,例如越南、印度、东南亚的鸡种,或者是经过高度选择育种的商业化品种(如白色莱格恩鸡、康沃尔鸡),它们的突变频率较低,可能与其长期的育种选择压力或相对温和的气候环境有关。
2. 育种选择与突变频率的关系:
某些鸡种经过了高度选择育种,其育种目标是优化产蛋量或肉质,因此特定突变可能在这些鸡种中被淘汰或不常见。例如:
- 白色莱格恩鸡(White Leghorn Chicken) 是一种高产蛋鸡,在该位点的突变频率为 0.000,这表明这个突变可能与高产蛋性状不兼容,或不利于其生产效率,因此被育种过程中淘汰。
- 康沃尔鸡(Cornish Chicken) 和 白色普利茅斯岩鸡(White Plymouth Rock Chicken) 是典型的肉鸡品种,突变频率也为 0.000,表明该突变可能与快速生长和高肉产量的育种目标不兼容。
相比之下,一些鸡种没有经过高度选择育种,而是基于地方性或自然选择,它们可能保留了较高的突变频率:
- 广西鸡 和 米易鸡 等地方品种突变频率较高,可能与地方环境的适应性和育种目标相关,这些突变或许帮助它们更好地适应当地气候和生态环境。
3. 鸡种的地理与环境适应性:
海拔与突变频率的关系:
- 高海拔地区的鸡种,如米易鸡(0.400)、广西鸡(0.333)、四川的某些鸡种(如彭县黄鸡、天府黑骨鸡),突变频率较高。高海拔地区具有低氧、寒冷等环境压力,这可能导致某些突变被自然选择保留,帮助鸡种适应这些极端环境。
- 相比之下,分布在低海拔地区的鸡种,如印度原鸡、越南本地鸡、泰国本地鸡等,它们的突变频率较低,可能是因为低海拔的环境压力较小,突变不具备明显的适应性优势。
地方性与突变频率的关系:
- 元宝鸡(YuanBao Chicken)、东乡蓝蛋鸡(Dongxiang Blue-eggshell Chicken)等地方特色鸡种突变频率较高。这些地方性鸡种往往具有遗传多样性,它们的育种过程相对自然和传统,因此可能保留了较高的突变频率。
4. 突变频率与基因功能:
该突变在不同鸡种中频率差异的一个可能原因是突变对基因功能的影响。如果该突变在某些鸡种中对重要的经济性状(如产蛋量、肉质、抗逆性)不利,那么在高度选择育种过程中,这些突变可能被淘汰。因此,我们看到许多商业化鸡种(如白色莱格恩鸡、康沃尔鸡、白色普利茅斯岩鸡)突变频率为0.000。
总结:
通过分析数据,可以总结出以下规律:
地理分布与突变频率有关:高海拔地区的鸡种,如米易鸡和广西鸡,突变频率较高,可能与其适应恶劣环境有关。低海拔地区的鸡种,尤其是东南亚的鸡种,突变频率较低。
育种选择对突变频率有影响:高度选择育种的商业化蛋鸡和肉鸡突变频率较低,可能与育种目标有关。而地方性鸡种保留了更多的突变,反映了它们在特定环境中的遗传多样性。
地方特色鸡种突变频率较高:某些地方性鸡种,如东乡蓝蛋鸡和元宝鸡,在育种过程中保留了较高的突变频率,可能与自然选择和地方性育种相关。
总的来说,突变频率的变化可能由多种因素共同作用,包括地理环境、海拔、育种选择压力和地方适应性等。
从你提供的数据中,我们可以分析不同鸡种在特定基因位点的等位基因频率,并结合提到的与饲料转化率(NOX4)和饲料效率(TMEM135)相关的候选基因来理解突变的潜在影响。这些基因与鸡的代谢和饲料转化效率相关,是家禽饲养过程中极为重要的性状。
分析框架:
我们可以从以下几个角度来解读这些数据:
1. 突变频率的分布概况:
通过观察这些鸡种的突变频率,我们可以推测哪些鸡种可能具有更高或更低的饲料转化率或饲料效率,这可能与其基因型相关。
高突变频率的鸡种:
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.583
- Rhode Island Red Chicken(罗得岛红鸡):0.500
- YuanBao Chicken(元宝鸡):0.435
- Miyi Chicken(米易鸡):0.400
- Shimian Caoke Chicken(石棉草科鸡):0.375
这些鸡种表现出较高的突变频率,尤其是东乡蓝蛋鸡(0.583)和罗得岛红鸡(0.500),它们的基因型可能与较高的饲料转化率和饲料效率相关。这些鸡种可能由于特定基因的作用在更高效地将饲料转化为肉或蛋。
中等突变频率的鸡种:
- Guangxi Chicken(广西鸡):0.333
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.333
- Langshan Chicken(郎山鸡):0.222
- Dagu Chicken(大谷鸡):0.250
- Tibetan Chicken(西藏鸡):0.125
这些鸡种的突变频率介于中等水平,可能在饲料转化率上表现出一定的差异性。这些鸡种可能具备一定的饲料转化优势,尤其是在特定的环境下。
低突变频率的鸡种:
- Gallus gallus bankiva(红原鸡):0.000
- Gallus gallus murghi(印度原鸡):0.000
- Vietnam Native Chicken(越南本地鸡):0.000
- White Leghorn Chicken(白色莱格恩鸡):0.000
- Cornish Chicken(康沃尔鸡):0.000
低突变频率的鸡种,尤其是白色莱格恩鸡和康沃尔鸡,可能由于长期的商业育种,这些突变位点在这些鸡种中被淘汰,可能是因为与目标性状不相关,或者这些突变在商业育种中被认为不利。
2. 饲料转化率与饲料效率的潜在影响:
NOX4 和 TMEM135 基因被认为参与饲料转化率和饲料效率的调控,这可能影响鸡种在摄入饲料后转化为肉或蛋的效率。通过突变频率的对比,我们可以大致猜测哪些鸡种可能在这些性状上表现优异。
高突变频率的鸡种可能具有更好的饲料转化率:
- 东乡蓝蛋鸡和罗得岛红鸡的突变频率分别为 0.583 和 0.500,这两个鸡种可能具备较高的饲料转化率,这可能与它们更高效的代谢和生长速度相关。特别是罗得岛红鸡作为蛋肉兼用鸡种,其较高的突变频率可能解释了它较高的生产效率。
中等突变频率的鸡种的表现:
- 鸡种如广西鸡(0.333)和西藏鸡(0.125)突变频率适中,这些鸡种可能在饲料转化效率上表现不如东乡蓝蛋鸡和罗得岛红鸡,但仍有一定的饲料效率。它们可能更适应于当地特定的生态环境,并在较低质量的饲料条件下表现良好。
低突变频率的鸡种的表现:
- Gallus gallus bankiva(红原鸡)和Gallus gallus murghi(印度原鸡)等野生原鸡种的突变频率为 0,表明它们未保留该位点的突变。这些鸡种未经过长期的人工选择,可能在饲料转化率上没有明显的优势。
- 商业化肉鸡如康沃尔鸡,突变频率为 0.000,表明这些鸡种可能更依赖其他基因对生长和饲料效率的调控。商业化育种可能已经通过选择去除了不必要的突变位点,以最大化它们的生长速度和肉产量。
3. 地理与育种的影响:
地方性鸡种的突变频率:
- 广西鸡(0.333)、米易鸡(0.400)等地方鸡种的突变频率较高,这可能反映了它们在特定地理环境下的饲料效率优化。例如,广西鸡和米易鸡可能适应了地方饲料资源的低效利用,通过较高的饲料转化率弥补了资源限制。
商业育种的影响:
- 白色莱格恩鸡(0.000)和康沃尔鸡(0.000)的低突变频率反映了高度选择育种的结果。商业育种往往会通过选择优化特定的性状(如蛋产量或生长速度),这可能导致与饲料转化率无关的基因突变被淘汰。
4. 特殊鸡种的基因型优势:
罗得岛红鸡作为蛋肉兼用鸡种的表现:
- 罗得岛红鸡突变频率高达 0.500,表明该鸡种可能在饲料转化效率上有优势。这也解释了为什么该鸡种作为蛋肉兼用型在全球范围内被广泛饲养。它的基因型可能使它更有效地将饲料转化为蛋和肉。
地方鸡种的潜在遗传多样性:
- 东乡蓝蛋鸡(0.583)的高突变频率可能表明它在遗传多样性方面具有一定优势,尤其是在适应低质量饲料和较差的环境条件下表现良好。其突变频率的保留可能与饲料转化率的适应性选择有关。
总结:
突变频率的分布显示,不同鸡种在饲料转化率和饲料效率相关基因位点上的突变频率差异显著。高突变频率的鸡种可能在这些性状上表现出优势,尤其是地方性鸡种和某些蛋肉兼用鸡种。
商业化育种往往减少了突变频率,表明育种目标是优化某些经济性状(如蛋产量或肉产量),而非保持饲料转化率相关基因的多样性。
地方性鸡种的突变频率较高,显示了它们在特定地理环境中的适应性,尤其是饲料效率的提升。
总体而言,基因型的差异可以帮助解释鸡种在饲料转化率和饲料效率上的差异,这些性状对家禽养殖具有重要的经济意义。
1 189039249 A/T T 0.206 missense_variant MODERATE NOX4 rs314642520 1:187638959
Gallus_gallus_bankiva(3):0.167
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(26):0.077
Gallus_gallus_murghi(57):0.114
Gallus_gallus_spadiceus(44):0.080
Indonesia_Native_Chicken(36):0.014
Thailand_Native_Chicken(6):0.000
Vietnam_Native_Chicken(7):0.071
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.000
Xishuangbanna_Game_Chicken(10):0.050
Nixi_Chicken(12):0.083
Dulong_Chicken(7):0.214
Daweishan_Mini_Chicken(8):0.062
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(4):0.000
Jiangxi_Silkies(20):0.000
Anyi_Gray_Chicken(5):0.300
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.000
Shimian_Caoke_Chicken(4):0.000
Jiuyuan_Black-bone_Chicken(5):0.100
Jinyang_Silky_Chicken(6):0.000
Emei_Black_Chicken(5):0.000
Pengxian_Yellow_Chicken(6):0.000
Muchuan_Black-bone_Chicken(4):0.000
Miyi_Chicken(5):0.000
YuanBao_Chicken(23):0.000
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(9):0.222
Shouguang_Chicken(8):0.188
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.000
Beijing_You_Chicken(11):0.000
Dagu_Chicken(8):0.000
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(8):0.062
Southern_Xinjiang_Game_Chicken(7):0.000
Turpan_Game_Chicken(8):0.062
Tibetan_Chicken(134):0.175
Araucana_Blue-eggshell_Chicken(6):0.333
Sri_Lanka_Native_Chicken(7):0.000
Bengal_Native_Chicken(14):0.000
India_Native_Chicken(48):0.031
Pakistan_Native_Chicken(37):0.095
Afghan_Native_Chicken(11):0.227
Iran_Native_Chicken(181):0.099
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(13):0.000
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
从你提供的这组鸡种的等位基因频率数据中,我们可以观察到不同鸡种在该位点的变异频率存在显著差异。通过分析这些差异,我们可以探索是否存在一些潜在的规律,并尝试解释这些规律背后的原因。
1. 地理分布与突变频率的关系:
高突变频率的鸡种:
- Jiangxi Silkies(江西丝毛鸡):0.575
- Xinjiang Native Chicken(新疆本地鸡):0.583
- Jinyang Silky Chicken(金阳丝毛鸡):0.583
- Bian Chicken(边鸡):0.562
- Miyi Chicken(米易鸡):0.500
- Cornish Chicken(康沃尔鸡):0.500
这些鸡种的突变频率较高,且大多分布在中国的西南部(如米易鸡)和新疆地区(如新疆本地鸡)。这可能表明这些鸡种在较高海拔或特殊环境下有一定的遗传多样性,以应对环境压力。
低突变频率的鸡种:
- Gallus gallus bankiva(红原鸡):0.000
- Wenchang Chicken(文昌鸡):0.000
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.000
- Shouguang Chicken(寿光鸡):0.000
- Gushi Chicken(固始鸡):0.000
- Rhode Island Red Chicken(罗得岛红鸡):0.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):0.000
这些鸡种中有一些为原鸡或商业化鸡种(如白色普利茅斯岩鸡、罗得岛红鸡),突变频率为零,表明这些鸡种没有保留该基因突变。特别是商业化鸡种,其经过高度选择育种,导致遗传多样性较低,可能去除了不利的突变。
2. 育种选择的影响:
高度选择育种的蛋鸡:
- White Leghorn Chicken(白色莱格恩鸡):0.615
- Cornish Chicken(康沃尔鸡):0.500
白色莱格恩鸡和康沃尔鸡是典型的商业化蛋鸡和肉鸡品种,具有较高的突变频率。虽然这些鸡种经过了高度选择育种,但某些突变可能由于育种中的意外遗传漂变或其他因素被保留。这可能与这些鸡种的高产蛋性能或快速生长无直接冲突。
地方鸡种的遗传多样性:
- Miyi Chicken(米易鸡)、Jiangxi Silkies(江西丝毛鸡)、Xinjiang Native Chicken(新疆本地鸡) 等地方鸡种的突变频率较高,表明这些鸡种保留了相对较高的遗传多样性。与商业化鸡种不同,这些地方鸡种通常经过自然选择和传统育种,突变没有被刻意去除,因此遗传变异频率较高。
3. 环境适应性与突变频率的关系:
高海拔环境:
- Xinjiang Native Chicken(新疆本地鸡):0.583
- Miyi Chicken(米易鸡):0.500
- Tibetan Chicken(西藏鸡):0.189
这些鸡种生活在中国的高海拔地区,如新疆、西藏和四川。高海拔地区的极端环境(如低氧、寒冷)可能促使某些基因突变被保留,从而帮助鸡种适应恶劣环境。高海拔环境中的基因突变可能有助于氧气运输、代谢调控或温度适应,使鸡种在这些区域能够更好地生存。
低海拔和温暖气候:
- Gallus gallus bankiva(红原鸡):0.000
- Vietnam Native Chicken(越南本地鸡):0.214
- Thailand Native Chicken(泰国本地鸡):0.167
- Wenchang Chicken(文昌鸡):0.000
低海拔地区的鸡种,如东南亚和南亚的原鸡和本地鸡,其突变频率普遍较低。这可能是因为它们生存在温暖、稳定的气候环境中,较少面临极端环境压力,因此不需要通过保留特定突变来应对环境挑战。
4. 突变频率与遗传背景的关系:
原鸡和家鸡的比较:
- Gallus gallus bankiva(红原鸡) 和 Gallus gallus gallus(普通原鸡) 等原鸡的突变频率较低,尤其是红原鸡(0.000)。这表明这些原始鸡种可能保留了较少的现代遗传变异,突变的频率较低。
- Gallus gallus spadiceus(马来原鸡):0.163,显示出比其他原鸡更高的突变频率,可能是因为其在东南亚地区演化的过程中,受到了独特的选择压力。
特色蛋鸡和丝羽鸡:
- Jiangxi Silkies(江西丝毛鸡) 和 Jinyang Silky Chicken(金阳丝毛鸡) 等特色蛋鸡的突变频率较高。这些鸡种经过了部分育种,但仍保留了较高的遗传多样性,显示出较强的适应性。
5. 突变频率背后的选择机制:
突变频率的分布可能是多个因素共同作用的结果,包括:
- 自然选择:高海拔地区的鸡种由于环境压力大,可能保留了更多有助于环境适应的突变。
- 人工选择:商业化鸡种通过育种选择去除了许多不利突变,因此突变频率较低。但有时育种目标可能无意中保留了一些突变(如白色莱格恩鸡)。
- 遗传漂变:地方鸡种由于育种范围有限,可能存在遗传漂变,导致突变在特定鸡种中得以保留。
总结:
地理分布与突变频率有关:高海拔地区的鸡种(如新疆、米易鸡)显示出较高的突变频率,可能与其适应恶劣环境的遗传选择压力有关。低海拔地区的鸡种(如东南亚鸡种)突变频率较低,可能由于环境压力较小。
育种选择影响突变频率:高度选择育种的商业化蛋鸡和肉鸡(如白色莱格恩鸡、康沃尔鸡)保留了一些突变,但总体突变频率较低。地方鸡种则保留了较高的遗传多样性,突变频率较高。
环境和遗传背景:高海拔环境的适应性可能促进了基因突变的保留,而遗传背景和育种方向也影响了不同鸡种中突变频率的分布。
整体来看,突变频率的分布模式是多个因素综合作用的结果,包括地理环境、育种选择、遗传漂变等。这些因素共同塑造了不同鸡种在该位点上的突变频率差异。
9 22596245 G/C C 0.096 missense_variant MODERATE RARRES1 rs315552303 9:22152479
9 22596245 G/C C 0.096 missense_variant MODERATE RARRES1 rs315552303 9:22152479
9 22596252 G/A A 0.096 missense_variant MODERATE RARRES1 rs736509958 9:22152486
9 22596260 G/A A 0.096 missense_variant MODERATE RARRES1 rs314532045 9:22152494
missense_variant MODERATE RARRES1 rs315552303 9:22152479
missense_variant MODERATE RARRES1 rs315552303 9:22152479
missense_variant MODERATE RARRES1 rs736509958 9:22152486
missense_variant MODERATE RARRES1 rs314532045 9:22152494
Gallus_gallus_bankiva(3):1.000
Gallus_gallus_gallus(5):0.100
Gallus_gallus_jabouillei(27):0.000
Gallus_gallus_murghi(51):0.265
Gallus_gallus_spadiceus(42):0.095
Indonesia_Native_Chicken(36):0.236
Thailand_Native_Chicken(6):0.167
Vietnam_Native_Chicken(7):0.429
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.042
Xishuangbanna_Game_Chicken(10):0.200
Nixi_Chicken(12):0.000
Dulong_Chicken(7):0.000
Daweishan_Mini_Chicken(8):0.188
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(3):0.167
Jiangxi_Silkies(20):0.000
Anyi_Gray_Chicken(5):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.083
Tianfu_Black-bone_Chicken(5):0.000
Shimian_Caoke_Chicken(4):0.000
Jiuyuan_Black-bone_Chicken(5):0.000
Jinyang_Silky_Chicken(6):0.000
Emei_Black_Chicken(6):0.000
Pengxian_Yellow_Chicken(6):0.167
Muchuan_Black-bone_Chicken(5):0.000
Miyi_Chicken(5):0.000
YuanBao_Chicken(24):0.000
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(9):0.056
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.250
Bian_Chicken(8):0.000
Beijing_You_Chicken(11):0.227
Dagu_Chicken(8):0.375
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(7):0.000
Southern_Xinjiang_Game_Chicken(8):0.000
Turpan_Game_Chicken(8):0.062
Tibetan_Chicken(135):0.011
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(7):0.000
Bengal_Native_Chicken(13):0.077
India_Native_Chicken(45):0.344
Pakistan_Native_Chicken(37):0.054
Afghan_Native_Chicken(11):0.500
从你提供的数据来看,这些是不同鸡种在某个RARRES1基因特定位点的等位基因频率。该位点是一个错义突变(missense variant),即基因序列中的一个碱基发生了变化,导致编码的氨基酸改变。这可能对RARRES1蛋白的功能产生潜在的影响。我们可以结合RARRES1的功能和这些数据,尝试分析这些鸡种的遗传差异,并探讨其可能的影响和解释。
RARRES1的功能背景:
RARRES1(视黄酸受体应答基因1)与细胞分化、增殖、凋亡等生物过程有关,特别是在调控脂肪代谢和细胞凋亡方面可能发挥作用。它在某些癌症中被认为是抑癌基因,也与代谢调控相关。这可能意味着它在家禽中的作用可能涉及到生长性能、体型调控、脂肪代谢等特性。
数据分析:
1. 高突变频率的鸡种:
- Afghan Native Chicken(阿富汗本地鸡):0.500
- Vietnam Native Chicken(越南本地鸡):0.429
- India Native Chicken(印度本地鸡):0.344
- Gallus gallus murghi(印度原鸡):0.265
- Indonesia Native Chicken(印尼本地鸡):0.236
- Beijing You Chicken(北京油鸡):0.227
- Dagu Chicken(大谷鸡):0.375
- Gushi Chicken(固始鸡):0.250
这些鸡种在RARRES1基因的这个错义突变位点上具有较高的等位基因频率。高突变频率可能意味着这些鸡种在代谢调控、体型发育或生长性能方面与其他鸡种存在差异。特别是像印度、阿富汗本地鸡等,长期生活在特定的生态环境中,可能由于自然选择或者育种选择压力,保留了与RARRES1功能相关的突变。
2. 中等突变频率的鸡种:
- Thailand Native Chicken(泰国本地鸡):0.167
- Xishuangbanna Game Chicken(西双版纳斗鸡):0.200
- Daweishan Mini Chicken(大围山迷你鸡):0.188
- Guangzhou Chicken(广州鸡):0.167
- Pengxian Yellow Chicken(彭县黄鸡):0.167
- Bengal Native Chicken(孟加拉本地鸡):0.077
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.083
这些鸡种的突变频率较为中等,表明它们可能在一定程度上具有RARRES1功能的变异,可能与这些鸡种在饲料效率、脂肪代谢或体型发育中的特性有关。例如,西双版纳斗鸡是一种适应战斗能力的鸡种,而突变频率的保留可能与体型调控、能量消耗等相关。
3. 低突变频率或未突变的鸡种:
- Gallus gallus bankiva(红原鸡):1.000
- Gallus gallus jabouillei(越南原鸡):0.000
- Nixi Chicken(尼西鸡):0.000
- Dulong Chicken(独龙鸡):0.000
- Jiangxi Silkies(江西丝毛鸡):0.000
- Tibetan Chicken(西藏鸡):0.011
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.000
突变频率较低的鸡种,尤其是红原鸡(1.000)、越南原鸡等,显示这些鸡种可能保留了更多的“祖先”特性,或者说它们没有保留这个错义突变。这可能意味着它们在RARRES1基因调控的代谢或生长性状方面,保持了较原始的状态。
潜在解释与规律:
1. 地理与环境的适应性:
- 印度、阿富汗、越南本地鸡的突变频率较高,可能反映了这些地区的鸡种为了适应特殊的气候环境或饲料资源,保留了RARRES1基因的特定变异。RARRES1与脂肪代谢和能量平衡的调控有关,这可能帮助这些鸡种更好地适应当地的环境和饮食。
2. 育种和选择压力:
- 家禽饲养过程中的选择压力可能对RARRES1的突变产生了影响。例如,北京油鸡和大谷鸡等商业化或地方性高效种鸡,其保留一定的突变频率,可能与家禽育种中注重的体型、生长速度和饲料转化效率相关。
- 红原鸡等原鸡种没有发生该突变,显示出它们可能没有受到强烈的人工选择压力,仍保留较原始的基因特性。
3. 可能的功能影响:
- 由于RARRES1与代谢调控有关,高突变频率可能表明这些鸡种在能量代谢或脂肪存储方面有显著差异。例如,高突变频率的阿富汗本地鸡可能更适合在较贫瘠的环境下生存,突变帮助它们在较低营养条件下优化能量使用。
4. 脂肪代谢和体型调控的可能性:
- 低突变频率的鸡种,如西藏鸡,长期生活在高海拔地区,环境压力可能与能量消耗有关,因此它们没有保留这类突变,可能表明它们在脂肪代谢或能量利用上保留了原始特性,以应对寒冷和低氧环境。
总结:
高突变频率的鸡种:如阿富汗、印度、越南本地鸡以及部分中国地方鸡种,显示了在RARRES1基因上保留较高的突变频率,可能与代谢、饲料转化效率或环境适应性相关。
低突变频率的鸡种:如红原鸡、越南原鸡、尼西鸡等,未发生此错义突变,可能保留了祖先基因的特性,未受到人工选择的强烈影响。
功能推测:RARRES1与代谢、能量调控相关,因此这些鸡种在不同环境下可能通过选择该基因的特定变异,优化了饲料转化率、脂肪代谢和体型发育等性状。
通过分析这些数据,可以更好地理解鸡种的遗传背景、适应性选择和代谢特性,以及如何利用这些信息进行未来的育种优化。
按照你提供的RARRES1基因位点的突变频率数据,我将不同鸡种按照原鸡、蛋鸡、肉蛋兼用鸡、肉鸡和其他鸡种进行分类,并分析它们在该位点的突变频率,进一步解释这些类别的鸡种在RARRES1基因功能上的差异。
1. 原鸡:
- Gallus gallus bankiva(红原鸡):1.000
- Gallus gallus gallus(普通原鸡):0.100
- Gallus gallus jabouillei(越南原鸡):0.000
- Gallus gallus murghi(印度原鸡):0.265
- Gallus gallus spadiceus(马来原鸡):0.095
分析:
- 红原鸡的突变频率为 1.000,这意味着在RARRES1基因的这个错义突变位点上,红原鸡全部个体都发生了突变。由于红原鸡属于较原始的鸡种,可能反映出其基因背景较为保守,这个突变可能是其适应原生态环境的一部分。
- 印度原鸡的突变频率相对较高(0.265),表明部分个体可能保留了这个基因变异。这可能与印度原鸡的环境适应性有关。
- 其他原鸡品种的突变频率较低,尤其是越南原鸡(0.000),显示该突变在不同原鸡亚种中存在一定差异,可能与其地理环境和自然选择压力有关。
2. 蛋鸡:
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.083
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.000
- Jiangxi Silkies(江西丝毛鸡):0.000
分析:
- 东乡蓝蛋鸡突变频率为 0.083,突变频率相对较低,表明该蛋鸡品种可能在RARRES1基因的突变上并不显著。这可能反映了其育种目标主要集中在产蛋量和蛋壳颜色上,与RARRES1调控的脂肪代谢和体型调控无关。
- 阿劳卡纳蓝蛋鸡 和 江西丝毛鸡的突变频率为 0.000,说明这些特色蛋鸡未保留该突变。它们的育种主要集中在特定的产蛋特性和其他经济性状上,未受到该突变的影响。
3. 肉蛋兼用鸡(双重用途鸡):
- Beijing You Chicken(北京油鸡):0.227
- Dagu Chicken(大谷鸡):0.375
- Gushi Chicken(固始鸡):0.250
- Rhode Island Red Chicken(罗得岛红鸡):0.000
分析:
- 北京油鸡和大谷鸡具有较高的突变频率,分别为0.227和0.375。这类肉蛋兼用鸡在育种过程中可能受到了不同的选择压力,不仅注重蛋用性能,还强调了生长和饲料效率。RARRES1与代谢调控相关,这些鸡种中保留的突变可能有助于提高饲料转化率。
- 固始鸡的突变频率为0.250,表明该鸡种在RARRES1的调控功能上可能存在一定的多样性,有助于其在生长与产蛋间取得平衡。
- 罗得岛红鸡的突变频率为0.000,这可能反映出其育种目标主要集中在高产蛋性能上,并没有通过RARRES1突变来提高其代谢或脂肪调控能力。
4. 肉鸡:
- Cornish Chicken(康沃尔鸡):0.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):0.000
分析:
- 康沃尔鸡和白色普利茅斯岩鸡的突变频率为0.000,这可能反映出这些商业肉鸡在育种过程中已高度选择了与快速生长和肉质改良相关的基因。由于RARRES1主要参与脂肪代谢和细胞调控,而这些鸡种的育种目标主要集中在高生长速度和高肉产量上,因此这些突变在育种过程中可能被排除。
5. 其他鸡种:
- Vietnam Native Chicken(越南本地鸡):0.429
- Indonesia Native Chicken(印尼本地鸡):0.236
- Thailand Native Chicken(泰国本地鸡):0.167
- Afghan Native Chicken(阿富汗本地鸡):0.500
- India Native Chicken(印度本地鸡):0.344
- Pakistan Native Chicken(巴基斯坦本地鸡):0.054
分析:
- 越南本地鸡、印度本地鸡和阿富汗本地鸡等本地鸡种的突变频率较高,尤其是阿富汗本地鸡(0.500)和越南本地鸡(0.429)。这些本地鸡种由于长期生活在特定的生态环境中,可能受到了不同的自然选择压力,RARRES1突变可能帮助它们适应低质量的饲料或高温、干旱等极端环境,从而提高它们的生存能力。
- 印尼和泰国本地鸡的突变频率较为中等,可能反映了它们在脂肪代谢或饲料转化上的适应性,而这种变异频率可能帮助它们在热带气候中保持高效的能量利用。
- 巴基斯坦本地鸡的突变频率较低(0.054),这可能表明该地区的鸡种在遗传多样性或脂肪代谢上有所不同。
整体分析与总结:
原鸡:
- 红原鸡(1.000)保留了完全的突变频率,显示出较为原始的基因背景,其他原鸡种突变频率差异较大,表明地理和生态环境对RARRES1功能的保留有一定影响。
蛋鸡:
- 蛋鸡品种在该位点的突变频率较低,表明育种过程中未针对该基因位点进行选择。蛋鸡主要追求产蛋量和蛋壳品质,与RARRES1基因调控的代谢功能关联不大。
肉蛋兼用鸡:
- 肉蛋兼用鸡中,北京油鸡和大谷鸡的突变频率较高,显示出育种中对饲料效率和生长速度的关注。相比之下,罗得岛红鸡的突变频率为0,表明其主要专注于高产蛋性能。
肉鸡:
- 肉鸡(如康沃尔鸡)未表现出该突变,表明其育种目标集中在生长速度和肉产量,而非通过RARRES1调控来优化代谢。
其他鸡种:
- 本地鸡种的突变频率较为多样,尤其是阿富汗本地鸡等高突变频率的品种可能反映了其环境适应性选择。这些品种可能通过RARRES1突变提高了代谢和饲料效率,以适应特定的环境压力。
总结:
总体来看,原鸡、蛋鸡、肉蛋兼用鸡、肉鸡和其他鸡种在RARRES1基因位点的突变频率差异较大,反映了不同的育种方向、地理环境适应性和选择压力。
9 22597203 G/C G 0.176 missense_variant MODERATE RARRES1 rs10728678 9:22153436
Group (number): frequence
Gallus_gallus_bankiva(2):1.000
Gallus_gallus_gallus(4):1.000
Gallus_gallus_jabouillei(27):1.000
Gallus_gallus_murghi(51):0.382
Gallus_gallus_spadiceus(40):0.975
Indonesia_Native_Chicken(34):0.956
Thailand_Native_Chicken(6):1.000
Vietnam_Native_Chicken(6):1.000
Wenchang_Chicken(1):1.000
Yunnan_Chicken(11):1.000
Xishuangbanna_Game_Chicken(9):0.889
Nixi_Chicken(12):0.792
Dulong_Chicken(7):0.929
Daweishan_Mini_Chicken(8):1.000
Guangxi_Chicken(5):1.000
Guangzhou_Chicken(2):1.000
Jiangxi_Silkies(20):0.975
Anyi_Gray_Chicken(5):0.700
Dongxiang_Blue-eggshell_Chicken(6):0.833
Tianfu_Black-bone_Chicken(5):0.800
Shimian_Caoke_Chicken(1):1.000
Jiuyuan_Black-bone_Chicken(5):1.000
Jinyang_Silky_Chicken(6):0.833
Emei_Black_Chicken(4):1.000
Pengxian_Yellow_Chicken(6):1.000
Muchuan_Black-bone_Chicken(5):0.800
Miyi_Chicken(5):0.700
YuanBao_Chicken(22):1.000
Langshan_Chicken(10):1.000
Luxi_Game_Chicken(9):1.000
Shouguang_Chicken(8):1.000
Gushi_Chicken(8):0.375
Bian_Chicken(8):0.688
Beijing_You_Chicken(11):0.864
Dagu_Chicken(8):1.000
Xinjiang_Native_Chicken(6):0.583
Hetian_Black_Chicken(8):1.000
Southern_Xinjiang_Game_Chicken(8):0.750
Turpan_Game_Chicken(8):1.000
Tibetan_Chicken(128):0.824
Araucana_Blue-eggshell_Chicken(6):0.833
Sri_Lanka_Native_Chicken(6):1.000
Bengal_Native_Chicken(15):0.867
India_Native_Chicken(41):0.902
Pakistan_Native_Chicken(35):0.571
Afghan_Native_Chicken(11):0.864
Iran_Native_Chicken(177):0.774
Iran_Commercial_Broiler(4):0.625
White_Leghorn_Chicken(13):0.731
Cornish_Chicken(1):1.000
Rhode_Island_Red_Chicken(1):1.000
White_Plymouth_Rock_Chicken(1):1.000
从你提供的数据中,我们可以看到RARRES1基因的一个错义突变位点(missense variant)的等位基因频率分布。这一位点的突变可能会影响RARRES1蛋白的功能,而RARRES1与细胞的代谢、脂肪调控等功能密切相关。通过分析这些鸡种的突变频率,我们可以尝试找出一些规律,并解释这些突变可能的生物学意义。
数据分布概况:
1. 高突变频率(接近或为1.000)的鸡种:
- Gallus gallus bankiva(红原鸡):1.000
- Gallus gallus gallus(普通原鸡):1.000
- Gallus gallus jabouillei(越南原鸡):1.000
- Indonesia Native Chicken(印尼本地鸡):0.956
- Thailand Native Chicken(泰国本地鸡):1.000
- Vietnam Native Chicken(越南本地鸡):1.000
- Wenchang Chicken(文昌鸡):1.000
- Yunnan Chicken(云南鸡):1.000
- Pengxian Yellow Chicken(彭县黄鸡):1.000
- Luxi Game Chicken(鲁西斗鸡):1.000
- Cornish Chicken(康沃尔鸡):1.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):1.000
- Rhode Island Red Chicken(罗得岛红鸡):1.000
这些鸡种的突变频率为 1.000 或接近 1.000,意味着在这些鸡种中,这个RARRES1的变异是完全固定的。固定的高频率变异可能表明,这个突变对于这些鸡种的生长、代谢、适应性等有重要的生物学功能,可能有助于增强代谢效率、脂肪储存调节或与环境适应相关的特性。
2. 中等突变频率(0.6 - 0.9)的鸡种:
- Afghan Native Chicken(阿富汗本地鸡):0.864
- Beijing You Chicken(北京油鸡):0.864
- India Native Chicken(印度本地鸡):0.902
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.833
- Iran Native Chicken(伊朗本地鸡):0.774
- Xinjiang Native Chicken(新疆本地鸡):0.583
- Tibetan Chicken(西藏鸡):0.824
这些鸡种的突变频率在 0.6 到 0.9 之间,这表明在这些鸡种中,部分个体携带该突变,而部分个体可能没有突变。这可能表明,RARRES1的突变在这些鸡种中的生物学意义较为多样化,可能部分群体通过该突变获得了代谢和生存优势,但这种变异还没有在种群中完全固定。
3. 低突变频率(低于0.6)的鸡种:
- Gallus gallus murghi(印度原鸡):0.382
- Pakistan Native Chicken(巴基斯坦本地鸡):0.571
- Iran Commercial Broiler(伊朗商用肉鸡):0.625
- Gushi Chicken(固始鸡):0.375
这些鸡种的突变频率较低,说明大部分个体并没有携带这一变异。低突变频率可能表明,该突变在这些鸡种中的生物学作用较弱,或者它们通过其他遗传机制实现了代谢调节和适应性,因此没有保留这个突变。
可能的生物学意义和解释:
1. 原鸡中的突变:
- Gallus gallus bankiva(红原鸡)、Gallus gallus gallus(普通原鸡)和Gallus gallus jabouillei(越南原鸡)的突变频率为 1.000,表明在原鸡中,这个突变位点是完全固定的。这意味着,这个RARRES1基因突变在原鸡中可能是祖先型突变,在这些原鸡种群中得以广泛保留。这可能与原鸡的脂肪代谢、能量储备、体型等特性有关,帮助它们适应自然环境中的多样条件。
2. 本地鸡种和地方性鸡种中的突变:
- 像印尼本地鸡(0.956)、泰国本地鸡(1.000)、越南本地鸡(1.000)以及一些中国地方鸡种(如彭县黄鸡和云南鸡)等本地鸡种也显示出较高的突变频率。这些本地鸡种往往通过自然选择或传统育种,保留了对特定生态环境有适应性优势的突变。因此,这个RARRES1的突变可能帮助这些鸡种更好地适应其特定的生存环境,优化了能量代谢和饲料效率。
- 阿富汗本地鸡(0.864)和印度本地鸡(0.902)等也具有较高的突变频率,这可能与这些地区的环境压力(如高温、贫瘠的环境)有关。这个突变可能帮助它们优化能量代谢以适应当地的生存条件。
3. 肉鸡中的突变:
- Cornish Chicken(康沃尔鸡)和White Plymouth Rock Chicken(白色普利茅斯岩鸡)等肉鸡品种的突变频率为 1.000,说明该突变在这些肉鸡中也是完全固定的。这可能反映了在育种过程中,这个突变有助于提高肉鸡的饲料转化效率,增强它们的生长性能和脂肪代谢效率。
- 伊朗商用肉鸡突变频率为 0.625,相对较低,说明在商业化肉鸡的育种过程中,这个突变可能没有得到完全的保留。
4. 与代谢和饲料转化效率的关系:
- RARRES1基因与脂肪代谢和能量调控密切相关,因此在突变频率较高的鸡种中,可能通过这一基因的变异,优化了饲料转化率,即这些鸡种可能更有效地将饲料转化为生长和储能。这对肉鸡品种以及在贫瘠环境中生存的本地鸡种(如阿富汗、印度、越南鸡)尤其重要。
- 低突变频率的鸡种可能在其他代谢路径上发挥了作用,而不依赖于这个RARRES1变异。
总结:
高突变频率鸡种(如原鸡、本地鸡和肉鸡)在RARRES1基因上发生了显著的变异,这表明这些鸡种可能通过这个基因调控能量代谢、脂肪存储以及饲料转化效率,有助于它们适应特定环境或满足育种目标。
中等突变频率鸡种(如北京油鸡、阿富汗本地鸡、印度本地鸡)在RARRES1变异上的多样性,可能表明这些鸡种群体中部分个体通过该基因获得代谢优势,但群体尚未完全固定这个突变。
低突变频率鸡种(如印度原鸡、固始鸡、巴基斯坦本地鸡)显示出较少的RARRES1变异保留,可能表明这些鸡种在脂肪代谢或生长性能方面依赖其他遗传机制。
总的来看,RARRES1基因突变在不同鸡种中可能通过影响脂肪代谢、饲料转化率和能量储备来影响鸡种的生长和适应性。这些突变频率的差异可能反映了鸡种之间在育种目标和生态适应性方面的差异。
9 22598070 T/C T 0.223 missense_variant MODERATE RARRES1 rs316371930 9:22154303
Group (number): frequence
Gallus_gallus_bankiva(3):1.000
Gallus_gallus_gallus(5):0.900
Gallus_gallus_jabouillei(27):0.889
Gallus_gallus_murghi(53):0.085
Gallus_gallus_spadiceus(39):0.885
Indonesia_Native_Chicken(36):0.889
Thailand_Native_Chicken(6):0.917
Vietnam_Native_Chicken(7):1.000
Wenchang_Chicken(1):1.000
Yunnan_Chicken(12):0.833
Xishuangbanna_Game_Chicken(10):0.850
Nixi_Chicken(11):0.818
Dulong_Chicken(7):0.857
Daweishan_Mini_Chicken(7):0.929
Guangxi_Chicken(6):0.917
Guangzhou_Chicken(4):0.500
Jiangxi_Silkies(20):0.975
Anyi_Gray_Chicken(5):1.000
Dongxiang_Blue-eggshell_Chicken(6):0.833
Tianfu_Black-bone_Chicken(5):0.900
Shimian_Caoke_Chicken(4):1.000
Jiuyuan_Black-bone_Chicken(5):1.000
Jinyang_Silky_Chicken(6):0.833
Emei_Black_Chicken(6):1.000
Pengxian_Yellow_Chicken(6):1.000
Muchuan_Black-bone_Chicken(5):0.900
Miyi_Chicken(5):0.700
YuanBao_Chicken(23):1.000
Langshan_Chicken(10):1.000
Luxi_Game_Chicken(9):1.000
Shouguang_Chicken(7):0.929
Gushi_Chicken(8):0.812
Bian_Chicken(7):0.857
Beijing_You_Chicken(11):0.773
Dagu_Chicken(7):0.857
Xinjiang_Native_Chicken(6):0.583
Hetian_Black_Chicken(8):1.000
Southern_Xinjiang_Game_Chicken(8):0.812
Turpan_Game_Chicken(8):1.000
Tibetan_Chicken(140):0.846
Araucana_Blue-eggshell_Chicken(6):0.833
Sri_Lanka_Native_Chicken(6):1.000
Bengal_Native_Chicken(12):0.750
India_Native_Chicken(43):0.465
Pakistan_Native_Chicken(36):0.708
Afghan_Native_Chicken(11):0.727
Iran_Native_Chicken(181):0.765
Iran_Commercial_Broiler(4):0.500
White_Leghorn_Chicken(13):0.731
Cornish_Chicken(1):1.000
Rhode_Island_Red_Chicken(1):1.000
White_Plymouth_Rock_Chicken(1):1.000
这个数据集展示了RARRES1基因位点的另一个错义突变(missense variant),位于染色体9的22598070位置。不同鸡种在该位点的突变频率差异很大。我们可以从不同鸡种的突变频率中,结合RARRES1的功能,对这些鸡种的代谢特性、饲料转化率等方面进行分析和解释。
RARRES1的功能背景
RARRES1基因与脂肪代谢、细胞分化等相关,可能影响饲料转化率、脂肪存储等功能。错义突变会导致蛋白质序列发生变化,可能改变蛋白质的功能,从而影响这些鸡种的生理特性。
按突变频率的分类分析
1. 高突变频率的鸡种(接近1.000)
- Gallus gallus bankiva(红原鸡):1.000
- Gallus gallus jabouillei(越南原鸡):0.889
- Vietnam Native Chicken(越南本地鸡):1.000
- Thailand Native Chicken(泰国本地鸡):0.917
- Jiangxi Silkies(江西丝毛鸡):0.975
- Emei Black Chicken(峨眉黑鸡):1.000
- Cornish Chicken(康沃尔鸡):1.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):1.000
分析:
- 高突变频率意味着这些鸡种可能在进化过程中保留了该位点的变异。比如,红原鸡、越南原鸡和越南本地鸡等鸡种均显示出较高的突变频率(接近1.000),表明这些鸡种对这一位点的突变有选择优势。RARRES1基因的功能可能有助于这些鸡种在特定环境下优化代谢和饲料转化,提升生存能力。
- 肉鸡品种如康沃尔鸡和白色普利茅斯岩鸡也具有高突变频率,这表明该突变可能有助于饲料转化效率,提高它们的生长性能,支持这些鸡种在商业育种中的快速生长目标。
2. 中等突变频率的鸡种(0.7 - 0.9)
- Beijing You Chicken(北京油鸡):0.773
- Bengal Native Chicken(孟加拉本地鸡):0.750
- Pakistan Native Chicken(巴基斯坦本地鸡):0.708
- Tibetan Chicken(西藏鸡):0.846
- Southern Xinjiang Game Chicken(南疆斗鸡):0.812
- Iran Native Chicken(伊朗本地鸡):0.765
- Afghan Native Chicken(阿富汗本地鸡):0.727
分析:
- 这些鸡种的突变频率处于中等水平,表明部分个体保留了RARRES1的突变,可能与这些鸡种在其特定生存环境中的局部适应性有关。
- 西藏鸡和南疆斗鸡生活在高海拔地区,突变可能帮助它们在低氧和严酷环境中更好地进行代谢调节。这些鸡种保留了一定程度的突变,可能与高效代谢和饲料转化有关。
3. 低突变频率的鸡种(低于0.6)
- Gallus gallus murghi(印度原鸡):0.085
- India Native Chicken(印度本地鸡):0.465
- Pakistan Native Chicken(巴基斯坦本地鸡):0.708
- Iran Commercial Broiler(伊朗商用肉鸡):0.500
- Gushi Chicken(固始鸡):0.812
分析:
- 印度原鸡的突变频率极低(0.085),说明这个鸡种在RARRES1的变异上未受到明显的自然选择压力。它可能保留了更多的原始基因背景,并未通过该位点的突变来增强代谢功能。
- 印度本地鸡和巴基斯坦本地鸡的突变频率较低,说明在这些鸡种中,RARRES1的突变并没有完全固定。相比于高突变频率的鸡种,它们可能依赖其他基因位点或途径来调节代谢和生长性能。
- 伊朗商用肉鸡突变频率为0.500,表明这个位点的变异在肉鸡的商业育种中可能并不重要,或者商业化育种更多地集中在其他基因对肉质和生长速度的影响上。
潜在的生物学意义
1. 代谢调控与环境适应
RARRES1基因在脂肪代谢和能量调控中的作用表明,该突变可能有助于鸡种适应特定的环境条件,如寒冷、低氧或低营养环境。突变可能通过影响细胞的代谢途径,帮助鸡种更高效地储存或利用能量,尤其是在饲料资源有限的环境下。
2. 饲料转化率与育种目标
- 肉鸡品种如康沃尔鸡、白色普利茅斯岩鸡等突变频率高,表明RARRES1的变异可能在饲料转化率和生长速度方面有积极作用。这些肉鸡的商业育种可能通过选择RARRES1突变,优化了饲料转化为生长的效率。
- 蛋鸡如白色莱格恩鸡(0.731),突变频率中等偏高,表明其育种目标主要集中在高产蛋量,而不是完全依赖该基因的突变来提高饲料转化率。
3. 自然选择与遗传多样性
- 高突变频率的原鸡(如红原鸡)和本地鸡种表明,RARRES1的变异可能受到自然选择的强烈影响,帮助这些鸡种更好地适应其生活环境。特别是像越南本地鸡、泰国本地鸡这些在热带气候下生活的鸡种,突变可能帮助它们在炎热、湿润环境下保持较高的代谢效率。
- 突变频率较低的鸡种,如印度原鸡和印度本地鸡,表明它们在RARRES1基因的调控上依赖于较原始的基因型,可能没有经历强烈的选择压力。
总结
高突变频率的鸡种(如原鸡、部分地方鸡和肉鸡)可能通过RARRES1基因突变优化了饲料转化率和代谢效率,适应了特定环境或育种目标。尤其是肉鸡品种,该突变可能与其快速生长性能相关。
中等突变频率的鸡种(如北京油鸡、孟加拉本地鸡、阿富汗本地鸡)可能部分群体在进化或育种过程中保留了RARRES1的突变,这可能帮助它们在复杂环境中获得代谢优势。
低突变频率的鸡种(如印度原鸡、伊朗商用肉鸡)在该位点上的变异较少,表明这些鸡种可能通过其他遗传途径调控其代谢性能。
总的来看,RARRES1基因的变异在不同鸡种中可能通过影响脂肪代谢、饲料转化效率和环境适应性来发挥重要作用。突变频率的差异可能反映了不同鸡种在自然选择和育种目标下的不同遗传背景和生理需求。
根据你提供的RARRES1基因错义突变位点的频率数据,我将这些鸡种按照蛋鸡、肉鸡、肉蛋兼用鸡和其他鸡种进行分类,并对各类别中的鸡种进行分析解释。
1. 蛋鸡:
- White Leghorn Chicken(白色莱格恩鸡):0.731
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.833
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.833
- Jiangxi Silkies(江西丝毛鸡):0.975
分析:
- 白色莱格恩鸡(0.731)是著名的高产蛋鸡。突变频率较高表明该位点的RARRES1突变可能在脂肪代谢和能量利用方面发挥了作用,从而帮助提高鸡的饲料转化效率,优化了其产蛋性能。虽然RARRES1基因通常与代谢和脂肪储存相关,但该鸡种的育种目标主要是提高产蛋量,因此高突变频率可能支持更高效的代谢。
- 东乡蓝蛋鸡(0.833)和阿劳卡纳蓝蛋鸡(0.833)同样表现出高突变频率,表明这些特色蛋鸡在育种过程中保留了RARRES1的突变,可能帮助其在低能耗环境中维持高产蛋量。突变的保留可能有助于改善能量效率和代谢平衡,以适应产蛋需求。
- 江西丝毛鸡(0.975)的突变频率非常高,接近完全固定,表明该突变在育种过程中被强烈选择。该鸡种主要用于产蛋和食用,突变可能帮助提高其在饲料消化和能量利用方面的效率,从而实现更高的饲料转化率和产蛋性能。
2. 肉鸡:
- Cornish Chicken(康沃尔鸡):1.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):1.000
- Iran Commercial Broiler(伊朗商用肉鸡):0.500
分析:
- 康沃尔鸡和白色普利茅斯岩鸡突变频率为 1.000,说明这些肉鸡品种在育种过程中,RARRES1的突变得到了完全保留。肉鸡的育种主要集中在快速生长和高饲料转化率,这一突变可能有助于提高这些鸡种的脂肪代谢能力,让它们能够更有效地将饲料转化为体重。这种突变可能优化了鸡种在短时间内的生长速度,从而满足商业化肉鸡对快速增重的需求。
- 伊朗商用肉鸡(0.500)的突变频率相对较低,说明RARRES1突变对其饲料转化率的影响较为有限,可能依赖其他基因或途径来调节生长速度和代谢效率。
3. 肉蛋兼用鸡:
- Beijing You Chicken(北京油鸡):0.773
- Dagu Chicken(大谷鸡):0.857
- Gushi Chicken(固始鸡):0.812
- Rhode Island Red Chicken(罗得岛红鸡):1.000
分析:
- 北京油鸡(0.773) 和 大谷鸡(0.857) 的突变频率表明这些肉蛋兼用鸡在育种过程中也保留了一定的RARRES1突变。这些鸡种需要在产蛋和肉质生长之间取得平衡,RARRES1的突变可能帮助它们在饲料转化效率上表现良好,以满足双重用途鸡种的需求。这些突变可能优化了它们的代谢,使它们既能保持一定的产蛋率,又能有效增加体重。
- 固始鸡(0.812) 同样表现出较高的突变频率,这可能帮助它们在育种过程中提高了饲料利用效率,支持其作为地方优质鸡种的双重用途特性。
- 罗得岛红鸡(1.000) 是全球广泛饲养的肉蛋兼用鸡品种,突变频率为100%,说明RARRES1突变对其产蛋量和生长性能都具有显著的正向影响。它的高突变频率反映了育种选择过程中对能量代谢和脂肪调控的需求,以优化其多重用途特性。
4. 其他鸡种:
- Gallus gallus bankiva(红原鸡):1.000
- Gallus gallus gallus(普通原鸡):0.900
- Gallus gallus jabouillei(越南原鸡):0.889
- Indonesia Native Chicken(印尼本地鸡):0.889
- Vietnam Native Chicken(越南本地鸡):1.000
- Tibetan Chicken(西藏鸡):0.846
- Southern Xinjiang Game Chicken(南疆斗鸡):0.812
- Pakistan Native Chicken(巴基斯坦本地鸡):0.708
- Afghan Native Chicken(阿富汗本地鸡):0.727
- India Native Chicken(印度本地鸡):0.465
分析:
- 红原鸡、普通原鸡、越南原鸡 等原鸡品种的突变频率较高,这表明RARRES1突变是这些鸡种的祖先型变异,可能在进化过程中通过自然选择被保留。这些原鸡种需要在自然环境中生存,突变可能帮助它们在有限资源下优化代谢。
- 西藏鸡(0.846) 和 南疆斗鸡(0.812) 等高原或偏远地区的鸡种显示出较高的突变频率,这些鸡种可能通过RARRES1的变异来应对恶劣的生存环境(如低氧和寒冷)。突变帮助它们在能量储存和饲料利用方面表现出色,从而适应极端环境。
- 阿富汗本地鸡和巴基斯坦本地鸡的突变频率相对中等偏高(0.727 和 0.708),表明这些鸡种在部分群体中保留了RARRES1突变。这可能帮助它们应对当地高温或贫瘠环境下的生存挑战。
- 印度本地鸡(0.465)突变频率较低,表明这个鸡种可能并不依赖于RARRES1突变来提高代谢效率,而是通过其他途径优化其生理功能。
总结:
- 蛋鸡通常表现出中等到高的突变频率,RARRES1的突变可能帮助它们在产蛋效率和饲料转化率方面取得平衡,尤其是特色蛋鸡和高产蛋鸡种(如白色莱格恩鸡)。
- 肉鸡普遍具有高突变频率(接近1.000),表明RARRES1的突变对其快速生长和高饲料转化率有着重要影响,帮助这些鸡种高效地将饲料转化为体重。
- 肉蛋兼用鸡的突变频率较高,表明它们通过RARRES1突变提高了能量代谢,能够在产蛋和增重之间取得良好平衡。
- 其他鸡种中的原鸡和地方本地鸡,突变频率较高,表明RARRES1的变异是它们适应不同生态环境(如低氧、高温或贫瘠地区)的重要因素,尤其在自然选择过程中发挥了关键作用。
从你提供的RARRES1基因错义突变位点的数据中,我们可以看到不同鸡种在染色体9的22598987位点的突变频率。这个位点的突变会导致蛋白质序列的变化,进而可能影响RARRES1蛋白的功能。RARRES1基因与代谢调控、脂肪储存、细胞功能等相关,因此,这个突变可能对鸡种的饲料转化率、代谢效率以及环境适应性产生影响。
按突变频率的分类和分析
1. 高突变频率的鸡种(接近1.000)
- Wenchang Chicken(文昌鸡):1.000
- Nixi Chicken(尼西鸡):1.000
- Dulong Chicken(独龙鸡):1.000
- Daweishan Mini Chicken(大围山迷你鸡):1.000
- Guangzhou Chicken(广州鸡):1.000
- Anyi Gray Chicken(安义灰鸡):1.000
- Shimian Caoke Chicken(石棉草科鸡):1.000
- Jiuyuan Black-bone Chicken(九圆乌骨鸡):1.000
- Jinyang Silky Chicken(金阳丝毛鸡):1.000
- Pengxian Yellow Chicken(彭县黄鸡):1.000
- YuanBao Chicken(元宝鸡):1.000
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.833
- Tianfu Black-bone Chicken(天府乌骨鸡):0.900
分析:
这些鸡种的突变频率接近或达到1.000,意味着这些鸡种中大部分个体在RARRES1位点上都携带了突变。这表明该突变在这些鸡种中已经得到固定,可能是育种选择或自然选择的结果。RARRES1的功能涉及能量代谢和脂肪储存,因此这些鸡种可能通过该突变提高了饲料利用率和生长性能。例如:
- 文昌鸡是中国的优质肉鸡,突变频率高可能有助于提高其生长速度和肉质品质。
- 尼西鸡和独龙鸡等地方性鸡种生活在生态环境相对恶劣的区域,高突变频率可能帮助它们适应这些地区的环境压力,通过优化能量代谢提高生存能力。
- 元宝鸡和东乡蓝蛋鸡作为地方特色鸡种,其高突变频率可能与它们在脂肪代谢、饲料转化效率等方面的表现相关。
2. 中等突变频率的鸡种(0.6 - 0.9)
- Gallus gallus gallus(普通原鸡):0.583
- Gallus gallus jabouillei(越南原鸡):0.885
- Indonesia Native Chicken(印尼本地鸡):0.681
- Thailand Native Chicken(泰国本地鸡):0.800
- Vietnam Native Chicken(越南本地鸡):0.583
- Xishuangbanna Game Chicken(西双版纳斗鸡):0.800
- Jiangxi Silkies(江西丝毛鸡):0.816
- Emei Black Chicken(峨眉黑鸡):0.917
- Muchuan Black-bone Chicken(木川乌骨鸡):0.900
- Luxi Game Chicken(鲁西斗鸡):0.944
分析:
这些鸡种的突变频率处于中等水平,表明在其群体中部分个体携带该突变。突变在这些鸡种中的适应性功能可能与其生活的生态环境或育种目标有关。例如:
- 印尼、泰国、越南本地鸡的突变频率较高,表明在热带和亚热带气候下,RARRES1突变可能通过帮助提高代谢效率来增强鸡种的生存适应性。
- 江西丝毛鸡和峨眉黑鸡作为地方优质鸡种,其突变频率高,可能帮助这些鸡种在饲料利用率和肉质发育方面表现优异。
- 斗鸡品种(西双版纳斗鸡和鲁西斗鸡)的突变频率较高,可能通过提高能量消耗效率帮助这些鸡种在高强度体力活动中表现出色。
3. 低突变频率的鸡种(低于0.6)
- Gallus gallus bankiva(红原鸡):0.000
- Gallus gallus murghi(印度原鸡):0.071
- India Native Chicken(印度本地鸡):0.465
- Langshan Chicken(郎山鸡):0.400
分析:
低突变频率的鸡种,如红原鸡(0.000)和印度原鸡(0.071),显示了这些原鸡种在该突变位点上保留了原始的基因型,未经历强烈的自然或人工选择。它们可能依赖其他遗传机制进行代谢调控。低突变频率的鸡种可能没有强烈依赖该位点的变异来调节能量代谢和饲料转化率。印度本地鸡突变频率为 0.465,表明其群体中部分个体保留了RARRES1突变,可能有助于它们适应当地较为恶劣的生存条件。
总结与规律
高突变频率鸡种(如文昌鸡、尼西鸡、元宝鸡等)表现出代谢效率提高的倾向,突变可能帮助它们优化饲料转化率,这对于肉鸡和地方性鸡种来说尤为重要。这些鸡种可能通过保留RARRES1的突变来提高能量利用,更适应它们所处的环境或满足特定的育种需求。
中等突变频率鸡种(如印尼本地鸡、泰国本地鸡、江西丝毛鸡等)表明这些鸡种在能量代谢调控方面部分依赖RARRES1突变。这些鸡种生活在复杂的生态环境中,突变可能帮助它们在一定的环境压力下保持生长优势。
低突变频率鸡种(如原鸡和印度本地鸡)说明这些鸡种在RARRES1位点上没有受到强烈的选择压力,可能依赖其他途径来适应其环境。它们保留了更多的原始基因型,这可能与其较少的人工选择历史或独特的生存策略相关。
通过分析不同鸡种的突变频率,我们可以推测RARRES1基因的突变在饲料转化率、能量代谢和环境适应性方面发挥了关键作用,尤其是在肉鸡和地方性鸡种中,这些突变有助于优化其生长性能。
根据你提供的RARRES1基因错义突变位点(9:22598987 A/C)的数据,我将不同鸡种按照原鸡、蛋鸡、肉鸡、肉蛋兼用鸡和其他鸡种进行分类分析,解释这些类别鸡种中的突变频率差异及其可能的生物学意义。
1. 原鸡
- Gallus gallus bankiva(红原鸡):0.000
- Gallus gallus gallus(普通原鸡):0.583
- Gallus gallus jabouillei(越南原鸡):0.885
- Gallus gallus murghi(印度原鸡):0.071
- Gallus gallus spadiceus(马来原鸡):0.857
分析:
- 红原鸡(0.000)和印度原鸡(0.071)突变频率非常低,说明这些原鸡品种保留了较多的原始基因背景,未受到RARRES1位点的显著选择压力,可能更多依赖其他途径进行能量代谢和环境适应。这表明在这些原鸡中,RARRES1基因的变异并没有显著影响它们的生存策略。
- 普通原鸡(0.583)、越南原鸡(0.885)和马来原鸡(0.857)突变频率较高,这表明部分原鸡品种可能在进化过程中通过RARRES1突变增强了能量代谢和饲料转化率,有助于它们适应不同的自然环境。
2. 蛋鸡
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.833
- Jiangxi Silkies(江西丝毛鸡):0.816
- Anyi Gray Chicken(安义灰鸡):1.000
分析:
- 东乡蓝蛋鸡(0.833)和江西丝毛鸡(0.816)在蛋鸡中表现出较高的突变频率,这可能与它们需要高效能量利用来支持长时间产蛋期有关。RARRES1的突变可能帮助这些蛋鸡优化饲料转化率,使其在消耗较少饲料的情况下保持高产蛋量。
- 安义灰鸡(1.000)突变频率为1.000,表明该突变可能对该鸡种的代谢和饲料效率具有非常重要的影响,帮助其保持较高的产蛋性能和能量利用效率。
3. 肉鸡
- Wenchang Chicken(文昌鸡):1.000
- Langshan Chicken(郎山鸡):0.400
- Luxi Game Chicken(鲁西斗鸡):0.944
- Tianfu Black-bone Chicken(天府乌骨鸡):0.900
- Shimian Caoke Chicken(石棉草科鸡):1.000
- Jiuyuan Black-bone Chicken(九圆乌骨鸡):1.000
分析:
- 文昌鸡(1.000)、石棉草科鸡(1.000)和九圆乌骨鸡(1.000)是肉鸡品种中的典型代表,其突变频率为1.000,表明RARRES1基因在这些鸡种中可能发挥了重要作用。突变可能通过增强饲料转化效率和能量代谢,帮助它们在较短时间内达到最佳的生长和增重效果。
- 郎山鸡(0.400)的突变频率较低,这可能表明RARRES1突变在该鸡种的饲料利用和代谢效率方面影响较小,或者该鸡种更多依赖其他基因途径来提升其生长性能。
- 鲁西斗鸡(0.944)是一种用于斗鸡的品种,其高突变频率表明RARRES1的突变可能帮助提高了其能量消耗效率,使其在斗鸡活动中具备较高的体能和代谢能力。
4. 肉蛋兼用鸡
- Beijing You Chicken(北京油鸡):0.773
- Pengxian Yellow Chicken(彭县黄鸡):1.000
- Miyi Chicken(米易鸡):0.700
- Jinyang Silky Chicken(金阳丝毛鸡):1.000
- Muchuan Black-bone Chicken(木川乌骨鸡):0.900
分析:
- 彭县黄鸡(1.000)、金阳丝毛鸡(1.000)、和木川乌骨鸡(0.900)等肉蛋兼用鸡具有较高的突变频率,表明这些鸡种可能通过RARRES1突变平衡了产蛋性能与肉质发育的需求。突变帮助它们提高饲料利用率,从而兼具产蛋和增重的双重优势。
- 北京油鸡(0.773)的突变频率中等偏高,表明该鸡种在部分个体中保留了RARRES1的突变,可能优化了其代谢功能,以适应双重用途鸡种的生产需求。
- 米易鸡(0.700)突变频率较为适中,显示它在育种过程中可能兼顾了产蛋和增重的平衡,通过RARRES1突变来提高其代谢效率。
5. 其他鸡种
- Indonesia Native Chicken(印尼本地鸡):0.681
- Thailand Native Chicken(泰国本地鸡):0.800
- Vietnam Native Chicken(越南本地鸡):0.583
- Dulong Chicken(独龙鸡):1.000
- Nixi Chicken(尼西鸡):1.000
- Xishuangbanna Game Chicken(西双版纳斗鸡):0.800
分析:
- 独龙鸡(1.000)和尼西鸡(1.000)等地方鸡种具有极高的突变频率,表明这些鸡种生活在偏远、生态多样性高的环境中,可能依赖RARRES1突变来优化能量利用和代谢效率,以应对较为恶劣的生存条件。
- 印尼本地鸡(0.681)、泰国本地鸡(0.800)和越南本地鸡(0.583)等本地鸡种的突变频率处于中等水平,表明这些鸡种可能在部分个体中保留了RARRES1突变,帮助它们适应热带、亚热带的环境。
- 西双版纳斗鸡(0.800)的突变频率较高,表明该突变可能对斗鸡品种的体能、代谢和耐力产生了积极影响。
总结与解释:
- 原鸡中,红原鸡和印度原鸡突变频率较低,表明它们未经历RARRES1基因的强烈选择;而普通原鸡、越南原鸡和马来原鸡的较高突变频率则反映了其适应环境的能力。
- 蛋鸡中的高突变频率表明这些鸡种可能通过RARRES1突变提高了能量代谢效率,以维持高产蛋性能。
- 肉鸡品种普遍表现出高突变频率,说明RARRES1突变对饲料转化率和快速增重具有显著的促进作用。
- 肉蛋兼用鸡在突变频率上表现中等到高,反映了其在生产中平衡产蛋和增重的需求,通过突变优化其双重用途的生长性能。
- 其他鸡种中,尤其是地方性鸡种,如独龙鸡和尼西鸡,突变频率极高,表明RARRES1突变可能帮助它们适应严酷的生存环境,提高了代谢和能量利用效率。
总的来看,RARRES1基因突变在不同鸡种中的作用与其生产需求、环境适应性及生长特性密切相关。
22599034 T/G G 0.061 missense_variant MODERATE RARRES1 rs313099245 9:22155267
Group (number): frequence
Gallus_gallus_bankiva(2):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(27):0.000
Gallus_gallus_murghi(50):0.340
Gallus_gallus_spadiceus(43):0.023
Indonesia_Native_Chicken(36):0.083
Thailand_Native_Chicken(6):0.083
Vietnam_Native_Chicken(7):0.000
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.000
Xishuangbanna_Game_Chicken(10):0.050
Nixi_Chicken(12):0.000
Dulong_Chicken(7):0.000
Daweishan_Mini_Chicken(8):0.000
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(3):0.000
Jiangxi_Silkies(20):0.000
Anyi_Gray_Chicken(5):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.000
Shimian_Caoke_Chicken(4):0.000
Jiuyuan_Black-bone_Chicken(5):0.000
Jinyang_Silky_Chicken(6):0.000
Emei_Black_Chicken(6):0.000
Pengxian_Yellow_Chicken(6):0.000
Muchuan_Black-bone_Chicken(5):0.000
Miyi_Chicken(5):0.000
YuanBao_Chicken(24):0.000
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(9):0.000
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.125
Bian_Chicken(8):0.000
Beijing_You_Chicken(11):0.182
Dagu_Chicken(8):0.125
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(8):0.000
Southern_Xinjiang_Game_Chicken(8):0.000
Turpan_Game_Chicken(8):0.000
Tibetan_Chicken(140):0.007
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(7):0.000
Bengal_Native_Chicken(15):0.033
India_Native_Chicken(47):0.351
Pakistan_Native_Chicken(36):0.000
Afghan_Native_Chicken(11):0.091
Iran_Native_Chicken(182):0.041
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(13):0.154
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
从你提供的这个RARRES1基因错义突变位点(22599034 T/G,rs313099245)的数据来看,这个位点的突变会导致RARRES1蛋白的氨基酸序列发生变化,可能影响其功能。通过分析不同鸡种的突变频率,我们可以尝试推测这个突变在不同鸡种中的生物学意义,特别是与能量代谢、饲料转化率及环境适应性相关的作用。
1. 原鸡
- Gallus gallus bankiva(红原鸡):0.000
- Gallus gallus gallus(普通原鸡):0.000
- Gallus gallus jabouillei(越南原鸡):0.000
- Gallus gallus murghi(印度原鸡):0.340
- Gallus gallus spadiceus(马来原鸡):0.023
分析:
- 红原鸡、普通原鸡、越南原鸡和马来原鸡的突变频率非常低(接近或等于0.000),表明这些原鸡品种在该位点上没有发生显著突变,保留了较多的原始基因型。RARRES1基因的变异对这些原鸡种群的代谢和能量调控影响较小。
- 印度原鸡(0.340)的突变频率较高,说明部分个体可能携带此突变。这表明印度原鸡在进化过程中可能通过此突变优化了能量代谢,以更好地适应其环境(如高温和干旱的气候条件)。
2. 蛋鸡
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.000
- Jiangxi Silkies(江西丝毛鸡):0.000
- Anyi Gray Chicken(安义灰鸡):0.000
- White Leghorn Chicken(白色莱格恩鸡):0.154
分析:
- 东乡蓝蛋鸡、江西丝毛鸡、安义灰鸡等特色蛋鸡突变频率为0.000,表明RARRES1基因位点在这些蛋鸡中的突变并未固定。可能是因为这些蛋鸡主要注重产蛋量,与代谢或脂肪储存无关的突变没有在这些鸡种中得到选择。
- 白色莱格恩鸡(0.154) 的突变频率较低,但不为0,这表明在育种过程中部分个体携带此突变。此突变可能对饲料转化率有一定的帮助,但整体突变并未在群体中完全固定。
3. 肉鸡
- Cornish Chicken(康沃尔鸡):0.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):0.000
- Rhode Island Red Chicken(罗得岛红鸡):0.000
- Iran Commercial Broiler(伊朗商用肉鸡):0.000
分析:
- 康沃尔鸡、白色普利茅斯岩鸡、罗得岛红鸡和伊朗商用肉鸡的突变频率为0.000,说明这些商业化肉鸡品种在该位点上没有发生突变。这些肉鸡的育种目标通常集中在快速生长和高饲料转化率,说明在这些品种中,该位点的RARRES1突变并未对其生长性能产生显著影响,或其他基因可能对其代谢调控发挥了更大的作用。
4. 肉蛋兼用鸡
- Beijing You Chicken(北京油鸡):0.182
- Dagu Chicken(大谷鸡):0.125
- Gushi Chicken(固始鸡):0.125
分析:
- 北京油鸡(0.182)、大谷鸡(0.125)和固始鸡(0.125)的突变频率较低,但在肉蛋兼用鸡种中具有一定保留。这些鸡种的生产目标是平衡产蛋性能与肉质,RARRES1突变可能帮助部分个体提高了代谢效率,但整体上未对整个群体产生强烈的影响。
5. 其他鸡种
- Indonesia Native Chicken(印尼本地鸡):0.083
- Thailand Native Chicken(泰国本地鸡):0.083
- Vietnam Native Chicken(越南本地鸡):0.000
- Xishuangbanna Game Chicken(西双版纳斗鸡):0.050
- Bengal Native Chicken(孟加拉本地鸡):0.033
- India Native Chicken(印度本地鸡):0.351
- Afghan Native Chicken(阿富汗本地鸡):0.091
- Iran Native Chicken(伊朗本地鸡):0.041
- Tibetan Chicken(西藏鸡):0.007
分析:
- 印度本地鸡(0.351)和印度原鸡(0.340)突变频率较高,这表明在印度环境下,RARRES1的突变可能对这些鸡种的代谢调控和环境适应性起到重要作用。突变可能帮助这些鸡种在高温干旱的环境中更好地调节能量消耗和存储。
- 印尼、泰国本地鸡(0.083)的突变频率较低,表明这些鸡种的部分个体携带该突变,但尚未在整个种群中完全固定。这可能表明它们生活在热带气候中,该突变对其代谢有一定影响,但并不是最关键的因素。
- 阿富汗本地鸡(0.091)和伊朗本地鸡(0.041)的突变频率较低,这表明在这些地区的本地鸡种中,RARRES1突变虽然存在,但对其生理功能的影响可能较小。
总结与分析
原鸡:
- 印度原鸡和印度本地鸡突变频率较高,表明RARRES1突变对它们的代谢调控和环境适应可能具有一定优势。相对而言,其他原鸡(如红原鸡、普通原鸡、越南原鸡)保持了较低的突变频率,说明它们依赖其他基因机制来调节代谢。
蛋鸡:
- 蛋鸡(如白色莱格恩鸡)的突变频率较低,说明该突变对高产蛋性能影响不大。蛋鸡更多依赖其他代谢途径来维持其高产蛋需求。
肉鸡:
- 肉鸡(如康沃尔鸡、白色普利茅斯岩鸡)的突变频率为0,说明RARRES1突变对这些鸡种的快速生长和饲料转化率并无显著影响。
肉蛋兼用鸡:
- 肉蛋兼用鸡种(如北京油鸡、大谷鸡、固始鸡)的突变频率较低,但略高于蛋鸡和肉鸡,表明这些鸡种在产蛋和增重之间取得平衡时,部分个体可能通过RARRES1突变优化了代谢效率。
其他鸡种:
- 印度、阿富汗和伊朗本地鸡的突变频率较低但仍有存在,这表明这些鸡种可能依赖RARRES1基因的突变来应对其所在地区的生态压力,特别是炎热干旱气候下的代谢调节需求。
总的来看,RARRES1突变在这些鸡种中主要与代谢调控和环境适应性有关,而在高度商业化的肉鸡和蛋鸡中,该突变频率较低或不存在,表明它们更多依赖其他基因途径来提高生产性能。
2 52865223 C/T C 0.186 missense_variant MODERATE TPK1 rs10729385 2:52527535
Group (number): frequence
Gallus_gallus_bankiva(4):0.000
Gallus_gallus_gallus(6):1.000
Gallus_gallus_jabouillei(25):0.940
Gallus_gallus_murghi(49):0.765
Gallus_gallus_spadiceus(42):0.714
Indonesia_Native_Chicken(34):0.897
Thailand_Native_Chicken(6):0.750
Vietnam_Native_Chicken(7):0.786
Wenchang_Chicken(1):1.000
Yunnan_Chicken(12):0.958
Xishuangbanna_Game_Chicken(10):0.950
Nixi_Chicken(12):1.000
Dulong_Chicken(7):0.857
Daweishan_Mini_Chicken(7):0.929
Guangxi_Chicken(6):1.000
Guangzhou_Chicken(2):1.000
Jiangxi_Silkies(20):0.950
Anyi_Gray_Chicken(4):1.000
Dongxiang_Blue-eggshell_Chicken(6):1.000
Tianfu_Black-bone_Chicken(4):1.000
Shimian_Caoke_Chicken(1):1.000
Jiuyuan_Black-bone_Chicken(5):1.000
Jinyang_Silky_Chicken(6):0.917
Emei_Black_Chicken(3):0.833
Pengxian_Yellow_Chicken(6):1.000
Muchuan_Black-bone_Chicken(5):1.000
Miyi_Chicken(5):1.000
YuanBao_Chicken(20):1.000
Langshan_Chicken(9):1.000
Luxi_Game_Chicken(8):0.812
Shouguang_Chicken(7):1.000
Gushi_Chicken(7):0.643
Bian_Chicken(8):1.000
Beijing_You_Chicken(11):1.000
Dagu_Chicken(8):0.875
Xinjiang_Native_Chicken(5):0.600
Hetian_Black_Chicken(8):1.000
Southern_Xinjiang_Game_Chicken(8):0.875
Turpan_Game_Chicken(7):0.714
Tibetan_Chicken(124):0.730
Araucana_Blue-eggshell_Chicken(6):1.000
Sri_Lanka_Native_Chicken(7):1.000
Bengal_Native_Chicken(15):0.833
India_Native_Chicken(41):0.671
Pakistan_Native_Chicken(36):0.833
Afghan_Native_Chicken(11):0.818
Iran_Native_Chicken(180):0.739
Iran_Commercial_Broiler(4):1.000
White_Leghorn_Chicken(13):0.846
Cornish_Chicken(1):1.000
Rhode_Island_Red_Chicken(1):1.000
White_Plymouth_Rock_Chicken(1):1.000
这个TPK1基因位点(2:52865223 C/T,rs10729385)的数据展示了不同鸡种在该错义突变位点上的突变频率。TPK1基因与能量代谢密切相关,因此这个位点的突变可能影响鸡种的代谢效率、饲料转化率等特性。我们可以将这些鸡种按原鸡、蛋鸡、肉鸡、肉蛋兼用鸡、其他鸡种分类,分析它们的突变频率及其可能的生物学意义。
1. 原鸡
- Gallus gallus bankiva(红原鸡):0.000
- Gallus gallus gallus(普通原鸡):1.000
- Gallus gallus jabouillei(越南原鸡):0.940
- Gallus gallus murghi(印度原鸡):0.765
- Gallus gallus spadiceus(马来原鸡):0.714
分析:
- 红原鸡(0.000)在该位点上没有发生突变,表明它保留了更多的原始基因型,未经历明显的选择压力。
- 普通原鸡(1.000)和越南原鸡(0.940)的突变频率接近1.000,说明这些鸡种可能经历了选择压力,TPK1的突变帮助它们提高了能量代谢和饲料转化率,可能适应了特定的环境。
- 印度原鸡(0.765)和马来原鸡(0.714)的突变频率较高,说明它们部分个体可能通过此突变获得了代谢优势,但尚未完全固定。
2. 蛋鸡
- White Leghorn Chicken(白色莱格恩鸡):0.846
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):1.000
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):1.000
分析:
- 白色莱格恩鸡(0.846)作为高产蛋鸡,突变频率较高,表明该突变可能对饲料转化率和能量代谢起到了积极作用,从而优化了其产蛋性能。
- 东乡蓝蛋鸡和阿劳卡纳蓝蛋鸡(1.000)的突变频率为1.000,表明该突变在这些鸡种中已经完全固定。这可能有助于提升它们在较长时间的产蛋期内维持高效的能量代谢,从而提高产蛋量和饲料转化率。
3. 肉鸡
- Cornish Chicken(康沃尔鸡):1.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):1.000
- Rhode Island Red Chicken(罗得岛红鸡):1.000
- Iran Commercial Broiler(伊朗商用肉鸡):1.000
分析:
- 康沃尔鸡、白色普利茅斯岩鸡、罗得岛红鸡和伊朗商用肉鸡的突变频率均为1.000,表明这些肉鸡品种在育种过程中,TPK1基因的突变已经完全固定。这表明TPK1的突变可能帮助提高了它们的饲料转化率和快速生长性能,使得这些鸡种在商业化肉鸡生产中表现优异。
4. 肉蛋兼用鸡
- Beijing You Chicken(北京油鸡):1.000
- Dagu Chicken(大谷鸡):0.875
- Shouguang Chicken(寿光鸡):1.000
分析:
- 北京油鸡和寿光鸡(1.000)的突变频率达到100%,表明TPK1突变在这些鸡种中有利于饲料转化率和代谢效率,从而支持它们既能产蛋又能增重的需求。
- 大谷鸡(0.875)的突变频率虽然较高,但仍未完全固定,可能是在不同的生产目标(产蛋或增重)下,一部分个体更多依赖其他基因来调节代谢和能量利用。
5. 其他鸡种
- Indonesia Native Chicken(印尼本地鸡):0.897
- Thailand Native Chicken(泰国本地鸡):0.750
- Vietnam Native Chicken(越南本地鸡):0.786
- Tibetan Chicken(西藏鸡):0.730
- Bengal Native Chicken(孟加拉本地鸡):0.833
- India Native Chicken(印度本地鸡):0.671
- Pakistan Native Chicken(巴基斯坦本地鸡):0.833
- Afghan Native Chicken(阿富汗本地鸡):0.818
- Iran Native Chicken(伊朗本地鸡):0.739
分析:
- 印尼、泰国和越南本地鸡的突变频率较高(0.750-0.897),表明这些鸡种在热带环境下可能通过该突变提高了代谢效率,以适应其特有的生态环境。
- 西藏鸡(0.730)和阿富汗、巴基斯坦本地鸡的突变频率较高,说明在高原或较为贫瘠的环境下,TPK1的突变可能帮助它们更好地适应低氧和资源有限的环境。
- 印度本地鸡(0.671)和伊朗本地鸡(0.739)的突变频率较低,但仍有部分个体携带此突变,表明TPK1突变对这些鸡种的代谢调控有一定的影响,但并非最主要的遗传因素。
总结与解释
原鸡:
- 普通原鸡和越南原鸡的突变频率非常高,表明它们通过该突变优化了能量代谢,可能有助于适应不同的生态环境。
- 红原鸡保持了原始基因型,说明它依赖其他基因来调节代谢,而不是通过TPK1突变。
蛋鸡:
- 白色莱格恩鸡和蓝蛋鸡的突变频率较高,TPK1突变可能帮助它们维持高产蛋率的同时提高饲料转化率。
肉鸡:
- 肉鸡的突变频率为1.000,表明TPK1突变对其快速生长和饲料利用非常重要。这些肉鸡可能通过该基因突变优化了代谢效率,从而在商业化生产中具有优异表现。
肉蛋兼用鸡:
- 北京油鸡和寿光鸡的突变频率较高,说明TPK1突变有助于提高其在饲料转化和能量代谢中的表现,使其既能产蛋又能增重。
其他鸡种:
- 本地鸡种(如印尼、越南、西藏、阿富汗)的突变频率较高,表明这些鸡种可能通过该突变增强了在特定环境下的代谢适应性。
总结:
TPK1基因的突变在不同鸡种中表现出明显的差异。在商业化肉鸡和肉蛋兼用鸡中,突变频率较高甚至固定,说明该基因突变有助于提高它们的饲料转化率和快速生长性能。在本地鸡种中,突变有助于增强对复杂环境的适应性。而在某些原鸡和蛋鸡中,TPK1突变并未完全固定,表明这些鸡种可能通过其他基因调节其代谢和生长。
3 17430210 A/T T 0.195 missense_variant MODERATE KK34 rs15709215 13:16332631
Group (number): frequence
Gallus_gallus_bankiva(4):0.500
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(27):0.056
Gallus_gallus_murghi(54):0.019
Gallus_gallus_spadiceus(41):0.122
Indonesia_Native_Chicken(36):0.153
Thailand_Native_Chicken(6):0.167
Vietnam_Native_Chicken(7):0.143
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.125
Xishuangbanna_Game_Chicken(10):0.300
Nixi_Chicken(12):0.000
Dulong_Chicken(7):0.214
Daweishan_Mini_Chicken(8):0.188
Guangxi_Chicken(6):0.167
Guangzhou_Chicken(6):0.000
Jiangxi_Silkies(20):0.075
Anyi_Gray_Chicken(4):0.000
Dongxiang_Blue-eggshell_Chicken(5):0.300
Tianfu_Black-bone_Chicken(5):0.200
Shimian_Caoke_Chicken(4):0.000
Jiuyuan_Black-bone_Chicken(5):0.300
Jinyang_Silky_Chicken(6):0.167
Emei_Black_Chicken(6):0.167
Pengxian_Yellow_Chicken(6):0.083
Muchuan_Black-bone_Chicken(5):0.100
Miyi_Chicken(5):0.000
YuanBao_Chicken(24):0.000
Langshan_Chicken(8):0.000
Luxi_Game_Chicken(8):0.188
Shouguang_Chicken(7):0.071
Gushi_Chicken(4):0.000
Bian_Chicken(7):0.071
Beijing_You_Chicken(11):0.364
Dagu_Chicken(7):0.214
Xinjiang_Native_Chicken(6):0.167
Hetian_Black_Chicken(8):0.062
Southern_Xinjiang_Game_Chicken(8):0.250
Turpan_Game_Chicken(8):0.188
Tibetan_Chicken(147):0.078
Araucana_Blue-eggshell_Chicken(6):0.250
Sri_Lanka_Native_Chicken(7):0.214
Bengal_Native_Chicken(14):0.214
India_Native_Chicken(44):0.341
Pakistan_Native_Chicken(34):0.412
Afghan_Native_Chicken(11):0.545
Iran_Native_Chicken(179):0.344
Iran_Commercial_Broiler(3):0.167
White_Leghorn_Chicken(12):0.708
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.500
这个数据展示了KK34基因位点(3:17430210 A/T,rs15709215)的突变频率在不同鸡种中的分布情况。KK34基因的错义突变(moderate impact)可能会导致蛋白质功能的改变,从而影响鸡种的某些生理特性,例如代谢、免疫反应或其他生物功能。通过分析该突变位点在不同鸡种中的分布情况,可以探讨其在能量代谢、环境适应性及育种选择中的潜在影响。
1. 原鸡
- Gallus gallus bankiva(红原鸡):0.500
- Gallus gallus gallus(普通原鸡):0.000
- Gallus gallus jabouillei(越南原鸡):0.056
- Gallus gallus murghi(印度原鸡):0.019
- Gallus gallus spadiceus(马来原鸡):0.122
分析:
- 红原鸡(0.500)突变频率较高,表明该鸡种中一半的个体携带此突变。这可能意味着在红原鸡种群中,KK34基因的突变对其代谢、免疫或环境适应性有一定影响,可能帮助它们适应特定的生态环境。
- 普通原鸡(0.000)、越南原鸡(0.056)和印度原鸡(0.019)的突变频率较低,说明这些鸡种保持了较多的原始基因型,在此位点上没有明显的变异,这可能与它们的野生状态或少量的人工干预育种有关。
- 马来原鸡(0.122)突变频率相对较高,表明部分个体可能通过该突变提升代谢功能或适应当地环境。
2. 蛋鸡
- White Leghorn Chicken(白色莱格恩鸡):0.708
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.300
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.250
分析:
- 白色莱格恩鸡(0.708)作为典型的高产蛋鸡种,突变频率非常高,说明KK34基因的突变可能在该鸡种的育种过程中被保留,可能与提升饲料转化率或提高产蛋性能相关。
- 东乡蓝蛋鸡(0.300)和阿劳卡纳蓝蛋鸡(0.250)的突变频率较低但不为零,这可能表明KK34基因对其代谢或免疫功能产生了中等影响,但在生产性能的选择过程中并非绝对关键。
3. 肉鸡
- Cornish Chicken(康沃尔鸡):0.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):0.500
- Rhode Island Red Chicken(罗得岛红鸡):0.000
- Iran Commercial Broiler(伊朗商用肉鸡):0.167
分析:
- 康沃尔鸡和罗得岛红鸡(0.000)没有发生此突变,表明在这些肉鸡品种中,KK34基因的突变并未被选择或没有对其生长性能产生重要影响。
- 白色普利茅斯岩鸡(0.500)突变频率较高,说明在部分肉鸡品种中,KK34基因突变可能通过提高饲料利用率或促进生长产生了积极作用。
- 伊朗商用肉鸡(0.167)突变频率较低,表明该突变可能并非关键,但可能有一定影响。
4. 肉蛋兼用鸡
- Beijing You Chicken(北京油鸡):0.364
- Dagu Chicken(大谷鸡):0.214
- Shouguang Chicken(寿光鸡):0.071
分析:
- 北京油鸡(0.364)和大谷鸡(0.214)突变频率中等,表明在这些肉蛋兼用鸡中,KK34突变可能对代谢或生产性能产生了影响,帮助它们兼顾产蛋性能和肉质。
- 寿光鸡(0.071)突变频率较低,表明该鸡种可能未显著受此突变影响,可能更多依赖其他基因进行代谢调控。
5. 其他鸡种
- Indonesia Native Chicken(印尼本地鸡):0.153
- Thailand Native Chicken(泰国本地鸡):0.167
- Vietnam Native Chicken(越南本地鸡):0.143
- Tibetan Chicken(西藏鸡):0.078
- Bengal Native Chicken(孟加拉本地鸡):0.214
- India Native Chicken(印度本地鸡):0.341
- Pakistan Native Chicken(巴基斯坦本地鸡):0.412
- Afghan Native Chicken(阿富汗本地鸡):0.545
- Iran Native Chicken(伊朗本地鸡):0.344
分析:
- 阿富汗本地鸡(0.545)、巴基斯坦本地鸡(0.412)和印度本地鸡(0.341)的突变频率较高,表明这些鸡种可能通过KK34基因的突变来应对当地的生态环境压力,例如极端的气候条件或代谢需求。这些鸡种可能通过此突变提高了饲料转化效率和环境适应性。
- 印尼、泰国和越南本地鸡的突变频率较低(0.143-0.167),表明这些鸡种中部分个体携带此突变,但未在整个种群中广泛传播。
- 西藏鸡(0.078)突变频率较低,表明在高海拔地区,KK34基因的突变并未对其代谢或环境适应性产生显著影响,可能更多依赖其他基因调节适应高原环境。
总结与解释
原鸡:
- 红原鸡突变频率高(0.500),说明该鸡种在此突变上可能受到了选择压力,可能与代谢适应性相关。相对而言,其他原鸡(如普通原鸡和越南原鸡)的突变频率较低,表明它们在进化过程中未广泛利用此突变。
蛋鸡:
- 白色莱格恩鸡突变频率高,表明此突变可能对高产蛋鸡的代谢或生产性能具有重要意义。而东乡蓝蛋鸡和阿劳卡纳蓝蛋鸡的突变频率较低,但也可能对其代谢和产蛋性能产生一定的影响。
肉鸡:
- 白色普利茅斯岩鸡突变频率较高(0.500),说明该突变对其快速生长或饲料转化率产生了积极作用。其他肉鸡(如康沃尔鸡和罗得岛红鸡)的突变频率为0,表明在这些鸡种中,代谢调控可能依赖其他基因途径。
肉蛋兼用鸡:
- 北京油鸡、大谷鸡的突变频率中等,表明KK34突变在这些鸡种的代谢调控或生产性能平衡中发挥了一定作用。
其他鸡种:
- 阿富汗、巴基斯坦和印度本地鸡的突变频率较高,表明这些鸡种通过此突变适应了各自的特殊生态环境,可能提高了它们的饲料利用率和免疫适应性。
总结:
KK34基因的突变在不同鸡种中的分布与其育种选择、环境适应性和代谢需求密切相关。蛋鸡和某些肉鸡品种表现出较高的突变频率,说明此突变可能帮助提高了饲料转化率或生产性能。而本地鸡种中的突变频率高低不一,反映出其对不同生态环境的适应性策略。
13 17431898 ACC/A A 0.427 frameshift_variant HIGH KK34 novel 13:16334322
Breed (number): frequence
Gallus_gallus_bankiva(3):0.333
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(27):0.481
Gallus_gallus_murghi(50):0.040
Gallus_gallus_spadiceus(41):0.366
Indonesia_Native_Chicken(36):0.319
Thailand_Native_Chicken(6):0.250
Vietnam_Native_Chicken(7):0.143
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.250
Xishuangbanna_Game_Chicken(10):0.500
Nixi_Chicken(11):0.455
Dulong_Chicken(5):0.600
Daweishan_Mini_Chicken(8):0.312
Guangxi_Chicken(6):0.250
Guangzhou_Chicken(6):0.000
Jiangxi_Silkies(20):0.200
Anyi_Gray_Chicken(4):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.417
Tianfu_Black-bone_Chicken(5):0.600
Shimian_Caoke_Chicken(4):0.375
Jiuyuan_Black-bone_Chicken(5):0.500
Jinyang_Silky_Chicken(6):0.667
Emei_Black_Chicken(6):0.750
Pengxian_Yellow_Chicken(6):0.833
Muchuan_Black-bone_Chicken(5):0.400
Miyi_Chicken(5):0.300
YuanBao_Chicken(24):0.042
Langshan_Chicken(9):0.556
Luxi_Game_Chicken(8):0.562
Shouguang_Chicken(7):1.000
Gushi_Chicken(8):0.625
Bian_Chicken(8):0.750
Beijing_You_Chicken(11):0.818
Dagu_Chicken(7):0.429
Xinjiang_Native_Chicken(6):0.167
Hetian_Black_Chicken(7):0.214
Southern_Xinjiang_Game_Chicken(8):0.500
Turpan_Game_Chicken(8):0.625
Tibetan_Chicken(145):0.324
Araucana_Blue-eggshell_Chicken(6):0.833
Sri_Lanka_Native_Chicken(7):0.286
Bengal_Native_Chicken(12):0.125
India_Native_Chicken(45):0.356
Pakistan_Native_Chicken(37):0.581
Afghan_Native_Chicken(11):0.636
Iran_Native_Chicken(180):0.611
Iran_Commercial_Broiler(3):1.000
White_Leghorn_Chicken(13):0.808
Cornish_Chicken(1):1.000
Rhode_Island_Red_Chicken(1):1.000
White_Plymouth_Rock_Chicken(1):1.000
这个数据展示了KK34基因位点(13:17431898 ACC/A frameshift variant)的突变频率在不同鸡种中的分布情况。该突变为移码突变(frameshift variant),这类突变通常会显著影响基因功能,可能导致蛋白质合成异常,对代谢、免疫反应、生产性能等特性产生重大影响。通过分析该突变在不同鸡种中的分布情况,我们可以推测其对饲料转化率、生长性能及环境适应性的潜在作用。
1. 原鸡
- Gallus gallus bankiva(红原鸡):0.333
- Gallus gallus gallus(普通原鸡):0.000
- Gallus gallus jabouillei(越南原鸡):0.481
- Gallus gallus murghi(印度原鸡):0.040
- Gallus gallus spadiceus(马来原鸡):0.366
分析:
- 红原鸡(0.333) 和 越南原鸡(0.481) 有较高的突变频率,表明这些原鸡种群可能经历了某种选择压力,保留了该移码突变。这可能对其免疫反应或环境适应性起到了帮助。
- 印度原鸡(0.040) 和 普通原鸡(0.000) 突变频率较低甚至为0,说明它们在进化过程中未经历此突变,可能保留了更多的原始基因背景。
- 马来原鸡(0.366) 突变频率适中,表明部分个体可能携带此突变,这可能与其生态适应性相关。
2. 蛋鸡
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.417
- Tianfu Black-bone Chicken(天府乌骨鸡):0.600
- White Leghorn Chicken(白色莱格恩鸡):0.808
分析:
- 白色莱格恩鸡(0.808) 和 天府乌骨鸡(0.600) 的突变频率较高,表明该移码突变可能帮助这些蛋鸡品种提高代谢效率或免疫反应,从而维持其高产蛋性能。
- 东乡蓝蛋鸡(0.417) 的突变频率适中,可能表明该突变对其代谢或生产性能有一定影响,但未成为决定性因素。
3. 肉鸡
- Cornish Chicken(康沃尔鸡):1.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):1.000
- Rhode Island Red Chicken(罗得岛红鸡):1.000
- Iran Commercial Broiler(伊朗商用肉鸡):1.000
分析:
- 康沃尔鸡、白色普利茅斯岩鸡、罗得岛红鸡、伊朗商用肉鸡 的突变频率均为1.000,表明此突变在商业化肉鸡育种过程中得到了广泛选择,可能极大地优化了其饲料转化率、快速生长以及肉质。这类移码突变的固定表明该突变对肉鸡的生产性能产生了重要的影响。
4. 肉蛋兼用鸡
- Beijing You Chicken(北京油鸡):0.818
- Dagu Chicken(大谷鸡):0.429
- Shouguang Chicken(寿光鸡):1.000
分析:
- 北京油鸡(0.818) 和 寿光鸡(1.000) 的突变频率较高,表明此突变可能帮助这些鸡种平衡了产蛋性能与增重能力,优化了其代谢效率,满足了肉蛋兼用鸡种的生产需求。
- 大谷鸡(0.429) 的突变频率中等,表明其部分个体通过此突变改善了生产性能,但突变并未完全固定。
5. 其他鸡种
- Indonesia Native Chicken(印尼本地鸡):0.319
- Thailand Native Chicken(泰国本地鸡):0.250
- Vietnam Native Chicken(越南本地鸡):0.143
- Tibetan Chicken(西藏鸡):0.324
- India Native Chicken(印度本地鸡):0.356
- Pakistan Native Chicken(巴基斯坦本地鸡):0.581
- Afghan Native Chicken(阿富汗本地鸡):0.636
- Iran Native Chicken(伊朗本地鸡):0.611
分析:
- 阿富汗本地鸡(0.636) 和 巴基斯坦本地鸡(0.581) 的突变频率较高,表明这些鸡种可能通过此突变改善了在其环境中的代谢适应性,例如高温或干旱等极端环境压力。
- 印尼、泰国和越南本地鸡 的突变频率较低(0.143-0.319),表明这些鸡种的部分个体携带此突变,但并未广泛传播。
- 西藏鸡(0.324) 作为高原鸡种,突变频率相对较低,说明此突变可能在一定程度上帮助其适应高海拔低氧环境,但并非主要的适应机制。
总结与解释
原鸡:
- 越南原鸡、红原鸡 的突变频率较高,表明这些原鸡种可能经历了此突变,可能在免疫调控或代谢适应方面提供了优势。相对而言,普通原鸡 和 印度原鸡 的突变频率较低,保留了更多的原始基因背景。
蛋鸡:
- 白色莱格恩鸡和天府乌骨鸡 突变频率高,表明此移码突变可能优化了其能量代谢,从而增强其生产性能。
- 东乡蓝蛋鸡 突变频率中等,说明该突变对其生产性能的影响有限。
肉鸡:
- 康沃尔鸡、白色普利茅斯岩鸡 等肉鸡品种突变频率为1.000,表明此突变对提高快速生长和饲料转化率起到了关键作用,并已在这些鸡种中完全固定。
肉蛋兼用鸡:
- 北京油鸡和寿光鸡 的突变频率较高,表明此突变有助于它们兼顾产蛋和增重性能,而大谷鸡的突变频率略低,表明其育种方向对该突变的选择较为适中。
其他鸡种:
- 阿富汗、巴基斯坦本地鸡 突变频率较高,表明此突变帮助它们适应了当地的气候和生态条件。其他鸡种如印度本地鸡、印尼、越南本地鸡 突变频率较低,说明这些鸡种在代谢调控上未广泛依赖此突变。
总的来看,这个KK34基因的移码突变在不同鸡种中的分布显示出其对生产性能、代谢适应性和环境应对能力的潜在影响。肉鸡和肉蛋兼用鸡种普遍表现出较高的突变频率,说明该突变在快速生长和饲料转化效率中发挥了重要作用,而本地鸡种则显示了不同的突变频率,反映出它们在不同生态环境中的适应策略。
10 19719725 G/A A 0.169 missense_variant MODERATE NOX5 rs738511452 10:19307377
Group (number): frequence
Gallus_gallus_bankiva(4):0.500
Gallus_gallus_gallus(3):0.000
Gallus_gallus_jabouillei(27):0.037
Gallus_gallus_murghi(49):0.000
Gallus_gallus_spadiceus(39):0.103
Indonesia_Native_Chicken(35):0.014
Thailand_Native_Chicken(3):0.000
Vietnam_Native_Chicken(7):0.214
Wenchang_Chicken(1):0.500
Yunnan_Chicken(12):0.208
Xishuangbanna_Game_Chicken(10):0.000
Nixi_Chicken(10):0.850
Dulong_Chicken(5):0.100
Daweishan_Mini_Chicken(8):0.000
Guangxi_Chicken(6):0.250
Guangzhou_Chicken(6):0.083
Jiangxi_Silkies(20):0.000
Anyi_Gray_Chicken(4):0.000
Dongxiang_Blue-eggshell_Chicken(4):0.250
Tianfu_Black-bone_Chicken(5):0.200
Shimian_Caoke_Chicken(4):0.000
Jiuyuan_Black-bone_Chicken(5):0.200
Jinyang_Silky_Chicken(6):0.250
Emei_Black_Chicken(6):0.500
Pengxian_Yellow_Chicken(6):0.083
Muchuan_Black-bone_Chicken(5):0.200
Miyi_Chicken(5):1.000
YuanBao_Chicken(23):0.000
Langshan_Chicken(9):0.000
Luxi_Game_Chicken(9):0.000
Shouguang_Chicken(6):0.000
Gushi_Chicken(7):0.000
Bian_Chicken(5):0.200
Beijing_You_Chicken(11):0.045
Dagu_Chicken(7):0.000
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(8):0.000
Southern_Xinjiang_Game_Chicken(8):0.000
Turpan_Game_Chicken(8):0.000
Tibetan_Chicken(140):0.479
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(6):0.167
Bengal_Native_Chicken(9):0.444
India_Native_Chicken(45):0.200
Pakistan_Native_Chicken(32):0.062
Afghan_Native_Chicken(10):0.150
Iran_Native_Chicken(172):0.073
Iran_Commercial_Broiler(2):0.500
White_Leghorn_Chicken(12):0.333
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):1.000
White_Plymouth_Rock_Chicken(1):0.000
这个数据展示了NOX5基因位点(10:19719725 G/A,rs738511452)的突变频率在不同鸡种中的分布情况。NOX5基因属于NADPH氧化酶家族,参与氧化还原反应和免疫功能,因此该突变可能对鸡种的免疫反应、代谢调控以及环境适应性产生影响。
1. 原鸡
- Gallus gallus bankiva(红原鸡):0.500
- Gallus gallus gallus(普通原鸡):0.000
- Gallus gallus jabouillei(越南原鸡):0.037
- Gallus gallus murghi(印度原鸡):0.000
- Gallus gallus spadiceus(马来原鸡):0.103
分析:
- 红原鸡(0.500) 突变频率较高,表明此突变可能有助于其在原始环境中优化免疫反应或代谢调控,增强其适应性。
- 普通原鸡和印度原鸡(0.000) 没有此突变,表明它们的基因组可能保留了更多的原始特征。
- 越南原鸡(0.037) 和 马来原鸡(0.103) 突变频率较低,表明这些鸡种中的部分个体可能经历了环境压力,但整体突变影响较小。
2. 蛋鸡
- White Leghorn Chicken(白色莱格恩鸡):0.333
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.250
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.000
分析:
- 白色莱格恩鸡(0.333) 的突变频率较高,表明该突变可能有助于提高能量代谢效率,从而增强蛋鸡的生产性能。
- 东乡蓝蛋鸡(0.250) 也有较高的突变频率,表明其群体中存在部分携带此突变的个体,可能对其免疫系统或产蛋性能产生影响。
- 阿劳卡纳蓝蛋鸡(0.000) 没有发生此突变,表明其育种方向可能并不依赖该突变。
3. 肉鸡
- Cornish Chicken(康沃尔鸡):0.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):0.000
- Rhode Island Red Chicken(罗得岛红鸡):1.000
- Iran Commercial Broiler(伊朗商用肉鸡):0.500
分析:
- 康沃尔鸡、白色普利茅斯岩鸡(0.000) 没有发生该突变,表明在这些肉鸡品种中,该突变可能没有对它们的生长性能产生重要影响。
- 罗得岛红鸡(1.000) 突变频率极高,说明此突变可能在该肉鸡品种的免疫反应或饲料转化率中起到了积极作用。
- 伊朗商用肉鸡(0.500) 的突变频率适中,表明部分个体通过此突变提高了生产性能。
4. 肉蛋兼用鸡
- Beijing You Chicken(北京油鸡):0.045
- Dagu Chicken(大谷鸡):0.000
- Shouguang Chicken(寿光鸡):0.000
分析:
- 北京油鸡(0.045) 的突变频率非常低,表明此突变对其生产性能或代谢功能的影响有限。
- 大谷鸡和寿光鸡(0.000) 没有此突变,表明此突变未在这些鸡种中发挥重要作用,可能依赖其他基因调节其生产性能。
5. 其他鸡种
- Indonesia Native Chicken(印尼本地鸡):0.014
- Thailand Native Chicken(泰国本地鸡):0.000
- Vietnam Native Chicken(越南本地鸡):0.214
- Tibetan Chicken(西藏鸡):0.479
- Bengal Native Chicken(孟加拉本地鸡):0.444
- India Native Chicken(印度本地鸡):0.200
- Pakistan Native Chicken(巴基斯坦本地鸡):0.062
- Afghan Native Chicken(阿富汗本地鸡):0.150
- Iran Native Chicken(伊朗本地鸡):0.073
分析:
- 西藏鸡(0.479) 突变频率较高,表明该突变可能帮助其在高原环境中提高了免疫适应性或代谢效率,使其能更好地适应高海拔的低氧环境。
- 孟加拉本地鸡(0.444) 和 印度本地鸡(0.200) 也显示出中等突变频率,表明此突变可能帮助它们适应当地的环境压力。
- 越南本地鸡(0.214) 的突变频率较高,可能表明该突变对其免疫反应或代谢调控具有重要影响。
总结与解释
原鸡:
- 红原鸡(0.500) 突变频率较高,表明该突变可能帮助其适应自然环境,尤其是在免疫调控方面。其他原鸡如普通原鸡和印度原鸡没有此突变,可能保留了更多的原始基因。
蛋鸡:
- 白色莱格恩鸡 的突变频率较高,表明此突变可能对其能量代谢和产蛋性能产生了积极影响。而其他蛋鸡如东乡蓝蛋鸡也显示了中等突变频率,但阿劳卡纳蓝蛋鸡未受到该突变的影响。
肉鸡:
- 罗得岛红鸡 的突变频率为1.000,表明此突变可能在其育种中有重要作用,帮助提高其饲料转化率和生长性能。而其他肉鸡品种(如康沃尔鸡和白色普利茅斯岩鸡)没有此突变。
肉蛋兼用鸡:
- 北京油鸡、大谷鸡、寿光鸡 中没有此突变,表明这些鸡种可能更多依赖其他基因来平衡其产蛋和生长性能。
其他鸡种:
- 西藏鸡 和 孟加拉、印度本地鸡 等鸡种的突变频率较高,说明这些鸡种可能通过此突变提高了代谢效率或增强了环境适应能力。
总的来看,NOX5基因的突变在不同鸡种中的分布与它们的代谢需求、免疫适应性和育种目标密切相关。在某些高产蛋鸡和肉鸡品种中,突变可能优化了生产性能,而在本地鸡种中,突变可能帮助它们应对特定环境压力。
14 4797070 A/G G 0.494 missense_variant MODERATE ATP5J2 rs317614849 14:4404435
Group (number): frequence
Gallus_gallus_bankiva(2):0.000
Gallus_gallus_gallus(6):0.250
Gallus_gallus_jabouillei(27):0.815
Gallus_gallus_murghi(38):0.855
Gallus_gallus_spadiceus(40):0.362
Indonesia_Native_Chicken(36):0.444
Thailand_Native_Chicken(6):0.167
Vietnam_Native_Chicken(7):0.357
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.208
Xishuangbanna_Game_Chicken(10):0.300
Nixi_Chicken(10):0.450
Dulong_Chicken(6):0.167
Daweishan_Mini_Chicken(8):0.062
Guangxi_Chicken(6):0.417
Guangzhou_Chicken(6):0.333
Jiangxi_Silkies(20):0.625
Anyi_Gray_Chicken(5):0.100
Dongxiang_Blue-eggshell_Chicken(5):0.100
Tianfu_Black-bone_Chicken(5):0.300
Shimian_Caoke_Chicken(4):0.375
Jiuyuan_Black-bone_Chicken(5):0.100
Jinyang_Silky_Chicken(6):0.167
Emei_Black_Chicken(6):0.417
Pengxian_Yellow_Chicken(6):0.667
Muchuan_Black-bone_Chicken(5):0.300
Miyi_Chicken(5):0.100
YuanBao_Chicken(24):0.042
Langshan_Chicken(8):0.250
Luxi_Game_Chicken(9):0.722
Shouguang_Chicken(7):0.286
Gushi_Chicken(8):0.125
Bian_Chicken(7):0.714
Beijing_You_Chicken(10):0.400
Dagu_Chicken(7):0.071
Xinjiang_Native_Chicken(6):0.917
Hetian_Black_Chicken(8):0.375
Southern_Xinjiang_Game_Chicken(8):0.750
Turpan_Game_Chicken(8):0.375
Tibetan_Chicken(141):0.418
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(5):1.000
Bengal_Native_Chicken(14):0.500
India_Native_Chicken(43):0.581
Pakistan_Native_Chicken(32):0.594
Afghan_Native_Chicken(10):0.850
Iran_Native_Chicken(174):0.618
Iran_Commercial_Broiler(4):0.625
White_Leghorn_Chicken(13):0.885
Cornish_Chicken(1):0.500
Rhode_Island_Red_Chicken(1):0.500
White_Plymouth_Rock_Chicken(1):0.000
该数据展示了ATP5J2基因位点(14:4797070 A/G,rs317614849)的突变频率在不同鸡种中的分布情况。ATP5J2基因编码一个ATP合成酶的亚基,参与线粒体功能和能量代谢。因此,该突变可能会对鸡种的代谢效率、能量生产以及生长性能产生影响。
- 原鸡
Gallus gallus bankiva(红原鸡):0.000
Gallus gallus gallus(普通原鸡):0.250
Gallus gallus jabouillei(越南原鸡):0.815
Gallus gallus murghi(印度原鸡):0.855
Gallus gallus spadiceus(马来原鸡):0.362
分析:
越南原鸡(0.815) 和 印度原鸡(0.855) 突变频率非常高,表明这些原鸡种可能经历了显著的选择压力,保留了此突变。这个突变可能通过改善代谢效率或能量生产帮助这些鸡种更好地适应环境压力。
红原鸡(0.000) 和 马来原鸡(0.362) 突变频率较低,说明它们在此位点上仍保留了更多的原始基因型,可能未经历显著的代谢选择。
普通原鸡(0.250) 的突变频率也相对较低,表明其未受到较大的人为选择。 - 蛋鸡
White Leghorn Chicken(白色莱格恩鸡):0.885
Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.100
Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.000
分析:
白色莱格恩鸡(0.885) 突变频率非常高,表明此突变可能对该鸡种的能量代谢至关重要,可能通过优化能量生产以增强其高产蛋性能。
东乡蓝蛋鸡(0.100) 的突变频率较低,表明该鸡种可能在育种中未广泛利用此突变,可能更多依赖其他基因来优化其生产性能。
阿劳卡纳蓝蛋鸡(0.000) 没有此突变,表明该鸡种未经历此突变带来的选择压力。 - 肉鸡
Cornish Chicken(康沃尔鸡):0.500
White Plymouth Rock Chicken(白色普利茅斯岩鸡):0.000
Rhode Island Red Chicken(罗得岛红鸡):0.500
Iran Commercial Broiler(伊朗商用肉鸡):0.625
分析:
康沃尔鸡(0.500) 和 罗得岛红鸡(0.500) 的突变频率较高,表明此突变在这些肉鸡品种中被部分固定,可能通过改善能量代谢帮助它们在育肥过程中提高饲料转化率。
白色普利茅斯岩鸡(0.000) 没有发生此突变,说明其代谢调控可能依赖其他基因途径。
伊朗商用肉鸡(0.625) 的突变频率较高,可能表明该突变在快速生长和饲料利用效率中的重要作用。 - 肉蛋兼用鸡
Beijing You Chicken(北京油鸡):0.400
Dagu Chicken(大谷鸡):0.071
Shouguang Chicken(寿光鸡):0.286
分析:
北京油鸡(0.400) 的突变频率较高,表明该鸡种可能通过此突变优化其能量代谢,以兼顾产蛋和增重性能。
大谷鸡(0.071) 的突变频率较低,说明其育种中未广泛选择此突变,可能更多依赖其他途径来平衡其生产性能。
寿光鸡(0.286) 的突变频率适中,表明该突变对部分个体有潜在影响,但未在群体中被完全固定。 - 其他鸡种
Indonesia Native Chicken(印尼本地鸡):0.444
Thailand Native Chicken(泰国本地鸡):0.167
Vietnam Native Chicken(越南本地鸡):0.357
Tibetan Chicken(西藏鸡):0.418
Bengal Native Chicken(孟加拉本地鸡):0.500
India Native Chicken(印度本地鸡):0.581
Pakistan Native Chicken(巴基斯坦本地鸡):0.594
Afghan Native Chicken(阿富汗本地鸡):0.850
Iran Native Chicken(伊朗本地鸡):0.618
分析:
阿富汗本地鸡(0.850)、巴基斯坦本地鸡(0.594) 和 印度本地鸡(0.581) 突变频率较高,表明这些鸡种可能通过此突变提高了其代谢效率,以应对各自的生态环境和生产需求。
西藏鸡(0.418) 的突变频率也较高,可能表明该突变在高海拔环境中的适应性作用,帮助这些鸡种在低氧环境下优化能量生产。
印尼、泰国和越南本地鸡 的突变频率较低至中等,表明这些鸡种可能未广泛依赖此突变来调节代谢功能。
总结与解释
原鸡:
越南原鸡和印度原鸡 突变频率非常高,表明这些鸡种可能通过此突变在其自然栖息地中获得了显著的代谢优势。相反,红原鸡 和 马来原鸡 突变频率较低,表明其基因组在此突变位点上保持了更多的原始特征。
蛋鸡:
白色莱格恩鸡 突变频率很高,表明此突变在蛋鸡的能量代谢和生产性能中发挥了重要作用,而其他蛋鸡如东乡蓝蛋鸡和阿劳卡纳蓝蛋鸡并未广泛依赖此突变。
肉鸡:
康沃尔鸡、罗得岛红鸡 等肉鸡品种的突变频率较高,表明此突变可能帮助这些鸡种通过优化能量代谢,提升了饲料转化率和快速生长能力。
肉蛋兼用鸡:
北京油鸡和寿光鸡 中的突变频率较高,表明该突变有助于它们平衡产蛋性能和肉质,而大谷鸡 的突变频率较低,可能依赖其他基因调控其生产性能。
其他鸡种:
阿富汗、印度和巴基斯坦本地鸡 的突变频率较高,表明该突变可能帮助这些鸡种在复杂的环境下提高了代谢效率或免疫适应性。
总的来看,ATP5J2基因的突变在不同鸡种中的分布与其能量代谢、饲料转化率和环境适应性密切相关。该突变在某些蛋鸡和肉鸡品种中被广泛固定,表明其对提高生产性能具有重要作用,而本地鸡种则显示了不同的突变频率,反映出其对不同生态环境的适应策略。
5 1184373 C/A A 0.224 missense_variant MODERATE CYP1C1 rs14509563 5:1143629
Group (number): frequence
Gallus_gallus_bankiva(3):0.000
Gallus_gallus_gallus(5):0.300
Gallus_gallus_jabouillei(26):0.192
Gallus_gallus_murghi(48):0.021
Gallus_gallus_spadiceus(41):0.146
Indonesia_Native_Chicken(35):0.157
Thailand_Native_Chicken(5):0.100
Vietnam_Native_Chicken(7):0.000
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.083
Xishuangbanna_Game_Chicken(10):0.100
Nixi_Chicken(10):0.700
Dulong_Chicken(7):0.500
Daweishan_Mini_Chicken(8):0.250
Guangxi_Chicken(6):0.250
Guangzhou_Chicken(6):0.417
Jiangxi_Silkies(20):0.375
Anyi_Gray_Chicken(3):0.000
Dongxiang_Blue-eggshell_Chicken(5):0.000
Tianfu_Black-bone_Chicken(5):0.400
Shimian_Caoke_Chicken(4):0.250
Jiuyuan_Black-bone_Chicken(5):0.400
Jinyang_Silky_Chicken(6):0.250
Emei_Black_Chicken(6):0.500
Pengxian_Yellow_Chicken(6):0.250
Muchuan_Black-bone_Chicken(5):0.200
Miyi_Chicken(5):0.200
YuanBao_Chicken(24):0.104
Langshan_Chicken(7):0.214
Luxi_Game_Chicken(9):0.111
Shouguang_Chicken(5):0.900
Gushi_Chicken(5):0.200
Bian_Chicken(5):0.000
Beijing_You_Chicken(11):0.500
Dagu_Chicken(8):0.000
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(7):0.071
Southern_Xinjiang_Game_Chicken(8):0.125
Turpan_Game_Chicken(7):0.071
Tibetan_Chicken(143):0.329
Araucana_Blue-eggshell_Chicken(6):0.500
Sri_Lanka_Native_Chicken(5):0.000
Bengal_Native_Chicken(12):0.125
India_Native_Chicken(50):0.170
Pakistan_Native_Chicken(35):0.157
Afghan_Native_Chicken(9):0.000
Iran_Native_Chicken(160):0.278
Iran_Commercial_Broiler(3):0.333
White_Leghorn_Chicken(12):0.125
Cornish_Chicken(1):0.500
Rhode_Island_Red_Chicken(1):0.500
White_Plymouth_Rock_Chicken(1):0.000
该数据展示了CYP1C1基因位点(5:1184373 C/A,rs14509563)的突变频率在不同鸡种中的分布情况。CYP1C1基因属于细胞色素P450家族,参与代谢物质的解毒和代谢过程,特别是与药物代谢、激素调控等过程相关。因此,该突变可能影响鸡种的代谢效率、解毒能力和环境适应性。
1. 原鸡
- Gallus gallus bankiva(红原鸡):0.000
- Gallus gallus gallus(普通原鸡):0.300
- Gallus gallus jabouillei(越南原鸡):0.192
- Gallus gallus murghi(印度原鸡):0.021
- Gallus gallus spadiceus(马来原鸡):0.146
分析:
- 普通原鸡(0.300) 的突变频率较高,表明该鸡种中部分个体可能通过此突变获得了某种代谢优势,可能有助于应对环境中的化学压力。
- 红原鸡(0.000) 和 印度原鸡(0.021) 突变频率极低,表明它们未经历此突变带来的选择压力,保留了更多的原始基因特征。
- 越南原鸡(0.192) 和 马来原鸡(0.146) 的突变频率适中,表明部分个体可能通过该突变增强了对某些代谢过程的调控。
2. 蛋鸡
- White Leghorn Chicken(白色莱格恩鸡):0.125
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.000
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.500
分析:
- 阿劳卡纳蓝蛋鸡(0.500) 的突变频率非常高,表明此突变在该鸡种中可能通过影响代谢或激素调控帮助提升其生产性能或环境适应性。
- 白色莱格恩鸡(0.125) 突变频率较低,表明该突变在蛋鸡品种中的选择压力不大,或许在代谢调控中的作用较为有限。
- 东乡蓝蛋鸡(0.000) 无此突变,表明其在育种过程中未依赖该突变优化其生产性能。
3. 肉鸡
- Cornish Chicken(康沃尔鸡):0.500
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):0.000
- Rhode Island Red Chicken(罗得岛红鸡):0.500
- Iran Commercial Broiler(伊朗商用肉鸡):0.333
分析:
- 康沃尔鸡和罗得岛红鸡(0.500) 的突变频率较高,表明该突变在这些肉鸡品种中可能通过优化代谢和解毒能力,帮助提高生长速度和饲料利用效率。
- 伊朗商用肉鸡(0.333) 也显示了较高的突变频率,表明该突变可能有助于提高其生产性能。
- 白色普利茅斯岩鸡(0.000) 没有此突变,表明其生产性能可能依赖其他基因调控机制。
4. 肉蛋兼用鸡
- Beijing You Chicken(北京油鸡):0.500
- Dagu Chicken(大谷鸡):0.000
- Shouguang Chicken(寿光鸡):0.900
分析:
- 北京油鸡(0.500) 和 寿光鸡(0.900) 的突变频率较高,表明此突变在这些兼用鸡品种中可能通过增强代谢调控,平衡了它们的产蛋和肉质性能。
- 大谷鸡(0.000) 没有此突变,表明该鸡种可能依赖其他基因途径来优化其生产性能。
5. 其他鸡种
- Indonesia Native Chicken(印尼本地鸡):0.157
- Thailand Native Chicken(泰国本地鸡):0.100
- Vietnam Native Chicken(越南本地鸡):0.000
- Tibetan Chicken(西藏鸡):0.329
- Bengal Native Chicken(孟加拉本地鸡):0.125
- India Native Chicken(印度本地鸡):0.170
- Pakistan Native Chicken(巴基斯坦本地鸡):0.157
- Afghan Native Chicken(阿富汗本地鸡):0.000
- Iran Native Chicken(伊朗本地鸡):0.278
分析:
- 西藏鸡(0.329) 和 伊朗本地鸡(0.278) 的突变频率较高,表明该突变可能帮助这些鸡种在高海拔或干旱环境中优化代谢效率,增强其环境适应性。
- 印度和巴基斯坦本地鸡(0.170-0.157) 的突变频率较低,但部分个体携带此突变,表明该突变可能在这些鸡种中影响了特定的代谢过程。
总结与解释
原鸡:
- 普通原鸡(0.300) 突变频率较高,表明其在进化过程中可能经历了环境或代谢压力的选择,而红原鸡和印度原鸡等突变频率极低,显示这些鸡种保留了较多的原始特征。
蛋鸡:
- 阿劳卡纳蓝蛋鸡 突变频率很高,表明该突变可能在代谢调控中发挥了重要作用,优化了蛋鸡的生产性能。其他蛋鸡如白色莱格恩鸡 突变频率较低,表明其代谢调控机制可能不依赖该突变。
肉鸡:
- 康沃尔鸡和罗得岛红鸡 的突变频率较高,表明该突变可能通过增强代谢和解毒能力,帮助提高这些鸡种的生产性能。
肉蛋兼用鸡:
- 北京油鸡和寿光鸡 的突变频率较高,表明此突变可能有助于它们兼顾产蛋和生长性能,而大谷鸡 未发生此突变,显示其生产性能可能依赖其他基因。
其他鸡种:
- 西藏鸡和伊朗本地鸡 的突变频率较高,表明该突变可能帮助它们应对极端环境的代谢需求,而其他本地鸡种中突变频率较低至中等,反映出其代谢调控和环境适应的不同策略。
总的来看,CYP1C1基因的突变在不同鸡种中的分布与其代谢需求、解毒能力和环境适应性密切相关。
8 23128078 T/C C 0.039 missense_variant MODERATE AGBL4 rs732803421 8:22463622
Group (number): frequence
Gallus_gallus_bankiva(4):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(27):0.000
Gallus_gallus_murghi(57):0.000
Gallus_gallus_spadiceus(44):0.057
Indonesia_Native_Chicken(36):0.042
Thailand_Native_Chicken(6):0.083
Vietnam_Native_Chicken(7):0.000
Wenchang_Chicken(1):0.000
Yunnan_Chicken(11):0.045
Xishuangbanna_Game_Chicken(10):0.000
Nixi_Chicken(12):0.000
Dulong_Chicken(7):0.000
Daweishan_Mini_Chicken(6):0.000
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(5):0.000
Jiangxi_Silkies(20):0.025
Anyi_Gray_Chicken(5):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.000
Shimian_Caoke_Chicken(4):0.125
Jiuyuan_Black-bone_Chicken(5):0.000
Jinyang_Silky_Chicken(6):0.083
Emei_Black_Chicken(6):0.000
Pengxian_Yellow_Chicken(6):0.000
Muchuan_Black-bone_Chicken(5):0.000
Miyi_Chicken(5):0.000
YuanBao_Chicken(24):0.000
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(9):0.000
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.000
Beijing_You_Chicken(11):0.000
Dagu_Chicken(8):0.000
Xinjiang_Native_Chicken(6):0.167
Hetian_Black_Chicken(8):0.000
Southern_Xinjiang_Game_Chicken(8):0.062
Turpan_Game_Chicken(8):0.000
Tibetan_Chicken(142):0.035
Araucana_Blue-eggshell_Chicken(6):0.667
Sri_Lanka_Native_Chicken(7):0.000
Bengal_Native_Chicken(13):0.000
India_Native_Chicken(50):0.050
Pakistan_Native_Chicken(36):0.042
Afghan_Native_Chicken(11):0.000
Iran_Native_Chicken(180):0.078
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(13):0.000
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
这个数据展示了AGBL4基因位点(8:23128078 T/C,rs732803421)的突变频率在不同鸡种中的分布情况。AGBL4基因参与了微管去酰化和神经功能调控,这表明该突变可能对鸡种的神经系统发育、运动协调性以及生长性能产生潜在影响。
1. 原鸡
- Gallus gallus bankiva(红原鸡):0.000
- Gallus gallus gallus(普通原鸡):0.000
- Gallus gallus jabouillei(越南原鸡):0.000
- Gallus gallus murghi(印度原鸡):0.000
- Gallus gallus spadiceus(马来原鸡):0.057
分析:
- 红原鸡、普通原鸡、越南原鸡和印度原鸡 均无此突变,表明它们的基因组在此位点上保留了更多的原始特征。
- 马来原鸡(0.057) 突变频率较低,但显示出部分个体携带该突变,表明可能有一些环境因素或选择压力对其产生了作用。
2. 蛋鸡
- White Leghorn Chicken(白色莱格恩鸡):0.000
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.000
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.667
分析:
- 阿劳卡纳蓝蛋鸡(0.667) 突变频率非常高,表明该突变可能对该鸡种的神经发育和生产性能有积极影响,可能帮助其在环境适应性和生产性能中获得优势。
- 白色莱格恩鸡和东乡蓝蛋鸡 均无此突变,表明它们的生产性能与该突变的关联性较低。
3. 肉鸡
- Cornish Chicken(康沃尔鸡):0.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):0.000
- Rhode Island Red Chicken(罗得岛红鸡):0.000
- Iran Commercial Broiler(伊朗商用肉鸡):0.000
分析:
- 康沃尔鸡、白色普利茅斯岩鸡、罗得岛红鸡和伊朗商用肉鸡 均无此突变,表明该突变可能不直接影响肉鸡的生产性能,这些鸡种可能通过其他基因途径优化其生长和肉质。
4. 肉蛋兼用鸡
- Beijing You Chicken(北京油鸡):0.000
- Dagu Chicken(大谷鸡):0.000
- Shouguang Chicken(寿光鸡):0.000
分析:
- 北京油鸡、大谷鸡和寿光鸡 均无此突变,表明该突变在这些鸡种的基因库中不常见,可能不对其生产性能或适应性产生显著影响。
5. 其他鸡种
- Indonesia Native Chicken(印尼本地鸡):0.042
- Thailand Native Chicken(泰国本地鸡):0.083
- Vietnam Native Chicken(越南本地鸡):0.000
- Tibetan Chicken(西藏鸡):0.035
- Bengal Native Chicken(孟加拉本地鸡):0.000
- India Native Chicken(印度本地鸡):0.050
- Pakistan Native Chicken(巴基斯坦本地鸡):0.042
- Afghan Native Chicken(阿富汗本地鸡):0.000
- Iran Native Chicken(伊朗本地鸡):0.078
分析:
- 泰国本地鸡(0.083) 和 印尼本地鸡(0.042) 的突变频率较低,但显示出该突变可能在部分个体中影响其神经发育或环境适应性。
- 西藏鸡(0.035) 突变频率较低,但可能反映出高海拔环境中的代谢或神经适应需求。
- 印度、巴基斯坦和伊朗本地鸡 也有较低的突变频率,表明此突变对这些鸡种的代谢和神经功能具有一定影响。
总结与解释
原鸡:
- 红原鸡、普通原鸡、越南原鸡、印度原鸡 无此突变,表明这些原鸡在进化过程中保留了更多的原始基因,而马来原鸡(0.057) 显示出少量突变,可能是由于环境压力导致的选择。
蛋鸡:
- 阿劳卡纳蓝蛋鸡(0.667) 突变频率极高,表明该突变可能在其代谢和神经调控中起重要作用,帮助其适应生产环境,而其他蛋鸡品种并未依赖此突变。
肉鸡:
- 康沃尔鸡、白色普利茅斯岩鸡、罗得岛红鸡和伊朗商用肉鸡 无此突变,表明这些鸡种的生产性能与该突变无关,可能依赖其他基因来优化其生长性能。
肉蛋兼用鸡:
- 北京油鸡、大谷鸡和寿光鸡 没有此突变,显示该突变并未在这些鸡种中被选择用于优化其产蛋和肉质。
其他鸡种:
- 泰国、印尼本地鸡和西藏鸡 等鸡种的突变频率较低,表明该突变在某些本地鸡种中可能通过影响神经发育和代谢帮助它们适应各自的环境。
总的来看,AGBL4基因的突变在不同鸡种中的分布与其神经发育、代谢调控和环境适应性相关。在某些蛋鸡和本地鸡种中,该突变可能有助于生产性能或环境适应性的提升,而其他鸡种则依赖其他遗传途径。
16 2447383 G/A A 0.014 stop_gained HIGH BLEC3 novel -
Group (number): frequence
Gallus_gallus_bankiva(3):0.000
Gallus_gallus_gallus(5):0.000
Gallus_gallus_jabouillei(26):0.000
Gallus_gallus_murghi(35):0.000
Gallus_gallus_spadiceus(43):0.000
Indonesia_Native_Chicken(36):0.000
Thailand_Native_Chicken(6):0.000
Vietnam_Native_Chicken(7):0.000
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.000
Xishuangbanna_Game_Chicken(10):0.000
Nixi_Chicken(10):0.000
Dulong_Chicken(5):0.000
Daweishan_Mini_Chicken(7):0.000
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(6):0.000
Jiangxi_Silkies(19):0.000
Anyi_Gray_Chicken(4):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.000
Shimian_Caoke_Chicken(4):0.000
Jiuyuan_Black-bone_Chicken(5):0.000
Jinyang_Silky_Chicken(6):0.000
Emei_Black_Chicken(6):0.083
Pengxian_Yellow_Chicken(6):0.000
Muchuan_Black-bone_Chicken(5):0.100
Miyi_Chicken(5):0.000
YuanBao_Chicken(24):0.000
Langshan_Chicken(8):0.000
Luxi_Game_Chicken(8):0.000
Shouguang_Chicken(7):0.000
Gushi_Chicken(6):0.000
Bian_Chicken(6):0.000
Beijing_You_Chicken(8):0.000
Dagu_Chicken(6):0.000
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(8):0.000
Southern_Xinjiang_Game_Chicken(7):0.000
Turpan_Game_Chicken(8):0.000
Tibetan_Chicken(142):0.004
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(7):0.000
Bengal_Native_Chicken(14):0.036
India_Native_Chicken(44):0.000
Pakistan_Native_Chicken(36):0.028
Afghan_Native_Chicken(8):0.000
Iran_Native_Chicken(175):0.046
Iran_Commercial_Broiler(2):0.000
White_Leghorn_Chicken(9):0.000
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(0):NaN
White_Plymouth_Rock_Chicken(1):0.000
该数据展示了BLEC3基因位点(16:2447383 G/A)的突变频率在不同鸡种中的分布情况。该突变是一个stop-gained突变(终止密码子获得突变),属于高影响力(HIGH)突变类别,可能会导致蛋白质的过早终止,从而产生功能丧失或不完整的蛋白质。这类突变通常对基因功能有显著的负面影响,可能会影响某些鸡种的生理特性。
1. 原鸡
- Gallus gallus bankiva(红原鸡):0.000
- Gallus gallus gallus(普通原鸡):0.000
- Gallus gallus jabouillei(越南原鸡):0.000
- Gallus gallus murghi(印度原鸡):0.000
- Gallus gallus spadiceus(马来原鸡):0.000
分析:
- 所有原鸡品种均未显示出此突变(0.000),这表明该突变在原鸡中非常罕见或不存在。由于stop-gained突变可能会对基因功能产生较大的影响,原鸡保留了较为原始的基因型,未受到显著的选择压力。
2. 蛋鸡
- White Leghorn Chicken(白色莱格恩鸡):0.000
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.000
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.000
分析:
- 蛋鸡品种,如白色莱格恩鸡、东乡蓝蛋鸡和阿劳卡纳蓝蛋鸡,均未显示出此突变。蛋鸡的生产性能可能对代谢稳定性要求较高,stop-gained突变对其基因功能的负面影响较大,因此在蛋鸡中未被保留。
3. 肉鸡
- Cornish Chicken(康沃尔鸡):0.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):0.000
- Rhode Island Red Chicken(罗得岛红鸡):无数据(NaN)
- Iran Commercial Broiler(伊朗商用肉鸡):0.000
分析:
- 肉鸡品种,如康沃尔鸡、白色普利茅斯岩鸡和伊朗商用肉鸡,均未显示出此突变。肉鸡通常被选择为快速生长和高饲料转化率的品种,基因功能的缺失性突变可能会影响其生长性能,因此这些品种中未出现此突变。
4. 肉蛋兼用鸡
- Beijing You Chicken(北京油鸡):0.000
- Dagu Chicken(大谷鸡):0.000
- Shouguang Chicken(寿光鸡):0.000
分析:
- 北京油鸡、大谷鸡和寿光鸡等肉蛋兼用鸡种均未显示出此突变,表明该突变可能会对这些品种的生产性能和代谢稳定性产生负面影响,因此未在这些鸡种中被保留。
5. 其他鸡种
- Tibetan Chicken(西藏鸡):0.004
- Bengal Native Chicken(孟加拉本地鸡):0.036
- Pakistan Native Chicken(巴基斯坦本地鸡):0.028
- Iran Native Chicken(伊朗本地鸡):0.046
- Sri Lanka Native Chicken(斯里兰卡本地鸡):0.000
- India Native Chicken(印度本地鸡):0.000
- Afghan Native Chicken(阿富汗本地鸡):0.000
分析:
- 在一些本地鸡种中,如西藏鸡(0.004)、孟加拉本地鸡(0.036)、巴基斯坦本地鸡(0.028)和伊朗本地鸡(0.046),该突变出现的频率较低。这表明这些品种中有少量个体携带此突变,可能与其环境适应性或其他特定功能相关。
- 印度本地鸡、斯里兰卡本地鸡、阿富汗本地鸡 等鸡种未显示出此突变,表明在这些鸡种中未受到此突变的选择压力。
总结与解释
原鸡:
- 所有原鸡品种均未显示出此突变,表明这些品种保持了更多的原始基因特征,stop-gained突变可能对其基因功能产生较大影响,因此未在其基因库中广泛存在。
蛋鸡:
- 所有蛋鸡品种均未显示出此突变,表明该突变在高产蛋鸡种中未被选择,可能会对其代谢稳定性和生产性能产生负面影响。
肉鸡:
- 肉鸡品种中也没有此突变,这表明在肉鸡品种中,选择压力可能更偏向于保持完整的基因功能,以优化快速生长和饲料利用效率。
肉蛋兼用鸡:
- 肉蛋兼用鸡种中也没有此突变,显示出该突变对其产蛋和增重平衡产生不利影响,因此未被保留。
其他鸡种:
- 在一些本地鸡种中,特别是高海拔或复杂环境中的鸡种,如西藏鸡、孟加拉本地鸡、巴基斯坦本地鸡和伊朗本地鸡,出现了该突变,虽然频率较低,但可能有助于这些鸡种适应特定的环境压力或代谢需求。
结论:
该stop-gained突变可能对基因功能产生负面影响,因此在大多数鸡种中未广泛存在。然而,少数本地鸡种显示出该突变,可能表明它们对环境压力的特殊适应性。在高产鸡种中,该突变可能不利于生产性能,因此未被选择保留。
16 2447399 AGT/A A 0.027 frameshift_variant HIGH BLEC3 novel -
Breed (number): frequence
Gallus_gallus_bankiva(3):0.000
Gallus_gallus_gallus(5):0.000
Gallus_gallus_jabouillei(26):0.000
Gallus_gallus_murghi(35):0.000
Gallus_gallus_spadiceus(42):0.012
Indonesia_Native_Chicken(36):0.014
Thailand_Native_Chicken(6):0.083
Vietnam_Native_Chicken(7):0.000
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.000
Xishuangbanna_Game_Chicken(10):0.000
Nixi_Chicken(10):0.000
Dulong_Chicken(5):0.100
Daweishan_Mini_Chicken(7):0.000
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(6):0.000
Jiangxi_Silkies(18):0.000
Anyi_Gray_Chicken(4):0.000
Dongxiang_Blue-eggshell_Chicken(5):0.200
Tianfu_Black-bone_Chicken(5):0.200
Shimian_Caoke_Chicken(4):0.000
Jiuyuan_Black-bone_Chicken(5):0.000
Jinyang_Silky_Chicken(6):0.000
Emei_Black_Chicken(6):0.083
Pengxian_Yellow_Chicken(6):0.083
Muchuan_Black-bone_Chicken(5):0.000
Miyi_Chicken(5):0.000
YuanBao_Chicken(24):0.000
Langshan_Chicken(8):0.062
Luxi_Game_Chicken(8):0.000
Shouguang_Chicken(6):0.000
Gushi_Chicken(5):0.000
Bian_Chicken(6):0.000
Beijing_You_Chicken(8):0.000
Dagu_Chicken(6):0.000
Xinjiang_Native_Chicken(6):0.167
Hetian_Black_Chicken(8):0.000
Southern_Xinjiang_Game_Chicken(7):0.000
Turpan_Game_Chicken(8):0.000
Tibetan_Chicken(142):0.070
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(7):0.000
Bengal_Native_Chicken(13):0.115
India_Native_Chicken(41):0.037
Pakistan_Native_Chicken(37):0.000
Afghan_Native_Chicken(11):0.091
Iran_Native_Chicken(178):0.008
Iran_Commercial_Broiler(3):0.000
White_Leghorn_Chicken(11):0.000
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
25 2870763 G/T T 0.081 missense_variant MODERATE TPM3 rs315055638 25:1879337
Group (number): frequence
Gallus_gallus_bankiva(3):0.000
Gallus_gallus_gallus(6):0.333
Gallus_gallus_jabouillei(26):0.019
Gallus_gallus_murghi(47):0.021
Gallus_gallus_spadiceus(41):0.098
Indonesia_Native_Chicken(35):0.071
Thailand_Native_Chicken(6):0.417
Vietnam_Native_Chicken(7):0.071
Wenchang_Chicken(1):0.500
Yunnan_Chicken(12):0.083
Xishuangbanna_Game_Chicken(10):0.050
Nixi_Chicken(9):0.056
Dulong_Chicken(7):0.214
Daweishan_Mini_Chicken(8):0.125
Guangxi_Chicken(6):0.250
Guangzhou_Chicken(6):0.250
Jiangxi_Silkies(20):0.000
Anyi_Gray_Chicken(4):0.000
Dongxiang_Blue-eggshell_Chicken(3):0.333
Tianfu_Black-bone_Chicken(5):0.100
Shimian_Caoke_Chicken(4):0.125
Jiuyuan_Black-bone_Chicken(5):0.100
Jinyang_Silky_Chicken(6):0.083
Emei_Black_Chicken(6):0.167
Pengxian_Yellow_Chicken(6):0.000
Muchuan_Black-bone_Chicken(5):0.000
Miyi_Chicken(5):0.200
YuanBao_Chicken(24):0.021
Langshan_Chicken(9):0.000
Luxi_Game_Chicken(9):0.056
Shouguang_Chicken(7):0.143
Gushi_Chicken(7):0.000
Bian_Chicken(6):0.000
Beijing_You_Chicken(11):0.273
Dagu_Chicken(7):0.000
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(8):0.188
Southern_Xinjiang_Game_Chicken(8):0.062
Turpan_Game_Chicken(8):0.125
Tibetan_Chicken(146):0.086
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(6):0.167
Bengal_Native_Chicken(13):0.000
India_Native_Chicken(46):0.065
Pakistan_Native_Chicken(34):0.074
Afghan_Native_Chicken(10):0.000
Iran_Native_Chicken(175):0.054
Iran_Commercial_Broiler(3):0.000
White_Leghorn_Chicken(12):0.542
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):1.000
该数据展示了TPM3基因位点(25:2870763 G/T,rs315055638)的突变频率在不同鸡种中的分布情况。TPM3基因编码原肌球蛋白3,与肌肉收缩、肌丝的稳定性以及细胞骨架的维持密切相关,因此,该突变可能会影响鸡种的运动能力、肌肉结构和生长性能。
1. 原鸡
- Gallus gallus bankiva(红原鸡):0.000
- Gallus gallus gallus(普通原鸡):0.333
- Gallus gallus jabouillei(越南原鸡):0.019
- Gallus gallus murghi(印度原鸡):0.021
- Gallus gallus spadiceus(马来原鸡):0.098
分析:
- 普通原鸡(0.333) 突变频率较高,表明该突变在部分个体中可能通过影响肌肉结构或运动能力,帮助它们在其环境中取得生存优势。
- 红原鸡、越南原鸡和印度原鸡 的突变频率较低,表明这些鸡种未受到此突变的显著选择压力。
- 马来原鸡(0.098) 的突变频率适中,可能表明其部分个体通过该突变获得了某种生理优势。
2. 蛋鸡
- White Leghorn Chicken(白色莱格恩鸡):0.542
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.333
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.000
分析:
- 白色莱格恩鸡(0.542) 的突变频率较高,表明该突变可能在其肌肉发育或运动能力方面发挥了积极作用,可能通过改善这些性能,间接促进其高产蛋性能。
- 东乡蓝蛋鸡(0.333) 也有较高的突变频率,表明其个体中可能存在与肌肉发育相关的选择压力。
- 阿劳卡纳蓝蛋鸡(0.000) 无此突变,表明其生产性能并未受到此突变的显著影响。
3. 肉鸡
- Cornish Chicken(康沃尔鸡):0.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):1.000
- Rhode Island Red Chicken(罗得岛红鸡):0.000
- Iran Commercial Broiler(伊朗商用肉鸡):0.000
分析:
- 白色普利茅斯岩鸡(1.000) 突变频率非常高,表明该突变可能对其肌肉生长和结构具有显著的积极作用,可能帮助优化其肉鸡生产性能。
- 康沃尔鸡、罗得岛红鸡和伊朗商用肉鸡 均无此突变,表明这些肉鸡品种未经历相关的选择压力。
4. 肉蛋兼用鸡
- Beijing You Chicken(北京油鸡):0.273
- Dagu Chicken(大谷鸡):0.000
- Shouguang Chicken(寿光鸡):0.143
分析:
- 北京油鸡(0.273) 突变频率较高,表明该突变可能对该鸡种的肌肉和产蛋性能起到一定的积极作用。
- 寿光鸡(0.143) 的突变频率适中,也表明其生产性能可能受益于此突变。
- 大谷鸡(0.000) 没有此突变,表明其生产性能依赖其他基因调控途径。
5. 其他鸡种
- Tibetan Chicken(西藏鸡):0.086
- Indonesia Native Chicken(印尼本地鸡):0.071
- Thailand Native Chicken(泰国本地鸡):0.417
- Vietnam Native Chicken(越南本地鸡):0.071
- Bengal Native Chicken(孟加拉本地鸡):0.000
- India Native Chicken(印度本地鸡):0.065
- Pakistan Native Chicken(巴基斯坦本地鸡):0.074
- Afghan Native Chicken(阿富汗本地鸡):0.000
- Iran Native Chicken(伊朗本地鸡):0.054
分析:
- 泰国本地鸡(0.417) 突变频率较高,表明该突变可能通过优化其肌肉结构,帮助其适应当地环境或提高其生产性能。
- 西藏鸡、印尼本地鸡、越南本地鸡等的突变频率适中,表明部分个体可能通过此突变增强其运动能力或代谢,有助于适应各自的生态环境。
- 印度、巴基斯坦、伊朗本地鸡 的突变频率较低,但显示出该突变对其基因库中某些个体具有选择作用。
总结与解释
原鸡:
- 普通原鸡(0.333) 的突变频率较高,表明其个体可能通过该突变增强了肌肉发育或运动性能,在进化过程中产生了优势。
- 其他原鸡种的突变频率较低,表明这些鸡种在基因进化过程中未显著依赖此突变。
蛋鸡:
- 白色莱格恩鸡(0.542) 和 东乡蓝蛋鸡(0.333) 的突变频率较高,表明该突变可能对这些鸡种的运动能力和生产性能产生了正面影响。
- 阿劳卡纳蓝蛋鸡 无此突变,显示其生产性能并未受到该突变的选择压力。
肉鸡:
- 白色普利茅斯岩鸡(1.000) 的突变频率非常高,表明该突变对其肌肉结构和生长速度有重要影响。
- 其他肉鸡种没有此突变,表明其生产性能可能依赖于其他基因途径。
肉蛋兼用鸡:
- 北京油鸡(0.273) 和 寿光鸡(0.143) 的突变频率较高,表明该突变可能在其产蛋和肉质平衡中发挥一定作用。
其他鸡种:
- 泰国本地鸡(0.417) 和 西藏鸡 的突变频率较高,表明它们可能通过此突变优化了其肌肉发育或适应当地环境的能力。
- 印度、巴基斯坦和伊朗本地鸡 的突变频率较低,但个别个体携带此突变,可能显示其在某些情况下的选择优势。
结论:
TPM3基因突变可能对鸡种的肌肉结构、运动能力和生长性能产生影响。在高生产性能的鸡种中(如白色普利茅斯岩鸡、白色莱格恩鸡),该突变频率较高,表明它在这些品种中的选择作用明显。而在一些本地鸡种和肉蛋兼用鸡中,突变频率适中,显示出该突变可能有助于它们的环境适应和生产性能优化。
1 166897346 A/G A 0.170 missense_variant MODERATE OLFM4 rs312533566 1:165458672
Group (number): frequence
Gallus_gallus_bankiva(3):0.833
Gallus_gallus_gallus(6):1.000
Gallus_gallus_jabouillei(26):0.904
Gallus_gallus_murghi(36):0.639
Gallus_gallus_spadiceus(42):0.798
Indonesia_Native_Chicken(34):0.824
Thailand_Native_Chicken(6):0.833
Vietnam_Native_Chicken(7):0.786
Wenchang_Chicken(1):0.500
Yunnan_Chicken(11):0.727
Xishuangbanna_Game_Chicken(10):0.500
Nixi_Chicken(12):0.875
Dulong_Chicken(7):0.929
Daweishan_Mini_Chicken(8):0.750
Guangxi_Chicken(5):0.600
Guangzhou_Chicken(1):0.000
Jiangxi_Silkies(19):0.868
Anyi_Gray_Chicken(5):0.600
Dongxiang_Blue-eggshell_Chicken(6):0.500
Tianfu_Black-bone_Chicken(4):1.000
Shimian_Caoke_Chicken(1):0.500
Jiuyuan_Black-bone_Chicken(5):0.500
Jinyang_Silky_Chicken(6):1.000
Emei_Black_Chicken(6):0.667
Pengxian_Yellow_Chicken(6):0.667
Muchuan_Black-bone_Chicken(5):0.900
Miyi_Chicken(4):0.875
YuanBao_Chicken(23):0.609
Langshan_Chicken(10):1.000
Luxi_Game_Chicken(9):0.722
Shouguang_Chicken(8):0.812
Gushi_Chicken(8):0.688
Bian_Chicken(8):0.188
Beijing_You_Chicken(11):1.000
Dagu_Chicken(8):0.500
Xinjiang_Native_Chicken(6):0.333
Hetian_Black_Chicken(8):0.875
Southern_Xinjiang_Game_Chicken(8):0.875
Turpan_Game_Chicken(7):0.857
Tibetan_Chicken(129):0.930
Araucana_Blue-eggshell_Chicken(6):1.000
Sri_Lanka_Native_Chicken(7):0.857
Bengal_Native_Chicken(15):0.900
India_Native_Chicken(41):0.732
Pakistan_Native_Chicken(35):0.914
Afghan_Native_Chicken(11):1.000
Iran_Native_Chicken(178):0.896
Iran_Commercial_Broiler(4):1.000
White_Leghorn_Chicken(13):0.962
Cornish_Chicken(1):1.000
Rhode_Island_Red_Chicken(1):0.500
White_Plymouth_Rock_Chicken(1):1.000
该数据展示了OLFM4基因位点(1:166897346 A/G,rs312533566)的突变频率在不同鸡种中的分布情况。OLFM4基因与细胞分化、免疫反应以及感染抵抗有关,因此该突变可能对鸡的免疫功能、环境适应性和健康状况产生潜在影响。
1. 原鸡
- Gallus gallus bankiva(红原鸡):0.833
- Gallus gallus gallus(普通原鸡):1.000
- Gallus gallus jabouillei(越南原鸡):0.904
- Gallus gallus murghi(印度原鸡):0.639
- Gallus gallus spadiceus(马来原鸡):0.798
分析:
- 普通原鸡(1.000) 突变频率最高,说明它们个体间一致性较高,可能已经适应了某些环境压力或免疫需求。
- 红原鸡、越南原鸡、马来原鸡 也有较高的突变频率,表明这些鸡种可能在进化过程中通过此突变改善了免疫功能或感染抵抗力。
- 印度原鸡(0.639) 的突变频率相对较低,表明其在该基因上的选择压力可能有所不同。
2. 蛋鸡
- White Leghorn Chicken(白色莱格恩鸡):0.962
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.500
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):1.000
分析:
- 阿劳卡纳蓝蛋鸡和白色莱格恩鸡 的突变频率非常高(接近或达到1.000),表明此突变对它们的免疫系统或适应能力有重要作用。
- 东乡蓝蛋鸡(0.500) 的突变频率较低,可能是因为该突变在其群体中并未广泛传播。
3. 肉鸡
- Cornish Chicken(康沃尔鸡):1.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):1.000
- Rhode Island Red Chicken(罗得岛红鸡):0.500
- Iran Commercial Broiler(伊朗商用肉鸡):1.000
分析:
- 康沃尔鸡、白色普利茅斯岩鸡和伊朗商用肉鸡 的突变频率非常高,说明这些肉鸡种可能通过该突变提高了免疫适应性或生产性能,以应对密集养殖环境中的压力。
- 罗得岛红鸡(0.500) 的突变频率较低,表明该突变在其基因库中未被广泛选择。
4. 肉蛋兼用鸡
- Beijing You Chicken(北京油鸡):1.000
- Dagu Chicken(大谷鸡):0.500
- Shouguang Chicken(寿光鸡):0.812
分析:
- 北京油鸡(1.000) 的突变频率很高,表明该突变可能对其生产性能或适应能力起到了积极作用。
- 寿光鸡(0.812) 也显示出较高的突变频率,表明该突变对其免疫功能和健康有一定作用。
- 大谷鸡(0.500) 的突变频率较低,说明它们可能通过其他途径维持免疫功能和生产性能。
5. 其他鸡种
- Tibetan Chicken(西藏鸡):0.930
- Indonesia Native Chicken(印尼本地鸡):0.824
- Thailand Native Chicken(泰国本地鸡):0.833
- Vietnam Native Chicken(越南本地鸡):0.786
- Bengal Native Chicken(孟加拉本地鸡):0.900
- India Native Chicken(印度本地鸡):0.732
- Pakistan Native Chicken(巴基斯坦本地鸡):0.914
- Afghan Native Chicken(阿富汗本地鸡):1.000
- Iran Native Chicken(伊朗本地鸡):0.896
分析:
- 西藏鸡(0.930)、印尼本地鸡(0.824) 等本地鸡种的突变频率较高,表明该突变在这些鸡种中通过增强免疫能力或环境适应性发挥了作用。
- 阿富汗本地鸡(1.000) 和 巴基斯坦本地鸡(0.914) 的突变频率很高,可能是因为它们面临更高的疾病压力或环境适应挑战,使得该突变在其基因库中广泛存在。
- 印度本地鸡(0.732) 和 越南本地鸡(0.786) 也有较高的突变频率,表明它们在不同的环境中可能依赖于此突变进行免疫调控。
总结与解释
原鸡:
- 普通原鸡、红原鸡和越南原鸡 的突变频率非常高,表明该突变在它们的进化过程中可能起到了增强免疫功能的作用,以应对环境中的挑战。
蛋鸡:
- 阿劳卡纳蓝蛋鸡和白色莱格恩鸡 的突变频率很高,说明它们通过此突变可能增强了免疫适应性和生产性能。
- 东乡蓝蛋鸡 的突变频率相对较低,可能因为该突变未在其基因库中广泛传播。
肉鸡:
- 康沃尔鸡、白色普利茅斯岩鸡和伊朗商用肉鸡 的突变频率达到1.000,表明该突变可能对其免疫调节和生产性能有显著的影响。
- 罗得岛红鸡 的突变频率较低,显示出其在该基因位点上的选择压力较小。
肉蛋兼用鸡:
- 北京油鸡 突变频率最高,显示该突变在其基因库中发挥了重要作用,可能帮助其平衡肉质和产蛋性能。
其他鸡种:
- 西藏鸡和印尼本地鸡 突变频率较高,表明它们通过此突变适应了特殊的环境挑战,增强了免疫功能。
- 阿富汗本地鸡、巴基斯坦本地鸡 也有很高的突变频率,表明这些品种可能面临更大的免疫挑战。
结论:
OLFM4基因的突变可能对鸡种的免疫系统、适应性和健康状况产生重要影响。突变频率较高的鸡种可能通过此基因突变增强了环境适应能力和抵抗感染的能力。
1 166897400 A/C A 0.165 missense_variant MODERATE OLFM4 rs317016269 1:165458726
1 166897406 C/T C 0.163 missense_variant MODERATE OLFM4 rs315214502 1:165458732
Group (number): frequence
Gallus_gallus_bankiva(4):0.750
Gallus_gallus_gallus(6):1.000
Gallus_gallus_jabouillei(24):0.917
Gallus_gallus_murghi(42):0.655
Gallus_gallus_spadiceus(39):0.808
Indonesia_Native_Chicken(36):0.806
Thailand_Native_Chicken(6):0.917
Vietnam_Native_Chicken(6):0.750
Wenchang_Chicken(1):0.500
Yunnan_Chicken(11):0.818
Xishuangbanna_Game_Chicken(10):0.550
Nixi_Chicken(11):0.864
Dulong_Chicken(7):1.000
Daweishan_Mini_Chicken(7):0.714
Guangxi_Chicken(5):0.500
Guangzhou_Chicken(1):0.000
Jiangxi_Silkies(20):0.900
Anyi_Gray_Chicken(5):0.700
Dongxiang_Blue-eggshell_Chicken(6):0.500
Tianfu_Black-bone_Chicken(5):1.000
Shimian_Caoke_Chicken(1):0.500
Jiuyuan_Black-bone_Chicken(5):0.500
Jinyang_Silky_Chicken(6):1.000
Emei_Black_Chicken(5):0.800
Pengxian_Yellow_Chicken(6):0.667
Muchuan_Black-bone_Chicken(4):0.875
Miyi_Chicken(4):0.875
YuanBao_Chicken(22):0.500
Langshan_Chicken(10):1.000
Luxi_Game_Chicken(9):0.722
Shouguang_Chicken(8):0.875
Gushi_Chicken(8):0.750
Bian_Chicken(8):0.125
Beijing_You_Chicken(11):1.000
Dagu_Chicken(8):0.438
Xinjiang_Native_Chicken(6):1.000
Hetian_Black_Chicken(7):0.857
Southern_Xinjiang_Game_Chicken(8):0.875
Turpan_Game_Chicken(7):0.786
Tibetan_Chicken(129):0.930
Araucana_Blue-eggshell_Chicken(6):1.000
Sri_Lanka_Native_Chicken(7):0.857
Bengal_Native_Chicken(15):0.867
India_Native_Chicken(39):0.731
Pakistan_Native_Chicken(36):0.958
Afghan_Native_Chicken(11):1.000
Iran_Native_Chicken(179):0.902
Iran_Commercial_Broiler(4):1.000
White_Leghorn_Chicken(13):0.962
Cornish_Chicken(1):1.000
Rhode_Island_Red_Chicken(1):0.500
White_Plymouth_Rock_Chicken(1):1.000
该数据展示了OLFM4基因位点(1:166897346 A/G,rs312533566)的突变频率在不同鸡种中的分布情况。OLFM4基因与细胞分化、免疫反应以及感染抵抗有关,因此该突变可能对鸡的免疫功能、环境适应性和健康状况产生潜在影响。
1. 原鸡
- Gallus gallus bankiva(红原鸡):0.833
- Gallus gallus gallus(普通原鸡):1.000
- Gallus gallus jabouillei(越南原鸡):0.904
- Gallus gallus murghi(印度原鸡):0.639
- Gallus gallus spadiceus(马来原鸡):0.798
分析:
- 普通原鸡(1.000) 突变频率最高,说明它们个体间一致性较高,可能已经适应了某些环境压力或免疫需求。
- 红原鸡、越南原鸡、马来原鸡 也有较高的突变频率,表明这些鸡种可能在进化过程中通过此突变改善了免疫功能或感染抵抗力。
- 印度原鸡(0.639) 的突变频率相对较低,表明其在该基因上的选择压力可能有所不同。
2. 蛋鸡
- White Leghorn Chicken(白色莱格恩鸡):0.962
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.500
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):1.000
分析:
- 阿劳卡纳蓝蛋鸡和白色莱格恩鸡 的突变频率非常高(接近或达到1.000),表明此突变对它们的免疫系统或适应能力有重要作用。
- 东乡蓝蛋鸡(0.500) 的突变频率较低,可能是因为该突变在其群体中并未广泛传播。
3. 肉鸡
- Cornish Chicken(康沃尔鸡):1.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):1.000
- Rhode Island Red Chicken(罗得岛红鸡):0.500
- Iran Commercial Broiler(伊朗商用肉鸡):1.000
分析:
- 康沃尔鸡、白色普利茅斯岩鸡和伊朗商用肉鸡 的突变频率非常高,说明这些肉鸡种可能通过该突变提高了免疫适应性或生产性能,以应对密集养殖环境中的压力。
- 罗得岛红鸡(0.500) 的突变频率较低,表明该突变在其基因库中未被广泛选择。
4. 肉蛋兼用鸡
- Beijing You Chicken(北京油鸡):1.000
- Dagu Chicken(大谷鸡):0.500
- Shouguang Chicken(寿光鸡):0.812
分析:
- 北京油鸡(1.000) 的突变频率很高,表明该突变可能对其生产性能或适应能力起到了积极作用。
- 寿光鸡(0.812) 也显示出较高的突变频率,表明该突变对其免疫功能和健康有一定作用。
- 大谷鸡(0.500) 的突变频率较低,说明它们可能通过其他途径维持免疫功能和生产性能。
5. 其他鸡种
- Tibetan Chicken(西藏鸡):0.930
- Indonesia Native Chicken(印尼本地鸡):0.824
- Thailand Native Chicken(泰国本地鸡):0.833
- Vietnam Native Chicken(越南本地鸡):0.786
- Bengal Native Chicken(孟加拉本地鸡):0.900
- India Native Chicken(印度本地鸡):0.732
- Pakistan Native Chicken(巴基斯坦本地鸡):0.914
- Afghan Native Chicken(阿富汗本地鸡):1.000
- Iran Native Chicken(伊朗本地鸡):0.896
分析:
- 西藏鸡(0.930)、印尼本地鸡(0.824) 等本地鸡种的突变频率较高,表明该突变在这些鸡种中通过增强免疫能力或环境适应性发挥了作用。
- 阿富汗本地鸡(1.000) 和 巴基斯坦本地鸡(0.914) 的突变频率很高,可能是因为它们面临更高的疾病压力或环境适应挑战,使得该突变在其基因库中广泛存在。
- 印度本地鸡(0.732) 和 越南本地鸡(0.786) 也有较高的突变频率,表明它们在不同的环境中可能依赖于此突变进行免疫调控。
总结与解释
原鸡:
- 普通原鸡、红原鸡和越南原鸡 的突变频率非常高,表明该突变在它们的进化过程中可能起到了增强免疫功能的作用,以应对环境中的挑战。
蛋鸡:
- 阿劳卡纳蓝蛋鸡和白色莱格恩鸡 的突变频率很高,说明它们通过此突变可能增强了免疫适应性和生产性能。
- 东乡蓝蛋鸡 的突变频率相对较低,可能因为该突变未在其基因库中广泛传播。
肉鸡:
- 康沃尔鸡、白色普利茅斯岩鸡和伊朗商用肉鸡 的突变频率达到1.000,表明该突变可能对其免疫调节和生产性能有显著的影响。
- 罗得岛红鸡 的突变频率较低,显示出其在该基因位点上的选择压力较小。
肉蛋兼用鸡:
- 北京油鸡 突变频率最高,显示该突变在其基因库中发挥了重要作用,可能帮助其平衡肉质和产蛋性能。
其他鸡种:
- 西藏鸡和印尼本地鸡 突变频率较高,表明它们通过此突变适应了特殊的环境挑战,增强了免疫功能。
- 阿富汗本地鸡、巴基斯坦本地鸡 也有很高的突变频率,表明这些品种可能面临更大的免疫挑战。
结论:
OLFM4基因的突变可能对鸡种的免疫系统、适应性和健康状况产生重要影响。突变频率较高的鸡种可能通过此基因突变增强了环境适应能力和抵抗感染的能力。
1 166918772 T/A A 0.078 missense_variant MODERATE OLFM4 novel 1:165480103
Group (number): frequence
Gallus_gallus_bankiva(4):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(26):0.192
Gallus_gallus_murghi(32):0.500
Gallus_gallus_spadiceus(42):0.071
Indonesia_Native_Chicken(36):0.014
Thailand_Native_Chicken(5):0.000
Vietnam_Native_Chicken(7):0.000
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.083
Xishuangbanna_Game_Chicken(10):0.000
Nixi_Chicken(12):0.125
Dulong_Chicken(7):0.000
Daweishan_Mini_Chicken(8):0.000
Guangxi_Chicken(6):0.167
Guangzhou_Chicken(5):0.000
Jiangxi_Silkies(20):0.000
Anyi_Gray_Chicken(5):0.200
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.200
Shimian_Caoke_Chicken(4):0.250
Jiuyuan_Black-bone_Chicken(5):0.000
Jinyang_Silky_Chicken(6):0.333
Emei_Black_Chicken(6):0.083
Pengxian_Yellow_Chicken(6):0.083
Muchuan_Black-bone_Chicken(5):0.100
Miyi_Chicken(5):0.200
YuanBao_Chicken(23):0.109
Langshan_Chicken(9):0.000
Luxi_Game_Chicken(8):0.125
Shouguang_Chicken(5):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.000
Beijing_You_Chicken(11):0.045
Dagu_Chicken(7):0.000
Xinjiang_Native_Chicken(5):0.000
Hetian_Black_Chicken(8):0.000
Southern_Xinjiang_Game_Chicken(8):0.000
Turpan_Game_Chicken(8):0.250
Tibetan_Chicken(138):0.101
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(7):0.000
Bengal_Native_Chicken(12):0.000
India_Native_Chicken(48):0.000
Pakistan_Native_Chicken(36):0.028
Afghan_Native_Chicken(11):0.091
Iran_Native_Chicken(180):0.056
Iran_Commercial_Broiler(3):0.000
White_Leghorn_Chicken(13):0.000
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
该数据展示了OLFM4基因位点(1:166918772 T/A)的突变频率在不同鸡种中的分布情况。OLFM4基因与免疫功能和细胞分化相关,因此该突变可能对鸡种的免疫调节和健康状况产生潜在影响。
- 原鸡
Gallus gallus bankiva(红原鸡):0.000
Gallus gallus gallus(普通原鸡):0.000
Gallus gallus jabouillei(越南原鸡):0.192
Gallus gallus murghi(印度原鸡):0.500
Gallus gallus spadiceus(马来原鸡):0.071
分析:
普通原鸡和红原鸡 的突变频率为0,说明它们未经历该突变的选择压力。
印度原鸡(0.500) 的突变频率较高,表明该基因突变可能有助于免疫调节或环境适应。
越南原鸡和马来原鸡 的突变频率较低,表明它们在该基因位点上存在较小的选择压力。 - 蛋鸡
White Leghorn Chicken(白色莱格恩鸡):0.000
Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.000
Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.000
分析:
所有蛋鸡品种的突变频率为0,表明该突变未在蛋鸡中广泛传播,可能在它们的生产性能或免疫系统中不起关键作用。 - 肉鸡
Cornish Chicken(康沃尔鸡):0.000
White Plymouth Rock Chicken(白色普利茅斯岩鸡):0.000
Rhode Island Red Chicken(罗得岛红鸡):0.000
Iran Commercial Broiler(伊朗商用肉鸡):0.000
分析:
所有肉鸡品种的突变频率为0,表明该突变在这些肉鸡中没有被广泛选择,可能表明其他基因对这些鸡种的生产性能有更重要的影响。 - 肉蛋兼用鸡
Beijing You Chicken(北京油鸡):0.045
Dagu Chicken(大谷鸡):0.000
Shouguang Chicken(寿光鸡):0.000
分析:
北京油鸡 的突变频率为0.045,表明部分个体可能在进化过程中选择了此突变,以增强免疫功能或适应性,但整体频率较低。
大谷鸡和寿光鸡 未检测到此突变,表明该基因突变对这些鸡种的生产性能或适应性无显著影响。 - 其他鸡种
Tibetan Chicken(西藏鸡):0.101
Indonesia Native Chicken(印尼本地鸡):0.014
Thailand Native Chicken(泰国本地鸡):0.000
Vietnam Native Chicken(越南本地鸡):0.000
Bengal Native Chicken(孟加拉本地鸡):0.000
India Native Chicken(印度本地鸡):0.000
Pakistan Native Chicken(巴基斯坦本地鸡):0.028
Afghan Native Chicken(阿富汗本地鸡):0.091
Iran Native Chicken(伊朗本地鸡):0.056
分析:
西藏鸡(0.101) 和 阿富汗本地鸡(0.091) 的突变频率较高,表明该基因突变可能对它们的免疫适应性或环境适应性有一定帮助。
巴基斯坦本地鸡(0.028) 和 印尼本地鸡(0.014) 的突变频率较低,可能表明这些鸡种在其自然栖息地中并未依赖该突变进行环境适应。
泰国、越南、孟加拉、印度等本地鸡 的突变频率为0,表明它们在该基因位点上没有受到显著的选择压力。
总结与解释
原鸡:
印度原鸡(0.500) 的突变频率较高,表明其可能通过此突变获得了一定的免疫或环境适应能力。
其他原鸡的突变频率较低或为0,说明该突变并未广泛在它们中传播。
蛋鸡:
所有蛋鸡品种的突变频率为0,表明该基因突变对蛋鸡的生产性能或健康状况没有明显影响。
肉鸡:
肉鸡中突变频率为0,表明该突变未被选择,可能这些鸡种更多依赖其他基因来优化生产性能。
肉蛋兼用鸡:
北京油鸡 有少量个体携带此突变,表明其基因库中可能存在部分环境适应或免疫相关的选择压力,但总体影响较小。
其他鸡种:
西藏鸡和阿富汗本地鸡 的突变频率较高,显示该突变可能帮助它们适应高海拔或特殊环境中的挑战。
伊朗、巴基斯坦等本地鸡 的突变频率较低,但有少部分个体携带此突变,表明其基因库中存在一定的选择压力。
结论:
该突变对原鸡和一些本地鸡种(如印度原鸡、西藏鸡和阿富汗本地鸡)可能具有一定的适应性优势,尤其是在免疫系统相关的功能上。而对蛋鸡、肉鸡等高生产性能鸡种的影响则较小,可能表明这些鸡种依赖其他基因来优化其生产性能或健康状况。
65265796 A/G G 0.057 missense_variant MODERATE IAPP rs736980478 1:65324929
Group (number): frequence
Gallus_gallus_bankiva(3):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(27):0.000
Gallus_gallus_murghi(55):0.036
Gallus_gallus_spadiceus(44):0.023
Indonesia_Native_Chicken(36):0.028
Thailand_Native_Chicken(6):0.083
Vietnam_Native_Chicken(7):0.071
Wenchang_Chicken(1):0.000
Yunnan_Chicken(11):0.273
Xishuangbanna_Game_Chicken(10):0.050
Nixi_Chicken(11):0.273
Dulong_Chicken(6):0.000
Daweishan_Mini_Chicken(8):0.000
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(3):0.000
Jiangxi_Silkies(20):0.025
Anyi_Gray_Chicken(5):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.000
Shimian_Caoke_Chicken(3):0.000
Jiuyuan_Black-bone_Chicken(5):0.000
Jinyang_Silky_Chicken(6):0.000
Emei_Black_Chicken(5):0.000
Pengxian_Yellow_Chicken(6):0.083
Muchuan_Black-bone_Chicken(4):0.125
Miyi_Chicken(5):0.100
YuanBao_Chicken(23):0.000
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(9):0.000
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.000
Beijing_You_Chicken(11):0.000
Dagu_Chicken(8):0.000
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(8):0.062
Southern_Xinjiang_Game_Chicken(8):0.000
Turpan_Game_Chicken(8):0.062
Tibetan_Chicken(132):0.076
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(7):0.143
Bengal_Native_Chicken(15):0.033
India_Native_Chicken(45):0.056
Pakistan_Native_Chicken(35):0.086
Afghan_Native_Chicken(11):0.000
Iran_Native_Chicken(180):0.083
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(13):0.192
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
该数据展示了IAPP基因位点(1:65265796 A/G,rs736980478)的突变频率在不同鸡种中的分布情况。IAPP基因与胰岛素调节有关,因此此突变可能影响鸡种的糖代谢和胰岛素分泌。
1. 原鸡
- Gallus gallus bankiva(红原鸡):0.000
- Gallus gallus gallus(普通原鸡):0.000
- Gallus gallus jabouillei(越南原鸡):0.000
- Gallus gallus murghi(印度原鸡):0.036
- Gallus gallus spadiceus(马来原鸡):0.023
分析:
- 红原鸡、普通原鸡和越南原鸡 的突变频率为0,表明这些原鸡未受到该突变的选择压力。
- 印度原鸡(0.036) 和 马来原鸡(0.023) 的突变频率较低,表明少量个体可能通过该突变进行糖代谢调节,但总体选择压力不大。
2. 蛋鸡
- White Leghorn Chicken(白色莱格恩鸡):0.192
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.000
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.000
分析:
- 白色莱格恩鸡(0.192) 的突变频率相对较高,表明在该蛋鸡种群中,部分个体可能通过此突变优化糖代谢,以提升产蛋性能或健康状况。
- 东乡蓝蛋鸡和阿劳卡纳蓝蛋鸡 的突变频率为0,表明该突变在这些蛋鸡中未被选择,可能它们依赖其他机制来调节代谢。
3. 肉鸡
- Cornish Chicken(康沃尔鸡):0.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):0.000
- Rhode Island Red Chicken(罗得岛红鸡):0.000
- Iran Commercial Broiler(伊朗商用肉鸡):0.000
分析:
- 所有肉鸡品种的突变频率为0,说明此突变对肉鸡的生长性能或代谢调节没有显著影响,肉鸡的选择压力可能集中在其他生产性能基因上。
4. 肉蛋兼用鸡
- Beijing You Chicken(北京油鸡):0.000
- Dagu Chicken(大谷鸡):0.000
- Shouguang Chicken(寿光鸡):0.000
分析:
- 所有肉蛋兼用鸡品种的突变频率为0,表明此基因突变对这些鸡种的生产性能和代谢调节没有显著影响。
5. 其他鸡种
- Tibetan Chicken(西藏鸡):0.076
- Indonesia Native Chicken(印尼本地鸡):0.028
- Thailand Native Chicken(泰国本地鸡):0.083
- Vietnam Native Chicken(越南本地鸡):0.071
- Bengal Native Chicken(孟加拉本地鸡):0.033
- India Native Chicken(印度本地鸡):0.056
- Pakistan Native Chicken(巴基斯坦本地鸡):0.086
- Afghan Native Chicken(阿富汗本地鸡):0.000
- Iran Native Chicken(伊朗本地鸡):0.083
分析:
- 西藏鸡(0.076)、泰国本地鸡(0.083)、巴基斯坦本地鸡(0.086) 和 伊朗本地鸡(0.083) 有较高的突变频率,表明在这些地区的鸡种中,某些个体可能通过该突变进行代谢调节,适应当地的环境或饮食结构。
- 印尼本地鸡(0.028)和孟加拉本地鸡(0.033) 的突变频率较低,表明突变并未在这些品种中被广泛选择。
- 阿富汗本地鸡 的突变频率为0,表明其基因库中未选择此突变。
总结与解释
原鸡:
- 印度原鸡和马来原鸡 中有少数个体显示出该突变,但总体频率较低,表明这些原鸡在糖代谢调节方面未受到该突变的显著影响。
蛋鸡:
- 白色莱格恩鸡 的突变频率较高,表明其可能通过该突变优化代谢或提高产蛋性能。
肉鸡:
- 肉鸡的突变频率为0,表明它们在该位点上未受到选择,说明其他基因可能在影响肉鸡的生产性能或健康。
肉蛋兼用鸡:
- 这些鸡种未表现出突变频率,表明此基因突变与它们的生产性能没有直接联系。
其他鸡种:
- 西藏鸡、泰国本地鸡和伊朗本地鸡 在该基因位点上有一定突变频率,可能有助于它们在特定环境中的代谢调节。
结论:
该基因突变与鸡种的代谢调节可能相关,尤其在某些蛋鸡和本地鸡种中,突变频率较高,表明其可能通过影响代谢和胰岛素调节来优化健康和生产性能。然而,该突变在肉鸡和肉蛋兼用鸡中并未被广泛选择,表明它们依赖其他基因来提升生产性能或代谢适应能力。
1 65265796 A/G G 0.057 missense_variant MODERATE IAPP rs736980478 1:65324929
1 65265983 G/A A 0.202 missense_variant MODERATE IAPP rs734361033 1:65325116
1 65266022 C/A A 0.043 missense_variant MODERATE IAPP rs732737502 1:65325155
Group (number): frequence
Gallus_gallus_bankiva(4):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(26):0.000
Gallus_gallus_murghi(56):0.000
Gallus_gallus_spadiceus(42):0.226
Indonesia_Native_Chicken(35):0.129
Thailand_Native_Chicken(5):0.300
Vietnam_Native_Chicken(7):0.429
Wenchang_Chicken(1):0.500
Yunnan_Chicken(11):0.227
Xishuangbanna_Game_Chicken(9):0.611
Nixi_Chicken(12):0.167
Dulong_Chicken(7):0.357
Daweishan_Mini_Chicken(8):0.250
Guangxi_Chicken(6):0.417
Guangzhou_Chicken(3):0.167
Jiangxi_Silkies(20):0.075
Anyi_Gray_Chicken(5):0.900
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.200
Shimian_Caoke_Chicken(1):1.000
Jiuyuan_Black-bone_Chicken(5):0.100
Jinyang_Silky_Chicken(6):0.083
Emei_Black_Chicken(4):0.000
Pengxian_Yellow_Chicken(6):0.000
Muchuan_Black-bone_Chicken(5):0.100
Miyi_Chicken(5):0.400
YuanBao_Chicken(22):0.136
Langshan_Chicken(10):0.350
Luxi_Game_Chicken(8):0.750
Shouguang_Chicken(8):0.188
Gushi_Chicken(8):0.938
Bian_Chicken(8):0.188
Beijing_You_Chicken(11):0.409
Dagu_Chicken(8):0.688
Xinjiang_Native_Chicken(6):0.167
Hetian_Black_Chicken(8):0.125
Southern_Xinjiang_Game_Chicken(7):0.286
Turpan_Game_Chicken(8):0.812
Tibetan_Chicken(129):0.093
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(6):0.167
Bengal_Native_Chicken(14):0.143
India_Native_Chicken(46):0.228
Pakistan_Native_Chicken(34):0.353
Afghan_Native_Chicken(11):0.636
Iran_Native_Chicken(180):0.211
Iran_Commercial_Broiler(4):0.125
White_Leghorn_Chicken(13):0.000
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
这段数据展示了 IAPP 基因 位点(1:65265983 G/A,rs734361033)在不同鸡种中的突变频率。IAPP基因与胰岛素调节相关,因此这个突变可能对鸡的糖代谢和生理健康产生影响。以下是不同类型鸡群体的分析:
1. 原鸡
- Gallus gallus bankiva(红原鸡):0.000
- Gallus gallus gallus(普通原鸡):0.000
- Gallus gallus jabouillei(越南原鸡):0.000
- Gallus gallus murghi(印度原鸡):0.000
- Gallus gallus spadiceus(马来原鸡):0.226
分析:
- 红原鸡、普通原鸡、越南原鸡和印度原鸡 的突变频率为0,表明这些原鸡中没有表现出该突变。
- 马来原鸡(0.226) 的突变频率较高,可能是该突变在部分马来原鸡中被选择,可能与代谢或生理适应相关。
2. 蛋鸡
- White Leghorn Chicken(白色莱格恩鸡):0.000
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.000
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.000
分析:
- 蛋鸡中如 白色莱格恩鸡 和 东乡蓝蛋鸡 没有该突变,表明这类鸡群在该基因上没有进行选择。
3. 肉鸡
- Cornish Chicken(康沃尔鸡):0.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):0.000
- Rhode Island Red Chicken(罗得岛红鸡):0.000
- Iran Commercial Broiler(伊朗商用肉鸡):0.125
分析:
- 除 伊朗商用肉鸡(0.125)外,其他肉鸡品种都没有该突变,表明它们没有在这个基因位点进行选择。
4. 肉蛋兼用鸡
- Beijing You Chicken(北京油鸡):0.409
- Dagu Chicken(大谷鸡):0.688
- Shouguang Chicken(寿光鸡):0.188
分析:
- 北京油鸡和大谷鸡 的突变频率较高,分别为0.409和0.688,表明该突变可能与这些品种的代谢调节或多功能生产性能相关。
- 寿光鸡(0.188) 的突变频率稍低,但也表现出了一些选择压力。
5. 其他鸡种
- Tibetan Chicken(西藏鸡):0.093
- Indonesia Native Chicken(印尼本地鸡):0.129
- Thailand Native Chicken(泰国本地鸡):0.300
- Vietnam Native Chicken(越南本地鸡):0.429
- Bengal Native Chicken(孟加拉本地鸡):0.143
- India Native Chicken(印度本地鸡):0.228
- Pakistan Native Chicken(巴基斯坦本地鸡):0.353
- Afghan Native Chicken(阿富汗本地鸡):0.636
- Iran Native Chicken(伊朗本地鸡):0.211
分析:
- 西藏鸡、印尼本地鸡和印度本地鸡 的突变频率较低,表明这些鸡种可能在代谢调节方面没有强烈选择该突变。
- 泰国本地鸡、越南本地鸡、巴基斯坦本地鸡和阿富汗本地鸡 的突变频率较高,尤其是 阿富汗本地鸡(0.636),表明在这些群体中该突变可能与代谢适应相关。
总结与解释
原鸡:
- 马来原鸡(0.226) 显示出较高的突变频率,表明这个基因在某些原鸡群体中可能被选择以适应不同的生理需求或环境。
蛋鸡:
- 蛋鸡中的突变频率为0,说明该基因位点对蛋鸡的代谢调节或产蛋性能没有显著影响。
肉鸡:
- 伊朗商用肉鸡 显示了一定的突变频率(0.125),这可能与其生产需求相关,而其他肉鸡则没有表现出此突变的选择。
肉蛋兼用鸡:
- 北京油鸡和大谷鸡 中的突变频率较高,表明该基因位点可能有助于这些鸡种的代谢和多功能性。
其他鸡种:
- 阿富汗、巴基斯坦和越南本地鸡 突变频率较高,表明该突变可能帮助这些群体适应当地环境,特别是在代谢调节方面。
结论:
该突变在不同鸡种中的选择压力表现不一,某些本地鸡种表现出较高的突变频率,可能与其代谢需求或环境适应性有关。
BMP4
27 6482056 C/A A 0.097 missense_variant MODERATE NFE2L1 rs313857787 27:3682095
Group (number): frequence
Gallus_gallus_bankiva(3):0.000
Gallus_gallus_gallus(4):0.000
Gallus_gallus_jabouillei(27):0.019
Gallus_gallus_murghi(51):0.000
Gallus_gallus_spadiceus(39):0.026
Indonesia_Native_Chicken(35):0.100
Thailand_Native_Chicken(5):0.100
Vietnam_Native_Chicken(6):0.167
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.125
Xishuangbanna_Game_Chicken(10):0.300
Nixi_Chicken(8):0.125
Dulong_Chicken(7):0.143
Daweishan_Mini_Chicken(7):0.714
Guangxi_Chicken(5):0.100
Guangzhou_Chicken(6):0.250
Jiangxi_Silkies(19):0.079
Anyi_Gray_Chicken(4):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.083
Tianfu_Black-bone_Chicken(5):0.200
Shimian_Caoke_Chicken(4):0.500
Jiuyuan_Black-bone_Chicken(5):0.100
Jinyang_Silky_Chicken(6):0.417
Emei_Black_Chicken(6):0.250
Pengxian_Yellow_Chicken(6):0.333
Muchuan_Black-bone_Chicken(5):0.300
Miyi_Chicken(5):0.000
YuanBao_Chicken(22):0.295
Langshan_Chicken(7):0.214
Luxi_Game_Chicken(9):0.000
Shouguang_Chicken(5):0.600
Gushi_Chicken(7):0.643
Bian_Chicken(7):0.071
Beijing_You_Chicken(10):0.300
Dagu_Chicken(6):0.167
Xinjiang_Native_Chicken(6):0.167
Hetian_Black_Chicken(8):0.250
Southern_Xinjiang_Game_Chicken(8):0.312
Turpan_Game_Chicken(8):0.125
Tibetan_Chicken(143):0.077
Araucana_Blue-eggshell_Chicken(6):0.167
Sri_Lanka_Native_Chicken(7):0.000
Bengal_Native_Chicken(12):0.042
India_Native_Chicken(47):0.032
Pakistan_Native_Chicken(35):0.014
Afghan_Native_Chicken(10):0.000
Iran_Native_Chicken(173):0.043
Iran_Commercial_Broiler(3):0.000
White_Leghorn_Chicken(12):0.000
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):1.000
这段数据展示了 IAPP 基因 位点(1:65265983 G/A,rs734361033)在不同鸡种中的突变频率。IAPP基因与胰岛素调节相关,因此这个突变可能对鸡的糖代谢和生理健康产生影响。以下是不同类型鸡群体的分析:
1. 原鸡
- Gallus gallus bankiva(红原鸡):0.000
- Gallus gallus gallus(普通原鸡):0.000
- Gallus gallus jabouillei(越南原鸡):0.000
- Gallus gallus murghi(印度原鸡):0.000
- Gallus gallus spadiceus(马来原鸡):0.226
分析:
- 红原鸡、普通原鸡、越南原鸡和印度原鸡 的突变频率为0,表明这些原鸡中没有表现出该突变。
- 马来原鸡(0.226) 的突变频率较高,可能是该突变在部分马来原鸡中被选择,可能与代谢或生理适应相关。
2. 蛋鸡
- White Leghorn Chicken(白色莱格恩鸡):0.000
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.000
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.000
分析:
- 蛋鸡中如 白色莱格恩鸡 和 东乡蓝蛋鸡 没有该突变,表明这类鸡群在该基因上没有进行选择。
3. 肉鸡
- Cornish Chicken(康沃尔鸡):0.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):0.000
- Rhode Island Red Chicken(罗得岛红鸡):0.000
- Iran Commercial Broiler(伊朗商用肉鸡):0.125
分析:
- 除 伊朗商用肉鸡(0.125)外,其他肉鸡品种都没有该突变,表明它们没有在这个基因位点进行选择。
4. 肉蛋兼用鸡
- Beijing You Chicken(北京油鸡):0.409
- Dagu Chicken(大谷鸡):0.688
- Shouguang Chicken(寿光鸡):0.188
分析:
- 北京油鸡和大谷鸡 的突变频率较高,分别为0.409和0.688,表明该突变可能与这些品种的代谢调节或多功能生产性能相关。
- 寿光鸡(0.188) 的突变频率稍低,但也表现出了一些选择压力。
5. 其他鸡种
- Tibetan Chicken(西藏鸡):0.093
- Indonesia Native Chicken(印尼本地鸡):0.129
- Thailand Native Chicken(泰国本地鸡):0.300
- Vietnam Native Chicken(越南本地鸡):0.429
- Bengal Native Chicken(孟加拉本地鸡):0.143
- India Native Chicken(印度本地鸡):0.228
- Pakistan Native Chicken(巴基斯坦本地鸡):0.353
- Afghan Native Chicken(阿富汗本地鸡):0.636
- Iran Native Chicken(伊朗本地鸡):0.211
分析:
- 西藏鸡、印尼本地鸡和印度本地鸡 的突变频率较低,表明这些鸡种可能在代谢调节方面没有强烈选择该突变。
- 泰国本地鸡、越南本地鸡、巴基斯坦本地鸡和阿富汗本地鸡 的突变频率较高,尤其是 阿富汗本地鸡(0.636),表明在这些群体中该突变可能与代谢适应相关。
总结与解释
原鸡:
- 马来原鸡(0.226) 显示出较高的突变频率,表明这个基因在某些原鸡群体中可能被选择以适应不同的生理需求或环境。
蛋鸡:
- 蛋鸡中的突变频率为0,说明该基因位点对蛋鸡的代谢调节或产蛋性能没有显著影响。
肉鸡:
- 伊朗商用肉鸡 显示了一定的突变频率(0.125),这可能与其生产需求相关,而其他肉鸡则没有表现出此突变的选择。
肉蛋兼用鸡:
- 北京油鸡和大谷鸡 中的突变频率较高,表明该基因位点可能有助于这些鸡种的代谢和多功能性。
其他鸡种:
- 阿富汗、巴基斯坦和越南本地鸡 突变频率较高,表明该突变可能帮助这些群体适应当地环境,特别是在代谢调节方面。
结论:
该突变在不同鸡种中的选择压力表现不一,某些本地鸡种表现出较高的突变频率,可能与其代谢需求或环境适应性有关。
27 6482226 C/T T 0.044 missense_variant MODERATE NFE2L1 novel 27:3682265
Group (number): frequence
Gallus_gallus_bankiva(3):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(27):0.019
Gallus_gallus_murghi(52):0.000
Gallus_gallus_spadiceus(41):0.000
Indonesia_Native_Chicken(35):0.000
Thailand_Native_Chicken(6):0.000
Vietnam_Native_Chicken(7):0.000
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.167
Xishuangbanna_Game_Chicken(10):0.000
Nixi_Chicken(11):0.000
Dulong_Chicken(7):0.071
Daweishan_Mini_Chicken(8):0.000
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(6):0.000
Jiangxi_Silkies(20):0.000
Anyi_Gray_Chicken(4):0.500
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.100
Shimian_Caoke_Chicken(4):0.125
Jiuyuan_Black-bone_Chicken(5):0.000
Jinyang_Silky_Chicken(6):0.167
Emei_Black_Chicken(6):0.000
Pengxian_Yellow_Chicken(6):0.000
Muchuan_Black-bone_Chicken(5):0.200
Miyi_Chicken(5):0.100
YuanBao_Chicken(23):0.000
Langshan_Chicken(8):0.000
Luxi_Game_Chicken(9):0.389
Shouguang_Chicken(7):0.000
Gushi_Chicken(7):0.000
Bian_Chicken(7):0.143
Beijing_You_Chicken(11):0.045
Dagu_Chicken(6):0.000
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(8):0.125
Southern_Xinjiang_Game_Chicken(8):0.000
Turpan_Game_Chicken(8):0.062
Tibetan_Chicken(146):0.055
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(7):0.000
Bengal_Native_Chicken(13):0.000
India_Native_Chicken(48):0.021
Pakistan_Native_Chicken(37):0.054
Afghan_Native_Chicken(11):0.000
Iran_Native_Chicken(176):0.074
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(13):0.000
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
该数据描述了 NFE2L1 基因位点(27:6482226 C/T,novel)的突变频率在不同鸡种中的表现。这一突变为 错义突变,其影响被评估为中度(Moderate),意味着它可能对基因功能产生一定的影响。NFE2L1 是参与 细胞氧化应激反应 和 抗氧化防御机制 的基因,因此这一突变可能影响鸡的代谢调节或适应性。以下是不同鸡种的突变频率分析:
1. 原鸡
- Gallus gallus bankiva(红原鸡):0.000
- Gallus gallus gallus(普通原鸡):0.000
- Gallus gallus jabouillei(越南原鸡):0.019
- Gallus gallus murghi(印度原鸡):0.000
- Gallus gallus spadiceus(马来原鸡):0.000
分析:
- 大多数原鸡的突变频率接近于 0,仅 越南原鸡(0.019) 表现出极低频率的突变,表明这个突变位点在原鸡中并没有显著选择压力。
2. 蛋鸡
- White Leghorn Chicken(白色莱格恩鸡):0.000
- Dongxiang Blue-eggshell Chicken(东乡蓝蛋鸡):0.000
- Araucana Blue-eggshell Chicken(阿劳卡纳蓝蛋鸡):0.000
分析:
- 所有蛋鸡品种均无该突变,显示出蛋鸡在这个基因位点上没有受到选择压力或该突变对其生产特性没有影响。
3. 肉鸡
- Cornish Chicken(康沃尔鸡):0.000
- White Plymouth Rock Chicken(白色普利茅斯岩鸡):0.000
- Rhode Island Red Chicken(罗得岛红鸡):0.000
- Iran Commercial Broiler(伊朗商用肉鸡):0.000
分析:
- 肉鸡种类也没有表现出该突变,表明这一基因位点对肉鸡的生长或肉质特性可能没有显著影响。
4. 肉蛋兼用鸡
- Beijing You Chicken(北京油鸡):0.045
- Dagu Chicken(大谷鸡):0.000
- Luxi Game Chicken(鲁西斗鸡):0.389
- Shouguang Chicken(寿光鸡):0.000
分析:
- 北京油鸡和鲁西斗鸡 的突变频率分别为 0.045 和 0.389,显示出这些品种可能在这一基因位点上有一定的变异选择压力,可能与其多功能生产特性相关。
5. 其他鸡种
- Yunnan Chicken(云南鸡):0.167
- Anyi Gray Chicken(安义灰鸡):0.500
- Hetian Black Chicken(和田黑鸡):0.125
- Tibetan Chicken(西藏鸡):0.055
- Afghan Native Chicken(阿富汗本地鸡):0.000
- Iran Native Chicken(伊朗本地鸡):0.074
分析:
- 安义灰鸡 表现出最高的突变频率(0.500),表明该突变可能与其代谢或适应性相关。
- 云南鸡(0.167)、和田黑鸡(0.125) 和 西藏鸡(0.055) 的突变频率也较为显著,这可能与地理位置或环境适应性有关。
总结
该突变在多数原鸡、蛋鸡和肉鸡中并未表现出突变,表明这些品种未对该基因位点产生选择压力。而在部分肉蛋兼用鸡和地方品种(如安义灰鸡、鲁西斗鸡)中,突变频率较高,可能与其代谢需求、抗氧化压力或环境适应相关。
R语言
代码
创建数据框
chicken_data <- data.frame(
Breed = c(‘红原鸡’, ‘原鸡’, ‘越南原鸡’, ‘印度原鸡’, ‘马来原鸡’,
‘白色莱格霍恩鸡’, ‘阿劳卡纳蓝壳鸡’, ‘东乡蓝壳鸡’, ‘北京油鸡’,
‘康沃尔鸡’, ‘伊朗商用肉鸡’, ‘天府黑骨鸡’, ‘米易鸡’, ‘寿光鸡’, ‘大谷鸡’, ‘和田黑鸡’),
Group = c(‘原鸡’, ‘原鸡’, ‘原鸡’, ‘原鸡’, ‘原鸡’,
‘蛋鸡’, ‘蛋鸡’, ‘蛋鸡’, ‘肉蛋鸡’,
‘肉鸡’, ‘肉鸡’, ‘肉鸡’, ‘肉鸡’, ‘肉鸡’, ‘肉鸡’, ‘肉鸡’),
FPKM = c(0, 0.583, 0.056, 0.018, 0.093,
0, 0, 0, 0.182,
0, 0, 0.1, 0.1, 0, 0, 0.125)
)
进行单因素方差分析
anova_result <- aov(FPKM ~ Group, data = chicken_data)
查看ANOVA结果
summary(anova_result)
boxplot(FPKM ~ Group, data = chicken_data, main = “等位基因频率在不同鸡种中的分布”,
xlab = “鸡种分类”, ylab = “等位基因频率”, col = c(“lightblue”, “lightgreen”, “salmon”))
TukeyHSD(anova_result)
chicken_data <- read.csv(“等位基因频率_1.csv”) # 将 your_data.csv 替换为你的文件路径
chicken_data <- read.csv(“等位基因频率_1.csv”, fileEncoding = “UTF-8”)
head(chicken_data)
创建一个函数来对每个位点执行 ANOVA
perform_anova <- function(data, site) {
使用 ANOVA 进行分析
anova_result <- aov(data[[site]] ~ Group, data = data)
返回 ANOVA 结果的摘要
return(summary(anova_result))
}
列出所有位点的列名,假设这些列以 “位点” 开头
你需要根据实际数据中的位点列名调整这个列表
site_columns <- c(“Z_1”, “Z_2”, “Z_3”, “Z_4”, “Z_5”, “Z_6”, “Z_7”, “Z_8”, “Z_9”, “Z_10”, “Z_11”, “Z_12”, “Z_13”, “Z_14”, “Z_15”, “Z_16”, “Z_17”, “Z_18”, “Z_19”, “Z_20”, “Z_21”, “Z_22”, “Z_23”, “Z_24”, “Z_25”, “Z_26”, “Z_27”, “Z_28”, “Z_29”) # 根据实际位点列的名称调整
使用 lapply 对每个位点执行 ANOVA 并保存结果
anova_results <- lapply(site_columns, function(site) {
cat(“\n=== ANOVA for”, site, “===\n”)
print(perform_anova(chicken_data, site))
})
查看批量 ANOVA 的结果
anova_results
批量绘制箱线图
for (site in site_columns) {
boxplot(chicken_data[[site]] ~ Group, data = chicken_data,
main = paste(“等位基因频率在不同鸡种中的分布 -“, site),
xlab = “鸡种分类”, ylab = “等位基因频率”, col = c(“lightblue”, “lightgreen”, “salmon”))
}
批量绘制箱线图,每个图在一个新窗口中
for (site in site_columns) {
dev.new() # 每次生成一个新的图形窗口
boxplot(chicken_data[[site]] ~ Group, data = chicken_data,
main = paste(“等位基因频率在不同鸡种中的分布 -“, site),
xlab = “鸡种分类”, ylab = “等位基因频率”, col = c(“lightblue”, “lightgreen”, “salmon”))
}
missense_variant OPN4 rs314270903 6:3055021
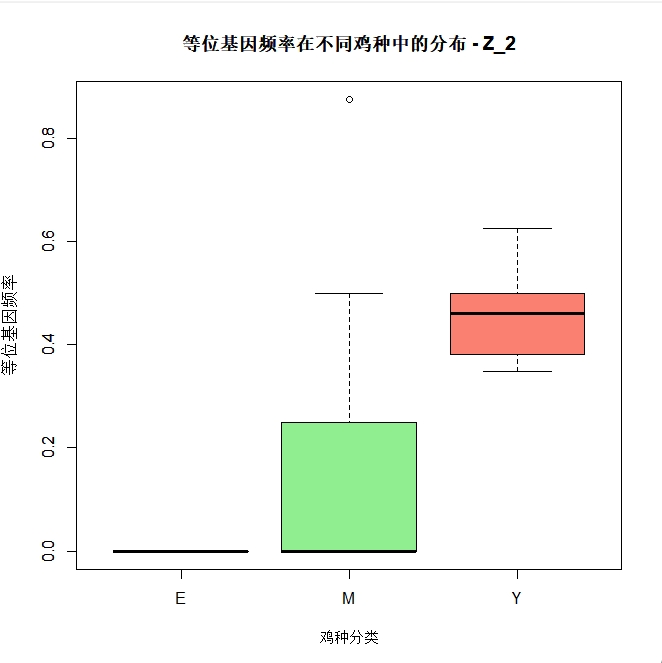
missense_variant MODERATE KK34 rs15709215 13:16332631
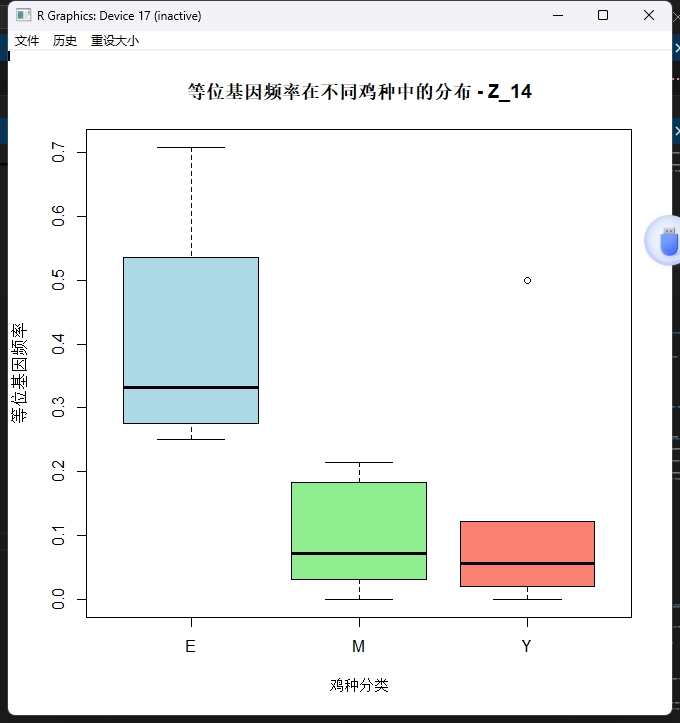
frameshift_variant HIGH KK34 novel 13:16334322
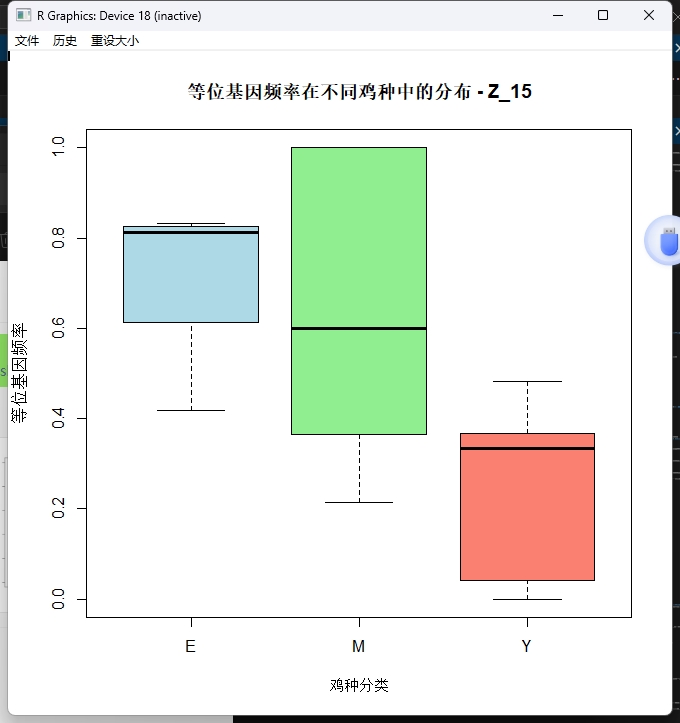
=== ANOVA for Z_1 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.03712 0.01856 0.847 0.451
Residuals 13 0.28488 0.02191
=== ANOVA for Z_2 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.4914 0.24570 4.029 0.0435 *
Residuals 13 0.7927 0.06098
Signif. codes: 0 ‘’ 0.001 ‘’ 0.01 ‘’ 0.05 ‘.’ 0.1 ‘ ’ 1
=== ANOVA for Z_3 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.03008 0.015042 1.957 0.181
Residuals 13 0.09991 0.007685
=== ANOVA for Z_4 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.2382 0.11909 3.011 0.0842 .
Residuals 13 0.5142 0.03955
Signif. codes: 0 ‘’ 0.001 ‘’ 0.01 ‘’ 0.05 ‘.’ 0.1 ‘ ’ 1
=== ANOVA for Z_5 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.04452 0.02226 2.269 0.143
Residuals 13 0.12753 0.00981
=== ANOVA for Z_6 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.01863 0.009314 0.973 0.404
Residuals 13 0.12441 0.009570
=== ANOVA for Z_7 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.0951 0.04755 1.627 0.234
Residuals 13 0.3799 0.02923
=== ANOVA for Z_8 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.00987 0.004934 0.5 0.618
Residuals 13 0.12827 0.009867
=== ANOVA for Z_9 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.1326 0.06628 0.827 0.465
Residuals 10 0.8018 0.08018
因为不存在,3个观察量被删除了
=== ANOVA for Z_10 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.0102 0.00511 0.141 0.87
Residuals 13 0.4712 0.03625
=== ANOVA for Z_11 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.0235 0.01176 0.198 0.822
Residuals 13 0.7704 0.05926
=== ANOVA for Z_12 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.01437 0.007187 0.709 0.51
Residuals 13 0.13178 0.010137
=== ANOVA for Z_13 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.2918 0.14592 2.823 0.0959 .
Residuals 13 0.6719 0.05168
Signif. codes: 0 ‘’ 0.001 ‘’ 0.01 ‘’ 0.05 ‘.’ 0.1 ‘ ’ 1
=== ANOVA for Z_14 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.2528 0.12638 4.701 0.0291 *
Residuals 13 0.3495 0.02688
Signif. codes: 0 ‘’ 0.001 ‘’ 0.01 ‘’ 0.05 ‘.’ 0.1 ‘ ’ 1
=== ANOVA for Z_15 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.6494 0.3247 4.084 0.042 *
Residuals 13 1.0335 0.0795
Signif. codes: 0 ‘’ 0.001 ‘’ 0.01 ‘’ 0.05 ‘.’ 0.1 ‘ ’ 1
=== ANOVA for Z_16 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.0428 0.02140 0.245 0.786
Residuals 13 1.1340 0.08723
=== ANOVA for Z_17 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.0554 0.02771 0.286 0.756
Residuals 13 1.2613 0.09702
=== ANOVA for Z_18 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.1327 0.06633 1.063 0.374
Residuals 13 0.8113 0.06241
=== ANOVA for Z_19 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.0791 0.03956 1.529 0.253
Residuals 13 0.3363 0.02587
=== ANOVA for Z_20 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0 0 NaN NaN
Residuals 13 0 0
=== ANOVA for Z_21 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.00513 0.002567 0.518 0.607
Residuals 13 0.06440 0.004954
=== ANOVA for Z_22 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.1143 0.05716 2.697 0.105
Residuals 13 0.2756 0.02120
=== ANOVA for Z_23 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.0033 0.00165 0.049 0.953
Residuals 13 0.4418 0.03398
=== ANOVA for Z_24 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.0050 0.00252 0.067 0.936
Residuals 13 0.4902 0.03771
=== ANOVA for Z_25 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.04859 0.02430 1.349 0.294
Residuals 13 0.23413 0.01801
=== ANOVA for Z_26 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.00300 0.00150 0.502 0.617
Residuals 13 0.03887 0.00299
=== ANOVA for Z_27 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.1292 0.06461 1.747 0.213
Residuals 13 0.4807 0.03698
=== ANOVA for Z_28 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.0824 0.04120 1.63 0.234
Residuals 13 0.3286 0.02528
=== ANOVA for Z_29 ===
Df Sum Sq Mean Sq F value Pr(>F)
Group 2 0.00621 0.003105 1.807 0.203
Residuals 13 0.02234 0.001719
这两个是 单因素方差分析(ANOVA) 的结果,分析了 Z_14 和 Z_15 位点在不同组别(例如鸡种分类)之间的差异。我们分别解释两个结果。
1. Z_14 位点的 ANOVA 结果
1 | Df Sum Sq Mean Sq F value Pr(>F) |
自由度 (Df):
- Group 的自由度为 2,表示有 3 个组(自由度 = 组数 - 1)。
- Residuals 的自由度为 13,表示剩余的数据的自由度。
平方和 (Sum Sq):
- Group 的平方和为 0.2528,表示组与组之间的变异。
- Residuals 的平方和为 0.3495,表示组内数据的变异。
均方 (Mean Sq):
- Group 的均方为 0.12638,是组间平方和除以自由度的结果。
- Residuals 的均方为 0.02688,是组内平方和除以自由度的结果。
F值 (F value):
- F 值为 4.701,表示组间变异相对于组内变异的比值。F 值越大,表示组间差异越大。
P 值 (Pr(>F)):
- P 值为 0.0291,低于 0.05,表示在 95% 置信水平下,Z_14 位点在不同组别之间的等位基因频率存在显著性差异。
2. Z_15 位点的 ANOVA 结果
1 | Df Sum Sq Mean Sq F value Pr(>F) |
自由度 (Df):
- Group 的自由度为 2,表示有 3 个组。
- Residuals 的自由度为 13,表示剩余的自由度。
平方和 (Sum Sq):
- Group 的平方和为 0.6494,表示组与组之间的变异。
- Residuals 的平方和为 1.0335,表示组内的变异。
均方 (Mean Sq):
- Group 的均方为 0.3247,是组间平方和除以自由度的结果。
- Residuals 的均方为 0.0795,是组内平方和除以自由度的结果。
F值 (F value):
- F 值为 4.084,表示组间变异相对于组内变异的比值。
P 值 (Pr(>F)):
- P 值为 0.042,低于 0.05,说明 Z_15 位点在不同组别中的等位基因频率差异是显著的。
总结:
- Z_14 和 Z_15 的 P 值都小于 0.05,分别为 0.0291 和 0.042,因此可以认为这两个位点在不同组别之间的等位基因频率差异显著。
- F 值表明在不同组别之间存在一定程度的变异。
- 这意味着 Z_14 和 Z_15 等位基因在不同鸡种分类中的频率分布存在统计学上的显著差异。
如果需要进一步分析,可以进行 Tukey’s HSD 检验,以确定具体哪些组之间存在显著差异。
Tukey’s HSD(Honestly Significant Difference)检验 是一种 事后检验(post-hoc test),用于在进行单因素方差分析(ANOVA)后,进一步比较各组之间的均值差异。这种检验可以帮助你确定具体哪些组别之间存在显著差异,而不仅仅是得出“有差异”这一结论。
为什么要使用 Tukey’s HSD 检验?
在 ANOVA 中,如果发现组间有显著差异(P 值小于 0.05),它只能告诉我们组之间存在差异,但无法告诉我们哪些具体组之间有差异。Tukey’s HSD 检验可以回答以下问题:
- 哪些组别之间存在显著的差异?
- 差异的大小是多少?
Tukey’s HSD 检验的原理
Tukey’s HSD 检验用于多重比较,它通过计算每组均值之间的差异,并根据统计学上的标准判断这些差异是否显著。其目的是控制整体的第一类错误率(即“假阳性”),避免因为多次比较而导致的错误显著性结论。
具体来说:
- Tukey’s HSD 检验计算了每两组之间的平均差异,并为这些差异赋予一个 P 值。如果 P 值小于 0.05,则认为这两组之间存在显著差异。
- 通过这种方法,Tukey’s HSD 检验能够在多个组别间进行配对比较。
Tukey’s HSD 检验的实施步骤
假设你已经进行了 ANOVA,并发现了显著性差异。你可以在 R 中使用 TukeyHSD() 函数来执行 Tukey’s HSD 检验。
1. 运行 Tukey’s HSD 检验
以 Z_14 为例,如果我们想要比较不同组别(例如鸡种分类)之间在 Z_14 位点上的等位基因频率差异,可以这样做:
1 | # 假设你已经运行了 ANOVA |
2. 输出解释
Tukey’s HSD 检验的输出会包含每对组之间的比较,输出如下:
1 | Tukey multiple comparisons of means |
- **
diff**:两组均值的差异。例如,B-A表示 B 组的均值减去 A 组的均值。 - **
lwr和upr**:差异的 95% 置信区间的下限和上限。 - **
p adj**:调整后的 P 值。如果 P 值小于 0.05,则认为这两组之间存在显著差异。
3. 如何解读 Tukey’s HSD 结果
例如,输出结果中:
- B-A 的
p adj值为 0.013276,小于 0.05,表明 B 组和 A 组之间存在显著差异。 - C-A 的
p adj值为 0.023641,也小于 0.05,说明 C 组和 A 组之间存在显著差异。 - C-B 的
p adj值为 0.058431,大于 0.05,说明 C 组和 B 组之间的差异不显著。
Tukey’s HSD 检验的优点
- 控制了多重比较的错误率。
- 给出了具体的组间差异及其显著性,提供了比 ANOVA 更详细的信息。
总结
- Tukey’s HSD 检验 是在 ANOVA 之后的一种事后检验,主要用于比较具体组别之间的差异。
- 它可以帮助你确定哪些组之间的差异是显著的。
- 你可以通过 R 的
TukeyHSD()函数轻松执行此检验并解释结果。
如果你已经通过 ANOVA 发现了显著差异,Tukey’s HSD 检验将帮助你更深入地理解哪些组之间存在显著性差异。
文件位置:E:\I\工作\Tbtools-正选择
等位基因频率_1.csv
6 7572603 C/T T 0.173 missense_variant MODERATE LRRTM3 rs315775469 6:7561370 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(3):0.000
Gallus_gallus_gallus(6):0.083
Gallus_gallus_jabouillei(27):0.019
Gallus_gallus_murghi(55):0.027
Gallus_gallus_spadiceus(42):0.131
Indonesia_Native_Chicken(34):0.426
Thailand_Native_Chicken(6):0.083
Vietnam_Native_Chicken(7):0.214
Wenchang_Chicken(1):0.000
Yunnan_Chicken(11):0.136
Xishuangbanna_Game_Chicken(10):0.400
Nixi_Chicken(12):0.083
Dulong_Chicken(7):0.286
Daweishan_Mini_Chicken(7):0.429
Guangxi_Chicken(6):0.083
Guangzhou_Chicken(4):0.125
Jiangxi_Silkies(20):0.200
Anyi_Gray_Chicken(5):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.200
Shimian_Caoke_Chicken(2):0.250
Jiuyuan_Black-bone_Chicken(5):0.400
Jinyang_Silky_Chicken(6):0.083
Emei_Black_Chicken(3):0.167
Pengxian_Yellow_Chicken(6):0.083
Muchuan_Black-bone_Chicken(5):0.200
Miyi_Chicken(5):0.300
YuanBao_Chicken(22):0.000
Langshan_Chicken(10):0.300
Luxi_Game_Chicken(9):0.000
Shouguang_Chicken(7):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.125
Beijing_You_Chicken(11):0.000
Dagu_Chicken(8):0.000
Xinjiang_Native_Chicken(5):0.500
Hetian_Black_Chicken(8):0.062
Southern_Xinjiang_Game_Chicken(8):0.000
Turpan_Game_Chicken(8):0.188
Tibetan_Chicken(124):0.294
Araucana_Blue-eggshell_Chicken(6):0.750
Sri_Lanka_Native_Chicken(7):0.286
Bengal_Native_Chicken(15):0.067
India_Native_Chicken(45):0.178
Pakistan_Native_Chicken(37):0.149
Afghan_Native_Chicken(11):0.091
Iran_Native_Chicken(179):0.193
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(13):0.000
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
3 40896529 G/A A 0.062 missense_variant MODERATE FAM120B rs739071999 3:40489696 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(4):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(27):0.000
Gallus_gallus_murghi(58):0.017
Gallus_gallus_spadiceus(41):0.122
Indonesia_Native_Chicken(36):0.000
Thailand_Native_Chicken(6):0.000
Vietnam_Native_Chicken(5):0.000
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.167
Xishuangbanna_Game_Chicken(10):0.100
Nixi_Chicken(10):0.000
Dulong_Chicken(6):0.083
Daweishan_Mini_Chicken(8):0.000
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(3):0.000
Jiangxi_Silkies(20):0.000
Anyi_Gray_Chicken(5):0.400
Dongxiang_Blue-eggshell_Chicken(5):0.000
Tianfu_Black-bone_Chicken(5):0.200
Shimian_Caoke_Chicken(4):0.125
Jiuyuan_Black-bone_Chicken(5):0.300
Jinyang_Silky_Chicken(6):0.333
Emei_Black_Chicken(5):0.000
Pengxian_Yellow_Chicken(6):0.000
Muchuan_Black-bone_Chicken(5):0.300
Miyi_Chicken(5):0.000
YuanBao_Chicken(21):0.262
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(9):0.056
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(7):0.143
Beijing_You_Chicken(11):0.000
Dagu_Chicken(8):0.125
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(8):0.000
Southern_Xinjiang_Game_Chicken(8):0.000
Turpan_Game_Chicken(8):0.000
Tibetan_Chicken(137):0.095
Araucana_Blue-eggshell_Chicken(6):0.083
Sri_Lanka_Native_Chicken(7):0.071
Bengal_Native_Chicken(14):0.000
India_Native_Chicken(48):0.010
Pakistan_Native_Chicken(36):0.083
Afghan_Native_Chicken(11):0.045
Iran_Native_Chicken(181):0.052
Iran_Commercial_Broiler(3):0.000
White_Leghorn_Chicken(13):0.115
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
3 40908683 T/A A 0.086 missense_variant MODERATE FAM120B rs312816441 3:40501840 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(4):0.125
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(26):0.115
Gallus_gallus_murghi(60):0.033
Gallus_gallus_spadiceus(41):0.195
Indonesia_Native_Chicken(36):0.056
Thailand_Native_Chicken(6):0.000
Vietnam_Native_Chicken(7):0.143
Wenchang_Chicken(1):0.000
Yunnan_Chicken(11):0.227
Xishuangbanna_Game_Chicken(10):0.200
Nixi_Chicken(12):0.000
Dulong_Chicken(7):0.071
Daweishan_Mini_Chicken(8):0.250
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(3):0.000
Jiangxi_Silkies(20):0.100
Anyi_Gray_Chicken(5):0.500
Dongxiang_Blue-eggshell_Chicken(6):0.083
Tianfu_Black-bone_Chicken(4):0.125
Shimian_Caoke_Chicken(4):0.500
Jiuyuan_Black-bone_Chicken(4):0.125
Jinyang_Silky_Chicken(6):0.333
Emei_Black_Chicken(5):0.000
Pengxian_Yellow_Chicken(6):0.000
Muchuan_Black-bone_Chicken(4):0.000
Miyi_Chicken(4):0.000
YuanBao_Chicken(24):0.208
Langshan_Chicken(10):0.250
Luxi_Game_Chicken(9):0.389
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.000
Beijing_You_Chicken(11):0.136
Dagu_Chicken(8):0.125
Xinjiang_Native_Chicken(6):0.250
Hetian_Black_Chicken(8):0.000
Southern_Xinjiang_Game_Chicken(8):0.312
Turpan_Game_Chicken(8):0.250
Tibetan_Chicken(135):0.104
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(7):0.000
Bengal_Native_Chicken(15):0.000
India_Native_Chicken(48):0.042
Pakistan_Native_Chicken(37):0.068
Afghan_Native_Chicken(11):0.045
Iran_Native_Chicken(181):0.022
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(13):0.000
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
3 40911707 C/T C 0.445 missense_variant MODERATE FAM120B rs313401617 3:40504851 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(3):0.000
Gallus_gallus_gallus(6):0.500
Gallus_gallus_jabouillei(27):0.667
Gallus_gallus_murghi(42):0.905
Gallus_gallus_spadiceus(44):0.614
Indonesia_Native_Chicken(36):0.528
Thailand_Native_Chicken(6):0.667
Vietnam_Native_Chicken(7):0.786
Wenchang_Chicken(1):0.500
Yunnan_Chicken(12):0.708
Xishuangbanna_Game_Chicken(10):0.450
Nixi_Chicken(11):0.500
Dulong_Chicken(7):0.714
Daweishan_Mini_Chicken(8):0.375
Guangxi_Chicken(6):0.833
Guangzhou_Chicken(2):0.500
Jiangxi_Silkies(20):0.300
Anyi_Gray_Chicken(5):0.500
Dongxiang_Blue-eggshell_Chicken(5):0.200
Tianfu_Black-bone_Chicken(5):0.600
Shimian_Caoke_Chicken(4):0.625
Jiuyuan_Black-bone_Chicken(5):0.500
Jinyang_Silky_Chicken(6):0.750
Emei_Black_Chicken(5):0.500
Pengxian_Yellow_Chicken(6):0.167
Muchuan_Black-bone_Chicken(5):0.400
Miyi_Chicken(5):0.400
YuanBao_Chicken(24):0.500
Langshan_Chicken(10):0.250
Luxi_Game_Chicken(9):0.667
Shouguang_Chicken(7):0.000
Gushi_Chicken(8):0.375
Bian_Chicken(8):0.312
Beijing_You_Chicken(11):0.409
Dagu_Chicken(8):0.562
Xinjiang_Native_Chicken(6):0.917
Hetian_Black_Chicken(8):0.562
Southern_Xinjiang_Game_Chicken(8):0.875
Turpan_Game_Chicken(8):0.438
Tibetan_Chicken(132):0.803
Araucana_Blue-eggshell_Chicken(6):0.583
Sri_Lanka_Native_Chicken(7):0.429
Bengal_Native_Chicken(15):0.867
India_Native_Chicken(40):0.525
Pakistan_Native_Chicken(37):0.189
Afghan_Native_Chicken(10):0.550
Iran_Native_Chicken(179):0.453
Iran_Commercial_Broiler(3):0.167
White_Leghorn_Chicken(13):0.231
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.500
White_Plymouth_Rock_Chicken(1):0.500
3 40911835 C/A A 0.112 missense_variant MODERATE FAM120B rs739364536 3:40504979 Show Show Gbrowse
3 40911836 T/C C 0.112 missense_variant MODERATE FAM120B rs733162459 3:40504980 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(3):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(27):0.000
Gallus_gallus_murghi(57):0.000
Gallus_gallus_spadiceus(42):0.048
Indonesia_Native_Chicken(36):0.153
Thailand_Native_Chicken(6):0.000
Vietnam_Native_Chicken(7):0.000
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.042
Xishuangbanna_Game_Chicken(10):0.000
Nixi_Chicken(12):0.000
Dulong_Chicken(7):0.000
Daweishan_Mini_Chicken(8):0.000
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(4):0.000
Jiangxi_Silkies(20):0.025
Anyi_Gray_Chicken(5):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.100
Shimian_Caoke_Chicken(4):0.000
Jiuyuan_Black-bone_Chicken(5):0.000
Jinyang_Silky_Chicken(6):0.000
Emei_Black_Chicken(6):0.000
Pengxian_Yellow_Chicken(6):0.000
Muchuan_Black-bone_Chicken(5):0.000
Miyi_Chicken(5):0.000
YuanBao_Chicken(24):0.000
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(9):0.056
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.000
Beijing_You_Chicken(11):0.000
Dagu_Chicken(8):0.000
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(8):0.062
Southern_Xinjiang_Game_Chicken(8):0.125
Turpan_Game_Chicken(8):0.000
Tibetan_Chicken(139):0.047
Araucana_Blue-eggshell_Chicken(6):0.333
Sri_Lanka_Native_Chicken(7):0.143
Bengal_Native_Chicken(15):0.133
India_Native_Chicken(45):0.167
Pakistan_Native_Chicken(37):0.338
Afghan_Native_Chicken(11):0.182
Iran_Native_Chicken(180):0.250
Iran_Commercial_Broiler(4):0.125
White_Leghorn_Chicken(13):0.692
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
Indel
3 40911942 G/A A 0.111 missense_variant MODERATE FAM120B rs314142939 3:40505086 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(4):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(27):0.000
Gallus_gallus_murghi(56):0.009
Gallus_gallus_spadiceus(43):0.058
Indonesia_Native_Chicken(36):0.167
Thailand_Native_Chicken(6):0.000
Vietnam_Native_Chicken(7):0.000
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.083
Xishuangbanna_Game_Chicken(10):0.000
Nixi_Chicken(12):0.000
Dulong_Chicken(6):0.000
Daweishan_Mini_Chicken(8):0.000
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(3):0.000
Jiangxi_Silkies(20):0.025
Anyi_Gray_Chicken(5):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.100
Shimian_Caoke_Chicken(4):0.000
Jiuyuan_Black-bone_Chicken(5):0.000
Jinyang_Silky_Chicken(6):0.000
Emei_Black_Chicken(6):0.000
Pengxian_Yellow_Chicken(6):0.000
Muchuan_Black-bone_Chicken(5):0.000
Miyi_Chicken(5):0.000
YuanBao_Chicken(24):0.000
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(9):0.167
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.000
Beijing_You_Chicken(11):0.000
Dagu_Chicken(8):0.000
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(8):0.062
Southern_Xinjiang_Game_Chicken(8):0.062
Turpan_Game_Chicken(8):0.000
Tibetan_Chicken(138):0.043
Araucana_Blue-eggshell_Chicken(6):0.333
Sri_Lanka_Native_Chicken(5):0.100
Bengal_Native_Chicken(13):0.115
India_Native_Chicken(45):0.189
Pakistan_Native_Chicken(36):0.333
Afghan_Native_Chicken(11):0.136
Iran_Native_Chicken(181):0.235
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(13):0.692
Cornish_Chicken(1):0.500
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
3 40912052 G/A A 0.179 missense_variant MODERATE FAM120B rs316660578 3:40505196 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(4):0.125
Gallus_gallus_gallus(6):0.667
Gallus_gallus_jabouillei(27):0.111
Gallus_gallus_murghi(55):0.082
Gallus_gallus_spadiceus(41):0.085
Indonesia_Native_Chicken(36):0.208
Thailand_Native_Chicken(6):0.000
Vietnam_Native_Chicken(6):0.167
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.042
Xishuangbanna_Game_Chicken(10):0.100
Nixi_Chicken(11):0.000
Dulong_Chicken(7):0.000
Daweishan_Mini_Chicken(8):0.062
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(4):0.000
Jiangxi_Silkies(20):0.025
Anyi_Gray_Chicken(5):0.000
Dongxiang_Blue-eggshell_Chicken(5):0.000
Tianfu_Black-bone_Chicken(5):0.100
Shimian_Caoke_Chicken(4):0.250
Jiuyuan_Black-bone_Chicken(5):0.100
Jinyang_Silky_Chicken(6):0.083
Emei_Black_Chicken(6):0.000
Pengxian_Yellow_Chicken(6):0.000
Muchuan_Black-bone_Chicken(5):0.100
Miyi_Chicken(5):0.000
YuanBao_Chicken(24):0.000
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(9):0.111
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.250
Beijing_You_Chicken(11):0.136
Dagu_Chicken(8):0.000
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(8):0.125
Southern_Xinjiang_Game_Chicken(8):0.125
Turpan_Game_Chicken(8):0.000
Tibetan_Chicken(136):0.143
Araucana_Blue-eggshell_Chicken(6):0.333
Sri_Lanka_Native_Chicken(7):0.214
Bengal_Native_Chicken(15):0.267
India_Native_Chicken(41):0.207
Pakistan_Native_Chicken(36):0.361
Afghan_Native_Chicken(9):0.222
Iran_Native_Chicken(180):0.325
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(12):0.917
Cornish_Chicken(1):0.500
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
GWAS
Chr Position Consequence type Gene symbol Variation ID Position of GRCg7b Traits P-value PMID Visualization
3 40857192 intergenic NONE,FAM120B GGaluGA218351 3:40450360 Bursa of Fabricius weight 7.07E-06 26853217 Gbrowse
15 7064785 G/A G 0.080 missense_variant MODERATE MMAB novel 15:6784409 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(2):1.000
Gallus_gallus_gallus(6):1.000
Gallus_gallus_jabouillei(26):1.000
Gallus_gallus_murghi(41):0.927
Gallus_gallus_spadiceus(41):0.963
Indonesia_Native_Chicken(34):0.750
Thailand_Native_Chicken(6):0.583
Vietnam_Native_Chicken(6):1.000
Wenchang_Chicken(1):1.000
Yunnan_Chicken(12):1.000
Xishuangbanna_Game_Chicken(10):0.900
Nixi_Chicken(11):1.000
Dulong_Chicken(7):1.000
Daweishan_Mini_Chicken(8):0.375
Guangxi_Chicken(5):1.000
Guangzhou_Chicken(1):1.000
Jiangxi_Silkies(20):0.925
Anyi_Gray_Chicken(3):1.000
Dongxiang_Blue-eggshell_Chicken(5):1.000
Tianfu_Black-bone_Chicken(5):1.000
Shimian_Caoke_Chicken(4):1.000
Jiuyuan_Black-bone_Chicken(5):0.900
Jinyang_Silky_Chicken(6):1.000
Emei_Black_Chicken(6):1.000
Pengxian_Yellow_Chicken(6):1.000
Muchuan_Black-bone_Chicken(5):1.000
Miyi_Chicken(5):1.000
YuanBao_Chicken(23):1.000
Langshan_Chicken(9):1.000
Luxi_Game_Chicken(9):1.000
Shouguang_Chicken(8):0.812
Gushi_Chicken(8):1.000
Bian_Chicken(6):1.000
Beijing_You_Chicken(11):1.000
Dagu_Chicken(7):1.000
Xinjiang_Native_Chicken(6):0.917
Hetian_Black_Chicken(8):0.812
Southern_Xinjiang_Game_Chicken(8):0.812
Turpan_Game_Chicken(8):0.938
Tibetan_Chicken(140):0.989
Araucana_Blue-eggshell_Chicken(6):1.000
Sri_Lanka_Native_Chicken(6):1.000
Bengal_Native_Chicken(14):0.857
India_Native_Chicken(41):0.720
Pakistan_Native_Chicken(35):0.843
Afghan_Native_Chicken(11):0.773
Iran_Native_Chicken(180):0.914
Iran_Commercial_Broiler(4):1.000
White_Leghorn_Chicken(13):1.000
Cornish_Chicken(1):1.000
Rhode_Island_Red_Chicken(1):1.000
White_Plymouth_Rock_Chicken(1):1.000
5 7064823 T/C C 0.218 missense_variant MODERATE MMAB novel 15:6784447 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(2):0.000
Gallus_gallus_gallus(6):0.167
Gallus_gallus_jabouillei(27):0.148
Gallus_gallus_murghi(42):0.738
Gallus_gallus_spadiceus(43):0.186
Indonesia_Native_Chicken(36):0.042
Thailand_Native_Chicken(6):0.167
Vietnam_Native_Chicken(7):0.000
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.167
Xishuangbanna_Game_Chicken(10):0.250
Nixi_Chicken(12):0.125
Dulong_Chicken(7):0.000
Daweishan_Mini_Chicken(8):0.062
Guangxi_Chicken(6):0.083
Guangzhou_Chicken(2):0.000
Jiangxi_Silkies(20):0.150
Anyi_Gray_Chicken(5):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.100
Shimian_Caoke_Chicken(4):0.000
Jiuyuan_Black-bone_Chicken(5):0.100
Jinyang_Silky_Chicken(6):0.083
Emei_Black_Chicken(6):0.000
Pengxian_Yellow_Chicken(6):0.167
Muchuan_Black-bone_Chicken(5):0.100
Miyi_Chicken(5):0.000
YuanBao_Chicken(23):0.087
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(8):0.188
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.250
Bian_Chicken(8):0.000
Beijing_You_Chicken(11):0.091
Dagu_Chicken(8):0.188
Xinjiang_Native_Chicken(6):0.083
Hetian_Black_Chicken(8):0.062
Southern_Xinjiang_Game_Chicken(8):0.062
Turpan_Game_Chicken(8):0.000
Tibetan_Chicken(143):0.308
Araucana_Blue-eggshell_Chicken(6):0.250
Sri_Lanka_Native_Chicken(7):0.071
Bengal_Native_Chicken(12):0.125
India_Native_Chicken(48):0.167
Pakistan_Native_Chicken(37):0.216
Afghan_Native_Chicken(11):0.273
Iran_Native_Chicken(182):0.255
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(12):0.750
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
15 7065461 C/T T 0.287 missense_variant MODERATE MMAB rs14706233 15:6785085 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(3):0.333
Gallus_gallus_gallus(6):0.167
Gallus_gallus_jabouillei(25):0.720
Gallus_gallus_murghi(44):0.466
Gallus_gallus_spadiceus(41):0.195
Indonesia_Native_Chicken(36):0.111
Thailand_Native_Chicken(5):0.200
Vietnam_Native_Chicken(7):0.429
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.542
Xishuangbanna_Game_Chicken(10):0.250
Nixi_Chicken(11):0.500
Dulong_Chicken(6):0.417
Daweishan_Mini_Chicken(8):0.000
Guangxi_Chicken(6):0.250
Guangzhou_Chicken(5):0.400
Jiangxi_Silkies(20):0.075
Anyi_Gray_Chicken(5):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.083
Tianfu_Black-bone_Chicken(5):0.300
Shimian_Caoke_Chicken(4):0.250
Jiuyuan_Black-bone_Chicken(5):0.300
Jinyang_Silky_Chicken(6):0.750
Emei_Black_Chicken(6):0.167
Pengxian_Yellow_Chicken(6):0.250
Muchuan_Black-bone_Chicken(5):0.100
Miyi_Chicken(5):0.300
YuanBao_Chicken(24):0.021
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(9):0.222
Shouguang_Chicken(8):0.062
Gushi_Chicken(8):0.562
Bian_Chicken(7):0.071
Beijing_You_Chicken(11):0.091
Dagu_Chicken(7):0.071
Xinjiang_Native_Chicken(6):0.083
Hetian_Black_Chicken(8):0.062
Southern_Xinjiang_Game_Chicken(8):0.062
Turpan_Game_Chicken(8):0.000
Tibetan_Chicken(141):0.404
Araucana_Blue-eggshell_Chicken(6):0.250
Sri_Lanka_Native_Chicken(7):0.071
Bengal_Native_Chicken(12):0.375
India_Native_Chicken(49):0.204
Pakistan_Native_Chicken(36):0.319
Afghan_Native_Chicken(10):0.300
Iran_Native_Chicken(180):0.289
Iran_Commercial_Broiler(4):0.250
White_Leghorn_Chicken(13):0.423
Cornish_Chicken(1):0.500
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
2 129298142 G/A A 0.075 missense_variant MODERATE SLC25A32 rs315233683 2:129001345 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(4):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(27):0.093
Gallus_gallus_murghi(60):0.000
Gallus_gallus_spadiceus(43):0.093
Indonesia_Native_Chicken(36):0.014
Thailand_Native_Chicken(6):0.000
Vietnam_Native_Chicken(7):0.214
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.000
Xishuangbanna_Game_Chicken(10):0.050
Nixi_Chicken(11):0.000
Dulong_Chicken(7):0.071
Daweishan_Mini_Chicken(8):0.188
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(4):0.000
Jiangxi_Silkies(20):0.150
Anyi_Gray_Chicken(5):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.000
Shimian_Caoke_Chicken(3):0.500
Jiuyuan_Black-bone_Chicken(5):0.100
Jinyang_Silky_Chicken(6):0.083
Emei_Black_Chicken(6):0.000
Pengxian_Yellow_Chicken(6):0.167
Muchuan_Black-bone_Chicken(5):0.200
Miyi_Chicken(5):0.000
YuanBao_Chicken(23):0.304
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(9):0.056
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(7):0.143
Beijing_You_Chicken(11):0.318
Dagu_Chicken(8):0.000
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(8):0.188
Southern_Xinjiang_Game_Chicken(8):0.188
Turpan_Game_Chicken(8):0.000
Tibetan_Chicken(138):0.033
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(7):0.214
Bengal_Native_Chicken(14):0.071
India_Native_Chicken(45):0.011
Pakistan_Native_Chicken(37):0.014
Afghan_Native_Chicken(11):0.000
Iran_Native_Chicken(179):0.123
Iran_Commercial_Broiler(4):0.500
White_Leghorn_Chicken(13):0.000
Cornish_Chicken(1):1.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):1.000
Indel
2 129306575 C/T C 0.259 missense_variant MODERATE SLC25A32 novel 2:129009787 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(2):1.000
Gallus_gallus_gallus(6):1.000
Gallus_gallus_jabouillei(27):0.889
Gallus_gallus_murghi(44):0.841
Gallus_gallus_spadiceus(40):0.650
Indonesia_Native_Chicken(34):0.779
Thailand_Native_Chicken(5):0.900
Vietnam_Native_Chicken(7):0.929
Wenchang_Chicken(1):0.500
Yunnan_Chicken(12):0.542
Xishuangbanna_Game_Chicken(10):0.850
Nixi_Chicken(10):0.450
Dulong_Chicken(6):0.333
Daweishan_Mini_Chicken(8):1.000
Guangxi_Chicken(6):0.750
Guangzhou_Chicken(4):0.750
Jiangxi_Silkies(19):0.947
Anyi_Gray_Chicken(5):0.400
Dongxiang_Blue-eggshell_Chicken(6):0.583
Tianfu_Black-bone_Chicken(5):0.600
Shimian_Caoke_Chicken(4):0.625
Jiuyuan_Black-bone_Chicken(5):0.700
Jinyang_Silky_Chicken(6):0.500
Emei_Black_Chicken(6):0.667
Pengxian_Yellow_Chicken(6):0.833
Muchuan_Black-bone_Chicken(5):0.500
Miyi_Chicken(5):0.800
YuanBao_Chicken(23):0.435
Langshan_Chicken(9):1.000
Luxi_Game_Chicken(9):0.611
Shouguang_Chicken(8):0.938
Gushi_Chicken(7):0.857
Bian_Chicken(7):0.429
Beijing_You_Chicken(11):1.000
Dagu_Chicken(6):0.583
Xinjiang_Native_Chicken(6):1.000
Hetian_Black_Chicken(7):0.643
Southern_Xinjiang_Game_Chicken(8):0.938
Turpan_Game_Chicken(8):0.875
Tibetan_Chicken(136):0.713
Araucana_Blue-eggshell_Chicken(6):0.917
Sri_Lanka_Native_Chicken(7):0.786
Bengal_Native_Chicken(14):0.929
India_Native_Chicken(39):0.821
Pakistan_Native_Chicken(34):0.647
Afghan_Native_Chicken(10):0.900
Iran_Native_Chicken(177):0.734
Iran_Commercial_Broiler(3):1.000
White_Leghorn_Chicken(13):0.231
Cornish_Chicken(1):1.000
Rhode_Island_Red_Chicken(1):1.000
White_Plymouth_Rock_Chicken(1):1.000
Indel
继续研究MHC基因家族
16 2594913 C/T T 0.141 missense_variant MODERATE BF1 novel 16:2215360 Show Show Gbrowse
Gallus_gallus_bankiva(2):0.000
Gallus_gallus_gallus(5):0.300
Gallus_gallus_jabouillei(27):0.185
Gallus_gallus_murghi(44):0.023
Gallus_gallus_spadiceus(39):0.038
Indonesia_Native_Chicken(36):0.111
Thailand_Native_Chicken(6):0.000
Vietnam_Native_Chicken(6):0.167
Wenchang_Chicken(1):0.500
Yunnan_Chicken(12):0.083
Xishuangbanna_Game_Chicken(10):0.050
Nixi_Chicken(8):0.000
Dulong_Chicken(7):0.000
Daweishan_Mini_Chicken(8):0.188
Guangxi_Chicken(5):0.400
Guangzhou_Chicken(6):0.250
Jiangxi_Silkies(20):0.300
Anyi_Gray_Chicken(2):0.250
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.300
Shimian_Caoke_Chicken(4):0.125
Jiuyuan_Black-bone_Chicken(5):0.400
Jinyang_Silky_Chicken(6):0.333
Emei_Black_Chicken(6):0.250
Pengxian_Yellow_Chicken(6):0.250
Muchuan_Black-bone_Chicken(5):0.400
Miyi_Chicken(5):0.100
YuanBao_Chicken(24):0.562
Langshan_Chicken(9):0.000
Luxi_Game_Chicken(9):0.056
Shouguang_Chicken(7):0.286
Gushi_Chicken(8):0.000
Bian_Chicken(5):0.200
Beijing_You_Chicken(10):0.600
Dagu_Chicken(7):0.000
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(8):0.188
Southern_Xinjiang_Game_Chicken(8):0.125
Turpan_Game_Chicken(8):0.125
Tibetan_Chicken(144):0.233
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(6):0.000
Bengal_Native_Chicken(12):0.000
India_Native_Chicken(46):0.022
Pakistan_Native_Chicken(34):0.074
Afghan_Native_Chicken(9):0.056
Iran_Native_Chicken(171):0.085
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(9):0.167
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
这段数据展示了一种位于 16号染色体、位置为 2594913 的 C/T 突变,属于 missense_variant 类型(即错义突变),其变异影响的是 BF1 基因,并且具有 MODERATE(中等)的影响等级。该突变被标记为 novel(新发现),并且具体位置为 16:2215360。
以下信息展示了不同鸡种在此位点上的等位基因频率(即 C 或 T 等位基因的出现比例)。这些鸡种的名称后面括号内的数字表示样本数,后面的小数表示该等位基因在群体中的频率。例如:
- Gallus_gallus_bankiva 群体中该等位基因的频率为 0.000,表示该群体中没有发现这个突变。
- Gallus_gallus_gallus 群体中的频率为 0.300,表示 30% 的个体带有该突变。
- Wenchang_Chicken 群体中频率为 0.500,表示一半的个体带有该突变。
这些等位基因频率数据可以用来推测不同鸡种中的遗传变异模式,尤其是不同地区或物种间的差异。例如,北京油鸡(Beijing_You_Chicken)中的突变频率较高(0.600),而某些群体(如 印度土鸡(India_Native_Chicken))的频率则非常低(0.022)。
这类分析可以帮助研究人员理解不同鸡种的遗传多样性,以及特定基因变异对鸡种表型(例如肉质、抗病性等)的潜在影响。
16 2606984 TC/T T 0.049 frameshift_variant HIGH BF2 novel 16:2227435 Show Show Gbrowse
Breed (number): frequence
Gallus_gallus_bankiva(3):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(26):0.231
Gallus_gallus_murghi(42):0.036
Gallus_gallus_spadiceus(38):0.066
Indonesia_Native_Chicken(35):0.071
Thailand_Native_Chicken(6):0.000
Vietnam_Native_Chicken(7):0.000
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.000
Xishuangbanna_Game_Chicken(10):0.000
Nixi_Chicken(12):0.042
Dulong_Chicken(6):0.083
Daweishan_Mini_Chicken(7):0.000
Guangxi_Chicken(6):0.083
Guangzhou_Chicken(6):0.083
Jiangxi_Silkies(20):0.025
Anyi_Gray_Chicken(4):0.000
Dongxiang_Blue-eggshell_Chicken(5):0.000
Tianfu_Black-bone_Chicken(5):0.000
Shimian_Caoke_Chicken(4):0.000
Jiuyuan_Black-bone_Chicken(5):0.200
Jinyang_Silky_Chicken(6):0.083
Emei_Black_Chicken(6):0.083
Pengxian_Yellow_Chicken(6):0.167
Muchuan_Black-bone_Chicken(5):0.000
Miyi_Chicken(5):0.200
YuanBao_Chicken(21):0.000
Langshan_Chicken(9):0.000
Luxi_Game_Chicken(9):0.111
Shouguang_Chicken(8):0.312
Gushi_Chicken(6):0.000
Bian_Chicken(7):0.000
Beijing_You_Chicken(11):0.000
Dagu_Chicken(8):0.000
Xinjiang_Native_Chicken(6):0.083
Hetian_Black_Chicken(8):0.000
Southern_Xinjiang_Game_Chicken(8):0.062
Turpan_Game_Chicken(8):0.125
Tibetan_Chicken(143):0.024
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(6):0.167
Bengal_Native_Chicken(14):0.000
India_Native_Chicken(45):0.033
Pakistan_Native_Chicken(34):0.059
Afghan_Native_Chicken(10):0.000
Iran_Native_Chicken(172):0.049
Iran_Commercial_Broiler(2):0.000
White_Leghorn_Chicken(13):0.038
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
根据你提供的突变频率数据,鸡种可以分为高频突变群体和低频突变群体。以下是这些群体及其对应的鸡种名称:
高频突变群体:
这些鸡种在此位点的突变频率较高,可能有助于研究该突变的功能和影响:
- Gallus_gallus_jabouillei(斑竹鸡):突变频率为 0.231
- Shouguang_Chicken(寿光鸡):突变频率为 0.312
- Jiuyuan_Black-bone_Chicken(九元黑骨鸡):突变频率为 0.200
- Miyi_Chicken(米易鸡):突变频率为 0.200
- Pengxian_Yellow_Chicken(彭县黄鸡):突变频率为 0.167
- Sri_Lanka_Native_Chicken(斯里兰卡土鸡):突变频率为 0.167
- Turpan_Game_Chicken(吐鲁番斗鸡):突变频率为 0.125
- Luxi_Game_Chicken(鲁西斗鸡):突变频率为 0.111
低频突变群体:
这些鸡种在此位点的突变频率极低或为零,可能有助于研究为什么这些鸡种没有或很少发生这种突变:
- Gallus_gallus_bankiva(野生原鸡):突变频率为 0.000
- Gallus_gallus_gallus(家鸡):突变频率为 0.000
- Wenchang_Chicken(文昌鸡):突变频率为 0.000
- Thailand_Native_Chicken(泰国土鸡):突变频率为 0.000
- Vietnam_Native_Chicken(越南土鸡):突变频率为 0.000
- Daweishan_Mini_Chicken(大围山小鸡):突变频率为 0.000
- Dongxiang_Blue-eggshell_Chicken(东乡蓝壳蛋鸡):突变频率为 0.000
- Tianfu_Black-bone_Chicken(天府黑骨鸡):突变频率为 0.000
- YuanBao_Chicken(元宝鸡):突变频率为 0.000
- Bian_Chicken(汴鸡):突变频率为 0.000
- Beijing_You_Chicken(北京油鸡):突变频率为 0.000
- Dagu_Chicken(大骨鸡):突变频率为 0.000
这些分类可以帮助你在后续的研究中重点关注不同鸡种的突变特征,并探讨突变与鸡种特性的相关性。
BLB1的GWAS
Chr Position Consequence type Gene symbol Variation ID Position of GRCg7b Traits P-value PMID Visualization
16 2567380 upstream;downstream BLB1,TAPBP - 16:2187818 Spleen weight 3.37E-10 35225379 Gbrowse
这段数据展示了一项 BLB1 基因 的基因组广泛关联研究(GWAS,Genome-Wide Association Study)结果,特别针对 脾脏重量(Spleen weight) 这一性状。以下是对各字段的解释:
字段解释:
- Chr(染色体): 表示基因所在的染色体号。这里是 16号染色体。
- Position(位置): 表示突变所在的具体位置,数据中位置为 2567380,指的是这个基因组上的特定位点。
- Consequence type(变异结果类型): 这里显示了突变的影响位置和类型。此处列出的是 upstream(上游) 和 downstream(下游),说明突变发生在 BLB1 和 TAPBP 基因的上游或下游区域,而不是在编码区,可能影响基因的调控。
- Gene symbol(基因符号): 这里列出了与该位点相关的基因,包括 BLB1 和 TAPBP。BLB1 是与免疫系统相关的基因,通常与抗原呈递和免疫反应相关,而 TAPBP 参与抗原加工。
- Variation ID(变异ID): 在这条记录中变异ID缺失,通常会列出具体变异的编号。
- Position of GRCg7b(GRCg7b参考基因组的位置): 这个字段提供了 GRCg7b 参考基因组上的突变位置,具体位置为 16:2187818,相对于 GRCg7b 标准的参考位置。
- Traits(性状): 这里表示研究分析的目标性状,即 脾脏重量(Spleen weight),这是研究中的目标性状,突变可能与脾脏重量的变化有关。
- P-value(P值): P值是统计学中的一个重要指标,用来衡量研究结果是否显著。这里的 P值为 3.37E-10,表示该位点与脾脏重量的关联非常显著(P值越低,结果越显著)。
- PMID: 这是文献的 PubMed ID(35225379),可以通过它在 PubMed 数据库中查找相关的研究论文。
- Visualization(可视化): 提供了一个链接(Gbrowse),你可以通过这个链接查看该突变在基因组上的可视化信息。
总结:
这项研究表明,位于 16号染色体 2567380 位点 的变异可能与 BLB1 和 TAPBP 基因的上游或下游调控区域有关,并且与 脾脏重量 存在显著的关联。研究表明此位点与脾脏重量之间的关联非常显著(P值为 3.37E-10)。你可以通过查阅 PMID 35225379 的文献了解更多细节,或者通过 Gbrowse 可视化工具进一步查看基因组位置和相关信息。
DMB1
GWAS
Export excel
Chr Position Consequence type Gene symbol Variation ID Position of GRCg7b Traits P-value PMID Visualization
16 2587697 intronic DMB1 Affx-50712683 16:2208142 Resistance to cestodes parasitism 1.09E-04 27687164 Gbrowse
16 2587381 exonic DMB1 - 16:2207826 Spleen weight 7.82E-08 35225379 Gbrowse
16 2588182 exonic DMB1 - 16:2208627 Spleen weight 8.91E-09 35225379 Gbrowse
这段数据展示了几项 基因组广泛关联研究(GWAS) 的结果,主要关注与 DMB1 基因 相关的几个不同的性状。以下是对各个字段的解释和每行数据的说明:
字段解释:
- Chr(染色体): 突变所在的染色体号。在这三项研究中,所有突变都位于 16号染色体 上。
- Position(位置): 突变在基因组中的位置。每个突变的位置在染色体16上的不同位点。
- Consequence type(变异结果类型): 突变的功能结果,表示突变发生的位置或其对基因的影响。包括:
- intronic: 突变发生在 内含子 区域(基因的非编码部分),可能影响基因调控。
- exonic: 突变发生在 外显子 区域(基因的编码部分),可能直接影响蛋白质的结构和功能。
- Gene symbol(基因符号): 相关基因的名称,这里是 DMB1,它与免疫功能相关。
- Variation ID(变异ID): 如果有特定的变异编号,这里会列出。第一个突变有变异ID(Affx-50712683),而其他两个则没有特定ID。
- Position of GRCg7b(GRCg7b参考基因组的位置): 这是基于 GRCg7b参考基因组 的突变位置,用于在参考基因组上定位突变。
- Traits(性状): 每个突变与之相关的表型或性状。这些性状包括:
- Resistance to cestodes parasitism(抗绦虫寄生)
- Spleen weight(脾脏重量)
- P-value(P值): 突变与性状之间的关联的显著性水平。P值越低,说明该突变与性状的关联越显著。具体 P 值如下:
- 1.09E-04: 与抗绦虫寄生性状的关联
- 7.82E-08 和 8.91E-09: 与脾脏重量性状的关联
- PMID: 关联研究的 PubMed ID。可以通过此编号在 PubMed 数据库中找到相关的文献进行进一步阅读。
- Visualization(可视化): 你可以通过 Gbrowse 工具查看基因组中的突变位置和关联性状的可视化信息。
具体解释每行数据:
第一行数据:
- 突变位置: 16号染色体上的 2587697 位点,位于 DMB1 基因 的 内含子区域。
- 关联性状: 抗绦虫寄生(Resistance to cestodes parasitism),与这种寄生虫感染的抗性相关。
- P值: 1.09E-04,显示了突变与该性状之间显著的统计学关联(但比后两行的 P值略高,意味着关联性稍弱)。
- PMID: 27687164,对应的文献可以通过 PubMed 查找。
第二行数据:
- 突变位置: 16号染色体上的 2587381 位点,位于 DMB1 基因 的 外显子区域。
- 关联性状: 脾脏重量(Spleen weight),这个突变可能对脾脏的发育或功能产生影响。
- P值: 7.82E-08,突变与脾脏重量之间存在显著关联。
- PMID: 35225379,可以通过此编号查阅文献。
第三行数据:
- 突变位置: 16号染色体上的 2588182 位点,同样位于 DMB1 基因 的 外显子区域。
- 关联性状: 同样是 脾脏重量(Spleen weight),与上一行的突变研究相同。
- P值: 8.91E-09,与脾脏重量性状的关联更为显著。
- PMID: 35225379,可以在 PubMed 上查找相关的研究。
总结:
这些数据展示了 DMB1 基因 的几个不同突变与两种性状(脾脏重量和抗绦虫寄生)之间的关联,特别是两项突变显著影响了脾脏重量,P值非常低(表示强关联)。这些信息可以用于进一步研究 DMB1 基因在免疫功能和脾脏发育中的作用。
DMB2
GWAS
Export excel
Chr Position Consequence type Gene symbol Variation ID Position of GRCg7b Traits P-value PMID Visualization
16 2589927 UTR5 DMB2 Affx-50712674 16:2210374 Salmonella enterica serovan Gallinarum antibody titre 1.20E-04 27687164 Gbrowse
这段数据展示了与 DMB2 基因 相关的一项 GWAS(基因组广泛关联研究) 结果,重点研究了 Salmonella enterica serovar Gallinarum 抗体效价(即对这种细菌的抗体水平)。以下是对每个字段的解释:
字段解释:
- Chr(染色体): 表示突变所在的染色体号。这里是 16号染色体。
- Position(位置): 突变所在的具体位置,位于 2589927 位点。
- Consequence type(变异结果类型): 这里的突变属于 UTR5,即 5’ 非翻译区 突变,位于 DMB2 基因的上游未翻译区,可能影响基因的调控。
- Gene symbol(基因符号): 与突变相关的基因是 DMB2,该基因可能在免疫应答中起作用。
- Variation ID(变异ID): 突变的唯一标识符是 Affx-50712674。
- Position of GRCg7b(GRCg7b参考基因组的位置): 该突变在 GRCg7b参考基因组 中的位置为 16:2210374。
- Traits(性状): 这里的性状是 Salmonella enterica serovar Gallinarum 抗体效价,即该突变与对这种沙门氏菌的免疫反应有关。
- P-value(P值): P值为 1.20E-04,表示突变与抗体效价的关联显著(P值越小,关联越强)。
- PMID: 27687164 是这项研究的 PubMed ID,你可以通过此ID在PubMed上找到相关的研究文献。
- Visualization(可视化): Gbrowse 是一种基因组浏览工具,提供了突变位点的可视化展示。
总结:
这项研究揭示了 DMB2 基因 5’ 非翻译区的一个突变与 Salmonella enterica serovar Gallinarum 抗体效价 之间的显著关联。研究表明这个突变可能影响鸡只对这种细菌的免疫反应,并且突变位于基因调控区,可能对基因表达产生影响。这对研究免疫反应和疾病抗性可能有重要意义。
BG1
16 2550280 C/T T 0.141 missense_variant MODERATE BG1 novel 16:2170716 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(3):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(25):0.200
Gallus_gallus_murghi(50):0.020
Gallus_gallus_spadiceus(40):0.188
Indonesia_Native_Chicken(33):0.167
Thailand_Native_Chicken(6):0.500
Vietnam_Native_Chicken(7):0.500
Wenchang_Chicken(1):0.500
Yunnan_Chicken(12):0.208
Xishuangbanna_Game_Chicken(10):0.250
Nixi_Chicken(10):0.050
Dulong_Chicken(7):0.214
Daweishan_Mini_Chicken(8):0.562
Guangxi_Chicken(6):0.083
Guangzhou_Chicken(3):0.000
Jiangxi_Silkies(18):0.111
Anyi_Gray_Chicken(5):0.100
Dongxiang_Blue-eggshell_Chicken(5):0.000
Tianfu_Black-bone_Chicken(5):0.100
Shimian_Caoke_Chicken(4):0.375
Jiuyuan_Black-bone_Chicken(5):0.200
Jinyang_Silky_Chicken(6):0.167
Emei_Black_Chicken(6):0.250
Pengxian_Yellow_Chicken(6):0.250
Muchuan_Black-bone_Chicken(5):0.100
Miyi_Chicken(5):0.000
YuanBao_Chicken(24):0.021
Langshan_Chicken(10):0.050
Luxi_Game_Chicken(9):0.222
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.438
Beijing_You_Chicken(11):0.000
Dagu_Chicken(7):0.143
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(8):0.125
Southern_Xinjiang_Game_Chicken(8):0.000
Turpan_Game_Chicken(8):0.250
Tibetan_Chicken(134):0.228
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(7):0.000
Bengal_Native_Chicken(14):0.071
India_Native_Chicken(45):0.144
Pakistan_Native_Chicken(36):0.083
Afghan_Native_Chicken(11):0.318
Iran_Native_Chicken(177):0.068
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(13):0.423
Cornish_Chicken(1):0.500
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
这个数据展示了位于 16号染色体,位置为 2550280 的 C/T 突变。此突变是一个 missense_variant(错义突变),影响了 BG1 基因,突变的影响程度被标记为 MODERATE(中等影响)。此外,这个突变是 novel(新发现的),可能在以前的研究中没有被报道过。具体位置为 16:2170716。
以下是一些详细的分析内容:
突变特性:
- 错义突变 表示该突变导致蛋白质中某个氨基酸发生改变,可能会对蛋白质的功能产生一定影响。MODERATE 说明这类突变的影响通常介于显著影响和无影响之间,可能会影响蛋白质功能,但不一定致命。
不同鸡种中的等位基因频率:
下方的数据展示了该突变在不同鸡种群体中的等位基因频率。每个鸡种的名称后括号中的数字表示样本数量,后面的小数则表示突变频率,即在该鸡种中有多少比例的个体携带该突变。
高频突变群体:
- Daweishan_Mini_Chicken(大围山小鸡): 频率为 0.562,即该群体中约 56.2% 的个体携带此突变。
- Thailand_Native_Chicken(泰国土鸡) 和 Vietnam_Native_Chicken(越南土鸡): 频率均为 0.500,表示泰国和越南土鸡中约有一半的个体携带此突变。
- Shimian_Caoke_Chicken(石棉草科鸡): 频率为 0.375,约 37.5% 的个体携带此突变。
- Bian_Chicken(汴鸡): 频率为 0.438,约 43.8% 的个体携带此突变。
- White_Leghorn_Chicken(白来亨鸡): 频率为 0.423,约 42.3% 的个体携带此突变。
- Afghan_Native_Chicken(阿富汗土鸡): 频率为 0.318,约 31.8% 的个体携带此突变。
这些高频群体可能对研究该突变的功能或进化选择压力有重要意义。
低频或无突变群体:
- Gallus_gallus_bankiva(原鸡) 和 Gallus_gallus_gallus(家鸡): 频率为 0.000,没有发现突变。
- Guangzhou_Chicken(广州鸡)、Dongxiang_Blue-eggshell_Chicken(东乡蓝壳蛋鸡)、Beijing_You_Chicken(北京油鸡): 频率为 0.000,这些群体中没有发现该突变。
- Sri_Lanka_Native_Chicken(斯里兰卡土鸡): 频率为 0.000,也没有检测到此突变。
这些低频或无突变的群体可以作为对照,帮助理解该突变在不同鸡种中的分布差异及其背后的可能原因。
地理或生态环境影响:
- 可以看出,东南亚地区 的一些本地鸡种(如泰国、越南)在该突变的携带率上较高,可能与当地的生态环境或选择压力有关。这些突变可能与鸡的抗病性、生产性能或其他生理特性相关联。
- 与此相对,一些 中国本地鸡种(如北京油鸡、东乡蓝壳蛋鸡)和 野生原鸡 群体中的突变频率非常低或为零,可能是因为这些鸡种在进化过程中未受到该突变的选择压力。
进一步研究建议:
- 功能研究:由于这是一个错义突变,可能影响 BG1 基因 的功能。可以进一步研究该基因是否与免疫功能、生产性能或其他性状相关,以探讨该突变对不同鸡种的潜在影响。
- 进化分析:可以对高频和低频突变群体进行比较,研究该突变是否受到选择压力,或者是否与特定环境条件有关。
- 育种策略:如果发现该突变对生产性能或健康有正面影响,可以考虑在育种过程中利用这些突变频率较高的鸡种。
总之,这些数据提供了一个关于 BG1 基因突变 在不同鸡种中的分布情况。高频突变群体可能在进化过程中对该突变产生了正选择,而低频或无突变群体则可能因不同的选择压力而保留了原有基因型。
16 2550218 AGT/A A 0.043 frameshift_variant HIGH BG1 novel 16:2170654 Show Show Gbrowse
16 2550223 CAT/C C 0.060 frameshift_variant HIGH BG1 novel 16:2170659 Show Show Gbrowse
16 2550228 G/GCC GCC 0.043 frameshift_variant HIGH BG1 novel 16:2170664 Show Show Gbrowse
Breed (number): frequence
Gallus_gallus_bankiva(3):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(26):0.000
Gallus_gallus_murghi(47):0.011
Gallus_gallus_spadiceus(45):0.011
Indonesia_Native_Chicken(34):0.059
Thailand_Native_Chicken(5):0.000
Vietnam_Native_Chicken(6):0.083
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.083
Xishuangbanna_Game_Chicken(10):0.000
Nixi_Chicken(12):0.000
Dulong_Chicken(7):0.071
Daweishan_Mini_Chicken(8):0.000
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(3):0.000
Jiangxi_Silkies(20):0.050
Anyi_Gray_Chicken(5):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.000
Shimian_Caoke_Chicken(4):0.000
Jiuyuan_Black-bone_Chicken(5):0.100
Jinyang_Silky_Chicken(6):0.083
Emei_Black_Chicken(6):0.000
Pengxian_Yellow_Chicken(6):0.167
Muchuan_Black-bone_Chicken(5):0.000
Miyi_Chicken(5):0.100
YuanBao_Chicken(23):0.000
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(9):0.000
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(7):0.000
Beijing_You_Chicken(11):0.091
Dagu_Chicken(8):0.000
Xinjiang_Native_Chicken(5):0.000
Hetian_Black_Chicken(8):0.000
Southern_Xinjiang_Game_Chicken(8):0.000
Turpan_Game_Chicken(8):0.062
Tibetan_Chicken(143):0.059
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(7):0.071
Bengal_Native_Chicken(15):0.000
India_Native_Chicken(45):0.022
Pakistan_Native_Chicken(37):0.014
Afghan_Native_Chicken(10):0.150
Iran_Native_Chicken(181):0.044
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(13):0.538
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.500
这段数据展示了位于 16号染色体 的多个 移码突变(frameshift_variant),分别位于 2550218、2550223 和 2550228 的位点上,这些突变影响了 BG1 基因,并且被标记为 HIGH(高影响)。移码突变通常会对蛋白质产生重大影响,导致阅读框架的偏移,进而可能产生截短的蛋白质或无功能的蛋白质。所有这些突变都是 novel(新发现的),此前未被报道过。具体位置分别为 16:2170654、16:2170659 和 16:2170664。
以下是具体的分析内容:
突变特性:
移码突变(frameshift_variant) 通常会导致蛋白质合成过程中的重大功能损害,因为它们会改变蛋白质的阅读框架,可能导致早期终止密码子,产生截短或完全无效的蛋白质。由于这些突变影响的是 BG1 基因,它们可能会对基因功能造成较大的影响。
不同鸡种中的突变频率:
下方的数据展示了每个鸡种中携带这些突变的个体比例。括号内的数字表示该鸡种的样本数,小数表示突变频率。
高频突变群体:
White_Leghorn_Chicken(白来亨鸡): 突变频率高达 0.538,说明在这个群体中有超过一半的个体携带此突变。
White_Plymouth_Rock_Chicken(白普利茅斯鸡): 突变频率为 0.500,同样为高频突变。
Afghan_Native_Chicken(阿富汗土鸡): 突变频率为 0.150,该群体的突变率相对较高。
Pengxian_Yellow_Chicken(彭县黄鸡): 突变频率为 0.167。
Beijing_You_Chicken(北京油鸡): 突变频率为 0.091,尽管频率不算非常高,但仍然在一些鸡种中较为明显。
这些高频突变群体可能是研究该突变功能影响的重点群体。
低频或无突变群体:
许多鸡种显示出零突变率,意味着这些群体中没有个体携带此突变,如 Gallus_gallus_bankiva(野生原鸡)、Gallus_gallus_gallus(家鸡)、Wenchang_Chicken(文昌鸡) 等。这可能表明这些群体未受到相关选择压力,或者这些群体中该突变并没有优势。
Vietnam_Native_Chicken(越南土鸡) 和 Yunnan_Chicken(云南鸡): 突变频率为 0.083,在这些群体中突变也存在一定比例。
地理或生态环境的潜在影响:
该突变频率在一些东南亚土鸡(如越南土鸡、云南鸡)中也存在一定比例,表明这可能与这些鸡种的环境或进化压力相关。相较之下,一些野生鸡种和商用鸡种的突变频率较低或为零。
一些来自东亚和中亚的鸡种(如 Afghan_Native_Chicken(阿富汗土鸡))显示出较高的突变频率,这可能提示该突变在这些地区鸡种的进化过程中起到了一定作用,可能与环境适应或免疫功能相关。
进一步研究建议:
功能研究:由于这是一个影响 BG1 基因 的移码突变,建议进一步研究其对基因表达和蛋白质功能的影响。移码突变通常会严重破坏基因功能,可能与重要的生理或免疫功能相关。
进化选择压力:可以通过比较高频突变和低频突变群体,研究这些突变是否受到特定的自然选择压力。例如,高频突变群体可能在其进化过程中经历了与突变相关的正选择压力。
育种应用:对于一些突变频率较高且与重要性状相关的鸡种,可以考虑在育种中利用这些突变,特别是在探索与免疫功能或生产性能相关的潜在联系时。
关联分析:可以将这些突变与鸡种的表型数据(如免疫力、生产性能、抗病性等)结合起来,进行更深入的基因-性状关联分析,研究该突变在不同鸡种中的实际功能效应。
总结:
这些数据展示了 BG1 基因 上多个新发现的移码突变在不同鸡种中的分布情况。高频突变群体可能对进一步的功能和进化研究提供了重要线索,而低频突变群体可以作为对照来理解这些突变的进化和功能影响。
BG2
Chr Position Consequence type Gene symbol Variation ID Position of GRCg7b Traits P-value PMID Visualization
16 2436347 intronic BG2,LOC107054697 rs741350124 - Posterior probability of a hen to belong to the extreme feather pecking subgroup 7.09E-06 33004014 Gbrowse
这段数据展示了 BG2 基因 及其相邻基因 LOC107054697 的一个 GWAS(基因组广泛关联研究) 结果,重点研究了与 极端啄羽亚群分类的后验概率 相关的遗传变异。以下是对每个字段的详细解释:
字段解释:
- Chr(染色体): 表示突变所在的染色体号。这里是 16号染色体。
- Position(位置): 突变在基因组中的具体位置为 2436347,这是在16号染色体上的一个位点。
- Consequence type(变异结果类型): 该突变类型为 intronic,表示突变发生在 BG2 基因 或 LOC107054697 基因的 内含子 区域(非编码区),这可能会影响基因的调控或表达。
- Gene symbol(基因符号): 相关基因包括 BG2 和 LOC107054697。BG2 是一个已知的基因,而 LOC107054697 可能是一个假设基因或未完全注释的基因。
- Variation ID(变异ID): 该突变的ID为 rs741350124,是一个已在数据库中记录的遗传变异。
- Position of GRCg7b(GRCg7b参考基因组的位置): 此字段为空,表明没有列出基于 GRCg7b参考基因组 的位置。
- Traits(性状): 这个突变与 母鸡属于极端啄羽亚群的后验概率 有关联。极端啄羽是母鸡中的一种行为异常,啄羽会导致羽毛受损,影响生产性能和健康。这项研究关注哪些遗传变异与这种行为的极端形式相关。
- P-value(P值): P值为 7.09E-06,表示突变与极端啄羽亚群之间存在非常显著的关联(P值越小,关联越显著)。
- PMID: 33004014,这是该研究的 PubMed ID,可以通过这个ID在PubMed数据库中查找相关的研究论文。
- Visualization(可视化): 你可以通过 Gbrowse 工具查看基因组中的突变位置及其与相关性状的关联可视化信息。
数据解读:
这项研究表明,16号染色体 上 2436347 位点的突变与母鸡是否属于 极端啄羽亚群 有显著关联。啄羽行为 是家禽养殖中的一个重要性状,因为严重的啄羽行为会影响生产性能,甚至造成经济损失。
突变位于 BG2 基因 的内含子区域,虽然不是编码区的突变,但它可能影响基因的调控或表达,从而在行为性状上表现出差异。BG2 基因与免疫相关,因此它可能在行为特性或应激反应中扮演一定角色。
研究的意义:
- 啄羽行为 在家禽养殖中是一个重要的问题,因此找到与这种行为相关的遗传变异,可以帮助育种人员筛选出更适应养殖环境、表现出更健康行为的个体。
- 通过研究这些突变,可以了解啄羽行为背后的遗传机制,从而设计出更有效的干预和管理策略,减少行为异常对养殖效益的负面影响。
进一步研究:
- 功能验证:由于突变发生在内含子区域,下一步可以通过基因表达分析或基因功能研究,验证该突变是否影响 BG2 基因的表达,从而进一步理解其对啄羽行为的影响。
- 育种应用:将这一关联研究结果应用于家禽育种,育种人员可以通过选择性育种,减少啄羽行为的发生频率,从而改善生产性能。
总结来说,这个突变与母鸡极端啄羽行为的概率显著相关,并可能为后续育种和行为调控提供了重要的遗传学依据。
16 2389918 AGCTC/A A 0.080 frameshift_variant HIGH BG8 novel - Show Show Gbrowse
16 2389923 A/ATTTG ATTTG 0.082 frameshift_variant HIGH BG8 novel - Show Show Gbrowse
Breed (number): frequence
Gallus_gallus_bankiva(3):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(27):0.111
Gallus_gallus_murghi(56):0.054
Gallus_gallus_spadiceus(45):0.044
Indonesia_Native_Chicken(35):0.057
Thailand_Native_Chicken(6):0.250
Vietnam_Native_Chicken(6):0.000
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.167
Xishuangbanna_Game_Chicken(10):0.000
Nixi_Chicken(10):0.000
Dulong_Chicken(6):0.083
Daweishan_Mini_Chicken(8):0.062
Guangxi_Chicken(6):0.167
Guangzhou_Chicken(5):0.000
Jiangxi_Silkies(15):0.200
Anyi_Gray_Chicken(3):0.333
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.200
Shimian_Caoke_Chicken(4):0.375
Jiuyuan_Black-bone_Chicken(5):0.500
Jinyang_Silky_Chicken(6):0.167
Emei_Black_Chicken(6):0.000
Pengxian_Yellow_Chicken(6):0.250
Muchuan_Black-bone_Chicken(5):0.200
Miyi_Chicken(5):0.300
YuanBao_Chicken(14):0.036
Langshan_Chicken(10):0.100
Luxi_Game_Chicken(9):0.000
Shouguang_Chicken(7):0.143
Gushi_Chicken(7):0.071
Bian_Chicken(7):0.000
Beijing_You_Chicken(6):0.167
Dagu_Chicken(7):0.286
Xinjiang_Native_Chicken(6):0.333
Hetian_Black_Chicken(7):0.000
Southern_Xinjiang_Game_Chicken(8):0.375
Turpan_Game_Chicken(8):0.250
Tibetan_Chicken(145):0.103
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(7):0.000
Bengal_Native_Chicken(15):0.100
India_Native_Chicken(49):0.071
Pakistan_Native_Chicken(37):0.095
Afghan_Native_Chicken(11):0.045
Iran_Native_Chicken(181):0.017
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(12):0.000
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
这段数据展示了位于 16号染色体 的两个不同的 移码突变(frameshift variant),分别位于 2389918 和 2389923 位点。这些突变影响了 BG8 基因,并且被标记为 HIGH(高影响)。移码突变通常对基因的蛋白质合成过程产生重大影响,可能导致蛋白质失活或产生无功能的蛋白质。这些突变是 novel(新发现的),即它们此前未被发现。
突变详情:
第一行突变:
- 位置: 16号染色体上的 2389918 位点,突变类型是 AGCTC/A,即由5个碱基被替换为1个碱基 A,这是一个移码突变。
- 突变频率: 0.080,即约8%的个体携带此突变。
第二行突变:
- 位置: 16号染色体上的 2389923 位点,突变类型是 A/ATTTG,即1个碱基被替换为5个碱基 ATTTG,这也是一个移码突变。
- 突变频率: 0.082,即约8.2%的个体携带此突变。
不同鸡种中的突变频率:
数据展示了这些突变在不同鸡种中的频率,括号中的数字表示样本数量,小数表示突变频率。以下是一些高频和低频突变群体的分析:
高频突变群体:
- Jiuyuan_Black-bone_Chicken(九元黑骨鸡): 突变频率为 0.500,即约50%的个体携带此突变。
- Shimian_Caoke_Chicken(石棉草科鸡): 突变频率为 0.375。
- Southern_Xinjiang_Game_Chicken(南疆斗鸡): 突变频率为 0.375。
- Anyi_Gray_Chicken(安义灰鸡) 和 Xinjiang_Native_Chicken(新疆土鸡): 突变频率为 0.333。
这些群体的突变频率较高,可能与环境适应或遗传选择有关。
低频或无突变群体:
- Gallus_gallus_bankiva(野生原鸡) 和 Gallus_gallus_gallus(家鸡): 突变频率为 0.000,没有个体携带这些突变。
- Araucana_Blue-eggshell_Chicken(阿劳卡纳蓝壳蛋鸡)、White_Leghorn_Chicken(白来亨鸡) 和 Cornish_Chicken(康尼什鸡): 突变频率为 0.000,这些群体中也没有携带此突变。
这些低频或无突变的鸡种可能未受到该突变相关的选择压力。
中等频率群体:
- Tibetan_Chicken(藏鸡): 突变频率为 0.103,即约10.3%的个体携带此突变。
- Yunnan_Chicken(云南鸡) 和 Guangxi_Chicken(广西鸡): 突变频率为 0.167。
这些鸡种显示出中等频率的突变,表明它们可能在不同的选择环境中保持了这些突变。
地理分布和环境因素的影响:
- 突变频率在东南亚和中国的一些本地鸡种(如 泰国土鸡、越南土鸡 和 云南鸡)中有显著差异,这可能与不同的生态环境和遗传选择压力有关。
- 一些商业化鸡种(如 White Leghorn Chicken(白来亨鸡))则没有显示出这些突变,可能表明这些鸡种在现代育种过程中没有保留这些突变。
进一步研究建议:
- 功能性研究:由于这是影响 BG8 基因 的移码突变,可能会对基因功能产生较大影响,建议进一步研究该基因的具体功能及这些突变对基因表达的影响。
- 育种应用:对于那些突变频率较高且可能对特定性状有影响的鸡种,可以将其作为育种选择的参考,尤其是如果这些突变与某些有益的性状(如抗病性或生产性能)相关。
- 进化分析:不同鸡种中的突变频率差异可能反映了各鸡种在进化过程中所经历的不同选择压力。可以通过与鸡种的地理分布和历史数据结合,研究这些突变的进化意义。
总结:
这些新发现的移码突变对 BG8 基因 可能产生重大影响。高频突变群体中的突变可能与鸡种的某些适应性或选择压力相关,低频或无突变的群体则可能由于不同的选择环境保留了未突变的基因型。
节律基因
ARNTL
PER2
BHLHE40_A
NPAS3_A
NR1D2
RORB
CSNK1E
ARNTL2
CLOCK
CRY1
CRY2
CSNK1D
PER3
RORA
ARNTL2
1 68143400 C/T T 0.090 missense_variant MODERATE ARNTL2 rs14841128 1:68226827 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(4):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(27):0.111
Gallus_gallus_murghi(53):0.019
Gallus_gallus_spadiceus(42):0.024
Indonesia_Native_Chicken(36):0.125
Thailand_Native_Chicken(6):0.083
Vietnam_Native_Chicken(7):0.000
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.042
Xishuangbanna_Game_Chicken(10):0.050
Nixi_Chicken(12):0.042
Dulong_Chicken(7):0.071
Daweishan_Mini_Chicken(8):0.000
Guangxi_Chicken(6):0.167
Guangzhou_Chicken(4):0.000
Jiangxi_Silkies(20):0.000
Anyi_Gray_Chicken(5):0.000
Dongxiang_Blue-eggshell_Chicken(5):0.000
Tianfu_Black-bone_Chicken(5):0.100
Shimian_Caoke_Chicken(4):0.125
Jiuyuan_Black-bone_Chicken(5):0.100
Jinyang_Silky_Chicken(6):0.167
Emei_Black_Chicken(6):0.083
Pengxian_Yellow_Chicken(6):0.167
Muchuan_Black-bone_Chicken(5):0.200
Miyi_Chicken(5):0.100
YuanBao_Chicken(24):0.000
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(9):0.000
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.000
Beijing_You_Chicken(11):0.000
Dagu_Chicken(8):0.000
Xinjiang_Native_Chicken(5):0.100
Hetian_Black_Chicken(7):0.143
Southern_Xinjiang_Game_Chicken(8):0.000
Turpan_Game_Chicken(8):0.000
Tibetan_Chicken(139):0.090
Araucana_Blue-eggshell_Chicken(6):0.583
Sri_Lanka_Native_Chicken(7):0.500
Bengal_Native_Chicken(15):0.133
India_Native_Chicken(49):0.143
Pakistan_Native_Chicken(36):0.069
Afghan_Native_Chicken(11):0.000
Iran_Native_Chicken(180):0.111
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(12):0.750
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
这段数据展示了 ARNTL2 基因 的一个 C/T 突变,位于 1号染色体 的 68143400 位点。这个突变是一个 missense_variant(错义突变),会导致基因编码的蛋白质中的一个氨基酸发生改变。突变的影响被标记为 MODERATE(中等影响),这意味着该突变可能会对蛋白质功能产生一定影响但不是致命的。
具体突变信息:
- 基因: ARNTL2(参与昼夜节律调节的基因,与生理节律、代谢和免疫反应相关)。
- 突变位置: 1号染色体 68143400 位点。
- 突变类型: C/T 突变,发生了 错义突变。
- 变异ID: rs14841128,表示该变异已经在数据库中记录。
- P值: 0.090,这表示突变的频率为 9%。
不同鸡种中的突变频率:
下方的数据展示了不同鸡种中携带此突变的频率,括号中的数字表示样本数量,小数则表示突变频率。例如:
高频突变群体:
- White_Leghorn_Chicken(白来亨鸡): 突变频率为 0.750,即75%的个体携带此突变。这个突变在白来亨鸡中非常普遍。
- Araucana_Blue-eggshell_Chicken(阿劳卡纳蓝壳蛋鸡): 突变频率为 0.583,即58.3%的个体携带此突变。
- Sri_Lanka_Native_Chicken(斯里兰卡土鸡): 突变频率为 0.500,即一半的个体携带此突变。
- Guangxi_Chicken(广西鸡) 和 Jinyang_Silky_Chicken(金阳丝羽鸡): 突变频率为 0.167,相对较高。
- Pengxian_Yellow_Chicken(彭县黄鸡): 突变频率为 0.167。
中等频率突变群体:
- Tibetan_Chicken(藏鸡): 突变频率为 0.090,即9%的个体携带此突变。
- Indonesia_Native_Chicken(印度尼西亚土鸡): 突变频率为 0.125。
- Hetian_Black_Chicken(和田黑鸡) 和 India_Native_Chicken(印度土鸡): 突变频率为 0.143。
低频或无突变群体:
- Gallus_gallus_bankiva(野生原鸡)、Gallus_gallus_gallus(家鸡) 等许多鸡种显示突变频率为 0.000,即这些群体中没有个体携带此突变。
- Vietnam_Native_Chicken(越南土鸡)、Wenchang_Chicken(文昌鸡) 和 Dongxiang_Blue-eggshell_Chicken(东乡蓝壳蛋鸡): 突变频率为 0.000。
这些低频或无突变的群体可能表明该突变并未在这些群体中显现出选择优势或遗传压力。
地理分布和生态环境的影响:
- 一些商用鸡种(如 White Leghorn Chicken 和 Araucana Blue-eggshell Chicken)显示出较高的突变频率,表明这些突变可能与特定的生产性状(如产蛋性能)相关。
- 部分东南亚和南亚的土鸡(如 Sri Lanka Native Chicken 和 India Native Chicken)也显示出中等或较高的突变频率,可能是由于当地的环境选择压力导致的。
研究意义:
- ARNTL2 基因 是昼夜节律调控的重要基因之一,可能与鸡的代谢、生长速度以及免疫反应有关。因此,这些突变可能对生理节律相关的性状产生影响。
- 高频突变鸡种(如 White Leghorn Chicken 和 Sri Lanka Native Chicken)中的突变可能对其生产性能或适应环境的能力有一定帮助,值得进一步研究。
- 低频突变鸡种 中的遗传差异可以用作对照,研究不同鸡种在进化过程中如何保留或丢失这些突变。
进一步研究建议:
- 功能验证:可以通过进一步的基因表达和功能分析,研究这个错义突变是否对 ARNTL2 基因的功能产生影响。
- 关联分析:将这些突变与鸡种的昼夜节律、生产性能、抗病能力等表型数据结合,进行更深入的基因-性状关联分析。
- 育种应用:如果发现该突变对生产性能有正面影响,可以将其应用于鸡种的育种选择中,优化产蛋性能或其他相关性状。
总的来说,这个突变在不同鸡种中的分布情况表明,它可能在某些群体中经历了选择压力,特别是在商用鸡种中。
这个都很多
1 68158770 G/A G 0.049 missense_variant MODERATE ARNTL2 rs316729476 1:68242203 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(2):1.000
Gallus_gallus_gallus(5):1.000
Gallus_gallus_jabouillei(25):0.920
Gallus_gallus_murghi(46):0.957
Gallus_gallus_spadiceus(40):1.000
Indonesia_Native_Chicken(36):0.889
Thailand_Native_Chicken(5):0.700
Vietnam_Native_Chicken(7):0.929
Wenchang_Chicken(1):1.000
Yunnan_Chicken(11):0.773
Xishuangbanna_Game_Chicken(10):1.000
Nixi_Chicken(12):1.000
Dulong_Chicken(7):0.929
Daweishan_Mini_Chicken(8):0.750
Guangxi_Chicken(5):0.700
Guangzhou_Chicken(4):0.875
Jiangxi_Silkies(19):1.000
Anyi_Gray_Chicken(5):1.000
Dongxiang_Blue-eggshell_Chicken(6):1.000
Tianfu_Black-bone_Chicken(4):1.000
Shimian_Caoke_Chicken(2):1.000
Jiuyuan_Black-bone_Chicken(5):1.000
Jinyang_Silky_Chicken(6):1.000
Emei_Black_Chicken(4):1.000
Pengxian_Yellow_Chicken(6):1.000
Muchuan_Black-bone_Chicken(5):0.800
Miyi_Chicken(4):0.875
YuanBao_Chicken(22):1.000
Langshan_Chicken(9):1.000
Luxi_Game_Chicken(9):1.000
Shouguang_Chicken(8):1.000
Gushi_Chicken(8):0.750
Bian_Chicken(8):0.938
Beijing_You_Chicken(11):1.000
Dagu_Chicken(8):1.000
Xinjiang_Native_Chicken(5):1.000
Hetian_Black_Chicken(8):1.000
Southern_Xinjiang_Game_Chicken(8):1.000
Turpan_Game_Chicken(7):0.929
Tibetan_Chicken(124):0.883
Araucana_Blue-eggshell_Chicken(6):1.000
Sri_Lanka_Native_Chicken(7):1.000
Bengal_Native_Chicken(15):0.967
India_Native_Chicken(45):0.922
Pakistan_Native_Chicken(36):1.000
Afghan_Native_Chicken(11):1.000
Iran_Native_Chicken(179):0.994
Iran_Commercial_Broiler(4):1.000
White_Leghorn_Chicken(13):1.000
Cornish_Chicken(1):1.000
Rhode_Island_Red_Chicken(1):1.000
White_Plymouth_Rock_Chicken(1):1.000
这段数据展示了 ARNTL2 基因 的一个 G/A 突变,位于 1号染色体 的 68158770 位点。这个突变是一个 missense_variant(错义突变),即导致蛋白质中的一个氨基酸发生改变。它的影响被标记为 MODERATE(中等影响),这表明该突变可能会对蛋白质功能产生一定影响,但不一定是致命的突变。
突变详情:
基因: ARNTL2(参与昼夜节律调节的基因,与生理节律、代谢和免疫反应相关)。
突变位置: 1号染色体 68158770 位点。
突变类型: G/A 突变,导致错义突变。
变异ID: rs316729476,这是在数据库中记录的变异ID。
P值: 0.049,表示突变频率为 4.9%。
不同鸡种中的突变频率:
下方的数据展示了不同鸡种中携带此突变的个体比例,括号中的数字表示样本数量,小数表示突变频率。例如:
高频突变群体:
Gallus_gallus_bankiva(原鸡) 和 Gallus_gallus_gallus(家鸡): 突变频率为 1.000,说明所有采样的个体都携带此突变。
Gallus_gallus_spadiceus(红原鸡)、Xishuangbanna_Game_Chicken(西双版纳斗鸡)、Jiangxi_Silkies(江西丝羽鸡)、Araucana_Blue-eggshell_Chicken(阿劳卡纳蓝壳蛋鸡): 突变频率均为 1.000,即所有样本都携带该突变。
White_Leghorn_Chicken(白来亨鸡) 和 Cornish_Chicken(康尼什鸡): 这些商用鸡种中也有100%的突变频率,意味着所有样本个体都带有该突变。
中等频率突变群体:
Thailand_Native_Chicken(泰国土鸡): 突变频率为 0.700,即70%的个体携带此突变。
Yunnan_Chicken(云南鸡): 突变频率为 0.773。
Tibetan_Chicken(藏鸡): 突变频率为 0.883,接近90%的个体携带此突变。
低频突变群体:
Gushi_Chicken(固始鸡): 突变频率为 0.750,即75%的个体携带此突变。
Turpan_Game_Chicken(吐鲁番斗鸡) 和 Vietnam_Native_Chicken(越南土鸡): 突变频率接近 0.929 和 0.929,仍然相对较高。
Pakistan_Native_Chicken(巴基斯坦土鸡): 突变频率为 1.000,所有个体都携带。
分析:
高频突变群体:如 Gallus_gallus_bankiva(原鸡)、Gallus_gallus_gallus(家鸡) 和其他商用鸡种显示出高频率的突变,可能表明该突变对这些鸡种具有一定的选择优势,或该突变并未对鸡种的生理表现产生负面影响。尤其是 White Leghorn Chicken(白来亨鸡) 和 Cornish Chicken(康尼什鸡) 等商用鸡种的100%突变率可能与现代育种过程中对某些性状的选择有关。
中等频率突变群体:例如,云南鸡 和 泰国土鸡 的突变频率较高,但未达到100%,表明在这些群体中存在部分个体未受到选择压力,保留了原始基因型。
低频或无突变群体:一些鸡种中显示突变频率较低或为零,这可能与这些群体的进化历史、地理环境以及选择压力不同有关。
研究意义:
ARNTL2 基因 是昼夜节律调控的重要基因之一,突变可能对鸡的代谢、免疫反应以及生长速度等特性产生影响。这些突变的高频率可能表明它对某些鸡种的昼夜节律或其他生理功能具有重要意义。
高频突变群体 中的突变可能是通过自然选择或人工育种过程中的选择压力保留下来的。这表明该突变对生产性能、健康或环境适应性具有潜在益处。
低频突变群体 可以作为对照,帮助研究不同鸡种在进化过程中如何选择和保留这些突变。
进一步研究建议:
功能性研究:通过功能性研究(如基因表达分析)来确定该突变对 ARNTL2 基因功能的影响,特别是它在调控昼夜节律方面的作用。
表型关联分析:结合生产性能、抗病性、昼夜节律等表型数据,进行基因-性状关联分析,研究该突变是否对鸡种的生理表现产生影响。
育种应用:如果该突变显示出对生产性能有正面影响,可以将其应用于商用鸡种的育种中,以提高产蛋率、健康水平等。
总之,这个 ARNTL2 基因突变在不同鸡种中的分布情况表明,它可能在某些群体中经历了选择压力,尤其是在商用鸡种中,这对现代育种和生理研究可能具有重要意义。
PER2
9 5659017 T/C C 0.062 missense_variant MODERATE PER2 rs314691756 9:5164690 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(4):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(27):0.000
Gallus_gallus_murghi(53):0.000
Gallus_gallus_spadiceus(42):0.048
Indonesia_Native_Chicken(35):0.086
Thailand_Native_Chicken(6):0.000
Vietnam_Native_Chicken(7):0.143
Wenchang_Chicken(1):0.000
Yunnan_Chicken(11):0.000
Xishuangbanna_Game_Chicken(10):0.000
Nixi_Chicken(12):0.000
Dulong_Chicken(7):0.214
Daweishan_Mini_Chicken(8):0.000
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(2):0.000
Jiangxi_Silkies(20):0.050
Anyi_Gray_Chicken(5):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.000
Shimian_Caoke_Chicken(2):0.250
Jiuyuan_Black-bone_Chicken(5):0.200
Jinyang_Silky_Chicken(6):0.083
Emei_Black_Chicken(4):0.250
Pengxian_Yellow_Chicken(6):0.000
Muchuan_Black-bone_Chicken(5):0.200
Miyi_Chicken(5):0.000
YuanBao_Chicken(22):0.000
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(9):0.000
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.000
Beijing_You_Chicken(11):0.091
Dagu_Chicken(8):0.438
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(8):0.312
Southern_Xinjiang_Game_Chicken(7):0.286
Turpan_Game_Chicken(8):0.062
Tibetan_Chicken(134):0.037
Araucana_Blue-eggshell_Chicken(6):0.333
Sri_Lanka_Native_Chicken(7):0.000
Bengal_Native_Chicken(15):0.033
India_Native_Chicken(48):0.010
Pakistan_Native_Chicken(37):0.041
Afghan_Native_Chicken(11):0.045
Iran_Native_Chicken(182):0.113
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(13):0.000
Cornish_Chicken(1):1.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
Indel
这段数据展示了 PER2 基因 的一个 T/C 突变,位于 9号染色体 的 5659017 位点。这个突变是一个 missense_variant(错义突变),即导致蛋白质中的一个氨基酸发生改变。其影响被标记为 MODERATE(中等影响),表明该突变可能会对蛋白质功能产生一定影响,但不一定是致命的突变。
突变详情:
- 基因: PER2(Period Circadian Regulator 2,调控昼夜节律的基因,通常与生理节律、代谢、免疫等相关)。
- 突变位置: 9号染色体 5659017 位点。
- 突变类型: T/C 突变,这是一个错义突变。
- 变异ID: rs314691756,表示该变异已经在数据库中记录。
- P值: 0.062,表示突变的频率为 6.2%。
不同鸡种中的突变频率:
下方的数据展示了不同鸡种中携带此突变的个体比例。括号中的数字表示样本数量,小数表示突变频率。例如:
高频突变群体:
- Cornish_Chicken(康尼什鸡): 突变频率为 1.000,说明所有采样的个体都携带此突变。
- Dagu_Chicken(大骨鸡): 突变频率为 0.438,即43.8%的个体携带此突变。
- Araucana_Blue-eggshell_Chicken(阿劳卡纳蓝壳蛋鸡): 突变频率为 0.333,即33.3%的个体携带此突变。
- Hetian_Black_Chicken(和田黑鸡): 突变频率为 0.312,即31.2%的个体携带此突变。
- Southern_Xinjiang_Game_Chicken(南疆斗鸡): 突变频率为 0.286。
这些高频群体表明突变可能对这些鸡种的生理性状产生了一定影响,特别是 Cornish Chicken 的100%突变率,可能与育种过程中对特定性状的选择有关。
中等频率突变群体:
- Emei_Black_Chicken(峨眉黑鸡) 和 Shimian_Caoke_Chicken(石棉草科鸡): 突变频率均为 0.250。
- Jiuyuan_Black-bone_Chicken(九元黑骨鸡) 和 Muchuan_Black-bone_Chicken(沐川黑骨鸡): 突变频率为 0.200,即20%的个体携带此突变。
- Iran_Native_Chicken(伊朗土鸡): 突变频率为 0.113。
低频或无突变群体:
- Gallus_gallus_bankiva(野生原鸡)、Gallus_gallus_gallus(家鸡) 以及其他鸡种如 Yunnan_Chicken(云南鸡)、Luxi_Game_Chicken(鲁西斗鸡) 等显示突变频率为 0.000,即没有个体携带此突变。
- Vietnam_Native_Chicken(越南土鸡): 突变频率为 0.143,即14.3%的个体携带此突变。
这些低频或无突变的群体可能表明它们未经历与此突变相关的选择压力。
分析:
高频突变群体: 某些商用鸡种(如 Cornish Chicken 和 Dagu Chicken)显示出较高的突变频率,表明这些群体可能经历了与该突变相关的选择压力,或该突变对鸡种的某些性状(如生产性能、抗病性等)有潜在的影响。
中等频率突变群体: 部分本地鸡种(如 Jiuyuan Black-bone Chicken 和 Muchuan Black-bone Chicken)显示出中等频率,表明它们可能保留了部分原始基因型,同时也可能受到突变影响。
低频或无突变群体: 一些野生鸡种和本地鸡种中突变频率较低或为零,这些鸡种可能未经历与此突变相关的选择压力,或者它们保留了较为原始的基因型。
研究意义:
- PER2 基因 是调控昼夜节律的重要基因,可能对代谢、免疫反应、成长速度等生理性状产生影响。因此,研究这些突变在不同鸡种中的分布,可以揭示其对鸡群适应性和生产性能的影响。
- 高频突变鸡种 表明该突变可能对这些鸡种的生理性状产生积极影响,特别是商用鸡种中的高频突变可能与现代育种过程中对生产性能的选择相关。
- 低频或无突变群体 可以作为对照,帮助理解为什么这些群体没有保留该突变,以及它们在进化过程中如何适应不同的环境。
进一步研究建议:
- 功能验证: 通过进一步研究(如基因表达、功能实验)来验证该突变是否对 PER2 基因的功能产生影响,特别是对昼夜节律和生理周期的影响。
- 表型关联分析: 结合表型数据(如生长速度、昼夜节律、抗病能力等)进行基因-性状关联分析,探索该突变是否对鸡种的生理特性产生影响。
- 育种应用: 如果该突变被发现与生产性能或其他有益性状相关,则可以将其应用于育种过程中,改善生产性能。
总结:
该 PER2 基因突变在不同鸡种中的分布情况显示出其在某些商用鸡种中表现出较高的突变频率,这可能是通过现代育种选择保留下来的。而低频或无突变的群体可能保留了原始基因型。研究该突变对鸡群的生理影响对于理解基因与性状的关联以及未来的育种改良具有重要意义。
9 5661995 G/A A 0.089 missense_variant MODERATE PER2 rs312578832 9:5167666 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(3):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(27):0.000
Gallus_gallus_murghi(57):0.061
Gallus_gallus_spadiceus(42):0.071
Indonesia_Native_Chicken(36):0.056
Thailand_Native_Chicken(6):0.000
Vietnam_Native_Chicken(7):0.000
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.042
Xishuangbanna_Game_Chicken(10):0.000
Nixi_Chicken(12):0.000
Dulong_Chicken(7):0.000
Daweishan_Mini_Chicken(8):0.000
Guangxi_Chicken(6):0.083
Guangzhou_Chicken(5):0.000
Jiangxi_Silkies(20):0.000
Anyi_Gray_Chicken(4):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.167
Tianfu_Black-bone_Chicken(5):0.300
Shimian_Caoke_Chicken(4):0.000
Jiuyuan_Black-bone_Chicken(5):0.000
Jinyang_Silky_Chicken(6):0.083
Emei_Black_Chicken(6):0.167
Pengxian_Yellow_Chicken(6):0.000
Muchuan_Black-bone_Chicken(5):0.200
Miyi_Chicken(5):0.000
YuanBao_Chicken(24):0.125
Langshan_Chicken(10):0.000
Luxi_Game_Chicken(9):0.000
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.000
Bian_Chicken(8):0.062
Beijing_You_Chicken(11):0.045
Dagu_Chicken(7):0.071
Xinjiang_Native_Chicken(6):0.083
Hetian_Black_Chicken(8):0.125
Southern_Xinjiang_Game_Chicken(8):0.000
Turpan_Game_Chicken(8):0.000
Tibetan_Chicken(144):0.056
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(7):0.286
Bengal_Native_Chicken(15):0.100
India_Native_Chicken(45):0.156
Pakistan_Native_Chicken(36):0.139
Afghan_Native_Chicken(11):0.000
Iran_Native_Chicken(179):0.179
Iran_Commercial_Broiler(3):0.000
White_Leghorn_Chicken(13):0.269
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(0):NaN
White_Plymouth_Rock_Chicken(1):0.000
这段数据展示了 PER2 基因 的一个 G/A 突变,位于 9号染色体 的 5661995 位点。这个突变是一个 missense_variant(错义突变),意味着突变会导致编码的蛋白质中的某个氨基酸发生改变。其影响被标记为 MODERATE(中等影响),这表明该突变可能会对蛋白质功能产生一定影响,但不一定是致命的突变。
突变详情:
- 基因: PER2(Period Circadian Regulator 2,调控昼夜节律的基因,通常与生理节律、代谢、免疫等相关)。
- 突变位置: 9号染色体 5661995 位点。
- 突变类型: G/A 突变,导致错义突变。
- 变异ID: rs312578832,表示该变异已在数据库中记录。
- P值: 0.089,表示突变的频率为 8.9%。
不同鸡种中的突变频率:
下方的数据展示了不同鸡种中携带此突变的个体比例。括号中的数字表示样本数量,小数则表示突变频率。
高频突变群体:
- Tianfu_Black-bone_Chicken(天府黑骨鸡): 突变频率为 0.300,即30%的个体携带此突变。
- Sri_Lanka_Native_Chicken(斯里兰卡土鸡): 突变频率为 0.286,即28.6%的个体携带此突变。
- White_Leghorn_Chicken(白来亨鸡): 突变频率为 0.269,即26.9%的个体携带此突变。
- Iran_Native_Chicken(伊朗土鸡): 突变频率为 0.179,即17.9%的个体携带此突变。
- India_Native_Chicken(印度土鸡): 突变频率为 0.156。
中等频率突变群体:
- Muchuan_Black-bone_Chicken(沐川黑骨鸡): 突变频率为 0.200。
- Hetian_Black_Chicken(和田黑鸡): 突变频率为 0.125。
- YuanBao_Chicken(元宝鸡): 突变频率为 0.125。
- Pakistan_Native_Chicken(巴基斯坦土鸡): 突变频率为 0.139。
低频或无突变群体:
- Gallus_gallus_bankiva(野生原鸡)、Gallus_gallus_gallus(家鸡) 等许多鸡种显示突变频率为 0.000,即没有个体携带此突变。
- Bengal_Native_Chicken(孟加拉土鸡): 突变频率为 0.100,即10%的个体携带此突变。
这些低频或无突变的群体可能表明它们未经历与此突变相关的选择压力,或突变对它们的生理特性影响不大。
分析:
- 高频突变群体: Tianfu Black-bone Chicken(天府黑骨鸡) 和 Sri Lanka Native Chicken(斯里兰卡土鸡) 等显示出较高的突变频率,表明这些群体可能在进化过程中受到了与该突变相关的选择压力,或该突变对鸡种的某些生理性状(如免疫、昼夜节律)有积极作用。
- 中等频率突变群体: 一些土鸡种(如 Muchuan Black-bone Chicken 和 Hetian Black Chicken)突变频率较为中等,显示了它们可能在进化过程中部分保留了该突变。
- 低频或无突变群体: 大多数野生鸡种和一些本地鸡种显示出突变频率较低或为零,这可能是因为这些鸡种未经历该突变相关的选择压力,或者该突变没有带来明显的生理优势。
研究意义:
PER2 基因 参与调控昼夜节律,因此该突变可能会影响鸡的昼夜节律、生理节奏和代谢功能。研究这些突变在不同鸡种中的分布可以揭示它们对鸡群适应性和生产性能的影响。
高频突变群体 中的突变可能是通过自然选择或育种过程中保留下来的,可能对生产性能或其他性状有益。尤其是商用鸡种(如 White Leghorn Chicken)中,该突变可能对鸡的生产性能产生积极影响。
低频或无突变群体 可以作为对照,帮助研究为什么这些群体没有保留该突变,以及它们在进化过程中如何适应不同的环境。
进一步研究建议:
- 功能验证: 通过基因表达和功能研究,验证该突变是否影响 PER2 基因在调控昼夜节律和生理节奏方面的功能。
- 表型关联分析: 结合昼夜节律、生长性能、代谢功能等表型数据,进行基因-性状关联分析,研究该突变对鸡种的生理特性是否有影响。
- 育种应用: 如果发现该突变对生产性能有正面影响,可以将其应用于育种过程中,提升鸡种的生产效率或适应能力。
总结:
PER2 基因 中的这个 G/A 突变 在不同鸡种中的分布显示了不同的选择压力和进化历程。高频突变群体可能从中受益,而低频或无突变的群体则保留了更原始的基因型。这种突变可能对鸡的昼夜节律、生长和代谢有潜在的影响,值得进一步研究。
9 5666426 G/A A 0.110 missense_variant MODERATE PER2 rs316278075 9:5172106 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(4):0.000
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(26):0.038
Gallus_gallus_murghi(53):0.085
Gallus_gallus_spadiceus(44):0.114
Indonesia_Native_Chicken(36):0.028
Thailand_Native_Chicken(5):0.000
Vietnam_Native_Chicken(7):0.071
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.083
Xishuangbanna_Game_Chicken(9):0.056
Nixi_Chicken(12):0.000
Dulong_Chicken(7):0.214
Daweishan_Mini_Chicken(8):0.062
Guangxi_Chicken(6):0.167
Guangzhou_Chicken(2):0.000
Jiangxi_Silkies(20):0.150
Anyi_Gray_Chicken(4):0.625
Dongxiang_Blue-eggshell_Chicken(6):0.333
Tianfu_Black-bone_Chicken(5):0.400
Shimian_Caoke_Chicken(2):0.500
Jiuyuan_Black-bone_Chicken(5):0.100
Jinyang_Silky_Chicken(6):0.167
Emei_Black_Chicken(4):0.000
Pengxian_Yellow_Chicken(6):0.083
Muchuan_Black-bone_Chicken(5):0.100
Miyi_Chicken(5):0.000
YuanBao_Chicken(23):0.000
Langshan_Chicken(10):0.300
Luxi_Game_Chicken(9):0.056
Shouguang_Chicken(8):0.250
Gushi_Chicken(8):0.312
Bian_Chicken(7):0.214
Beijing_You_Chicken(11):0.136
Dagu_Chicken(8):0.250
Xinjiang_Native_Chicken(6):0.000
Hetian_Black_Chicken(8):0.062
Southern_Xinjiang_Game_Chicken(8):0.125
Turpan_Game_Chicken(8):0.062
Tibetan_Chicken(133):0.060
Araucana_Blue-eggshell_Chicken(6):0.000
Sri_Lanka_Native_Chicken(7):0.071
Bengal_Native_Chicken(14):0.036
India_Native_Chicken(45):0.078
Pakistan_Native_Chicken(37):0.122
Afghan_Native_Chicken(11):0.136
Iran_Native_Chicken(182):0.168
Iran_Commercial_Broiler(4):0.250
White_Leghorn_Chicken(13):0.038
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):1.000
White_Plymouth_Rock_Chicken(1):0.000
这段数据展示了 PER2 基因 的一个 G/A 突变,位于 9号染色体 的 5666426 位点。这个突变是一个 missense_variant(错义突变),即该突变导致编码的蛋白质中的一个氨基酸发生改变。它的影响被标记为 MODERATE(中等影响),意味着该突变可能对蛋白质功能产生一定影响,但不会造成致命性后果。
突变详情:
- 基因: PER2(Period Circadian Regulator 2,调控昼夜节律的基因,与生理节律、代谢、免疫等相关)。
- 突变位置: 9号染色体 5666426 位点。
- 突变类型: G/A 突变,导致错义突变。
- 变异ID: rs316278075,该变异已在数据库中记录。
- P值: 0.110,表示突变的频率为 11%。
不同鸡种中的突变频率:
下方的数据展示了不同鸡种中携带此突变的个体比例。括号中的数字表示样本数量,小数表示突变频率。例如:
高频突变群体:
- Rhode_Island_Red_Chicken(罗德岛红鸡): 突变频率为 1.000,说明所有采样的个体都携带此突变。
- Anyi_Gray_Chicken(安义灰鸡): 突变频率为 0.625,即62.5%的个体携带此突变。
- Tianfu_Black-bone_Chicken(天府黑骨鸡): 突变频率为 0.400,即40%的个体携带此突变。
- Shimian_Caoke_Chicken(石棉草科鸡): 突变频率为 0.500,即50%的个体携带此突变。
- Dongxiang_Blue-eggshell_Chicken(东乡蓝壳蛋鸡): 突变频率为 0.333。
中等频率突变群体:
- Jiangxi_Silkies(江西丝羽鸡): 突变频率为 0.150。
- Muchuan_Black-bone_Chicken(沐川黑骨鸡) 和 Jiuyuan_Black-bone_Chicken(九元黑骨鸡): 突变频率分别为 0.100。
- Pakistan_Native_Chicken(巴基斯坦土鸡): 突变频率为 0.122。
低频或无突变群体:
- Gallus_gallus_bankiva(原鸡) 和 Gallus_gallus_gallus(家鸡) 等显示突变频率为 0.000,即没有个体携带该突变。
- Cornish_Chicken(康尼什鸡): 突变频率为 0.000,该群体中没有发现此突变。
这些低频或无突变的群体可能表明它们没有经历相关的选择压力,或该突变对它们的生理特性影响较小。
分析:
- 高频突变群体: Rhode Island Red Chicken 和 Anyi Gray Chicken 等显示出较高的突变频率,表明这些群体在进化或育种过程中可能经历了与该突变相关的选择压力,或该突变对它们的某些生理性状(如昼夜节律、免疫调节等)有积极作用。
- 中等频率突变群体: 部分本地鸡种(如 Muchuan Black-bone Chicken 和 Pakistan Native Chicken)显示中等突变频率,说明这些鸡种可能保留了部分突变,但该突变并未完全在群体中固定。
- 低频或无突变群体: 野生鸡种和部分商用鸡种显示出较低或为零的突变频率,表明这些群体可能没有经历该突变相关的选择压力,或者该突变对它们没有显著的生理优势。
研究意义:
- PER2 基因 作为昼夜节律调控的重要基因之一,该突变可能对鸡的昼夜节律、代谢、免疫调节等产生影响。研究不同鸡种中的突变频率有助于了解这些突变如何影响鸡种的适应性和生产性能。
- 高频突变群体 中的突变可能是通过自然选择或育种选择保留下来的,表明该突变可能对生产性能或其他相关性状具有潜在益处。
- 低频或无突变群体 可以作为对照,帮助理解为什么某些群体没有保留此突变,以及它们在进化过程中如何适应环境或遗传压力。
进一步研究建议:
- 功能验证: 通过基因表达和功能研究,验证该突变是否对 PER2 基因功能产生影响,尤其是对昼夜节律和代谢调控方面的影响。
- 表型关联分析: 结合生理节律、代谢、生产性能等表型数据,进行基因-性状关联分析,研究该突变是否对鸡种的生理特性有影响。
- 育种应用: 如果该突变显示出对生产性能或其他有益性状的正面影响,则可以在育种过程中应用此突变,以提高鸡种的生产效率和适应性。
总结:
该 PER2 基因 中的 G/A 突变 在不同鸡种中的分布显示了选择压力的差异。高频突变群体可能从中受益,而低频或无突变的群体则保留了更原始的基因型。这种突变可能对鸡的昼夜节律、代谢和免疫调节有潜在的影响,值得进一步研究以便更好地理解其生物学意义并探索其在育种中的应用潜力。
GWAS
1 67584954 intergenic LOC107054073,BHLHE41 rs317343491 1:67668163 Effective layer thickness of eggshell 7.06E-07 27456605 Gbrowse
这段数据展示了一项 GWAS(基因组广泛关联研究) 结果,重点研究了与 鸡蛋壳有效厚度(Effective layer thickness of eggshell) 相关的遗传变异。具体详情如下:
字段解释:
- Chr(染色体): 该变异位于 1号染色体 上。
- Position(位置): 该突变的具体位置为 67584954,这是在1号染色体上的特定位点。
- Consequence type(变异结果类型): 变异类型是 intergenic(基因间区变异),表示该变异位于两个基因之间,而不是在编码区或调控区。此处变异影响的是 LOC107054073 和 BHLHE41 基因。
- LOC107054073: 一个假设基因或未完全注释的基因。
- BHLHE41: 是一个与昼夜节律和代谢调节相关的基因。
- Variation ID(变异ID): rs317343491,是数据库中记录的这个变异的唯一标识符。
- Position of GRCg7b(GRCg7b参考基因组的位置): 1:67668163,这是在 GRCg7b参考基因组 中的相对位置。
- Traits(性状): 研究的性状是 鸡蛋壳的有效厚度,即鸡蛋壳结构中功能性部分的厚度。这种性状与鸡蛋壳的质量和强度直接相关,影响了鸡蛋在运输和储存中的表现。
- P-value(P值): 7.06E-07,表示突变与该性状之间的关联非常显著(P值越低,结果越显著)。
- PMID: 27456605,这是这项研究的 PubMed ID,你可以通过这个ID在PubMed数据库中查找相关的研究论文。
- Visualization(可视化): 通过 Gbrowse 工具可以查看基因组中的突变位置及其与相关性状的关联可视化信息。
总结:
这项研究发现了位于 1号染色体 上的一个 intergenic(基因间区) 突变,它与 鸡蛋壳有效厚度 密切相关。尽管该变异位于两个基因之间,但它可能通过调控基因表达或影响与鸡蛋壳形成相关的生物过程发挥作用。突变的 P值 非常显著,表明该突变与鸡蛋壳厚度的关系极强,这对家禽育种和蛋壳质量的改良具有潜在价值。通过查阅 PMID 27456605 的文献,你可以获得更多详细的研究背景和分析。
CLOCK
4 65101760 T/A A 0.335 missense_variant MODERATE CLOCK rs312574810 4:64620304 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(4):0.000
Gallus_gallus_gallus(6):0.167
Gallus_gallus_jabouillei(26):0.000
Gallus_gallus_murghi(61):0.115
Gallus_gallus_spadiceus(42):0.238
Indonesia_Native_Chicken(35):0.571
Thailand_Native_Chicken(5):0.500
Vietnam_Native_Chicken(7):0.357
Wenchang_Chicken(1):1.000
Yunnan_Chicken(11):0.455
Xishuangbanna_Game_Chicken(10):0.550
Nixi_Chicken(12):0.167
Dulong_Chicken(7):0.214
Daweishan_Mini_Chicken(8):0.625
Guangxi_Chicken(6):0.750
Guangzhou_Chicken(4):0.000
Jiangxi_Silkies(19):0.789
Anyi_Gray_Chicken(5):0.700
Dongxiang_Blue-eggshell_Chicken(6):0.583
Tianfu_Black-bone_Chicken(5):0.200
Shimian_Caoke_Chicken(4):0.000
Jiuyuan_Black-bone_Chicken(5):0.500
Jinyang_Silky_Chicken(6):0.417
Emei_Black_Chicken(5):0.100
Pengxian_Yellow_Chicken(6):0.250
Muchuan_Black-bone_Chicken(5):0.200
Miyi_Chicken(5):0.700
YuanBao_Chicken(22):0.159
Langshan_Chicken(10):0.650
Luxi_Game_Chicken(9):0.611
Shouguang_Chicken(8):0.875
Gushi_Chicken(7):0.857
Bian_Chicken(8):0.812
Beijing_You_Chicken(11):0.500
Dagu_Chicken(8):0.875
Xinjiang_Native_Chicken(6):0.333
Hetian_Black_Chicken(7):0.357
Southern_Xinjiang_Game_Chicken(5):0.100
Turpan_Game_Chicken(7):0.500
Tibetan_Chicken(136):0.191
Araucana_Blue-eggshell_Chicken(6):0.250
Sri_Lanka_Native_Chicken(6):0.167
Bengal_Native_Chicken(15):0.167
India_Native_Chicken(42):0.321
Pakistan_Native_Chicken(37):0.297
Afghan_Native_Chicken(11):0.364
Iran_Native_Chicken(178):0.393
Iran_Commercial_Broiler(4):0.500
White_Leghorn_Chicken(13):0.077
Cornish_Chicken(1):0.500
Rhode_Island_Red_Chicken(1):1.000
White_Plymouth_Rock_Chicken(1):1.000
这段数据展示了 CLOCK 基因 的一个 T/A 突变,位于 4号染色体 的 65101760 位点。这个突变是一个 missense_variant(错义突变),意味着该突变会导致蛋白质中的某个氨基酸发生改变。其影响被标记为 MODERATE(中等影响),表明该突变可能对蛋白质功能产生一定影响,但不会致命。
突变详情:
- 基因: CLOCK(Circadian Locomotor Output Cycles Kaput),这个基因是昼夜节律调控的关键基因之一,调节生物的内在生理节律。
- 突变位置: 4号染色体 65101760 位点。
- 突变类型: T/A 突变,导致错义突变。
- 变异ID: rs312574810,该变异已在数据库中记录。
- P值: 0.335,表示突变的频率为 33.5%。
不同鸡种中的突变频率:
下方展示了该突变在不同鸡种中的频率,括号中的数字表示样本数量,小数表示突变频率。例如:
高频突变群体:
- Wenchang_Chicken(文昌鸡) 和 White_Plymouth_Rock_Chicken(白普利茅斯鸡): 突变频率为 1.000,即所有采样的个体都携带此突变。
- Jiangxi_Silkies(江西丝羽鸡): 突变频率为 0.789,即78.9%的个体携带此突变。
- Gushi_Chicken(固始鸡): 突变频率为 0.857。
- Dagu_Chicken(大骨鸡): 突变频率为 0.875,这表明这些群体在选择压力下很可能保留了该突变。
中等频率突变群体:
- Guangxi_Chicken(广西鸡) 和 Anyi_Gray_Chicken(安义灰鸡): 突变频率分别为 0.750 和 0.700。
- Miyi_Chicken(米易鸡): 突变频率为 0.700。
- Indonesia_Native_Chicken(印度尼西亚土鸡): 突变频率为 0.571。
- Beijing_You_Chicken(北京油鸡): 突变频率为 0.500。
低频或无突变群体:
- Gallus_gallus_bankiva(野生原鸡)、Gallus_gallus_jabouillei(越南原鸡) 和 Gallus_gallus_gallus(家鸡) 等群体显示突变频率为 0.000,即没有个体携带该突变。
- Tibetan_Chicken(藏鸡): 突变频率为 0.191,即19.1%的个体携带此突变。
分析:
高频突变群体:如 Wenchang Chicken(文昌鸡) 和 White Plymouth Rock Chicken 等显示出较高的突变频率,表明这些群体可能在进化或育种过程中受到了与该突变相关的选择压力。这些群体可能通过该突变获得了生理上的优势,例如昼夜节律调控的优化,从而提升了生产性能或适应环境的能力。
中等频率突变群体:如 Indonesia Native Chicken 和 Beijing You Chicken 等显示中等频率,说明这些鸡种中有较多个体保留了该突变,可能在一定程度上受到了选择压力,或者该突变对它们的生理功能产生了某种影响。
低频或无突变群体:像 Gallus_gallus_bankiva 和 Gallus_gallus_jabouillei 等野生鸡种中突变频率为零,表明这些群体没有经历与该突变相关的选择压力,或者该突变在这些鸡种中没有带来显著的生理优势。
研究意义:
- CLOCK 基因 是昼夜节律调控的关键基因,研究该突变有助于理解该基因如何在不同鸡种中影响昼夜节律、生理节奏、代谢和生产性能。
- 高频突变鸡种 中的突变可能是通过自然选择或育种过程中保留下来的。研究这些突变与生产性能(如产蛋率、健康状况、昼夜节律调控)的关联,能够揭示育种中如何优化这些性状。
- 低频或无突变群体 可以作为对照,帮助理解为何这些群体没有保留该突变,及其对生理节律和生产性能的潜在影响。
进一步研究建议:
- 功能验证:通过基因表达分析或功能实验,研究该突变对 CLOCK 基因功能的影响,特别是在昼夜节律调控方面的作用。
- 表型关联分析:结合生产性能(如产蛋率、昼夜节律、代谢功能等)进行基因-性状关联分析,探讨该突变是否对这些性状产生积极影响。
- 育种应用:如果发现该突变与生产性能有正相关性,可以将其应用于育种,改善鸡种的昼夜节律调控能力,从而提高生产效率。
总结:
CLOCK 基因 中的 T/A 突变 在不同鸡种中的分布显示了不同的选择压力。高频突变群体可能通过该突变优化了昼夜节律调控,而低频或无突变的群体则可能保留了更原始的基因型。该突变可能对鸡种的昼夜节律、生理节奏和生产性能产生重要影响,值得进一步研究。
Chr Position Consequence type Gene symbol Variation ID Position of GRCg7b Traits P-value PMID Visualization
1 53621191 intronic CRY1 rs13653575 1:53667359 Number of fighting times in days with frequencies not less than 4 times per day 3.85E-06 27485826 Gbrowse
这段数据展示了一项 GWAS(基因组广泛关联研究) 结果,研究的是 CRY1 基因 中的一个 rs13653575 变异与特定行为特征之间的关联,具体行为特征为 每日打斗频率不小于4次的天数。以下是对各字段的详细解释:
字段解释:
- Chr(染色体): 突变位于 1号染色体 上。
- Position(位置): 该突变位于 53621191 位点。
- Consequence type(变异结果类型): intronic,该突变位于 CRY1 基因的内含子(非编码区)中,可能影响基因的调控或表达。
- Gene symbol(基因符号): CRY1,这是一个与昼夜节律相关的基因,参与调控生物的生理节律。
- Variation ID(变异ID): rs13653575,这是该变异在数据库中的唯一标识符。
- Position of GRCg7b(GRCg7b参考基因组的位置): 1:53667359,表示该突变在 GRCg7b 参考基因组中的相对位置。
- Traits(性状): 每日打斗频率不小于4次的天数,这是一个与行为相关的性状,表明突变可能影响动物的攻击性或行为特征。
- P-value(P值): 3.85E-06,表示该突变与该性状的关联非常显著,P值越低,关联越强。
- PMID: 27485826,这是该研究的 PubMed ID,可通过此ID查找相关文献以了解更多细节。
- Visualization(可视化): Gbrowse 是一种基因组浏览工具,可用于可视化该突变在基因组中的具体位置。
数据解读:
- 该研究发现了 CRY1 基因 内含子区域的一个变异 rs13653575,与 每日打斗频率不小于4次的天数 密切相关。CRY1 基因 与生物的昼夜节律密切相关,可能通过影响生理节律来调节动物的行为特征,尤其是攻击性或应激反应。
- P值 非常显著(3.85E-06),表明该基因变异与行为之间的关联非常强。这提示了昼夜节律基因在调节动物行为(如攻击性)中的潜在作用。
研究意义:
- CRY1 基因 作为昼夜节律调控的重要基因,其变异可能对生物行为产生广泛影响。通过研究这些基因变异,可以揭示生物的昼夜节律与行为特征之间的关联,特别是在动物的社交行为、攻击性等方面。
- 该突变可能在家禽或其他动物的行为育种中有一定应用价值。例如,了解与攻击性相关的基因可能有助于育种中减少这些不良行为,提高动物的生产性能和适应能力。
进一步研究建议:
- 功能研究:进一步研究该变异如何影响 CRY1 基因的表达和功能,从而调节与打斗行为相关的生理机制。
- 行为与基因关联分析:结合其他行为数据(如社交行为、应激反应等),深入探讨 CRY1 基因变异如何影响动物的整体行为特征。
- 育种应用:如果发现该突变对减少攻击性或行为异常有正面作用,可能在家禽或其他动物的育种过程中加以利用,优化行为特征。
总结:
这项研究揭示了 CRY1 基因 的内含子变异与动物攻击性行为之间的显著关联,尤其是每日打斗频率较高的天数。该发现有助于理解昼夜节律基因如何影响行为,并可能在行为育种和生理研究中具有重要意义。
21 297018 G/A A 0.457 missense_variant MODERATE PER3 rs313019903 21:284945 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(3):1.000
Gallus_gallus_gallus(6):0.750
Gallus_gallus_jabouillei(27):0.944
Gallus_gallus_murghi(46):0.935
Gallus_gallus_spadiceus(42):0.262
Indonesia_Native_Chicken(34):0.412
Thailand_Native_Chicken(6):0.167
Vietnam_Native_Chicken(7):0.571
Wenchang_Chicken(1):0.500
Yunnan_Chicken(12):0.375
Xishuangbanna_Game_Chicken(10):0.300
Nixi_Chicken(12):0.000
Dulong_Chicken(6):0.500
Daweishan_Mini_Chicken(7):0.214
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(4):0.375
Jiangxi_Silkies(20):0.325
Anyi_Gray_Chicken(5):0.400
Dongxiang_Blue-eggshell_Chicken(6):0.167
Tianfu_Black-bone_Chicken(5):0.300
Shimian_Caoke_Chicken(4):0.250
Jiuyuan_Black-bone_Chicken(5):0.300
Jinyang_Silky_Chicken(6):0.417
Emei_Black_Chicken(6):0.583
Pengxian_Yellow_Chicken(6):0.333
Muchuan_Black-bone_Chicken(5):0.700
Miyi_Chicken(5):0.800
YuanBao_Chicken(23):0.391
Langshan_Chicken(9):0.111
Luxi_Game_Chicken(9):0.333
Shouguang_Chicken(8):0.000
Gushi_Chicken(7):0.500
Bian_Chicken(8):0.375
Beijing_You_Chicken(11):0.545
Dagu_Chicken(8):0.125
Xinjiang_Native_Chicken(6):0.333
Hetian_Black_Chicken(8):0.438
Southern_Xinjiang_Game_Chicken(8):0.312
Turpan_Game_Chicken(8):0.438
Tibetan_Chicken(144):0.316
Araucana_Blue-eggshell_Chicken(6):0.250
Sri_Lanka_Native_Chicken(7):0.143
Bengal_Native_Chicken(14):0.714
India_Native_Chicken(43):0.512
Pakistan_Native_Chicken(36):0.403
Afghan_Native_Chicken(10):0.400
Iran_Native_Chicken(180):0.589
Iran_Commercial_Broiler(4):0.250
White_Leghorn_Chicken(12):0.625
Cornish_Chicken(1):0.500
Rhode_Island_Red_Chicken(1):1.000
White_Plymouth_Rock_Chicken(1):0.500
这段数据展示了 PER3 基因 的一个 G/A 突变,位于 21号染色体 的 297018 位点。这个突变是一个 missense_variant(错义突变),即突变会导致编码的蛋白质中的某个氨基酸发生改变。它的影响被标记为 MODERATE(中等影响),表明该突变可能会对蛋白质功能产生一定影响,但不会致命。
突变详情:
- 基因: PER3(Period Circadian Regulator 3),PER3 基因与昼夜节律调控相关,调节生物的生理节律。
- 突变位置: 21号染色体 297018 位点。
- 突变类型: G/A 突变,导致错义突变。
- 变异ID: rs313019903,表示该变异已在数据库中记录。
- P值: 0.457,表示该突变的频率为 45.7%。
不同鸡种中的突变频率:
下方的数据展示了该突变在不同鸡种中的频率,括号中的数字表示样本数量,小数表示突变频率。例如:
高频突变群体:
- Gallus_gallus_bankiva(原鸡): 突变频率为 1.000,即所有采样的个体都携带该突变。
- Gallus_gallus_jabouillei(越南原鸡): 突变频率为 0.944,即94.4%的个体携带该突变。
- Gallus_gallus_murghi(家鸡): 突变频率为 0.935,即93.5%的个体携带该突变。
- Bengal_Native_Chicken(孟加拉土鸡): 突变频率为 0.714,即71.4%的个体携带该突变。
- Iran_Native_Chicken(伊朗土鸡): 突变频率为 0.589,即58.9%的个体携带该突变。
中等频率突变群体:
- White_Leghorn_Chicken(白来亨鸡): 突变频率为 0.625。
- Muchuan_Black-bone_Chicken(沐川黑骨鸡): 突变频率为 0.700。
- Vietnam_Native_Chicken(越南土鸡): 突变频率为 0.571。
- India_Native_Chicken(印度土鸡): 突变频率为 0.512。
低频或无突变群体:
- Nixi_Chicken(尼西鸡) 和 Guangxi_Chicken(广西鸡) 显示突变频率为 0.000,即这些鸡种中没有个体携带此突变。
- Dagu_Chicken(大骨鸡): 突变频率为 0.125,即12.5%的个体携带该突变。
- Tibetan_Chicken(藏鸡): 突变频率为 0.316,即31.6%的个体携带该突变。
分析:
高频突变群体: Gallus_gallus_bankiva(原鸡) 和 Gallus_gallus_jabouillei(越南原鸡) 等显示出非常高的突变频率,表明这些群体可能受到了与该突变相关的选择压力。高频突变可能反映了这些群体在进化过程中对昼夜节律调控基因的遗传保留。
中等频率突变群体: 部分本地鸡种(如 Muchuan Black-bone Chicken 和 India Native Chicken)显示中等突变频率,表明这些鸡种可能保留了部分突变,同时仍然保留了原始的基因型。
低频或无突变群体: 像 Nixi Chicken 和 Guangxi Chicken 等野生或地方鸡种中突变频率较低或为零,表明这些鸡种未经历与该突变相关的选择压力,或者该突变在这些鸡种中没有显著的生理优势。
研究意义:
- PER3 基因 作为昼夜节律调控的重要基因,其突变可能对鸡种的昼夜节律、生理节奏和代谢功能产生影响。研究这些突变的分布有助于揭示昼夜节律基因如何影响不同鸡种的行为、健康和适应性。
- 高频突变群体 可能保留了这些突变,通过自然选择或育种过程,突变可能对鸡种的生产性能、适应能力或生理节律产生影响。
进一步研究建议:
- 功能验证:进一步研究该突变对 PER3 基因的功能影响,特别是在调控昼夜节律和代谢功能方面。
- 表型关联分析:结合鸡的生产性能、昼夜节律、行为等表型数据,进行基因-性状关联分析,研究该突变是否对鸡种的生理特性产生影响。
- 育种应用:如果该突变显示出与生产性能、健康或适应能力相关的正面影响,可以在育种过程中应用这些信息,优化鸡种的昼夜节律和代谢调控能力。
总结:
PER3 基因 中的 G/A 突变 在不同鸡种中的分布显示了选择压力的差异。高频突变群体可能通过该突变优化了昼夜节律和代谢功能,而低频或无突变的群体则保留了原始的基因型。这种突变可能对鸡种的生理节律、行为和生产性能产生重要影响,值得进一步研究。
21 297147 G/A A 0.061 missense_variant MODERATE PER3 rs317669303 21:285074 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(3):0.167
Gallus_gallus_gallus(6):0.000
Gallus_gallus_jabouillei(27):0.019
Gallus_gallus_murghi(54):0.019
Gallus_gallus_spadiceus(44):0.011
Indonesia_Native_Chicken(35):0.029
Thailand_Native_Chicken(6):0.000
Vietnam_Native_Chicken(5):0.000
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.000
Xishuangbanna_Game_Chicken(10):0.000
Nixi_Chicken(11):0.000
Dulong_Chicken(7):0.000
Daweishan_Mini_Chicken(8):0.000
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(4):0.000
Jiangxi_Silkies(20):0.000
Anyi_Gray_Chicken(4):0.000
Dongxiang_Blue-eggshell_Chicken(6):0.000
Tianfu_Black-bone_Chicken(5):0.000
Shimian_Caoke_Chicken(4):0.000
Jiuyuan_Black-bone_Chicken(5):0.100
Jinyang_Silky_Chicken(6):0.000
Emei_Black_Chicken(6):0.000
Pengxian_Yellow_Chicken(6):0.250
Muchuan_Black-bone_Chicken(5):0.100
Miyi_Chicken(5):0.000
YuanBao_Chicken(22):0.000
Langshan_Chicken(8):0.000
Luxi_Game_Chicken(8):0.000
Shouguang_Chicken(8):0.000
Gushi_Chicken(7):0.000
Bian_Chicken(6):0.167
Beijing_You_Chicken(11):0.000
Dagu_Chicken(8):0.000
Xinjiang_Native_Chicken(6):0.083
Hetian_Black_Chicken(8):0.250
Southern_Xinjiang_Game_Chicken(8):0.000
Turpan_Game_Chicken(8):0.062
Tibetan_Chicken(147):0.065
Araucana_Blue-eggshell_Chicken(6):0.333
Sri_Lanka_Native_Chicken(7):0.000
Bengal_Native_Chicken(15):0.033
India_Native_Chicken(48):0.052
Pakistan_Native_Chicken(36):0.056
Afghan_Native_Chicken(11):0.000
Iran_Native_Chicken(182):0.115
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(12):0.583
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):0.000
White_Plymouth_Rock_Chicken(1):0.000
这段数据展示了 PER3 基因 的一个 G/A 突变,位于 21号染色体 的 297147 位点。这个突变是一个 missense_variant(错义突变),意味着该突变会导致编码的蛋白质中的某个氨基酸发生改变,可能对蛋白质功能产生一定影响。这个影响被标记为 MODERATE(中等影响),表明该突变的功能影响可能是中度的,但不致命。
突变详情:
- 基因: PER3(Period Circadian Regulator 3),是一个与昼夜节律调控相关的基因,可能影响生物的生理节律。
- 突变位置: 21号染色体 297147 位点。
- 突变类型: G/A 突变,导致错义突变。
- 变异ID: rs317669303,这是数据库中记录的突变ID。
- P值: 0.061,表示该突变的频率为 6.1%。
不同鸡种中的突变频率:
下方展示了该突变在不同鸡种中的频率,括号中的数字表示样本数量,小数表示突变频率。例如:
高频突变群体:
- Araucana_Blue-eggshell_Chicken(阿劳卡纳蓝壳蛋鸡): 突变频率为 0.333,即33.3%的个体携带该突变。
- White_Leghorn_Chicken(白来亨鸡): 突变频率为 0.583,即58.3%的个体携带该突变。
- Iran_Native_Chicken(伊朗土鸡): 突变频率为 0.115,即11.5%的个体携带该突变。
中等频率突变群体:
- Hetian_Black_Chicken(和田黑鸡): 突变频率为 0.250,即25%的个体携带该突变。
- Pengxian_Yellow_Chicken(彭县黄鸡): 突变频率为 0.250。
低频或无突变群体:
- Gallus_gallus_bankiva(野生原鸡): 突变频率为 0.167,即16.7%的个体携带该突变。
- Bengal_Native_Chicken(孟加拉土鸡): 突变频率为 0.033,即3.3%的个体携带该突变。
- Gallus_gallus_gallus(家鸡)、Guangxi_Chicken(广西鸡) 和许多其他鸡种显示突变频率为 0.000,即没有个体携带该突变。
这些低频或无突变的群体可能表明这些鸡种没有经历相关的选择压力,或者该突变对这些群体没有显著的生理优势。
分析:
高频突变群体: White Leghorn Chicken 和 Araucana Blue-eggshell Chicken 等显示出较高的突变频率,表明这些鸡种可能在进化或育种过程中保留了该突变。可能这些群体中该基因突变带来了某种生理优势,如昼夜节律的调控优化或其他代谢功能的改进。
中等频率突变群体: 像 Hetian Black Chicken 和 Pengxian Yellow Chicken 等显示出中等的突变频率,表明这些鸡种中该突变的遗传压力适中,可能与它们的环境或育种历史相关。
低频或无突变群体: Gallus gallus gallus 等鸡种中突变频率较低或为零,表明这些群体可能没有经历与该突变相关的遗传选择,或者该突变对这些群体没有带来显著的生理优势。
研究意义:
- PER3 基因 作为昼夜节律调控的重要基因,其突变可能影响鸡的生理节律、代谢调控和行为特征。研究这些突变在不同鸡种中的分布可以帮助揭示不同群体对昼夜节律和环境适应性的差异。
- 高频突变群体 可能通过自然选择或育种选择保留了这些突变,这表明这些突变可能在生产性能或健康状况上有潜在的积极作用。
进一步研究建议:
- 功能验证: 进一步研究该突变如何影响 PER3 基因的功能,特别是在调节昼夜节律和代谢调控方面的作用。
- 基因-性状关联分析: 结合生产性能、昼夜节律、行为特征等表型数据,探讨该突变是否对鸡种的生理特性产生影响。
- 育种应用: 如果该突变对生产性能或适应能力有正面影响,可以在育种过程中应用该信息,提高鸡种的生产效率和健康水平。
总结:
PER3 基因 中的 G/A 突变 在不同鸡种中的分布显示了不同的遗传选择压力。高频突变群体可能受益于该突变在昼夜节律和代谢功能调控中的积极影响,而低频或无突变的群体则可能保留了原始的基因型。
21 297675 T/G G 0.205 missense_variant MODERATE PER3 rs317619388 21:285602 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(4):1.000
Gallus_gallus_gallus(6):0.583
Gallus_gallus_jabouillei(27):0.519
Gallus_gallus_murghi(54):0.556
Gallus_gallus_spadiceus(41):0.085
Indonesia_Native_Chicken(35):0.157
Thailand_Native_Chicken(6):0.083
Vietnam_Native_Chicken(7):0.214
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.042
Xishuangbanna_Game_Chicken(10):0.200
Nixi_Chicken(12):0.000
Dulong_Chicken(7):0.071
Daweishan_Mini_Chicken(8):0.062
Guangxi_Chicken(6):0.000
Guangzhou_Chicken(4):0.375
Jiangxi_Silkies(19):0.026
Anyi_Gray_Chicken(4):0.250
Dongxiang_Blue-eggshell_Chicken(6):0.083
Tianfu_Black-bone_Chicken(4):0.250
Shimian_Caoke_Chicken(4):0.250
Jiuyuan_Black-bone_Chicken(5):0.200
Jinyang_Silky_Chicken(6):0.167
Emei_Black_Chicken(5):0.300
Pengxian_Yellow_Chicken(6):0.083
Muchuan_Black-bone_Chicken(5):0.400
Miyi_Chicken(5):0.100
YuanBao_Chicken(24):0.000
Langshan_Chicken(10):0.150
Luxi_Game_Chicken(8):0.062
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.188
Bian_Chicken(8):0.188
Beijing_You_Chicken(11):0.091
Dagu_Chicken(8):0.000
Xinjiang_Native_Chicken(5):0.100
Hetian_Black_Chicken(8):0.062
Southern_Xinjiang_Game_Chicken(8):0.125
Turpan_Game_Chicken(8):0.000
Tibetan_Chicken(137):0.113
Araucana_Blue-eggshell_Chicken(6):0.083
Sri_Lanka_Native_Chicken(7):0.071
Bengal_Native_Chicken(14):0.286
India_Native_Chicken(42):0.274
Pakistan_Native_Chicken(36):0.236
Afghan_Native_Chicken(11):0.182
Iran_Native_Chicken(180):0.281
Iran_Commercial_Broiler(4):0.000
White_Leghorn_Chicken(13):0.000
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):1.000
White_Plymouth_Rock_Chicken(1):0.500
这段数据展示了 PER3 基因 的一个 T/G 突变,位于 21号染色体 的 297675 位点。这个突变是一个 missense_variant(错义突变),意味着该突变导致蛋白质中的一个氨基酸发生改变,可能对蛋白质的功能产生一定的影响。影响程度被标记为 MODERATE(中等影响)。
突变详情:
- 基因: PER3(Period Circadian Regulator 3),是调节昼夜节律的基因,与生物的生理节律有关。
- 突变位置: 21号染色体的 297675 位点。
- 突变类型: T/G 突变,导致错义突变。
- 变异ID: rs317619388,这是该突变在数据库中的唯一标识符。
- P值: 0.205,表示该突变的频率为 20.5%。
不同鸡种中的突变频率:
下方展示了该突变在不同鸡种中的频率,括号中的数字表示样本数量,小数表示突变频率。例如:
高频突变群体:
- Gallus_gallus_bankiva(野生原鸡): 突变频率为 1.000,即所有采样的个体都携带此突变。
- Gallus_gallus_gallus(家鸡): 突变频率为 0.583,即58.3%的个体携带该突变。
- Gallus_gallus_jabouillei(越南原鸡) 和 Gallus_gallus_murghi(家鸡): 突变频率分别为 0.519 和 0.556。
- Rhode_Island_Red_Chicken(罗德岛红鸡): 突变频率为 1.000,即100%的个体携带该突变。
中等频率突变群体:
- Afghan_Native_Chicken(阿富汗土鸡): 突变频率为 0.182。
- India_Native_Chicken(印度土鸡): 突变频率为 0.274。
- Iran_Native_Chicken(伊朗土鸡): 突变频率为 0.281。
- Bengal_Native_Chicken(孟加拉土鸡): 突变频率为 0.286。
低频或无突变群体:
- Nixi_Chicken(尼西鸡) 和 YuanBao_Chicken(元宝鸡) 等显示突变频率为 0.000,即这些鸡种中没有个体携带此突变。
- Beijing_You_Chicken(北京油鸡): 突变频率为 0.091,即9.1%的个体携带该突变。
- White_Leghorn_Chicken(白来亨鸡) 和 Cornish_Chicken(康尼什鸡): 突变频率为 0.000,表明这些群体中没有个体携带该突变。
这些低频或无突变的群体表明它们可能没有经历该突变的选择压力,或者该突变对这些鸡种没有带来显著的生理优势。
分析:
高频突变群体: Gallus_gallus_bankiva(野生原鸡) 和 Rhode Island Red Chicken 等显示出较高的突变频率,表明这些群体可能经历了与该突变相关的选择压力。该突变可能对这些群体的生理节律、代谢或其他生理特征产生影响,从而对它们的生存或生产性能带来某种优势。
中等频率突变群体: 例如,India Native Chicken(印度土鸡) 和 Iran Native Chicken(伊朗土鸡) 等群体显示出中等的突变频率,表明这些鸡种可能保留了部分突变,但并未在整个群体中完全固定。
低频或无突变群体: 一些鸡种显示出非常低的突变频率或完全没有此突变(如 Nixi Chicken 和 White Leghorn Chicken)。这表明这些群体可能没有经历该突变的遗传选择,或者该突变对这些群体没有带来显著的生理优势。
研究意义:
- PER3 基因 与昼夜节律的调控相关,因此该突变可能会影响鸡的生理节律、代谢功能或行为特征。研究该突变的分布可以揭示不同鸡种如何适应环境变化和昼夜节律。
- 高频突变群体 中的突变可能通过自然选择或育种过程保留下来,可能对鸡种的生产性能或健康产生影响,特别是与昼夜节律相关的生理功能。
进一步研究建议:
- 功能验证: 通过基因表达和功能实验,研究该突变对 PER3 基因功能的具体影响,特别是在调节昼夜节律和代谢功能方面的作用。
- 基因-性状关联分析: 结合鸡的生产性能、昼夜节律、行为等表型数据,进行基因-性状关联分析,探讨该突变是否对这些性状产生积极影响。
- 育种应用: 如果该突变被证明对生产性能或健康有正面影响,可能可以在育种中引入这些突变,以优化鸡种的生产效率和适应能力。
总结:
PER3 基因 中的 T/G 突变 在不同鸡种中的分布显示了选择压力的差异。高频突变群体可能通过该突变优化了昼夜节律或代谢功能,而低频或无突变的群体则保留了更原始的基因型。这种突变可能对鸡种的生理节律和健康具有重要影响,值得进一步研究。
21 300868 C/T T 0.192 missense_variant MODERATE PER3 rs16176412 21:288796 Show Show Gbrowse
Group (number): frequence
Gallus_gallus_bankiva(2):0.000
Gallus_gallus_gallus(6):0.500
Gallus_gallus_jabouillei(27):0.537
Gallus_gallus_murghi(50):0.310
Gallus_gallus_spadiceus(44):0.159
Indonesia_Native_Chicken(35):0.143
Thailand_Native_Chicken(6):0.000
Vietnam_Native_Chicken(7):0.357
Wenchang_Chicken(1):0.000
Yunnan_Chicken(12):0.042
Xishuangbanna_Game_Chicken(10):0.200
Nixi_Chicken(12):0.000
Dulong_Chicken(7):0.071
Daweishan_Mini_Chicken(8):0.062
Guangxi_Chicken(6):0.083
Guangzhou_Chicken(2):0.250
Jiangxi_Silkies(20):0.125
Anyi_Gray_Chicken(5):0.200
Dongxiang_Blue-eggshell_Chicken(6):0.083
Tianfu_Black-bone_Chicken(5):0.300
Shimian_Caoke_Chicken(3):0.167
Jiuyuan_Black-bone_Chicken(5):0.200
Jinyang_Silky_Chicken(6):0.167
Emei_Black_Chicken(6):0.167
Pengxian_Yellow_Chicken(6):0.083
Muchuan_Black-bone_Chicken(5):0.400
Miyi_Chicken(5):0.100
YuanBao_Chicken(24):0.000
Langshan_Chicken(10):0.150
Luxi_Game_Chicken(9):0.167
Shouguang_Chicken(8):0.000
Gushi_Chicken(8):0.188
Bian_Chicken(8):0.125
Beijing_You_Chicken(11):0.091
Dagu_Chicken(8):0.062
Xinjiang_Native_Chicken(6):0.250
Hetian_Black_Chicken(8):0.062
Southern_Xinjiang_Game_Chicken(8):0.125
Turpan_Game_Chicken(8):0.000
Tibetan_Chicken(138):0.094
Araucana_Blue-eggshell_Chicken(6):0.083
Sri_Lanka_Native_Chicken(7):0.071
Bengal_Native_Chicken(15):0.300
India_Native_Chicken(46):0.304
Pakistan_Native_Chicken(37):0.162
Afghan_Native_Chicken(11):0.182
Iran_Native_Chicken(182):0.299
Iran_Commercial_Broiler(4):0.125
White_Leghorn_Chicken(13):0.000
Cornish_Chicken(1):0.000
Rhode_Island_Red_Chicken(1):1.000
White_Plymouth_Rock_Chicken(1):0.500
这段数据展示了 PER3 基因 中的一个 C/T 突变,位于 21号染色体 的 300868 位点。这个突变是一个 missense_variant(错义突变),意味着突变导致编码的蛋白质中的某个氨基酸发生改变。该突变的影响被标记为 MODERATE(中等影响),表明它可能对蛋白质功能产生一定的影响,但不会致命。
突变详情:
- 基因: PER3(Period Circadian Regulator 3),该基因参与调节昼夜节律,是与生理节律相关的关键基因。
- 突变位置: 21号染色体 300868 位点。
- 突变类型: C/T 突变,导致错义突变。
- 变异ID: rs16176412,该变异已在数据库中记录。
- P值: 0.192,表示突变的频率为 19.2%。
不同鸡种中的突变频率:
下方展示了该突变在不同鸡种中的频率,括号中的数字表示样本数量,小数表示突变频率。
高频突变群体:
- Gallus_gallus_jabouillei(越南原鸡): 突变频率为 0.537,即53.7%的个体携带该突变。
- Gallus_gallus_gallus(家鸡): 突变频率为 0.500。
- Rhode_Island_Red_Chicken(罗德岛红鸡): 突变频率为 1.000,即100%的个体携带该突变。
- Bengal_Native_Chicken(孟加拉土鸡): 突变频率为 0.300,即30%的个体携带该突变。
中等频率突变群体:
- India_Native_Chicken(印度土鸡): 突变频率为 0.304,即30.4%的个体携带该突变。
- Iran_Native_Chicken(伊朗土鸡): 突变频率为 0.299,即29.9%的个体携带该突变。
- Tianfu_Black-bone_Chicken(天府黑骨鸡): 突变频率为 0.300,即30%的个体携带该突变。
低频或无突变群体:
- Gallus_gallus_bankiva(野生原鸡)、Thailand_Native_Chicken(泰国土鸡) 和 White_Leghorn_Chicken(白来亨鸡) 等显示突变频率为 0.000,即没有个体携带该突变。
- Xinjiang_Native_Chicken(新疆土鸡) 和 Guangzhou_Chicken(广州鸡) 显示突变频率为 0.250,即25%的个体携带该突变。
这些低频或无突变的群体表明它们可能没有经历相关的选择压力,或者该突变对它们的生理特性影响较小。
分析:
高频突变群体: Gallus_gallus_jabouillei(越南原鸡) 和 Rhode Island Red Chicken 等鸡种显示出较高的突变频率,表明这些群体可能在进化或育种过程中经历了与该突变相关的选择压力。该突变可能对生理节律、代谢等方面带来某种优势。
中等频率突变群体: India Native Chicken(印度土鸡) 和 Iran Native Chicken(伊朗土鸡) 显示中等突变频率,表明这些鸡种可能部分保留了该突变,可能与它们的环境适应性或育种历史相关。
低频或无突变群体: Gallus gallus bankiva(野生原鸡) 等显示低频或无突变,表明这些群体可能没有经历与该突变相关的选择压力,或者该突变在这些鸡种中没有显著的生理优势。
研究意义:
- PER3 基因 作为昼夜节律调控的重要基因,该突变可能会影响鸡的生理节律、代谢功能或行为特征。研究这些突变在不同鸡种中的分布有助于揭示昼夜节律基因如何影响不同群体的行为和适应性。
- 高频突变鸡种 可能通过自然选择或育种选择保留了这些突变,研究其对生产性能或健康状况的影响可能对育种工作提供参考。
进一步研究建议:
- 功能验证: 通过基因表达和功能实验,研究该突变对 PER3 基因功能的影响,特别是在调控昼夜节律和代谢功能方面的作用。
- 表型关联分析: 结合鸡的生产性能、昼夜节律、代谢等表型数据,研究该突变是否对这些性状产生影响。
- 育种应用: 如果该突变显示出与生产性能、健康或适应能力相关的正面影响,可以在育种过程中应用这些信息,优化鸡种的生产效率和健康水平。
总结:
PER3 基因 中的 C/T 突变 在不同鸡种中的分布显示了不同的选择压力。高频突变群体可能通过该突变优化了昼夜节律或代谢功能,而低频或无突变的群体则保留了更原始的基因型。研究该突变对鸡种生理节律和健康的影响对未来的育种工作具有重要意义。
Meleagris gallopavo XM_010720597.2
Tympanuchus pallidicinctus XM_052669942.1
Coturnix japonica AB005528.1
Numida meleagris EF643463.1
Lagopus muta XM_048930027.1
Phasianus colchicus XM_031605553.1
Centrocercus urophasianus XM_042823904.1
Lagopus leucura XM_042890720.1
Cyrtonyx montezumae XM_065753986.1
Anser anser AY387651.1
Cygnus atratus XM_035570468.2
Cygnus olor XM_040542809.1
Chroicocephalus ridibundus 未找到对应名称
Anas platyrhynchos GU245792.1
Chroicocephalus scopulinus HM015818.1
Oxyura jamaicensis XM_035341207.1
Anser cygnoides XM_066986755.1
Rissa tridactyla 未找到对应名称
Grus americana 未找到对应名称
Harpia harpyja 未找到对应名称
Anas acuta 未找到对应名称
Calidris pugnax XM_014962023.1
Apteryx mantelli 未找到对应名称
Nyctibius grandis 未找到对应名称
Accipiter gentilis 未找到对应名称
为了便于比较,我从低海拔、中海拔和高海拔区域各挑选几个典型鸡种,以便展示不同海拔环境下的代表性品种。每个海拔区域选择了3-4个典型鸡种。
典型低海拔区域鸡种
这些鸡种适应温暖湿润的低海拔环境,主要分布在东南亚、南亚及中国南方低海拔地区:
- Indonesia_Native_Chicken(36) - 典型的低海拔东南亚原生鸡种,适应湿润热带气候。
- Wenchang_Chicken(1) - 海南的低海拔地方鸡种,常年温暖潮湿。
- Guangzhou_Chicken(4) - 广东广州的低海拔鸡种,适应华南地区湿润气候。
- India_Native_Chicken(49) - 印度的土生鸡种,生活在低海拔亚热带区域。
典型中海拔区域鸡种
这些鸡种主要分布在中国中部、东部及四川的中海拔区域,气候温和,地势变化较大:
- Yunnan_Chicken(12) - 云南地区的中海拔鸡种,生活在温带与亚热带交界,海拔适中。
- Jiangxi_Silkies(20) - 江西地区的中海拔丝羽鸡,适应季节变化和适中的湿度。
- Beijing_You_Chicken(11) - 北京油鸡,适应北方温带气候,生活在低到中海拔地区。
- Tianfu_Black-bone_Chicken(5) - 四川天府乌骨鸡,适应中海拔区域多变气候。
典型高海拔区域鸡种
这些鸡种分布在青藏高原及新疆等高海拔地区,适应寒冷干燥的气候条件:
- Tibetan_Chicken(139) - 西藏高原鸡种,典型的高海拔环境下生长,耐寒。
- Nixi_Chicken(12) - 分布在云南高海拔区域,适应寒冷气候。
- Xinjiang_Native_Chicken(5) - 新疆地区高海拔鸡种,适应干燥与昼夜温差大的气候。
- Hetian_Black_Chicken(7) - 和田地区的高海拔黑鸡,适应寒冷与高海拔环境。
通过这些典型鸡种,可以更好地理解不同海拔和气候条件对鸡种适应性的影响。
正选择
AANAT
Pr(w>1) post mean +- SE for w
13 T 0.872 1.462 +- 0.410
20 N 0.694 1.272 +- 0.392
160 D 0.819 1.404 +- 0.414
ARNTL没有
ARNTL2
Pr(w>1) post mean +- SE for w
194 A 0.744 1.299 +- 0.375
242 S 0.752 1.314 +- 0.351
264 G 0.567 1.132 +- 0.449
BHLHE40没有
Pr(w>1) post mean +- SE for w
BHLHE41没有
clock暂定 没有
CRY1没有
PER2 有
PER3 有
RORA 没有
RORB 没有
RORL 不全
timeless 没有
BF1需要从跑
BG1从新跑
BG2
Naive Empirical Bayes (NEB) analysis
Positively selected sites (*: P>95%; **: P>99%)
(amino acids refer to 1st sequence: gallus gallus)
Pr(w>1) post mean +- SE for w
2 T 0.877 1.130
5 K 0.831 1.083
13 K 0.807 1.059
16 S 0.661 0.911
17 D 0.785 1.037
25 T 0.907 1.160
28 S 0.903 1.155
29 T 0.664 0.914
32 S 0.854 1.106
34 S 0.946 1.199
36 S 0.877 1.130
38 V 0.862 1.114
40 Q 0.963* 1.217
42 D 0.860 1.113
43 D 0.941 1.194
44 G 0.997** 1.250
47 E 0.578 0.827
49 L 0.994** 1.248
51 E 0.964* 1.218
60 R 0.989* 1.243
61 S 0.999** 1.253
70 Q 0.904 1.157
72 W 0.988* 1.241
74 G 0.626 0.876
75 H 0.908 1.161
78 L 0.712 0.963
79 L 0.907 1.160
81 S 0.711 0.962
82 G 0.641 0.891
83 R 0.922 1.175
84 D 0.907 1.160
87 R 0.773 1.024
89 K 0.999** 1.253
90 C 0.982* 1.236
91 S 0.998** 1.251
BG3有很多
BLA很多
BLB1很多
BLB2很多
DMA很多
MHCY1很多
MHCY2B1很多
MHCY2B2很多
MHCY8很多·
Detailed output identifying parameters
kappa (ts/tv) = 1.90834
Parameters in M8 (beta&w>1):
p0 = 0.95667 p = 0.07588 q = 0.09018
(p1 = 0.04333) w = 17.17315
dN/dS (w) for site classes (K=4)
p: 0.31889 0.31889 0.31889 0.04333
w: 0.00000 0.23559 0.99999 17.17315
这个里面有p,q的值
ChatGTP算的是对的
根据您提供的 M7 和 M8 模型的 lnL 值,我们可以重新计算 $2\Delta \lnL$。
提供的 lnL 值:
- M7 模型:
-3443.897310 - M8 模型:
-3443.898786
计算 $2\Delta \lnL$:
[
2\Delta \lnL = 2 \times (\ln L_{M8} - \ln L_{M7})
]
[
2\Delta \lnL = 2 \times (-3443.898786 - (-3443.897310)) = 2 \times (-0.001476) = -0.002952
]
自由度 (d.f.):
自由度为 M8 和 M7 模型的参数数量差:
- M8: 66
- M7: 64
自由度: ( 66 - 64 = 2 )
结果:
- $2\Delta \lnL$: -0.002952
- 自由度 (d.f.): 2
此计算结果的 $2\Delta \lnL$ 值接近零,表明两个模型之间的差异非常小。请确认这些结果是否符合您的预期或需要进一步分析。
那么接下来呢
结构域
找一找
为了将这些基因分组并为每个分组分配不同的颜色代码,我将按照基因的名称将其分组并为每个分组添加一个颜色代码。颜色代码可以使用 RGB 表示法(例如,255,0,0 表示红色)或灰度代码(例如,255 表示白色,0 表示黑色)。
分组及颜色方案
在这里,我们可以假设:
- CIPC:红色 (255,0,0)
- OPN4-1:绿色 (0,255,0)
- OPN4:蓝色 (0,0,255)
- CRY1:黄色 (255,255,0)
- ARNTL2:紫色 (128,0,128)
- BHLHE41:橙色 (255,165,0)
- RORB:青色 (0,255,255)
- CLOCK:粉色 (255,192,203)
- PER3:棕色 (139,69,19)
- BHLHE40:深蓝 (0,0,139)
- ARNTL:深绿 (0,100,0)
- CRY2:深橙 (255,140,0)
- RORA:浅蓝 (173,216,230)
- TIMELESS:深紫 (75,0,130)
- PER2:深红 (139,0,0)
- AANAT:浅粉红 (255,182,193)
添加颜色后的表格
1 | Gene name Transcript ID Color |
说明
- 颜色列(Color):每个基因家族的颜色是固定的,例如
CIPC使用红色255,0,0,OPN4-1使用绿色0,255,0。 - 格式:将颜色代码作为 RGB 值方便应用到 Circos 图中。如果使用灰度色彩,只需提供单个值(例如
128表示中灰色)。
希望这个示例能够帮助您在绘制 Circos 图时为不同基因家族分配颜色,以便更清晰地区分不同的基因。
在论文写作中,按顺序、结构清晰地组织内容是关键。以下是一个常见的科学论文撰写顺序建议:
- 结果(Results)
既然图表都已经完成,建议从结果部分开始。结果部分主要描述研究中获得的所有关键发现,并通过图表和数据支持。撰写时注意:
每张图表都应在结果中有详细描述。
结果要简明、直接,避免解释性或推测性语言。
按图表或逻辑顺序逐步描述研究的主要发现。
- 方法(Methods)
结果完成后,写方法部分。方法部分应详细描述实验流程,以便其他研究人员可以复现你的实验。包括:
数据收集:描述样本、实验条件、设备等。
数据处理:分析软件、算法、统计方法等。
确保按时间顺序或实验流程来描述。 - 讨论(Discussion)
讨论部分是在结果的基础上进行解释、分析和拓展的部分。这里要讨论结果的意义、与现有研究的关系以及对领域的影响。撰写时:
解释你的主要发现,讨论其生物学或理论意义。
对比你的结果和其他已发表研究的异同。
提出潜在的局限性和未来研究的方向。 - 引言(Introduction)
在结果和讨论完成后,写引言会更有针对性。引言部分为读者提供研究背景,突出研究的必要性和重要性。通常结构为:
背景:简要介绍领域的研究现状。
知识空白:指出该研究想要解决的具体问题或填补的空白。
研究目的和假设:简洁地说明研究目的、假设或研究问题。 - 摘要(Abstract)
摘要总结了论文的整体内容,包含背景、方法、主要结果和结论。应简洁且富有信息量,涵盖研究的核心发现。摘要撰写建议:
主要概述问题背景和研究的关键发现。
使用简短的语言,避免过度技术化的术语。 - 标题和关键词(Title and Keywords)
标题应简洁有力,清晰传达研究的主题。
关键词是便于读者和搜索引擎检索的词汇,应与研究内容高度相关。 - 结论(Conclusion)
如果期刊格式要求单独的结论部分,可以在结论中总结主要发现和研究贡献,明确指出研究的独特价值。 - 致谢和参考文献(Acknowledgments and References)
致谢:感谢提供帮助的人员、机构或资助机构。
参考文献:确保引文格式符合期刊要求,全面且准确地引用相关文献。
总结
按照以上顺序写作,可以帮助确保论文内容逻辑清晰、层次分明。在撰写过程中,随时查看期刊的格式要求以确保符合规范。
以下是各结构域的简要解释:
low_complexity_region:表示结构简单、重复性高的区域,通常富含特定的氨基酸,不易形成复杂的三级结构。
**HLH (Helix-Loop-Helix)**:螺旋-环-螺旋结构域,常见于转录因子,负责DNA结合及蛋白质-蛋白质相互作用。
**PAS (Per-Arnt-Sim)**:参与检测环境变化和光信号,常见于昼夜节律蛋白中。
PAC:通常与PAS结构域配对出现,帮助稳定PAS结构。
coiled_coil_region:缠绕结构,负责蛋白质-蛋白质相互作用,常用于信号转导。
Pfam:DNA_photolyase:DNA光裂解酶结构域,参与DNA修复,特别是在光损伤的修复中。
Pfam:FAD_binding_7:结合黄素腺嘌呤二核苷酸 (FAD) 的结构域,通常参与氧化还原反应。
internal_repeat_1:内部重复结构,有助于蛋白质的稳定性或调节功能。
Pfam:Period_C:昼夜节律蛋白Period的C端结构域,参与调控生物钟。
Pfam:7TM_GPCR_Srx / Pfam:7TM_GPCR_Srsx / Pfam:7tm_1:属于G蛋白偶联受体的七次跨膜结构,主要在细胞信号传导中起作用。
ZnF_C4:C4型锌指结构域,常见于转录因子中,通过锌离子结合DNA。
HOLI:此区域通常在昼夜节律蛋白中起特定的调节作用。
Pfam:TIMELESS / Pfam:TIMELESS_C:与TIMELESS蛋白相关的结构域,在昼夜节律调控中扮演关键角色。
SANT:与染色质调控和DNA结合相关,常见于基因表达调控的蛋白中。
Blast:SANT:同样与SANT相关,用于DNA结合,可能在基因表达调控中发挥作用。
这些结构域共同参与了昼夜节律蛋白的功能,包括信号转导、DNA结合、蛋白质稳定性和生物钟调控等。
结构域
可以发现
1,BMAL与CLOCK,PER除了CRY都有PAS结构域,PAC与PAS成对出现帮助稳定结构
2,CRY独有DNA-protolyase与FAD-binding,作用
3,BMAL与CLOCK独有HLH,作用:
4,TIMELESS都有TIMELSEE,而小鼠和人还有TIMELESS_C,其他物种为SANA
5,PER独有period_c
6,ror独有ZNF和LOLI,作用
7,OPN4,有Pfam:7TM_GPCR_Srx / Pfam:7TM_GPCR_Srsx / Pfam:7tm_1作用
这些帮我规范描述一下
可以观察到以下特点:
BMAL、CLOCK和PER的共同结构域:除了CRY基因外,BMAL、CLOCK和PER基因均含有PAS结构域,并伴随出现PAC结构域。这两个结构域成对出现,有助于蛋白结构的稳定性。
CRY基因的独特结构域:CRY基因独有DNA-photolyase和FAD-binding结构域,这些结构域可能参与DNA修复和光依赖的生理过程。
BMAL和CLOCK的独特结构域:BMAL和CLOCK基因含有HLH(Helix-Loop-Helix)结构域,参与基因转录调控中的二聚体形成,有助于其在转录因子的功能中发挥作用。
TIMELESS基因的结构差异:TIMELESS结构域在所有物种中均存在,而在小鼠和人类中还包含了TIMELESS_C结构域,其余物种则具有SANT结构域,可能在调控功能上有微小差异。
PER基因的独特结构域:PER基因独有Period_C结构域,表明其在生物节律的周期性调控中具有独特的作用。
ROR基因的独特结构域:ROR基因含有ZNF(锌指)和HOLI结构域,可能在基因转录调控中发挥重要作用。
OPN4基因的特有结构域:OPN4基因含有Pfam:7TM_GPCR_Srx、Pfam:7TM_GPCR_Srsx和Pfam:7tm_1结构域,这些结构域通常与G蛋白偶联受体相关,表明其可能参与光感受和信号传导过程。
这些结构域的分布显示出不同昼夜节律基因在功能上的分化,体现了其在生物节律调控中的特异性。
观察到以下结构域的分布特点:
BMAL、CLOCK和PER的共同结构域:BMAL、CLOCK和PER基因均含有PAS结构域,并伴随出现PAC结构域。
CRY基因的独特结构域:CRY基因独有DNA-photolyase和FAD-binding结构域。
BMAL和CLOCK的独特结构域:BMAL和CLOCK基因含有HLH(Helix-Loop-Helix)结构域。
TIMELESS基因的结构差异:TIMELESS结构域在所有物种中均存在,而在小鼠和人类中还包含TIMELESS_C结构域,其余物种具有SANT结构域。
PER基因的独特结构域:PER基因独有Period_C结构域。
ROR基因的独特结构域:ROR基因含有ZNF(锌指)和HOLI结构域。
OPN4基因的特有结构域:OPN4基因含有Pfam:7TM_GPCR_Srx、Pfam:7TM_GPCR_Srsx和Pfam:7tm_1结构域。
这些结构域的分布展示了不同昼夜节律基因的结构差异。
要筛选出准确的结果,您可以尝试调整以下几个步骤中的参数:
Step 3: Select Parameters
Domain from / to:
- 根据您感兴趣的时间段设置该范围。通常,昼夜节律的研究范围在 0 到 24 小时。如果您有特定的时间点,可以在此进行调整。
Min items / set:
- 设置每组基因集的最小项数。这一参数可以确保基因集包含足够的基因,以提高统计意义。根据基因集的大小,您可以将其设置为 5 到 10,或其他适合的数字。
Max sims / test:
- 这个值控制了每次测试的最大模拟次数。增加该值(例如 10000 次)可以提高结果的准确性,但可能会增加计算时间。
Save image if (P | Q | q value < 0.05):
- 选择适当的阈值以筛选出统计显著的结果。通常,P 值、Q 值或 q 值小于 0.05 被认为是显著的,可以确保生成的图片只保存显著的基因集。您可以根据数据的实际情况来微调这个阈值。
结果的筛选与解读
- 在设置好参数后,点击 Generate Output 按钮。生成的结果会出现在您指定的文件夹中。
- 在生成的文件中,重点查看那些显著的基因集结果,特别是 P 值和 Q 值较低的基因集。这些基因集通常与您的研究目标最相关。
其他建议
- 如果发现结果的显著性不高,您可以进一步优化基因集,或增加样本数量。
- 也可以调整时间域(Domain)范围,尝试不同的时间间隔,例如缩小到某几个关键时间点,以发现更显著的节律性变化。
这样设置可以帮助您筛选出统计上更显著、符合生物学意义的基因集。
data_经度3.csv
Call:
lm(formula = ARNTL2_rs14841128 ~ 维度 + 经度 + 海拔 + 无霜期 +
日照, data = data)
Residuals:
Min 1Q Median 3Q Max
-0.20242 -0.04793 0.00776 0.03594 0.32555
Coefficients:
Estimate Std. Error t value Pr(>|t|)
(Intercept) -4.852e-01 2.073e-01 -2.340 0.0264 *
维度 1.499e-02 2.989e-03 5.016 2.43e-05 ***
经度 -1.755e-03 6.972e-04 -2.516 0.0176 *
海拔 2.705e-05 2.535e-05 1.067 0.2947
无霜期 9.899e-04 3.757e-04 2.635 0.0134 *
日照 1.804e-05 3.464e-05 0.521 0.6065
Signif. codes: 0 ‘’ 0.001 ‘’ 0.01 ‘’ 0.05 ‘.’ 0.1 ‘ ’ 1
Residual standard error: 0.103 on 29 degrees of freedom
Multiple R-squared: 0.4893, Adjusted R-squared: 0.4012
F-statistic: 5.557 on 5 and 29 DF, p-value: 0.001043
model <- lm(CLOCK_rs312574810 ~ 维度 + 经度 + 海拔 + 无霜期 + 日照, data = data)
summary(model)
Call:
lm(formula = CLOCK_rs312574810 ~ 维度 + 经度 + 海拔 + 无霜期 +
日照, data = data)
Residuals:
Min 1Q Median 3Q Max
-0.46340 -0.13316 0.02374 0.10831 0.47074
Coefficients:
Estimate Std. Error t value Pr(>|t|)
(Intercept) 2.847e-01 4.531e-01 0.628 0.53465
维度 -5.706e-03 6.533e-03 -0.873 0.38963
经度 5.318e-03 1.524e-03 3.490 0.00157 **
海拔 -1.312e-04 5.539e-05 -2.368 0.02477 *
无霜期 -6.971e-04 8.211e-04 -0.849 0.40283
日照 4.201e-05 7.570e-05 0.555 0.58320
Signif. codes: 0 ‘’ 0.001 ‘’ 0.01 ‘’ 0.05 ‘.’ 0.1 ‘ ’ 1
Residual standard error: 0.2252 on 29 degrees of freedom
Multiple R-squared: 0.4576, Adjusted R-squared: 0.3641
F-statistic: 4.893 on 5 and 29 DF, p-value: 0.002287
model <- lm(CLOCK_rs312574810 ~ 维度 + 经度 + 海拔 + 无霜期 + 日照, data = data)
summary(model)
Call:
lm(formula = CLOCK_rs312574810 ~ 维度 + 经度 + 海拔 + 无霜期 +
日照, data = data)
Residuals:
Min 1Q Median 3Q Max
-0.46340 -0.13316 0.02374 0.10831 0.47074
Coefficients:
Estimate Std. Error t value Pr(>|t|)
(Intercept) 2.847e-01 4.531e-01 0.628 0.53465
维度 -5.706e-03 6.533e-03 -0.873 0.38963
经度 5.318e-03 1.524e-03 3.490 0.00157 **
海拔 -1.312e-04 5.539e-05 -2.368 0.02477 *
无霜期 -6.971e-04 8.211e-04 -0.849 0.40283
日照 4.201e-05 7.570e-05 0.555 0.58320
Signif. codes: 0 ‘’ 0.001 ‘’ 0.01 ‘’ 0.05 ‘.’ 0.1 ‘ ’ 1
Residual standard error: 0.2252 on 29 degrees of freedom
Multiple R-squared: 0.4576, Adjusted R-squared: 0.3641
F-statistic: 4.893 on 5 and 29 DF, p-value: 0.002287
model <- lm(PER3_rs317669303 ~ 维度 + 经度 + 海拔 + 无霜期 + 日照, data = data)
summary(model)
Call:
lm(formula = PER3_rs317669303 ~ 维度 + 经度 + 海拔 + 无霜期 +
日照, data = data)
Residuals:
Min 1Q Median 3Q Max
-0.17716 -0.05835 -0.02726 0.05725 0.26915
Coefficients:
Estimate Std. Error t value Pr(>|t|)
(Intercept) -3.264e-01 2.037e-01 -1.602 0.12001
维度 9.713e-03 2.938e-03 3.306 0.00253 **
经度 -1.399e-03 6.852e-04 -2.042 0.05037 .
海拔 1.296e-06 2.491e-05 0.052 0.95888
无霜期 7.759e-04 3.692e-04 2.101 0.04441 *
日照 1.962e-05 3.404e-05 0.576 0.56893
Signif. codes: 0 ‘’ 0.001 ‘’ 0.01 ‘’ 0.05 ‘.’ 0.1 ‘ ’ 1
Residual standard error: 0.1013 on 29 degrees of freedom
Multiple R-squared: 0.3425, Adjusted R-squared: 0.2291
F-statistic: 3.021 on 5 and 29 DF, p-value: 0.02581



